Macromolecole Biologiche. Metodi di simulazione
|
|
|
- Linda Rosso
- 6 anni fa
- Visualizzazioni
Transcript
1 Metodi di simulazione
2 Dinamica molecolare Tecnica di simulazione che permette lo studio del moto e delle proprietà di un sistema di particelle. Moti localizzati (da 0.01 a 5 Å, da a 10-1 s) - fluttuazioni atomiche - movimenti di catene laterali - movimenti di loop Moti a corpo rigido (da 1 a 10 Å, da 10-9 a 1 s) - movimenti di eliche - movimenti di domini - movimenti di subunità Moti su larga scala (> 5 Å, da 10-7 a 10-3 s) - transizioni eliche-coil - associazione/dissociazione - folding/unfolding
3 Dinamica molecolare A T ambiente si dimostra che vale l approssimazione della meccanica classica, purchè i moti abbiano tempi caratteristici del ps (10-12 s) o siano più lunghi. Una molecola biologica viene approssimata ad un network di sfere (particelle di Lennard-Jones) con carica puntiforme al loro centro, collegate da molle (legami covalenti). Le particelle si trovano in un campo di energia potenziale che si modifica in funzione delle posizioni raggiunte dagli atomi del sistema.
4 Dinamica molecolare Le simulazioni di dinamica molecolare permettono lo studio di complessi processi dinamici che hanno luogo nei sistemi biologici. Per esempio: Stabilità delle proteine Cambi conformazionali Folding delle proteine Riconoscimento molecolare: proteine, DNA, membrane, complessi Trasporto ionico in sistemi biologici e permette di effettuare studi di Drugdesign Determinazione di strutture 3D di macromolecole biologiche
5 Dinamica molecolare Per simulare la dinamica di una macromolecola sono necessarie: - descrizione della struttura: coordinate iniziali (file PDB a cui si aggiungono gli atomi di H) - funzione energia potenziale Scopo della simulazione è risolvere le equazioni del moto per un sistema di N atomi: la soluzione, cioè le coordinate del sistema in funzione del tempo, rappresenta le traiettorie degli atomi che compongono la molecola. Le simulazioni di dinamica molecolare si basano sulla seconda legge di Newton: F i = m i a i i = 1,, N (numero atomi del sistema) Dalla conoscenza delle forze che agiscono su ciascun atomo è possibile determinare l accelerazione di ciascun atomo del sistema.
6 Dinamica molecolare L integrazione delle equazioni del moto consente di ottenere una traiettoria che descrive la variazione nel tempo delle posizioni, velocità ed accelerazioni delle particelle. Le simulazioni di dinamica molecolare sono in genere calcolate sulla scala dei ns (10-9 s). F i = m i a i i = 1,, N (numero atomi del sistema) F i =m i dv i /d t = m i d 2 r i /d t 2 inoltre F i = - dv/d r i dove V = energia potenziale Per moti uniformemente accelerati (a = costante): ma quindi a i =dv i /dt v i (t) = a i t+ v i (t 0 ) v i =dr i /dt r i (t) = v i t+ r i (t 0 ) r i (t) = a i t 2 + v i (t 0 )t + r i (t 0 ) dove a i = - (1/m i ) dv/d r i
7 Dinamica molecolare Per calcolare una traiettoria è quindi necessario conoscere le posizioni iniziali degli atomi, una iniziale distribuzione delle velocità e l accelerazione (determinata come gradiente di una funzione di energia potenziale). Le equazioni del moto sono deterministiche, nel senso che le posizioni e le velocità al tempo t = t 0 determinano le posizioni e le velocità al generico tempo t. Le posizioni iniziali si possono ottenere da strutture sperimentali risolte con le metodologie della diffrazione di raggi X su monocristalli o mediante risonanza magnetico-nucleare (NMR). La distribuzione delle velocità iniziali sono derivate da una distribuzione Maxwelliana random corrispondente alla T desiderata: m i p(v i ) = exp [-m i v i2 /2K B T] 2πK B T
8 Dinamica molecolare m i p(v i ) = exp [-m i v i2 /2K B T] 2πK B T p(v i ) = probabilità che l atomo i-esimo abbia velocità v i alla temperatura T. L iniziale distribuzione random delle velocità viene scelta in modo tale che non ci sia momento totale della quantità di moto, cioè: N P = Σ i=1 m i v i = 0
9 Funzione Energia Potenziale Per calcoli di dinamica molecolare su sistemi biologici vengono utilizzate funzioni energia potenziale empiriche capaci di riprodurre le proprietà fisiche del sistema fornendo un buon compromesso fra accuratezza ed efficienza computazionale. Limitazioni: tali funzioni energia potenziale non possono riprodurre drastici cambi nella struttura elettronica degli atomi del sistema. Per esempio non possono essere modellati eventi come la formazione o la rottura di legami covalenti (in questo caso occorre un approccio quanto-meccanico). L energia potenziale del sistema è funzione delle posizioni atomiche (R, in coordinate cartesiane) di tutti gli atomi che compongono il sistema. Essa è definita come la somma di termini interno (o di legame ) ed esterni (o di non-legame ): V(R) = V legame +V non-legame
10 Funzione Energia Potenziale I termini di legame risultano dalla somma: V legame =V bond-stretch + V angle-bend + V torsions
11 Funzione Energia Potenziale V bond-stretch : potenziale armonico che rappresenta l interazione tra coppie di atomi separati da un legame covalente (coppie 1,2). 1 2 V bond-stretch = Σ coppie 1,2 K l (l l 0 ) 2 l 0 = lunghezza ideale di legame K l = costante che determina la forza del legame l 0 e K l dipendono dai tipi di atomi legati covalentemente
12 Funzione Energia Potenziale V bond-stretch : potenziale armonico che associato all alterazione degli angoli di legame attorno al valore ideale θ 0. V bond-bend = Σ angoli K θ (θ θ 0 ) 2 θ 0 = angolo ideale fra 3 atomi legati covalentemente K θ = costante che determina la forza del legame θ 0 e K θ dipendono dai tipi di atomi legati covalentemente
13 Funzione Energia Potenziale V torsions : potenziale (periodico) associato all angolo di torsione che modella la presenza di barriere steriche fra atomi separati da 3 legami covalenti (coppie 1,4) V torsions = Σ coppie 1,4 K φ (1 cos(nφ)) 2 φ 0 = angolo diedro n = coefficiente di simmetria (=1,2,3) K φ = costante di proporzionalità
14 Funzione Energia Potenziale I termini di non legame risultano dalla somma: V non-legame = V van-der-waals + V elettrostatico V van-der-waals = Σ coppie [(A ik /r ik 12 ) [(B ik /r ik6 )] non legate A ik e B ik = costanti dipendenti dagli atomi r ik = distanza degli atomi V elettrostatico = Σ coppie q i q k /Dr ik non legate q i e q k = cariche elettriche degli atomi D = costante dielettrica del mezzo
15 Funzione Energia Potenziale Per velocizzare il calcolo del potenziale, si possono introdurre dei cutoff per le interazioni di non legame (per esempio, cutoff di 12 Å per le interazioni di Coulomb). Manca un termine esplicito per le interazioni di legame a idrogeno. Per una dinamica realistica bisognerebbe esplicitare il solvente (una o due shell di idratazione della macromolecola), che scherma parzialmente le cariche q i e q j.
16 Solvente - Trattamento implicito : le molecole d acqua non sono incluse nella simulazione ma viene utilizzata una costante dielettrica efficace dipendente dalla distanza. - Trattamento esplicito : le molecole d acqua non sono incluse nella simulazione. Occorre introdurre condizioni di bordo per: evitare che le molecole d acqua diffondano lontano dalla proteina durante la simulazione poter usare un numero limitato di molecole d acqua
17 Dinamica molecolare L integrazione delle equazioni del moto non è banale, perché il moto degli atomi modifica i valori delle energie potenziali di interazione e quindi delle forze agenti sugli atomi stessi. L integrazione delle equazioni del moto viene fatta per intervalli di tempo molto piccoli (1 fs = s) in modo tale da mantenere costanti le quantità fisiche rilevanti. La lunghezza totale di una simulazione è dell ordine dei ns (10-9 s). Gli algoritmi matematici utilizzati per l integrazione sono: - Leap frog -Verlet
18 Dinamica molecolare Minimizzazione dell energia Prima di iniziare la dinamica, può essere utile minimizzare l energia, per eliminare distorsioni strutturali che potrebbero portare ad energie troppo elevate e a non convergenza. La configurazione stabile di una molecola è quella di minima energia (gradiente del potenziale = 0 rispetto alle posizioni degli atomi). L energia del sistema ha un minimo in quei punti nello spazio delle configurazioni in cui le forze che agiscono sugli atomi sono bilanciate.
19 Dinamica molecolare Configurazione iniziale del sistema (t = 0): Struttura cristallografica, NMR, o modello teorico costruito per omologia (si aggiungono gli atomi di H). Scegliere una configurazione iniziale prossima a quella da simulare. Prima di iniziare la simulazione è utile minimizzare l energia della struttura (rimozione di forti interazioni di van der Waals che potrebbero portare a locali distorsioni della struttura ed a simulazioni instabili. Se necessario, si aggiungono le molecole d acqua e si compie una nuova minimizzazione della struttura. Si assegnano a ciascun atomo le velocità iniziali a bassa T, e le equazioni del moto sono integrate per fare evolvere il sistema nel tempo. Periodicamente vengono assegnate nuove velocità a T gradatamente più elevate e viene ripetuta la simulazione di dinamica molecolare. La procedura è ciclizzata fino a che non si raggiunge la T desiderata. Durante la dinamica vengono monitorate le proprietà del sistema per verificare che esse siano stabili rispetto al tempo. Se la T cresce o decresce significativamente, le velocità vengono riscalate in modo che le T torni ai valori iniziali. Simulazione di dinamica molecolare per il tempo che si desidera (ps - ns). Analisi dei risultati (traiettorie,.. ecc).
20 Analisi dei risultati Una volta che il sistema ha raggiunto l equilibrio, è possibile calcolare alcune proprietà del sistema, osservando l evoluzione temporale delle sue coordinate e velocità: - analisi delle traiettorie; - analisi delle energie medie (potenziale, cinetica, totale); - calcolo della velocità del centro di massa; - calcolo del raggio di girazione: R G = Σ i m i (r i r cm ) 2 Σ i m i r i r cm = distanza fra l atomo i ed il centro di massa - monitoraggio nel tempo di specifici legami, angoli di legame, angoli diedri, distanze fra atomi, per osservare cambiamenti nella struttura;
21 Analisi dei risultati - calcolo della root mean squared deviation (rmsd) di atomi della molecola rispetto ad una struttura di riferimento (non necessariamente quella a t = 0): rmsd (r 1, r 2 ) = 1 Σ i (r 1,i r 2,i ) 2 N r 1 = (x 1,1,.., x 1,N ) r 2 = (x 2,1,.., x 2,N ) - calcolo delle fluttuazioni di rmsd rmsd fluct i = 1 Σ f (r if rave i ) 2 N f - andamento del plot di Ramachandran nel tempo (variazione della struttura secondaria).
Diagramma di Ramachandran
 Chimica Biologica A.A. 2010-2011 Diagramma di Ramachandran Diagramma di Ramachandran Catena polipeptidica La formazione in successione di legami peptidici genera la cosiddetta catena principale o scheletro
Chimica Biologica A.A. 2010-2011 Diagramma di Ramachandran Diagramma di Ramachandran Catena polipeptidica La formazione in successione di legami peptidici genera la cosiddetta catena principale o scheletro
La Dinamica Molecolare nello Studio dei Biosistemi
 Chapter 5 La Dinamica Molecolare nello Studio dei Biosistemi Un approccio computazionale molto usato sia nella scienza dei materiali che nello studio di biomolecole è la dinamica molecolare (MD). Con questo
Chapter 5 La Dinamica Molecolare nello Studio dei Biosistemi Un approccio computazionale molto usato sia nella scienza dei materiali che nello studio di biomolecole è la dinamica molecolare (MD). Con questo
RISOLUZIONE DI PROBLEMI DI FISICA
 RISOUZIONE DI PROBEMI DI FISICA Problema 1 Una massa puntiforme m = 2 kg è soggetta ad una forza centrale con associata energia potenziale radiale U( r) 6 A =, dove A = 2 J m 6. Il momento angolare della
RISOUZIONE DI PROBEMI DI FISICA Problema 1 Una massa puntiforme m = 2 kg è soggetta ad una forza centrale con associata energia potenziale radiale U( r) 6 A =, dove A = 2 J m 6. Il momento angolare della
Le Biomolecole II parte. Lezioni d'autore di Giorgio Benedetti
 Le Biomolecole II parte Lezioni d'autore di Giorgio Benedetti LA STRUTTURA TERZIARIA DI UNA PROTEINA La struttura tridimensionale adottata da una proteina è detta struttura terziaria. Essa prende in considerazione
Le Biomolecole II parte Lezioni d'autore di Giorgio Benedetti LA STRUTTURA TERZIARIA DI UNA PROTEINA La struttura tridimensionale adottata da una proteina è detta struttura terziaria. Essa prende in considerazione
Dipartimento Scientifico-Tecnologico
 ISTITUTO TECNICO STATALE LUIGI STURZO Castellammare di Stabia - NA Anno scolastico 2012-13 Dipartimento Scientifico-Tecnologico CHIMICA, FISICA, SCIENZE E TECNOLOGIE APPLICATE Settore Economico Indirizzi:
ISTITUTO TECNICO STATALE LUIGI STURZO Castellammare di Stabia - NA Anno scolastico 2012-13 Dipartimento Scientifico-Tecnologico CHIMICA, FISICA, SCIENZE E TECNOLOGIE APPLICATE Settore Economico Indirizzi:
Ettore Vitali. Dinamica Molecolare. Nozioni di base e tecniche avanzate
 Ettore Vitali Dinamica Molecolare Nozioni di base e tecniche avanzate Sommario NVE-ensemble : dinamica di un sistema isolato. Tecniche di base, campo di applicabilità, affidabilità dei risultati NVT-ensemble
Ettore Vitali Dinamica Molecolare Nozioni di base e tecniche avanzate Sommario NVE-ensemble : dinamica di un sistema isolato. Tecniche di base, campo di applicabilità, affidabilità dei risultati NVT-ensemble
approfondimento Lavoro ed energia
 approfondimento Lavoro ed energia Lavoro compiuto da una forza costante W = F. d = F d cosθ dimensioni [W] = [ML T - ] Unità di misura del lavoro N m (Joule) in MKS dine cm (erg) in cgs N.B. Quando la
approfondimento Lavoro ed energia Lavoro compiuto da una forza costante W = F. d = F d cosθ dimensioni [W] = [ML T - ] Unità di misura del lavoro N m (Joule) in MKS dine cm (erg) in cgs N.B. Quando la
OSCILLATORE ARMONICO SEMPLICE
 OSCILLATORE ARMONICO SEMPLICE Un oscillatore è costituito da una particella che si muove periodicamente attorno ad una posizione di equilibrio. Compiono moti oscillatori: il pendolo, un peso attaccato
OSCILLATORE ARMONICO SEMPLICE Un oscillatore è costituito da una particella che si muove periodicamente attorno ad una posizione di equilibrio. Compiono moti oscillatori: il pendolo, un peso attaccato
Rappresentazione grafica di sistemi atomici e molecolari: editor e visualizzatori ESERCITAZIONE 5
 Rappresentazione grafica di sistemi atomici e molecolari: editor e visualizzatori ESERCITAZIONE 5 Editor e visualizzatori Spesso è utile rappresentare graficamente la struttura atomica o molecolare del
Rappresentazione grafica di sistemi atomici e molecolari: editor e visualizzatori ESERCITAZIONE 5 Editor e visualizzatori Spesso è utile rappresentare graficamente la struttura atomica o molecolare del
Tutorato di Fisica 2 Anno Accademico 2010/2011
 Matteo Luca Ruggiero DIFIS@Politecnico di Torino Tutorato di Fisica 2 Anno Accademico 2010/2011 () 2 1.1 Una carica q è posta nell origine di un riferimento cartesiano. (1) Determinare le componenti del
Matteo Luca Ruggiero DIFIS@Politecnico di Torino Tutorato di Fisica 2 Anno Accademico 2010/2011 () 2 1.1 Una carica q è posta nell origine di un riferimento cartesiano. (1) Determinare le componenti del
1.La forma delle molecole 2.La teoria VSEPR 3.Molecole polari e apolari 4.Le forze intermolecolari 5.Legami a confronto
 1.La forma delle molecole 2.La teoria VSEPR 3.Molecole polari e apolari 4.Le forze intermolecolari 5.Legami a confronto 1 1. La forma delle molecole Molte proprietà delle sostanze dipendono dalla forma
1.La forma delle molecole 2.La teoria VSEPR 3.Molecole polari e apolari 4.Le forze intermolecolari 5.Legami a confronto 1 1. La forma delle molecole Molte proprietà delle sostanze dipendono dalla forma
SCIENZE INTEGRATE CHIMICA
 SCIENZE INTEGRATE CHIMICA Classi 2 e TECNICO ECONOMICO (REL- AMM-SPO) PROGRAMMAZIONE ANNUALE: SEQUENZA DI LAVORO U.D.A. Periodo Ore lezione 1. Classificazione della materia: stati fisici e miscugli settembre
SCIENZE INTEGRATE CHIMICA Classi 2 e TECNICO ECONOMICO (REL- AMM-SPO) PROGRAMMAZIONE ANNUALE: SEQUENZA DI LAVORO U.D.A. Periodo Ore lezione 1. Classificazione della materia: stati fisici e miscugli settembre
ATOMO. Legge della conservazione della massa Legge delle proporzioni definite Dalton
 Democrito IV secolo A.C. ATOMO Lavoisier Proust Legge della conservazione della massa Legge delle proporzioni definite Dalton (808) Teoria atomica Gay-Lussac volumi di gas reagiscono secondo rapporti interi
Democrito IV secolo A.C. ATOMO Lavoisier Proust Legge della conservazione della massa Legge delle proporzioni definite Dalton (808) Teoria atomica Gay-Lussac volumi di gas reagiscono secondo rapporti interi
Integrazione delle equazioni del moto
 Giorgio Pastore - note per il corso di Laboratorio di Calcolo Integrazione delle equazioni del moto In generale, le equazioni del moto della meccanica newtoniana si presentano nella forma di sistemi di
Giorgio Pastore - note per il corso di Laboratorio di Calcolo Integrazione delle equazioni del moto In generale, le equazioni del moto della meccanica newtoniana si presentano nella forma di sistemi di
Ottimizzazione della geometria. Ottimizzazione della geometria A.A ! " B. Civalleri Chimica Computazionale a.a
 Ottimizzazione della geometria A.A. 2006-07 07! " B. Civalleri Chimica Computazionale a.a. 2006-07 1 Ottimizzazione della geometria Definizioni (I) Superficie di energia potenziale (PES) La PES descrive
Ottimizzazione della geometria A.A. 2006-07 07! " B. Civalleri Chimica Computazionale a.a. 2006-07 1 Ottimizzazione della geometria Definizioni (I) Superficie di energia potenziale (PES) La PES descrive
Insegnante: Prof.ssa La Salandra Incoronata
 LICEO SCIENTIFICO STATALE G. MARCONI FOGGIA PROGRAMMA DI Fisica Classe IVB Anno Scolastico 2014-2015 Insegnante: Prof.ssa La Salandra Incoronata TERMODINAMICA: LE LEGGIDEI GAS IDEALI E LA LORO INTERPRETAZIONE
LICEO SCIENTIFICO STATALE G. MARCONI FOGGIA PROGRAMMA DI Fisica Classe IVB Anno Scolastico 2014-2015 Insegnante: Prof.ssa La Salandra Incoronata TERMODINAMICA: LE LEGGIDEI GAS IDEALI E LA LORO INTERPRETAZIONE
Chimica Biologica A.A α-elica foglietto β reverse turn
 Chimica Biologica A.A. 2010-2011 α-elica foglietto β reverse turn Str. Secondaria sperimentalmente osservata: Si distinguono fondamentalmente tre tipi di strutture secondarie: α elica foglietto β reverse
Chimica Biologica A.A. 2010-2011 α-elica foglietto β reverse turn Str. Secondaria sperimentalmente osservata: Si distinguono fondamentalmente tre tipi di strutture secondarie: α elica foglietto β reverse
gruppo amminico Gli aminoacidi polimerizzano durante la sintesi delle proteine mediante la formazione di legami peptidici. gruppo carbossilico
 gruppo amminico Gli aminoacidi polimerizzano durante la sintesi delle proteine mediante la formazione di legami peptidici. gruppo carbossilico Il legame peptidico si ha quando il gruppo carbossilico (-
gruppo amminico Gli aminoacidi polimerizzano durante la sintesi delle proteine mediante la formazione di legami peptidici. gruppo carbossilico Il legame peptidico si ha quando il gruppo carbossilico (-
Conoscenze FISICA LES CLASSE TERZA SAPERI MINIMI
 FISICA LES SAPERI MINIMI CLASSE TERZA LE GRANDEZZE FISICHE E LA LORO MISURA Nuovi principi per indagare la natura. Il concetto di grandezza fisica. Misurare una grandezza fisica. L impossibilità di ottenere
FISICA LES SAPERI MINIMI CLASSE TERZA LE GRANDEZZE FISICHE E LA LORO MISURA Nuovi principi per indagare la natura. Il concetto di grandezza fisica. Misurare una grandezza fisica. L impossibilità di ottenere
Corso di Chimica Generale CL Biotecnologie
 Corso di Chimica Generale CL Biotecnologie STATI DELLA MATERIA Prof. Manuel Sergi MATERIA ALLO STATO GASSOSO MOLECOLE AD ALTA ENERGIA CINETICA GRANDE DISTANZA TRA LE MOLECOLE LEGAMI INTERMOLECOLARI DEBOLI
Corso di Chimica Generale CL Biotecnologie STATI DELLA MATERIA Prof. Manuel Sergi MATERIA ALLO STATO GASSOSO MOLECOLE AD ALTA ENERGIA CINETICA GRANDE DISTANZA TRA LE MOLECOLE LEGAMI INTERMOLECOLARI DEBOLI
CRISTALLOGRAFIA AI RAGGI X E MODELLISTICA MOLECOLARE
 CRISTALLOGRAFIA AI RAGGI X E MODELLISTICA MOLECOLARE LA STRUTTURA TRIDIMENSIONALE DEGLI ACIDI NUCLEICI, E PIU IN GENERALE DELLE MACROMOLECOLE BIOLOGICHE, PUO ESSERE STUDIATA CON LA METODICA DELLA CRISTALLOGRAFIA
CRISTALLOGRAFIA AI RAGGI X E MODELLISTICA MOLECOLARE LA STRUTTURA TRIDIMENSIONALE DEGLI ACIDI NUCLEICI, E PIU IN GENERALE DELLE MACROMOLECOLE BIOLOGICHE, PUO ESSERE STUDIATA CON LA METODICA DELLA CRISTALLOGRAFIA
Diffrazione di Raggi-X da Monocristalli A.A Marco Nardini Dipartimento di Scienze Biomolecolari e Biotecnologie Università di Milano
 Diffrazione di Raggi-X da Monocristalli A.A. 2009-2010 Marco Nardini Dipartimento di Scienze Biomolecolari e Biotecnologie Università di Milano Raccolta Dati di Diffrazione: Diffrazione di Raggi X Raccolta
Diffrazione di Raggi-X da Monocristalli A.A. 2009-2010 Marco Nardini Dipartimento di Scienze Biomolecolari e Biotecnologie Università di Milano Raccolta Dati di Diffrazione: Diffrazione di Raggi X Raccolta
Macromolecole Biologiche. La struttura secondaria (I)
 La struttura secondaria (I) La struttura secondaria Struttura primaria PRPLVALLDGRDETVEMPILKDVATVAFCDAQSTQEIHE Struttura secondaria La struttura secondaria Le strutture secondarie sono disposizioni regolari
La struttura secondaria (I) La struttura secondaria Struttura primaria PRPLVALLDGRDETVEMPILKDVATVAFCDAQSTQEIHE Struttura secondaria La struttura secondaria Le strutture secondarie sono disposizioni regolari
Molecole biologiche. Il loro comportamento è determinato da. Solvente (acqua, ph) Flessibilità (perché sono catene lunghe) Tempi caratteristici
 Molecole biologiche Macromolecole: Proteine e Acidi nucleici catene polimeriche di aminoacidi e nucleotidi formate da 103 a 106 atomi, con una massa molecolare compresa tra 103 a 1012 amu (1 amu è circa
Molecole biologiche Macromolecole: Proteine e Acidi nucleici catene polimeriche di aminoacidi e nucleotidi formate da 103 a 106 atomi, con una massa molecolare compresa tra 103 a 1012 amu (1 amu è circa
Esercitazione 1. Matteo Luca Ruggiero 1. Anno Accademico 2010/ Dipartimento di Fisica del Politecnico di Torino
 Esercitazione 1 Matteo Luca Ruggiero 1 1 Dipartimento di Fisica del Politecnico di Torino Anno Accademico 2010/2011 ML Ruggiero (DIFIS) Esercitazione 1: Elettrostatica E1.2010/2011 1 / 29 Sommario 1 Riferimenti
Esercitazione 1 Matteo Luca Ruggiero 1 1 Dipartimento di Fisica del Politecnico di Torino Anno Accademico 2010/2011 ML Ruggiero (DIFIS) Esercitazione 1: Elettrostatica E1.2010/2011 1 / 29 Sommario 1 Riferimenti
Introduzione alla chimica organica. 1. Regola ottetto 2. Teoria del legame 3. Geometria delle molecole
 Introduzione alla chimica organica 1. Regola ottetto 2. Teoria del legame 3. Geometria delle molecole La chimica organica tratta di pochissimi atomi che si possono combinare in moltissimi modi Grande importanza
Introduzione alla chimica organica 1. Regola ottetto 2. Teoria del legame 3. Geometria delle molecole La chimica organica tratta di pochissimi atomi che si possono combinare in moltissimi modi Grande importanza
Capitolo 12. Moto oscillatorio
 Moto oscillatorio INTRODUZIONE Quando la forza che agisce su un corpo è proporzionale al suo spostamento dalla posizione di equilibrio ne risulta un particolare tipo di moto. Se la forza agisce sempre
Moto oscillatorio INTRODUZIONE Quando la forza che agisce su un corpo è proporzionale al suo spostamento dalla posizione di equilibrio ne risulta un particolare tipo di moto. Se la forza agisce sempre
Macromolecole Biologiche. La struttura secondaria (II)
 La struttura secondaria (II) Nello stesso anno (1951) in cui proposero l α elica, Pauling e Corey postularono anche l esistenza di un altra struttura secondaria: il foglietto β (β-sheet). Dopo l α elica,
La struttura secondaria (II) Nello stesso anno (1951) in cui proposero l α elica, Pauling e Corey postularono anche l esistenza di un altra struttura secondaria: il foglietto β (β-sheet). Dopo l α elica,
FISICA delle APPARECCHIATURE per RADIOTERAPIA
 Anno Accademico 2012-2013 Corso di Laurea in Tecniche Sanitarie di Radiologia Medica per Immagini e Radioterapia FISICA delle APPARECCHIATURE per RADIOTERAPIA Marta Ruspa 20.01.13 M. Ruspa 1 ONDE ELETTROMAGNETICHE
Anno Accademico 2012-2013 Corso di Laurea in Tecniche Sanitarie di Radiologia Medica per Immagini e Radioterapia FISICA delle APPARECCHIATURE per RADIOTERAPIA Marta Ruspa 20.01.13 M. Ruspa 1 ONDE ELETTROMAGNETICHE
U.D. CHIMICA classe 2 a TECN. (CAT) CHIMICA TECNOLOGICO (CAT) PROGRAMMAZIONE ANNUALE: SEQUENZA DI LAVORO
 CHIMICA Classe 2 a TECNOLOGICO (CAT) PROGRAMMAZIONE ANNUALE: SEQUENZA DI LAVORO U.D. Periodo Ore lezione 1. Nomenclatura molecole inorganiche (ripasso) settembre 6 2. Struttura atomica e tavola periodica
CHIMICA Classe 2 a TECNOLOGICO (CAT) PROGRAMMAZIONE ANNUALE: SEQUENZA DI LAVORO U.D. Periodo Ore lezione 1. Nomenclatura molecole inorganiche (ripasso) settembre 6 2. Struttura atomica e tavola periodica
Indice 3. Note di utilizzo 9. Ringraziamenti 10. Introduzione 11
 Indice Indice 3 Note di utilizzo 9 Ringraziamenti 10 Introduzione 11 Capitolo 1 Grandezze fisiche e schematizzazione dei sistemi materiali 13 1.1 Grandezze fisiche ed operazione di misura 13 1.2 Riferimento
Indice Indice 3 Note di utilizzo 9 Ringraziamenti 10 Introduzione 11 Capitolo 1 Grandezze fisiche e schematizzazione dei sistemi materiali 13 1.1 Grandezze fisiche ed operazione di misura 13 1.2 Riferimento
CAPITOLO. 1 Gli strumenti di misura Gli errori di misura L incertezza nelle misure La scrittura di una misura 38
 Indice LA MATEMATICA PER COMINCIARE 2 LA MISURA DI UNA GRANDEZZA 1 Le proporzioni 1 2 Le percentuali 2 3 Le potenze di 10 3 Proprietà delle potenze 3 4 Seno, coseno e tangente 5 5 I grafici 6 6 La proporzionalità
Indice LA MATEMATICA PER COMINCIARE 2 LA MISURA DI UNA GRANDEZZA 1 Le proporzioni 1 2 Le percentuali 2 3 Le potenze di 10 3 Proprietà delle potenze 3 4 Seno, coseno e tangente 5 5 I grafici 6 6 La proporzionalità
Lezione 3. Principi generali della Meccanica Cinematica, Statica e Dinamica
 Lezione 3 Principi generali della Meccanica Cinematica, Statica e Dinamica Premessa L Universo in cui viviamo costituisce un sistema dinamico, cioè un sistema in evoluzione nel tempo secondo opportune
Lezione 3 Principi generali della Meccanica Cinematica, Statica e Dinamica Premessa L Universo in cui viviamo costituisce un sistema dinamico, cioè un sistema in evoluzione nel tempo secondo opportune
Chimica e laboratorio
 ITIS H.HERTZ Progetto Monoennio Chimica e laboratorio PARTE PRIMA I MODULO: Struttura atomica e molecolare della materia PESO : 70% UNITA ORARIE PREVISTE : 20 h Unità A: ATOMI Descrivere le caratteristiche
ITIS H.HERTZ Progetto Monoennio Chimica e laboratorio PARTE PRIMA I MODULO: Struttura atomica e molecolare della materia PESO : 70% UNITA ORARIE PREVISTE : 20 h Unità A: ATOMI Descrivere le caratteristiche
CENNI SUL TIPO DI FORZE
 CENNI SUL TIPO DI FORZE Forze deboli che influenzano la struttura delle proteine: le interazioni di van der Waals repulsione attrazione Forze attrattive dovute a interazioni istantanee che si generano
CENNI SUL TIPO DI FORZE Forze deboli che influenzano la struttura delle proteine: le interazioni di van der Waals repulsione attrazione Forze attrattive dovute a interazioni istantanee che si generano
 1 anno fisica -potenze di 10, equivalenze e notazione scientifica -misure ed incertezze -grandezze scalari e vettoriali e relative operazioni -esprimere il risultato di una misura e saper rappresentare
1 anno fisica -potenze di 10, equivalenze e notazione scientifica -misure ed incertezze -grandezze scalari e vettoriali e relative operazioni -esprimere il risultato di una misura e saper rappresentare
Istituto Professionale di Stato Maffeo Pantaleoni di Frascati SCHEDA PROGRAMMAZIONE DIDATTICA DISCIPLINARE
 Istituto Professionale di Stato Maffeo Pantaleoni di Frascati SCHEDA PROGRAMMAZIONE DIDATTICA DISCIPLINARE ANNO SCOLASTICO 2013/2014 CLASSI 1 sez, A B C D E F G H MATERIA DOCENTEScienze Integrate: FISICA
Istituto Professionale di Stato Maffeo Pantaleoni di Frascati SCHEDA PROGRAMMAZIONE DIDATTICA DISCIPLINARE ANNO SCOLASTICO 2013/2014 CLASSI 1 sez, A B C D E F G H MATERIA DOCENTEScienze Integrate: FISICA
Sulla superficie interna del guscio sferico (induzione totale) si avrà la carica indotta q distribuita uniformemente, quindi
 1) Una sfera conduttrice di raggio r = 5 cm possiede una carica q = 10 8 C ed è posta nel centro di un guscio sferico conduttore, di raggio interno R = 20 cm, posto in contatto con la terra (a massa).
1) Una sfera conduttrice di raggio r = 5 cm possiede una carica q = 10 8 C ed è posta nel centro di un guscio sferico conduttore, di raggio interno R = 20 cm, posto in contatto con la terra (a massa).
Macromolecole Biologiche. La struttura secondaria (III)
 La struttura secondaria (III) Reverse turn Le proteine globulari hanno una forma compatta, dovuta a numerose inversioni della direzione della catena polipeptidica che le compone. Molte di queste inversioni
La struttura secondaria (III) Reverse turn Le proteine globulari hanno una forma compatta, dovuta a numerose inversioni della direzione della catena polipeptidica che le compone. Molte di queste inversioni
La struttura elettronica degli atomi
 1 In unità atomiche: a 0 me 0,59A unità di lunghezza e H 7, ev a H=Hartree unità di energia L energia dell atomo di idrogeno nello stato fondamentale espresso in unità atomiche è: 4 0 me 1 e 1 E H 13,
1 In unità atomiche: a 0 me 0,59A unità di lunghezza e H 7, ev a H=Hartree unità di energia L energia dell atomo di idrogeno nello stato fondamentale espresso in unità atomiche è: 4 0 me 1 e 1 E H 13,
1. Le forze intermolecolari 2. Molecole polari e apolari 3. Le forze dipolo-dipolo e le forze di London 4. Il legame a idrogeno 5. Legami a confronto
 Unità n 12 Le forze intermolecolari e gli stati condensati della materia 1. Le forze intermolecolari 2. Molecole polari e apolari 3. Le forze dipolo-dipolo e le forze di London 4. Il legame a idrogeno
Unità n 12 Le forze intermolecolari e gli stati condensati della materia 1. Le forze intermolecolari 2. Molecole polari e apolari 3. Le forze dipolo-dipolo e le forze di London 4. Il legame a idrogeno
Capitolo 12 Le forze intermolecolari e gli stati condensati della materia
 Capitolo 12 Le forze intermolecolari e gli stati condensati della materia 1. Le forze intermolecolari 2. Molecole polari e apolari 3. Le forze dipolo-dipolo e le forze di London 4. Il legame a idrogeno
Capitolo 12 Le forze intermolecolari e gli stati condensati della materia 1. Le forze intermolecolari 2. Molecole polari e apolari 3. Le forze dipolo-dipolo e le forze di London 4. Il legame a idrogeno
Lezione n. 19. L equazione. di Schrodinger L atomo. di idrogeno Orbitali atomici. 02/03/2008 Antonino Polimeno 1
 Chimica Fisica - Chimica e Tecnologia Farmaceutiche Lezione n. 19 L equazione di Schrodinger L atomo di idrogeno Orbitali atomici 02/03/2008 Antonino Polimeno 1 Dai modelli primitivi alla meccanica quantistica
Chimica Fisica - Chimica e Tecnologia Farmaceutiche Lezione n. 19 L equazione di Schrodinger L atomo di idrogeno Orbitali atomici 02/03/2008 Antonino Polimeno 1 Dai modelli primitivi alla meccanica quantistica
GLI ORBITALI ATOMICI
 GLI ORBITALI ATOMICI Orbitali atomici e loro rappresentazione Le funzioni d onda Ψ n che derivano dalla risoluzione dell equazione d onda e descrivono il moto degli elettroni nell atomo si dicono orbitali
GLI ORBITALI ATOMICI Orbitali atomici e loro rappresentazione Le funzioni d onda Ψ n che derivano dalla risoluzione dell equazione d onda e descrivono il moto degli elettroni nell atomo si dicono orbitali
Meccanica del punto materiale
 Meccanica del punto materiale Princìpi della dinamica. Forze. Momento angolare. Antonio Pierro @antonio_pierro_ (https://twitter.com/antonio_pierro_) Per consigli, suggerimenti, eventuali errori o altro
Meccanica del punto materiale Princìpi della dinamica. Forze. Momento angolare. Antonio Pierro @antonio_pierro_ (https://twitter.com/antonio_pierro_) Per consigli, suggerimenti, eventuali errori o altro
Generalità delle onde elettromagnetiche
 Generalità delle onde elettromagnetiche Ampiezza massima: E max (B max ) Lunghezza d onda: (m) E max (B max ) Periodo: (s) Frequenza: = 1 (s-1 ) Numero d onda: = 1 (m-1 ) = v Velocità della luce nel vuoto
Generalità delle onde elettromagnetiche Ampiezza massima: E max (B max ) Lunghezza d onda: (m) E max (B max ) Periodo: (s) Frequenza: = 1 (s-1 ) Numero d onda: = 1 (m-1 ) = v Velocità della luce nel vuoto
Molecole. 04/09/13 3-MOL-0.doc 0
 Molecole 04/09/13 3-MOL-0.doc 0 Legame covalente H 2 + Il potenziale cui è soggetto l elettrone ha 2 minimi equivalenti 1) H + si avvicina a H 2) Se la barriera diventa abbastanza sottile la probabilità
Molecole 04/09/13 3-MOL-0.doc 0 Legame covalente H 2 + Il potenziale cui è soggetto l elettrone ha 2 minimi equivalenti 1) H + si avvicina a H 2) Se la barriera diventa abbastanza sottile la probabilità
Dinamica delle Strutture
 Corso di Laurea magistrale in Ingegneria Civile e per l Ambiente e il Territorio Dinamica delle Strutture Prof. Adolfo SANTINI Ing. Francesco NUCERA Prof. Adolfo Santini - Dinamica delle Strutture 1 Dinamica
Corso di Laurea magistrale in Ingegneria Civile e per l Ambiente e il Territorio Dinamica delle Strutture Prof. Adolfo SANTINI Ing. Francesco NUCERA Prof. Adolfo Santini - Dinamica delle Strutture 1 Dinamica
Comune ordine di riempimento degli orbitali di un atomo
 Comune ordine di riempimento degli orbitali di un atomo Le energie relative sono diverse per differenti elementi ma si possono notare le seguenti caratteristiche: (1) La maggior differenza di energia si
Comune ordine di riempimento degli orbitali di un atomo Le energie relative sono diverse per differenti elementi ma si possono notare le seguenti caratteristiche: (1) La maggior differenza di energia si
DEDUZIONE DEL TEOREMA DELL'ENERGIA CINETICA DELL EQUAZIONE SIMBOLICA DELLA DINAMICA
 DEDUZIONE DEL TEOREMA DELL'ENERGIA CINETICA DELL EQUAZIONE SIMBOLICA DELLA DINAMICA Sia dato un sistema con vincoli lisci, bilaterali e FISSI. Ricaviamo, dall equazione simbolica della dinamica, il teorema
DEDUZIONE DEL TEOREMA DELL'ENERGIA CINETICA DELL EQUAZIONE SIMBOLICA DELLA DINAMICA Sia dato un sistema con vincoli lisci, bilaterali e FISSI. Ricaviamo, dall equazione simbolica della dinamica, il teorema
Lezione 5 Moti di particelle in un campo magnetico
 Lezione 5 Moti di particelle in un campo magnetico G. Bosia Universita di Torino G. Bosia - Fisica del plasma confinato Lezione 5 1 Moto di una particella carica in un campo magnetico Il confinamento del
Lezione 5 Moti di particelle in un campo magnetico G. Bosia Universita di Torino G. Bosia - Fisica del plasma confinato Lezione 5 1 Moto di una particella carica in un campo magnetico Il confinamento del
scaricato da I peptidi risultano dall unione di due o più aminoacidi mediante un legame COVALENTE
 Legame peptidico I peptidi risultano dall unione di due o più aminoacidi mediante un legame COVALENTE tra il gruppo amminico di un aminoacido ed il gruppo carbossilico di un altro. 1 Catene contenenti
Legame peptidico I peptidi risultano dall unione di due o più aminoacidi mediante un legame COVALENTE tra il gruppo amminico di un aminoacido ed il gruppo carbossilico di un altro. 1 Catene contenenti
UNIVERSITÀ DEGLI STUDI DI TERAMO CORSO DI LAUREA IN BIOTECNOLOGIE CORSO MONODISCIPLINARE: BIOCHIMICA (6CFU)
 UNIVERSITÀ DEGLI STUDI DI TERAMO CORSO DI LAUREA IN BIOTECNOLOGIE CORSO MONODISCIPLINARE: BIOCHIMICA (6CFU) Roberto Giacominelli Stuffler IL C.M. BIOCHIMICA È SUDDIVISO IN DUE UNITÀ DIDATTICHE: A) BIOCHIMICA
UNIVERSITÀ DEGLI STUDI DI TERAMO CORSO DI LAUREA IN BIOTECNOLOGIE CORSO MONODISCIPLINARE: BIOCHIMICA (6CFU) Roberto Giacominelli Stuffler IL C.M. BIOCHIMICA È SUDDIVISO IN DUE UNITÀ DIDATTICHE: A) BIOCHIMICA
IL LEGAME CHIMICO. Per descrivere come gli elettroni si distribuiscono nell atomo attorno al nucleo si può far riferimento al MODELLO A GUSCI
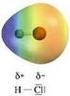 IL LEGAME CIMICO Come dagli atomi si costruiscono le molecole 02/19/08 0959 PM 1 Per descrivere come gli elettroni si distribuiscono nell atomo attorno al nucleo si può far riferimento al MODELLO A GUSCI
IL LEGAME CIMICO Come dagli atomi si costruiscono le molecole 02/19/08 0959 PM 1 Per descrivere come gli elettroni si distribuiscono nell atomo attorno al nucleo si può far riferimento al MODELLO A GUSCI
Configurazioni elettroniche e periodicità
 Configurazioni elettroniche e periodicità Le configurazioni elettroniche dei vari elementi sono una funzione periodica del numero atomico Z. Gli elementi che appartengono allo stesso gruppo nella tavola
Configurazioni elettroniche e periodicità Le configurazioni elettroniche dei vari elementi sono una funzione periodica del numero atomico Z. Gli elementi che appartengono allo stesso gruppo nella tavola
Proprietà comuni. Il gruppo α-carbossilico b è un acido più forte del gruppo carbossilico degli acidi alifatici
 Gli aminoacidi Proprietà comuni Il gruppo α-carbossilico b è un acido più forte del gruppo carbossilico degli acidi alifatici paragonabili Il gruppo α-aminico è un acido più forte (o una base più debole
Gli aminoacidi Proprietà comuni Il gruppo α-carbossilico b è un acido più forte del gruppo carbossilico degli acidi alifatici paragonabili Il gruppo α-aminico è un acido più forte (o una base più debole
In un punto qualsiasi (P) della traiettoria è definita la direzione tangente t e la direzione perpendicolare n. d dt
 Moti piani su traiettorie qualsiasi In un punto qualsiasi (P) della traiettoria è definita la direzione tangente t e la direzione perpendicolare n. n ˆ P ˆ t traiettoria La velocità in ogni punto della
Moti piani su traiettorie qualsiasi In un punto qualsiasi (P) della traiettoria è definita la direzione tangente t e la direzione perpendicolare n. n ˆ P ˆ t traiettoria La velocità in ogni punto della
ATOMI MONOELETTRONICI
 ATOMI MONOELETTRONICI L equazione di Schrödinger per gli atomi contenenti un solo elettrone (atomo di idrogeno, ioni He +, Li 2+ ) può essere risolta in maniera esatta e le soluzioni ottenute permettono
ATOMI MONOELETTRONICI L equazione di Schrödinger per gli atomi contenenti un solo elettrone (atomo di idrogeno, ioni He +, Li 2+ ) può essere risolta in maniera esatta e le soluzioni ottenute permettono
Le interazioni deboli:
 Le interazioni deboli: sono legami non covalenti sono da 1 a 3 ordini di grandezza più deboli dei legami covalenti sono alcune volte maggiori della tendenza a dissociare dovuta all agitazione termica delle
Le interazioni deboli: sono legami non covalenti sono da 1 a 3 ordini di grandezza più deboli dei legami covalenti sono alcune volte maggiori della tendenza a dissociare dovuta all agitazione termica delle
Struttura Elettronica degli Atomi Meccanica quantistica
 Prof. A. Martinelli Struttura Elettronica degli Atomi Meccanica quantistica Dipartimento di Farmacia 1 Il comportamento ondulatorio della materia 2 1 Il comportamento ondulatorio della materia La diffrazione
Prof. A. Martinelli Struttura Elettronica degli Atomi Meccanica quantistica Dipartimento di Farmacia 1 Il comportamento ondulatorio della materia 2 1 Il comportamento ondulatorio della materia La diffrazione
Traslazioni. Debora Botturi ALTAIR. Debora Botturi. Laboratorio di Sistemi e Segnali
 Traslazioni ALTAIR http://metropolis.sci.univr.it Argomenti Velocitá ed accelerazione di una massa che trasla Esempio: massa che trasla con condizioni iniziali date Argomenti Argomenti Velocitá ed accelerazione
Traslazioni ALTAIR http://metropolis.sci.univr.it Argomenti Velocitá ed accelerazione di una massa che trasla Esempio: massa che trasla con condizioni iniziali date Argomenti Argomenti Velocitá ed accelerazione
Unità didattica 2. Seconda unità didattica (Fisica) 1. Corso integrato di Matematica e Fisica per il Corso di Farmacia
 Unità didattica 2 Dinamica Leggi di Newton.. 2 Le forze 3 Composizione delle forze 4 Esempio di forza applicata...5 Esempio: il piano inclinato.. 6 Il moto del pendolo.. 7 La forza gravitazionale 9 Lavoro
Unità didattica 2 Dinamica Leggi di Newton.. 2 Le forze 3 Composizione delle forze 4 Esempio di forza applicata...5 Esempio: il piano inclinato.. 6 Il moto del pendolo.. 7 La forza gravitazionale 9 Lavoro
Markov Chains and Markov Chain Monte Carlo (MCMC)
 Markov Chains and Markov Chain Monte Carlo (MCMC) Alberto Garfagnini Università degli studi di Padova December 11, 2013 Catene di Markov Discrete dato un valore x t del sistema ad un istante di tempo fissato,
Markov Chains and Markov Chain Monte Carlo (MCMC) Alberto Garfagnini Università degli studi di Padova December 11, 2013 Catene di Markov Discrete dato un valore x t del sistema ad un istante di tempo fissato,
Dinamica Rotazionale
 Dinamica Rotazionale Richiamo: cinematica rotazionale, velocità e accelerazione angolare Energia cinetica rotazionale: momento d inerzia Equazione del moto rotatorio: momento delle forze Leggi di conservazione
Dinamica Rotazionale Richiamo: cinematica rotazionale, velocità e accelerazione angolare Energia cinetica rotazionale: momento d inerzia Equazione del moto rotatorio: momento delle forze Leggi di conservazione
Grandezze angolari. Lineare Angolare Relazione x θ x = rθ. m I I = mr 2 F N N = rf sin θ 1 2 mv2 1
 Grandezze angolari Lineare Angolare Relazione x θ x = rθ v ω v = ωr a α a = αr m I I = mr 2 F N N = rf sin θ 1 2 mv2 1 2 Iω 2 Energia cinetica In forma vettoriale: v = ω r questa collega la velocità angolare
Grandezze angolari Lineare Angolare Relazione x θ x = rθ v ω v = ωr a α a = αr m I I = mr 2 F N N = rf sin θ 1 2 mv2 1 2 Iω 2 Energia cinetica In forma vettoriale: v = ω r questa collega la velocità angolare
Raffinamento Cristallografico e Validazione A.A. 2010-2011. Marco Nardini Dipartimento di Scienze Biomolecolari e Biotecnologie Università di Milano
 Raffinamento Cristallografico e Validazione A.A. 2010-2011 Marco Nardini Dipartimento di Scienze Biomolecolari e Biotecnologie Università di Milano Cristalli Raffinamento Data collection ρ (x,y,z) Modello
Raffinamento Cristallografico e Validazione A.A. 2010-2011 Marco Nardini Dipartimento di Scienze Biomolecolari e Biotecnologie Università di Milano Cristalli Raffinamento Data collection ρ (x,y,z) Modello
Programma di fisica. Classe 1^ sez. F A. S. 2015/2016. Docente: prof. ssa Laganà Filomena Donatella
 Programma di fisica. Classe 1^ sez. F A. S. 2015/2016 Docente: prof. ssa Laganà Filomena Donatella MODULO 1: LE GRANDEZZE FISICHE. Notazione scientifica dei numeri, approssimazione, ordine di grandezza.
Programma di fisica. Classe 1^ sez. F A. S. 2015/2016 Docente: prof. ssa Laganà Filomena Donatella MODULO 1: LE GRANDEZZE FISICHE. Notazione scientifica dei numeri, approssimazione, ordine di grandezza.
Il tipo di legame chimico influenza in maniera fondamentale le caratteristiche macroscopiche del materiale.
 Il tipo di legame chimico influenza in maniera fondamentale le caratteristiche macroscopiche del materiale. 1 Nei materiali si distinguono cinque tipi di legame. Nei ceramici solo tre sono importanti:
Il tipo di legame chimico influenza in maniera fondamentale le caratteristiche macroscopiche del materiale. 1 Nei materiali si distinguono cinque tipi di legame. Nei ceramici solo tre sono importanti:
VII ESERCITAZIONE - 29 Novembre 2013
 VII ESERCITAZIONE - 9 Novembre 013 I. MOMENTO DI INERZIA DEL CONO Calcolare il momento di inerzia di un cono omogeneo massiccio, di altezza H, angolo al vertice α e massa M, rispetto al suo asse di simmetria.
VII ESERCITAZIONE - 9 Novembre 013 I. MOMENTO DI INERZIA DEL CONO Calcolare il momento di inerzia di un cono omogeneo massiccio, di altezza H, angolo al vertice α e massa M, rispetto al suo asse di simmetria.
Risultati della teoria di Hartree
 Risultati della teoria di Hartree Il potenziale è a simmetria sferica, come nell atomo di idrogeno, quindi: ψ n, l, m = Rn, l ( r) Θ l, m ( θ ) Φ m ( ϕ ) l l l La dipendenza angolare delle autofunzioni
Risultati della teoria di Hartree Il potenziale è a simmetria sferica, come nell atomo di idrogeno, quindi: ψ n, l, m = Rn, l ( r) Θ l, m ( θ ) Φ m ( ϕ ) l l l La dipendenza angolare delle autofunzioni
IN UN ATOMO SI DISTINGUE UN NUCLEO CARICO POSITIVAMENTE ATTORNO AL QUALE RUOTANO PARTICELLE CARICHE NEGATIVAMENTE: GLI ELETTRONI (e - ) (-)
 LA VITA, LA CHIMICA E L ACQUA PER INIZIARE QUALCHE CENNO DI CHIMICA LA MATERIA E FATTA DI COMBINAZIONI DI ELEMENTI. GLI ELEMENTI SONO COMPOSTI DA SINGOLI ATOMI, LE PIU PICCOLE UNITA CHE MANTENGONO LE PROPRIETA
LA VITA, LA CHIMICA E L ACQUA PER INIZIARE QUALCHE CENNO DI CHIMICA LA MATERIA E FATTA DI COMBINAZIONI DI ELEMENTI. GLI ELEMENTI SONO COMPOSTI DA SINGOLI ATOMI, LE PIU PICCOLE UNITA CHE MANTENGONO LE PROPRIETA
FISICA PROGRAMMAZIONE INIZIALE
 ANNO SCOLASTICO: 2015-2016 INSEGNANTE: PODELLA GIUSEPPE FISICA PROGRAMMAZIONE INIZIALE CLASSE: 1^A SETTORE: MANUTENZIONE E ASSISTENZA TECNICA INDIRIZZO: OPERATORE ELETTRICO FINALITA DELLA DISCIPLINA (finalità
ANNO SCOLASTICO: 2015-2016 INSEGNANTE: PODELLA GIUSEPPE FISICA PROGRAMMAZIONE INIZIALE CLASSE: 1^A SETTORE: MANUTENZIONE E ASSISTENZA TECNICA INDIRIZZO: OPERATORE ELETTRICO FINALITA DELLA DISCIPLINA (finalità
FISICA E LABORATORIO INDIRIZZO C.A.T. CLASSE PRIMA. OBIETTIVI U. D. n 1.2: La rappresentazione di dati e fenomeni
 FISICA E LABORATORIO INDIRIZZO C.A.T. CLASSE PRIMA Le competenze di base a conclusione dell obbligo di istruzione sono le seguenti: Osservare, descrivere ed analizzare fenomeni appartenenti alla realtà
FISICA E LABORATORIO INDIRIZZO C.A.T. CLASSE PRIMA Le competenze di base a conclusione dell obbligo di istruzione sono le seguenti: Osservare, descrivere ed analizzare fenomeni appartenenti alla realtà
Attrito statico e attrito dinamico
 Forza di attrito La presenza delle forze di attrito fa parte dell esperienza quotidiana. Se si tenta di far scorrere un corpo su una superficie, si sviluppa una resistenza allo scorrimento detta forza
Forza di attrito La presenza delle forze di attrito fa parte dell esperienza quotidiana. Se si tenta di far scorrere un corpo su una superficie, si sviluppa una resistenza allo scorrimento detta forza
Legame Chimico. Legame Chimico
 Legame Chimico Fra due atomi o gruppi di atomi esiste un legame chimico se le forze agenti tra essi danno luogo alla formazione di un aggregato di atomi sufficientemente stabile da consentire di svelarne
Legame Chimico Fra due atomi o gruppi di atomi esiste un legame chimico se le forze agenti tra essi danno luogo alla formazione di un aggregato di atomi sufficientemente stabile da consentire di svelarne
La struttura delle proteine
 La struttura delle proteine Funzioni delle proteine Strutturali Contrattili Trasporto Riserva Ormonali Enzimatiche Protezione Struttura della proteina Struttura secondaria: ripiegamento locale della catena
La struttura delle proteine Funzioni delle proteine Strutturali Contrattili Trasporto Riserva Ormonali Enzimatiche Protezione Struttura della proteina Struttura secondaria: ripiegamento locale della catena
LICEO SCIENTIFICO STATALE MICHELANGELO CAGLIARI
 LICEO SCIENTIFICO STATALE MICHELANGELO CAGLIARI PROGRAMMA DI MATEMATICA CLASSE III B A. S. 2016-2017 PROGRAMMA DI MATEMATICA RICHIAMI su equazioni di primo e secondo grado, sistemi di due equazioni in
LICEO SCIENTIFICO STATALE MICHELANGELO CAGLIARI PROGRAMMA DI MATEMATICA CLASSE III B A. S. 2016-2017 PROGRAMMA DI MATEMATICA RICHIAMI su equazioni di primo e secondo grado, sistemi di due equazioni in
PIANO DI LAVORO DEL PROFESSORE
 ISTITUTO DI ISTRUZIONE SUPERIORE STATALE IRIS VERSARI Cesano Maderno (MI) PIANO DI LAVORO DEL PROFESSORE Indirizzo: x LICEO SCIENTIFICO LICEO SCIENTIFICO Scienze Applicate LICEO SCIENZE UMANE ISTITUTO
ISTITUTO DI ISTRUZIONE SUPERIORE STATALE IRIS VERSARI Cesano Maderno (MI) PIANO DI LAVORO DEL PROFESSORE Indirizzo: x LICEO SCIENTIFICO LICEO SCIENTIFICO Scienze Applicate LICEO SCIENZE UMANE ISTITUTO
PIANO DI LAVORO DEL DOCENTE prof. DIMONOPOLI A.S. 2015/2016 CLASSE 4ALS MATERIA: FISICA
 PIANO DI LAVORO DEL DOCENTE prof. DIMONOPOLI A.S. 2015/2016 CLASSE 4ALS MATERIA: FISICA Strategie didattiche: Le lezioni frontali saranno associate a delle esperienze di laboratorio per accompagnare la
PIANO DI LAVORO DEL DOCENTE prof. DIMONOPOLI A.S. 2015/2016 CLASSE 4ALS MATERIA: FISICA Strategie didattiche: Le lezioni frontali saranno associate a delle esperienze di laboratorio per accompagnare la
Esercitazione VI - Leggi della dinamica III
 Esercitazione VI - Leggi della dinamica III Esercizio 1 I corpi 1, 2 e 3 rispettivamente di massa m 1 = 2kg, m 2 = 3kg ed m 3 = 4kg sono collegati come in figura tramite un filo inestensibile. Trascurando
Esercitazione VI - Leggi della dinamica III Esercizio 1 I corpi 1, 2 e 3 rispettivamente di massa m 1 = 2kg, m 2 = 3kg ed m 3 = 4kg sono collegati come in figura tramite un filo inestensibile. Trascurando
Compito del 14 giugno 2004
 Compito del 14 giugno 004 Un disco omogeneo di raggio R e massa m rotola senza strisciare lungo l asse delle ascisse di un piano verticale. Il centro C del disco è collegato da una molla di costante elastica
Compito del 14 giugno 004 Un disco omogeneo di raggio R e massa m rotola senza strisciare lungo l asse delle ascisse di un piano verticale. Il centro C del disco è collegato da una molla di costante elastica
ORBITA ORBIT LI ALI MOLECOLARI
 ORBITALI MOLECOLARI Una molecola è dotata di una serie di orbitali detti orbitali molecolari Gli elettroni risiedono negli orbitali molecolari che, in molti casi, sono distribuiti (delocalizzati) su tutta
ORBITALI MOLECOLARI Una molecola è dotata di una serie di orbitali detti orbitali molecolari Gli elettroni risiedono negli orbitali molecolari che, in molti casi, sono distribuiti (delocalizzati) su tutta
Lezione n. 26. Principi generali della spettroscopia IR. 02/03/2008 Antonino Polimeno 1
 Chimica Fisica - Chimica e Tecnologia Farmaceutiche Lezione n. 26 Principi generali della spettroscopia IR 02/03/2008 Antonino Polimeno 1 Spettroscopia infrarossa (1) - La spettroscopia infrarossa studia
Chimica Fisica - Chimica e Tecnologia Farmaceutiche Lezione n. 26 Principi generali della spettroscopia IR 02/03/2008 Antonino Polimeno 1 Spettroscopia infrarossa (1) - La spettroscopia infrarossa studia
Esercizi di elettrostatica (prima parte)
 Esercizi di elettrostatica (prima parte) Esercizi di elettrostatica: forza di coulomb, campo elettrico. 1. Date tre cariche elettriche puntiformi identiche ( Q ) poste ai vertici di un triangolo equilatero
Esercizi di elettrostatica (prima parte) Esercizi di elettrostatica: forza di coulomb, campo elettrico. 1. Date tre cariche elettriche puntiformi identiche ( Q ) poste ai vertici di un triangolo equilatero
Problemi di Fisica. Elettromagnetismo. La Carica Elettrica e la Legge di Coulomb
 Problemi di isica Elettromagnetismo La arica Elettrica e la Legge di oulomb Data la distribuzione di carica rappresentata in figura, calcolare la forza totale che agisce sulla carica Q posta nell origine
Problemi di isica Elettromagnetismo La arica Elettrica e la Legge di oulomb Data la distribuzione di carica rappresentata in figura, calcolare la forza totale che agisce sulla carica Q posta nell origine
Metodi Pseudopotenziale
 Oltre HF Metodi Pseudopotenziale Il moto degli elettroni interni è poco influenzato dall'intorno molecolare Il calcolo può essere semplificato modificando lo hamiltonano: limitandosi a calcolare solo il
Oltre HF Metodi Pseudopotenziale Il moto degli elettroni interni è poco influenzato dall'intorno molecolare Il calcolo può essere semplificato modificando lo hamiltonano: limitandosi a calcolare solo il
PIANO DI STUDIO D ISTITUTO
 PIANO DI STUDIO D ISTITUTO Materia: FISICA Casse 2 1 Quadrimestre Modulo 1 - RIPASSO INIZIALE Rappresentare graficamente nel piano cartesiano i risultati di un esperimento. Distinguere fra massa e peso
PIANO DI STUDIO D ISTITUTO Materia: FISICA Casse 2 1 Quadrimestre Modulo 1 - RIPASSO INIZIALE Rappresentare graficamente nel piano cartesiano i risultati di un esperimento. Distinguere fra massa e peso
Il legame ionico legame ionico
 Il legame ionico Il legame ionico è il legame che si realizza quando un atomo d un elemento fortemente elettropositivo (e quindi caratterizzato da bassa energia di ionizzazione) si combina con un atomo
Il legame ionico Il legame ionico è il legame che si realizza quando un atomo d un elemento fortemente elettropositivo (e quindi caratterizzato da bassa energia di ionizzazione) si combina con un atomo
Cinematica. Velocità. Riferimento Euleriano e Lagrangiano. Accelerazione. Elementi caratteristici del moto. Tipi di movimento
 Cinematica Velocità Riferimento Euleriano e Lagrangiano Accelerazione Elementi caratteristici del moto Tipi di movimento Testo di riferimento Citrini-Noseda par. 3.1 par. 3.2 par 3.3 fino a linee di fumo
Cinematica Velocità Riferimento Euleriano e Lagrangiano Accelerazione Elementi caratteristici del moto Tipi di movimento Testo di riferimento Citrini-Noseda par. 3.1 par. 3.2 par 3.3 fino a linee di fumo
Programma ministeriale (Matematica)
 SIMULAZIONE DELLA PROVA DI AMMISSIONE AI CORSI DI LAUREA E DI LAUREA MAGISTRALE A CICLO UNICO DIRETTAMENTE FINALIZZATI ALLA FORMAZIONE DI ARCHITETTO Anno Accademico 2015/2016 Test di Fisica e Matematica
SIMULAZIONE DELLA PROVA DI AMMISSIONE AI CORSI DI LAUREA E DI LAUREA MAGISTRALE A CICLO UNICO DIRETTAMENTE FINALIZZATI ALLA FORMAZIONE DI ARCHITETTO Anno Accademico 2015/2016 Test di Fisica e Matematica
POLITECNICO DI MILANO Fondamenti di Fisica Sperimentale, a. a I appello, 12 luglio 2016
 POLITECNICO DI MILANO Fondamenti di Fisica Sperimentale, a. a. 015-16 I appello, 1 luglio 016 Giustificare le risposte e scrivere in modo chiaro e leggibile. Scrivere in stampatello nome, cognome, matricola
POLITECNICO DI MILANO Fondamenti di Fisica Sperimentale, a. a. 015-16 I appello, 1 luglio 016 Giustificare le risposte e scrivere in modo chiaro e leggibile. Scrivere in stampatello nome, cognome, matricola
Il problema dei due corpi La dinamica planetaria
 Il problema dei due corpi La dinamica planetaria La Meccanica Classica Lagrange Hamilton Jacobi Vettori Per rendere conto della 3-dimensionalità in fisica, e in matematica, si usano delle grandezze più
Il problema dei due corpi La dinamica planetaria La Meccanica Classica Lagrange Hamilton Jacobi Vettori Per rendere conto della 3-dimensionalità in fisica, e in matematica, si usano delle grandezze più
CAMPO MAGNETICO Proprietà della magnetite (Fe 3 O 4 ): attira a sé materiali ferrosi o altre sostanze dette magnetiche Poli del magnete = parti in
 CAMPO MAGNETICO Proprietà della magnetite (Fe 3 O 4 ): attira a sé materiali ferrosi o altre sostanze dette magnetiche Poli del magnete = parti in cui si evidenzia tale proprietà Proprietà magnetiche possono
CAMPO MAGNETICO Proprietà della magnetite (Fe 3 O 4 ): attira a sé materiali ferrosi o altre sostanze dette magnetiche Poli del magnete = parti in cui si evidenzia tale proprietà Proprietà magnetiche possono
DISCIPLINA: Matematica CLASSE: 3^ SEZ.: SCIENTIFICO. Alunno/a: Voto proposto dal Consiglio:
 Viale Papa Giovanni XXIII 25 DISCIPLINA: Matematica CLASSE: 3^ SEZ.: SCIENTIFICO Alunno/a: Voto proposto dal Consiglio: : Disequazioni: o Irrazionali o Con valori assoluti Geometria Analitica: o Punto
Viale Papa Giovanni XXIII 25 DISCIPLINA: Matematica CLASSE: 3^ SEZ.: SCIENTIFICO Alunno/a: Voto proposto dal Consiglio: : Disequazioni: o Irrazionali o Con valori assoluti Geometria Analitica: o Punto
FORZE INTERMOLECOLARI
 FORZE INTERMOLECOLARI Le forze intermolecolari sono forze di attrazione che si stabiliscono tra le molecole che costituiscono una sostanza Determinano la tendenza delle molecole ad avvicinarsi. Per ogni
FORZE INTERMOLECOLARI Le forze intermolecolari sono forze di attrazione che si stabiliscono tra le molecole che costituiscono una sostanza Determinano la tendenza delle molecole ad avvicinarsi. Per ogni
LA CHIMICA DEL CARBONIO
 LA CHIMICA DEL CARBONIO E QUELLA PARTE DELLA CHIMICA CHE STUDIA IL CARBONIO E TUTTI I SUOI DERIVATI. I COMPOSTI DEL CARBONIO POSSONO ESSERE NATURALI (PROTEINE, ACIDI NUCLEICI, LIPIDI E CARBOIDRATI) colesterolo
LA CHIMICA DEL CARBONIO E QUELLA PARTE DELLA CHIMICA CHE STUDIA IL CARBONIO E TUTTI I SUOI DERIVATI. I COMPOSTI DEL CARBONIO POSSONO ESSERE NATURALI (PROTEINE, ACIDI NUCLEICI, LIPIDI E CARBOIDRATI) colesterolo
MOMENTI DI INERZIA PER CORPI CONTINUI
 MOMENTI D INERZIA E PENDOLO COMPOSTO PROF. FRANCESCO DE PALMA Indice 1 INTRODUZIONE -------------------------------------------------------------------------------------------------------------- 3 2 MOMENTI
MOMENTI D INERZIA E PENDOLO COMPOSTO PROF. FRANCESCO DE PALMA Indice 1 INTRODUZIONE -------------------------------------------------------------------------------------------------------------- 3 2 MOMENTI
Ricordiamo ora che a è legata ad x (derivata seconda) ed otteniamo
 Moto armonico semplice Consideriamo il sistema presentato in figura in cui un corpo di massa m si muove lungo l asse delle x sotto l azione della molla ideale di costante elastica k ed in assenza di forze
Moto armonico semplice Consideriamo il sistema presentato in figura in cui un corpo di massa m si muove lungo l asse delle x sotto l azione della molla ideale di costante elastica k ed in assenza di forze
Valitutti, Falasca, Tifi, Gentile. Chimica. concetti e modelli.blu
 Valitutti, Falasca, Tifi, Gentile Chimica concetti e modelli.blu 2 Capitolo 15 Le forze intermolecolari e gli stati condensati della materia 3 Sommario 1. Le forze intermolecolari 2. Molecole polari e
Valitutti, Falasca, Tifi, Gentile Chimica concetti e modelli.blu 2 Capitolo 15 Le forze intermolecolari e gli stati condensati della materia 3 Sommario 1. Le forze intermolecolari 2. Molecole polari e
Approfondimento sulla dinamica molecolare
 Approfondimento sulla dinamica molecolare 1. La valutazione delle grandezze termodinamiche nella dinamica molecolare Negli studi di dinamica molecolare siamo spesso interessati a esaminare l andamento
Approfondimento sulla dinamica molecolare 1. La valutazione delle grandezze termodinamiche nella dinamica molecolare Negli studi di dinamica molecolare siamo spesso interessati a esaminare l andamento
