Il primer utilizzato può essere specifico per il gene che si intende amplificare oppure aspecifico (oligo (dt) oppure random esameri).
|
|
|
- Gioacchino Galli
- 8 anni fa
- Visualizzazioni
Transcript
1 Retrotrascrizione l mrna viene convertito in cdna per mezzo dell enzima trascrittasi inversa (DNA polimerasi RNAdipendenti ricavate dai virus della mieloblastosi aviaria AMV o della leucemia murina di moloney MuLV) in presenza di nucleotidi e di un singolo primer. Il primer utilizzato può essere specifico per il gene che si intende amplificare oppure aspecifico (oligo (dt) oppure random esameri). 1
2 Il risultato della reazione di retrotrascrizione produce degli ibridi RNA-DNA. Per clonare le molecole di cdna, le catene di RNA devono essere distrutte e sostituite da DNA. Un metodo per far ciò consiste nell uso di RNasi H, che taglia l RNA negli ibridi; oppure L RNA viene allontanato dal DNA per semplice denaturazione ottenuta con riscaldamento. Il cdna fa poi da stampo nella successiva reazione di riamplificazione (PCR classica) in cui si utilizzano primers gene specifici (oppure un primer specifico ed un primer aspecifico). 2
3 PCR DNA polimerasi: enzima capace di produrre una catena di DNA complementare ad una catena a singolo filamento. Necessita di uno stampo e di un innesco con un 3 -OH libero. La PCR (reazione a catena della polimerasi) consente l amplificazione di un frammento di DNA specifico a partire da una minima quantità di DNA stampo. La reazione richiede: uno stampo di DNA, una miscela di nucleotidi e due inneschi (primers) che definiscono i punti di inizio della sintesi del DNA. Se si parte da DNA a doppio filamento è necessario separare le catene perché i primers possano poi legarsi alla zona a loro complementare. La PCR, quindi, consiste nel ripetersi di cicli in cui si fa variare la temperatura: a) denaturazione (94-95 C) rottura dei legami idrogeno e separazione dei filamenti b) appaiamento (T specifica) i primers legano la catena nella zona a loro complementare c) estensione (T ottimale per la polimerasi in uso) produzione dei frammenti Alla fine di x cicli di PCR, il prodotto viene controllato: tramite gel di agarosio oppure tramite sequenziamento ed utilizzato. 3
4 Scelta dei primers: la scelta dei primers viene effettuata seguendo alcuni criteri: a) devono avere una lunghezza compresa tra 17 e 30 nucleotidi b) la percentuale di GC ideale è del 50%; se il contenuto di GC è più basso sii devono usare primers lunghi per evitare Tm troppo basse c) evitare sequenze che contengano lunghe ripetizioni di singoli nucleotidi (più di 3-4) d) i primers non dovrebbero presentare strutture secondarie significative e) i primers non devono presentare complementarietà tra loro Scelta dei Primers 1) Cercare la sequenza del gene di interesse in banca dati 2) Identificare inizio e fine dell ORF (se si vuole clonare la porzione codificante) 3) Scrivere sequenza dei primers cercando di rispettare le regole dette Ad esempio >AK agtcgcggct gcgagatttg ggcacttttg ggggtgccgg tggcccgggc cgatggcgca 61 aggttgggca ggcttctctg aggaggaact gaggagacta aagcagacta aagggtacaa 121 gtgccctggc ctctggtctg actccagtag actcatgagg agacaaacca caaagttatg 181 tgatagtaga tattgcaaga acttgcttca gagacaagag gaacctcact ctgccgggga 241 ttggatggag cttgggaaga tttcacaaag tttgtgtgtt agcagaggcg cattttccag 301 gatccatttg aaccacagcg acgtctcccc gcgaagaaaa gtcgacaaca acttcagcga 361 gaaaaagccc ttgtagagca aagccaaaaa cttgggcttc aagatggatc aacctcatta 421 cttccagagc agctgctttc agcaccaaaa cagagaccat gaaactaaag cggatccaga 481 aggagttgca ggctttagat gacatggtgt cagctgacat tggaattctc aggaaccgga 541 ttgatcaggc cagcttagac tattcatacg ctcggaagcg gtttgacagg gctgaagcag 601 agtacattgc agcaaagcta gatatacagc gcaagactga gataaaagag caactcactg 661 aacacctttg tacgatcata cagcaaaatg agctccgaaa ggccaagaag ttggaggagt 721 tgatgcaaca actagatgta gaagccgatg aagagacttt ggagcttgag gtggaggtcg 781 agagattgct acacaaacaa gaagtagaat caaggagacc agtggttcgt ttagagaggc 841 catttcagcc tgcggaggag agtgtgacat tagaatttgc taaagagaac agaaagtgtc 901 aagaacaagc tgtttcccca aaggtagatg accagtgtgg aaattccagt agcatcccct 961 ttcttagtcc aaactgccca aatcaagaag gtaatgacat ttcagctgct ttggccacat 1021 gaagttctgg tattcttttg agctaatatg gtattgagta aagtatactt tttgcagtag 1081 atcatgccct gacctccaat aaaaacctct ttaaaacaat gctgattttt gaattcatga 1141 ttagttttag taaattaata ggtttggcca ttctaaaatc caaaattatg ataactgtat 1201 ttctaggggt atgtttcacc ttgattttgg cccggttctt tcagtgttcc gtttaccctt 1261 tttactgaaa gtaagtgact taaaaggatg gaagaaaaac tacatggttg gagtgttttt 1321 agatcagata aatatagaaa agtaaaatgg aaaatgatac tcaataccta gttaaactca 4
5 Se possibile la miscela di reazione va preparata in ghiaccio o si devono utilizzare Taq (es. AmpliTaq Gold) modificate che sono in grado di partire solo dopo essere state portate a 95 C. In tal modo si ce rca di minimizzare il rischio che i primer annilino a regioni non desiderate. Nested PCR: per ridurre il rischio di aspecifici si ricorre alla nested PCR. In questo caso il prodotto di una prima reazione di PCR viene usato come stampo per una seconda razione in cui si usano oligonucleotidi posti più internamente rispetto alla coppia iniziale. Polymerase chain reaction (PCR) Consente l amplificazione del DNA stampo. A. applicazioni B. Componenti della reazione C. procedura 5
6 A. PCR applicazioni Amplificazione del DNA per clonaggio di geni mutagenesi amplificazione di sequenze B. PCR componenti della reazione stampo (~10 4 molecole) DNA polimerasi termostabile (Taq or Pfu polimerasi) 2 DNA primers (10 17 molecole) 4 deossinucleotidi tampone I 2 primers legano il DNA su filamenti opposti primers stampo 5' Riscaldamento: separa I filamenti Raffreddamento: appaiamento dei primers 5' Primer #1 Primer #2 6
7 C. procedura 1. denaturare il DNA stampo stampo primers DNA polimerasi Denaturaz. a 94 C 2 appaiamento dei primers appaiamento a ~ 50ºC primers legano la regione complementare 3. estensione utilizzando la DNA polimerasi estensione a 72ºC 4. ripetizione steps 1-3, ~ 35 volte (35 cicli) 7
8 secondo ciclo denaturazione secondo ciclo appaiamento secondo ciclo estensione 8
9 35 cicli stampo Prodotto finale I primers sono incorporati nel prodotto Prodotto ottenuto da I molecola di stampo = (quantità di stampo) x 2 (numero di cicli) = (1) x 2 35 = 3.4 x molecole 34,000,000,000 Real Time PCR La PCR Real Time è in grado di misurare in tempo reale la concentrazione iniziale di una sequenza target in un campione biologico. Gli strumenti per PCR Real Time, oltre a fungere da termociclatori, eccitano i fluorocromi presenti nei campioni e convogliano quindi la fluorescenza emessa in risposta fino ad uno spettrografo. Appositi software acquisiscono lo spettro di emissione di ogni singolo campione per tutta la durata della PCR e convertono la variazione di fluorescenza del reporter in una rappresentazione in tempo reale della cinetica d amplificazione. 9
10 Il calcolo della quantità di DNA dei campioni incogniti viene effettuata determinando il ciclo della PCR (ciclo soglia, Ct) in cui viene raggiunto il valore soglia di fluorescenza del reporter e dove cioè i segnali di amplificazione specifici sono separabili da quelli del rumore di fondo del sistema. Il numero dei cicli necessari perché un campione raggiunga il suo Ct è inversamente proporzionale al numero di copie target presente inizialmente. Fluorescenza Cicli di amplificazione Il vantaggio in termini di precisione e di intervallo di quantificazione rispetto alle PCR tradizionali, è dovuto alla possibilità di quantificare il DNA al ciclo soglia, che è sempre calcolato nella fase esponenziale della reazione PCR, fase in cui i reagenti sono ancora lontani dall esaurimento e gli elementi di variabilità sono così ridotti al minimo. 10
11 SYBR Green: principio SYBR Green I Utilizza una molecola fluorescente non specifica che si lega al solco minore del DNA SYBR Green All inizio del processo di amplificazione, la miscela di reazione contiene DNA denaturato, primers e la molecola fluorescente 11
12 SYBR Green Dopo l annealing dei primers, si legano poche molecole fluorescenti alla doppia elica. SYBR Green Durante l elongazione si verifica un aumento di fluorescenza che corrisponde all aumento del numero di copie dell amplicone SYBR green Metodica semplice Possono essere utilizzati primers in uso in qualitativa Non costosa Non-specifica La molecola fluorescente si lega random a tutte le doppie e l i c h e, i n c l u d e n d o i d i m e r i d i p r i m e r s È necessario ottimizzare la metodica per evitare la f o r m a z i o n e d i p r o d o t t i a s p e c i f i c i 12
13 In seguito sono state utilizzate delle sonde caratterizzate dal fatto di essere un oligonucleotide dotato sia di un fluorocromo reporter che di un quencher. Quando la sonda è intatta, la fluorescenza del reporter è spenta dalla vicinanza del quencher; ma quando la sonda è rotta dalla Taq polimerasi, l attività dei fluorocromi viene rilevata. Uno dei saggi più diffusi per PCR real-time è il sistema TaqMan, il quale utilizza una sonda contenente due fluorocromi: FAM (6-carboxy-fluorescein) come reporter fluorescente legato covalentemente all estremità in 5 e TAMRA (6-carboxy-tetramethyl-rhodamine) come quencher fluorescente legato covalentemente all estremità in 3. Se è avvenuta l ibridazione, l attività 5 esonucleasica della Taq polimerasi rompe la sonda interna durante la fase di estensione, emettendo un segnale di fluorescenza. La possibilità di utilizzare vari tipi di fluorocromi per marcare sonde diverse consente di rilevare contemporaneamente più di una sequenza target in una sola reazione, realizzando così una reazione in multiplex. Sonda TaqMan Presenta all estremità 5 un fluoroforo Reporter ed all estremità 3 una molecola Quencher
14 Reporter-Quencher 5 REPORTER (R): fluorocromo ad alta energia che emette fluorescenza 3 QUENCHER (Q): fluorocromo a bassa energia che spegne la fluorescenza del reporter R Q 5 3 Se R e Q si trovano vicini, Q spegne l'effetto di R perchè i fotoni di R vengono assorbiti da Q Real-Time PCR: attività 5 >3 esonucleasica R Q 5 R Q R Q L aumento di fluorescenza del Reporter è direttamente proporzionale al numero di ampliconi generati Forward primer Probe Reverse primer 14
15 Real-Time PCR: la reazione COMPONENTI DELLA REAZIONE: 1) DNA target 2) DNA polimerasi 3) Due oligonucleotidi 4) dntps 5) Probe fluorescente Run Real-Time thermal cycle 3 min 95 C 15 s 50 cycles 50 C Activates Amplitaq Gold 55 C 65 C 1 min 2 min 30 s Activates UNG (Uracile N-Glicosilasi) Sonde FRET (Fluorescence Resonance Energy Transfer) Simili alle sonde TaqMan perché si legano al DNA bersaglio e vengono idrolizzate, ci sono però due sonde ognuna marcata con un solo fluorocromo (accettore e donatore) Quando le sonde non sono legate alle sequenze target il segnale fluorescente proveniente dall'accettore non è rilevato donatore accettore Durante lo step di annealing PCR, entrambe le sonde FRET ibridizzano alle sequenze target: ciò avvicina il fluoroforo donatore all'accettore permettendo il trasferimento di energia tra i due fluorofori e la produzione di un segnale fluorescente da parte dell'accettore che viene rilevato. 15
Real Time PCR. La PCR Real Time è in grado di misurare in tempo reale la concentrazione iniziale di una sequenza target in un campione biologico.
 eal Time PC La PC eal Time è in grado di misurare in tempo reale la concentrazione iniziale di una sequenza target in un campione biologico. Gli strumenti per PC eal Time, oltre a fungere da termociclatori,
eal Time PC La PC eal Time è in grado di misurare in tempo reale la concentrazione iniziale di una sequenza target in un campione biologico. Gli strumenti per PC eal Time, oltre a fungere da termociclatori,
Si può ottenere un a grande quantità di copie di DNA a partire da una singola molecola di DNA stampo La reazione è semplice ed automatizzabile E
 Si può ottenere un a grande quantità di copie di DNA a partire da una singola molecola di DNA stampo La reazione è semplice ed automatizzabile E possibile scegliere selettivamente cosa amplificare (specificità)
Si può ottenere un a grande quantità di copie di DNA a partire da una singola molecola di DNA stampo La reazione è semplice ed automatizzabile E possibile scegliere selettivamente cosa amplificare (specificità)
di Milazzo Gabriele Mangiagli Graziella Paternò Valentina Lomagno Valeria Mangione Enza Prof. C. Di Pietro
 di Milazzo Gabriele Mangiagli Graziella Paternò Valentina Lomagno Valeria Mangione Enza Prof. C. Di Pietro Polymerase Chain Reaction Inventata a metà degli anni 80 da Kary Mullis, è a tutt oggi uno strumento
di Milazzo Gabriele Mangiagli Graziella Paternò Valentina Lomagno Valeria Mangione Enza Prof. C. Di Pietro Polymerase Chain Reaction Inventata a metà degli anni 80 da Kary Mullis, è a tutt oggi uno strumento
AMPLIFICAZIONE IN VITRO DEL DNA REAZIONE A CATENA DELLA POLIMERASI (PCR)
 AMPLIFICAZIONE IN VITRO DEL DNA REAZIONE A CATENA DELLA POLIMERASI (PCR) PCR: reazione polimerasica a catena Inventata da Kary Mullis negli anni 80 (premio Nobel 1993) Serve per ottenere una grande quantita
AMPLIFICAZIONE IN VITRO DEL DNA REAZIONE A CATENA DELLA POLIMERASI (PCR) PCR: reazione polimerasica a catena Inventata da Kary Mullis negli anni 80 (premio Nobel 1993) Serve per ottenere una grande quantita
PCR - Polymerase Chain Reaction. ideata nel 1983 da Kary B. Mullis il quale ottenne, per questo, il premio Nobel per la chimica (1993).
 End point PCR vs quantitative Real-Time PCR PCR - Polymerase Chain Reaction ideata nel 1983 da Kary B. Mullis il quale ottenne, per questo, il premio Nobel per la chimica (1993). Questa tecnica, utilizzando
End point PCR vs quantitative Real-Time PCR PCR - Polymerase Chain Reaction ideata nel 1983 da Kary B. Mullis il quale ottenne, per questo, il premio Nobel per la chimica (1993). Questa tecnica, utilizzando
PRINCIPALI TIPI DI PCR a) PRINCIPALI TIPI DI PCR b)
 PRINCIPALI TIPI DI PCR a) RT-PCR: serve a valutare l espressione di un gene tramite l amplificazione dell mrna da esso trascritto PCR COMPETITIVA: serve a valutare la concentrazione iniziale di DNA o RNA
PRINCIPALI TIPI DI PCR a) RT-PCR: serve a valutare l espressione di un gene tramite l amplificazione dell mrna da esso trascritto PCR COMPETITIVA: serve a valutare la concentrazione iniziale di DNA o RNA
PCR. PCR o reazione di polimerizzazione a catena. Amplificazione esponenziale di DNA. Puo amplificare un tratto di DNA per piu di 1 milione di volte
 PCR Prof.ssa Flavia Frabetti PCR o reazione di polimerizzazione a catena Fine anni 80 Amplificazione esponenziale di DNA. Puo amplificare un tratto di DNA per piu di 1 milione di volte Permette di estrarre
PCR Prof.ssa Flavia Frabetti PCR o reazione di polimerizzazione a catena Fine anni 80 Amplificazione esponenziale di DNA. Puo amplificare un tratto di DNA per piu di 1 milione di volte Permette di estrarre
Isolamento e purificazione di DNA e RNA. -Separare gli acidi nucleici da altri componenti cellulari (lipidi e proteine)
 Isolamento e purificazione di DNA e RNA -Rompere la membrana cellulare -Separare gli acidi nucleici da altri componenti cellulari (lipidi e proteine) -Separare gli acidi nucleici tra loro -Rompere la membrana
Isolamento e purificazione di DNA e RNA -Rompere la membrana cellulare -Separare gli acidi nucleici da altri componenti cellulari (lipidi e proteine) -Separare gli acidi nucleici tra loro -Rompere la membrana
REAZIONE A CATENA DELLA POLIMERASI. ( PCR =Polymerase Chain Reaction)
 REAZIONE A CATENA DELLA POLIMERASI ( PCR =Polymerase Chain Reaction) Verso la metà degli anni 80, il biochimico Kary Mullis mise a punto un metodo estremamente rapido e semplice per produrre una quantità
REAZIONE A CATENA DELLA POLIMERASI ( PCR =Polymerase Chain Reaction) Verso la metà degli anni 80, il biochimico Kary Mullis mise a punto un metodo estremamente rapido e semplice per produrre una quantità
La reazione a catena della polimerasi (PCR) di Ofelia Leone e Vincenzo Mandarino
 La reazione a catena della polimerasi (PCR) di Ofelia Leone e Vincenzo Mandarino La Polymerase Chain Reaction (PCR) o reazione di amplificazione a catena è una tecnica che permette di amplificare una specifica
La reazione a catena della polimerasi (PCR) di Ofelia Leone e Vincenzo Mandarino La Polymerase Chain Reaction (PCR) o reazione di amplificazione a catena è una tecnica che permette di amplificare una specifica
SEQUENZIAMENTO DEL DNA
 SEQUENZIAMENTO DEL DNA Il metodo di Sanger per determinare la sequenza del DNA Il metodo manuale La reazione enzimatica Elettroforesi in gel denaturante di poliacrilammide Autoradiografia Il metodo automatico
SEQUENZIAMENTO DEL DNA Il metodo di Sanger per determinare la sequenza del DNA Il metodo manuale La reazione enzimatica Elettroforesi in gel denaturante di poliacrilammide Autoradiografia Il metodo automatico
PCR - Polymerase Chain Reaction
 PCR - Polymerase Chain Reaction ideata nel 1983 da Kary B. Mullis il quale ottenne, per questo, il premio Nobel per la chimica (1993). Questa tecnica, utilizzando i principi della duplicazione del DNA,
PCR - Polymerase Chain Reaction ideata nel 1983 da Kary B. Mullis il quale ottenne, per questo, il premio Nobel per la chimica (1993). Questa tecnica, utilizzando i principi della duplicazione del DNA,
Metodiche Molecolari
 Metodiche Molecolari La rivelazione degli acidi nucleici virali è un altro saggio che può essere utilizzato sia per verificare la presenza di un virus in un determinato campione biologico, sia per studiare
Metodiche Molecolari La rivelazione degli acidi nucleici virali è un altro saggio che può essere utilizzato sia per verificare la presenza di un virus in un determinato campione biologico, sia per studiare
TECNICHE DI BIOLOGIA MOLECOLARE. LA REAZIONE POLIMERASICA A CATENA Principi teorici e aspetti pratici
 TECNICHE DI BIOLOGIA MOLECOLARE LA REAZIONE POLIMERASICA A CATENA Principi teorici e aspetti pratici POLYMERASE CHAIN REACTION (PCR) 1955 A. Kronembreg e coll. (Stanford University) scoprono la DNA-polimerasi
TECNICHE DI BIOLOGIA MOLECOLARE LA REAZIONE POLIMERASICA A CATENA Principi teorici e aspetti pratici POLYMERASE CHAIN REACTION (PCR) 1955 A. Kronembreg e coll. (Stanford University) scoprono la DNA-polimerasi
Analisi dei marcatori molecolari della pluripotenza e del differenziamento delle cellule embrionali staminali (ES) murine
 Training Course 2010 Stem Cell Differentiation Napoli, 9-12 Novembre Analisi dei marcatori molecolari della pluripotenza e del differenziamento delle cellule embrionali staminali (ES) murine Cristina D
Training Course 2010 Stem Cell Differentiation Napoli, 9-12 Novembre Analisi dei marcatori molecolari della pluripotenza e del differenziamento delle cellule embrionali staminali (ES) murine Cristina D
PRINCIPALI APPLICAZIONI DELLA PCR. PRINCIPALI TIPI DI PCR a) PRINCIPALI TIPI DI PCR b) PRINCIPALI TIPI DI PCR a)
 EAZIONE A CATENA DELLA POLIMEASI (PC) PINCIPALI APPLICAZIONI DELLA PC UPPE primer LOWE primer GENE X 1. Identificazione di agenti patogeni nell uomo, negli animali o negli alimenti (batteri e virus) 2.
EAZIONE A CATENA DELLA POLIMEASI (PC) PINCIPALI APPLICAZIONI DELLA PC UPPE primer LOWE primer GENE X 1. Identificazione di agenti patogeni nell uomo, negli animali o negli alimenti (batteri e virus) 2.
PCR. (Reazione a catena della polimerasi) ESTRAZIONE del DNA da gel di AGAROSIO. Corso di INGEGNERIA GENETICA, Prof. Renato Fani,
 PCR (Reazione a catena della polimerasi) & ESTRAZIONE del DNA da gel di AGAROSIO Corso di INGEGNERIA GENETICA, Prof. Renato Fani, ESERCITAZIONE DI LAB. N.2 La PCR (Polymerase Chain Reaction) è una tecnica
PCR (Reazione a catena della polimerasi) & ESTRAZIONE del DNA da gel di AGAROSIO Corso di INGEGNERIA GENETICA, Prof. Renato Fani, ESERCITAZIONE DI LAB. N.2 La PCR (Polymerase Chain Reaction) è una tecnica
Analisi Molecolare di sequenze di acidi nucleici
 Analisi Molecolare di sequenze di acidi nucleici 1. L Analisi di restrizione di frammenti o RFLP (Restriction Fragment Lenght Polymorphism) di DNA comporta lo studio delle dimensioni dei frammenti di DNA
Analisi Molecolare di sequenze di acidi nucleici 1. L Analisi di restrizione di frammenti o RFLP (Restriction Fragment Lenght Polymorphism) di DNA comporta lo studio delle dimensioni dei frammenti di DNA
Tecniche molecolari per lo studio degli acidi nucleici
 Tecniche molecolari per lo studio degli acidi nucleici Prof.ssa Flavia Frabetti aa. 2010-11 Estrazione acidi nucleici (DNA o RNA) Verifica tramite elettroforesi su gel di agarosio Amplificazione o clonaggio
Tecniche molecolari per lo studio degli acidi nucleici Prof.ssa Flavia Frabetti aa. 2010-11 Estrazione acidi nucleici (DNA o RNA) Verifica tramite elettroforesi su gel di agarosio Amplificazione o clonaggio
Dopo aver effettuato la PCR, all interno della soluzione oltre al tratto amplificato sono presenti: primers, dntps, Taq polimerasi e tampone di
 Dopo aver effettuato la PCR, all interno della soluzione oltre al tratto amplificato sono presenti: primers, dntps, Taq polimerasi e tampone di reazione Inizialmente i 20 µl dell amplificato vengono
Dopo aver effettuato la PCR, all interno della soluzione oltre al tratto amplificato sono presenti: primers, dntps, Taq polimerasi e tampone di reazione Inizialmente i 20 µl dell amplificato vengono
Quantitative Real-time PCR
 Quantitative Real-time PCR Tecnica che consente la simultanea amplificazione e quantificazione del DNA target AMPLIFICAZIONE: prevede essenzialmente gli step di una classica PCR QUANTIFICAZIONE: effettuata
Quantitative Real-time PCR Tecnica che consente la simultanea amplificazione e quantificazione del DNA target AMPLIFICAZIONE: prevede essenzialmente gli step di una classica PCR QUANTIFICAZIONE: effettuata
I marcatori molecolari. Dipartimento di Scienze Agronomiche e Genetica Vegetale Agraria Corso di Genetica Agraria Giovanna Attene
 I marcatori molecolari Dipartimento di Scienze Agronomiche e Genetica Vegetale Agraria Corso di Genetica Agraria Giovanna Attene Marcatori molecolari del DNA I marcatori molecolari sono sequenze di DNA
I marcatori molecolari Dipartimento di Scienze Agronomiche e Genetica Vegetale Agraria Corso di Genetica Agraria Giovanna Attene Marcatori molecolari del DNA I marcatori molecolari sono sequenze di DNA
Note Tecniche al LightCycler Selezione di sonde di ibridazione per LightCycler. Olfert Landt e Andreas Nitsche, TIB MOLBIOL, Berlino
 Note Tecniche al LightCycler Selezione di sonde di ibridazione per LightCycler Olfert Landt e Andreas Nitsche, TIB MOLBIOL, Berlino 1. Introduzione Scopo di questa nota La detezione di amplicon specifici
Note Tecniche al LightCycler Selezione di sonde di ibridazione per LightCycler Olfert Landt e Andreas Nitsche, TIB MOLBIOL, Berlino 1. Introduzione Scopo di questa nota La detezione di amplicon specifici
PCR Polymerase Chain Reaction = Reazione a catena della polimerasi
 PR Polymerase hain Reaction = Reazione a catena della polimerasi mplifica un frammento di D di cui si conosce almeno in parte la sequenza Utilizza un enzima, la D Polimerasi, per copiare una molecola di
PR Polymerase hain Reaction = Reazione a catena della polimerasi mplifica un frammento di D di cui si conosce almeno in parte la sequenza Utilizza un enzima, la D Polimerasi, per copiare una molecola di
Come si traccia un alimento di origine animale? Dalle lasagne con carne di cavallo. alla realtà di ogni giorno
 Editoriale n.10 Newsletter aprile 2013 Come si traccia un alimento di origine animale? Dalle lasagne con carne di cavallo alla realtà di ogni giorno Identificare la specie, un obiettivo fondamentale quando
Editoriale n.10 Newsletter aprile 2013 Come si traccia un alimento di origine animale? Dalle lasagne con carne di cavallo alla realtà di ogni giorno Identificare la specie, un obiettivo fondamentale quando
Metodiche di analisi del DNA (cenni) (Ingegneria genetica)
 DNA Metodiche di analisi del DNA (cenni) (Ingegneria genetica) Principali tecniche di base Enzimi di restrizione (Endonucleasi) Gel elettroforesi Ibridizzazione PCR (Polymerase Chain Reaction) Sequenziamento
DNA Metodiche di analisi del DNA (cenni) (Ingegneria genetica) Principali tecniche di base Enzimi di restrizione (Endonucleasi) Gel elettroforesi Ibridizzazione PCR (Polymerase Chain Reaction) Sequenziamento
Protocollo Crime Scene Investigation
 Protocollo Crime Scene Investigation Precauzioni da adottare in laboratorio: - non mangiare o bere - indossare sempre i guanti quando si maneggiano i tubini, i gel, le micropipette - nel dubbio, chiedere!
Protocollo Crime Scene Investigation Precauzioni da adottare in laboratorio: - non mangiare o bere - indossare sempre i guanti quando si maneggiano i tubini, i gel, le micropipette - nel dubbio, chiedere!
Biotecnologie applicate all ispezione degli alimenti di origine animale
 Prof.ssa Tiziana Pepe Evoluzioni della tecnica PCR Biotecnologie applicate all ispezione degli alimenti di origine animale Dip. di Medicina Veterinaria e Produzioni animali tiziana.pepe@unina.it Nested
Prof.ssa Tiziana Pepe Evoluzioni della tecnica PCR Biotecnologie applicate all ispezione degli alimenti di origine animale Dip. di Medicina Veterinaria e Produzioni animali tiziana.pepe@unina.it Nested
8-06-2010. BLOTTING degli acidi nucleici: RT-PCR SOUTHERN BLOTTING NORTHERN BLOTTING. BLOTTING delle proteine: NORTHERN BLOTTING SOUTHERN BLOTTING
 8-06-2010 TECNICHE PER L ANALISI DELL ESPRESSIONE GENICA BLOTTING degli acidi nucleici: RT-PCR REAL TIME PCR SOUTHERN BLOTTING NORTHERN BLOTTING NORTHERN BLOTTING BLOTTING delle proteine: MICROARRAYS MACROARRAYS
8-06-2010 TECNICHE PER L ANALISI DELL ESPRESSIONE GENICA BLOTTING degli acidi nucleici: RT-PCR REAL TIME PCR SOUTHERN BLOTTING NORTHERN BLOTTING NORTHERN BLOTTING BLOTTING delle proteine: MICROARRAYS MACROARRAYS
LEZIONE X FUNZIONAMENTO E APPLICAZIONI DELLA PCR. Dott. Paolo Cascio
 LEZIONE X FUNZIONAMENTO E APPLICAZIONI DELLA PCR Dott. Paolo Cascio Tecnica della reazione a catena della DNA polimerasi o PCR (Polymerase Chain Reaction) 1) Introdotta da Kary Mullis alla metà degli anni
LEZIONE X FUNZIONAMENTO E APPLICAZIONI DELLA PCR Dott. Paolo Cascio Tecnica della reazione a catena della DNA polimerasi o PCR (Polymerase Chain Reaction) 1) Introdotta da Kary Mullis alla metà degli anni
ANALISI POST-GENOMICHE TRASCRITTOMA: CONTENUTO DI RNA DI UNA CELLULA.
 TECNICHE PER L ANALISI DELL ESPRESSIONE GENICA RT-PCR REAL TIME PCR NORTHERN BLOTTING ANALISI POST-GENOMICHE Conoscere la sequenza genomica di un organismo non è che l inizio di una serie di esperimenti
TECNICHE PER L ANALISI DELL ESPRESSIONE GENICA RT-PCR REAL TIME PCR NORTHERN BLOTTING ANALISI POST-GENOMICHE Conoscere la sequenza genomica di un organismo non è che l inizio di una serie di esperimenti
Metodi di analisi mutazionale
 Metodi di analisi mutazionale I metodi impiegati per l analisi di mutazioni o polimorfismi nel DNA genomico possono essere suddivise in due principali categorie: (1) metodi per individuare mutazioni note,
Metodi di analisi mutazionale I metodi impiegati per l analisi di mutazioni o polimorfismi nel DNA genomico possono essere suddivise in due principali categorie: (1) metodi per individuare mutazioni note,
Applicazione dei metodi rapidi alla microbiologia alimentare: Real Time PCR per la determinazione dei virus enterici
 "Focus su sicurezza d'uso e nutrizionale degli alimenti" 21-22 Novembre 2005 Applicazione dei metodi rapidi alla microbiologia alimentare: Real Time PCR per la determinazione dei virus enterici Simona
"Focus su sicurezza d'uso e nutrizionale degli alimenti" 21-22 Novembre 2005 Applicazione dei metodi rapidi alla microbiologia alimentare: Real Time PCR per la determinazione dei virus enterici Simona
Lezione XLI-XLII martedì 17-1-2012
 Lezione XLI-XLII martedì 17-1-2012 corso di genomica aula 8 orario : Martedì ore 14.00-16.00 Giovedì ore 13.00-15.00 Esami 31- gennaio 2012 7- febbraio 2012 28 - febbraio 2012 D. Frezza Esercitazione II
Lezione XLI-XLII martedì 17-1-2012 corso di genomica aula 8 orario : Martedì ore 14.00-16.00 Giovedì ore 13.00-15.00 Esami 31- gennaio 2012 7- febbraio 2012 28 - febbraio 2012 D. Frezza Esercitazione II
Controllo ufficiale degli OGM nel settore agroalimentare
 Controllo ufficiale degli OGM nel settore agroalimentare Ugo Marchesi Istituto Zooprofilattico Sperimentale Lazio e Toscana Centro di Referenza Nazionale per la ricerca di OGM ugo.marchesi@izslt.it ORGANISMI
Controllo ufficiale degli OGM nel settore agroalimentare Ugo Marchesi Istituto Zooprofilattico Sperimentale Lazio e Toscana Centro di Referenza Nazionale per la ricerca di OGM ugo.marchesi@izslt.it ORGANISMI
Analisi di polimorfismi usati per la caratterizzazione di profili genetici in campioni di. DNA umano. 22-26 giugno 2009
 Analisi di polimorfismi usati per la caratterizzazione di profili genetici in campioni di 22-26 giugno 2009 DNA umano 1 GENETICA FORENSE La genetica forense applica tecniche di biologia molecolare al fine
Analisi di polimorfismi usati per la caratterizzazione di profili genetici in campioni di 22-26 giugno 2009 DNA umano 1 GENETICA FORENSE La genetica forense applica tecniche di biologia molecolare al fine
Metodica fu ideata nel 1983
 Metodica fu ideata nel 1983 PCR - Polymerase Chain Reaction ideata nel 1983 da Kary B. Mullis il quale ottenne, per questo, il premio Nobel per la chimica (1993). Questa tecnica, utilizzando i principi
Metodica fu ideata nel 1983 PCR - Polymerase Chain Reaction ideata nel 1983 da Kary B. Mullis il quale ottenne, per questo, il premio Nobel per la chimica (1993). Questa tecnica, utilizzando i principi
Protocollo di Real-Time RT-PCR per la diagnosi del fitoplasma della Moria del Pero. Claudio Ratti, Chiara Lanzoni e Carlo Poggi Pollini
 Protocollo di Real-Time RT-PCR per la diagnosi del fitoplasma della Moria del Pero Claudio Ratti, Chiara Lanzoni e Carlo Poggi Pollini Moria del pero (Candidatus Phytoplasma pyri) Fitoplasmi: Microrganismi
Protocollo di Real-Time RT-PCR per la diagnosi del fitoplasma della Moria del Pero Claudio Ratti, Chiara Lanzoni e Carlo Poggi Pollini Moria del pero (Candidatus Phytoplasma pyri) Fitoplasmi: Microrganismi
immagine Biologia applicata alla ricerca bio-medica Materiale Didattico Docente: Di Bernardo
 Esperto in processi innovativi di sintesi biomolecolare applicata a tecniche di epigenetica Materiale Didattico Biologia applicata alla ricerca bio-medica immagine Docente: Di Bernardo HUMAN GENOME PROJECT
Esperto in processi innovativi di sintesi biomolecolare applicata a tecniche di epigenetica Materiale Didattico Biologia applicata alla ricerca bio-medica immagine Docente: Di Bernardo HUMAN GENOME PROJECT
SAGE: Serial Analysis of Gene Expression
 SAGE: Serial Analysis of Gene Expression L insieme di tutti gli mrna presenti in una cellula si definisce trascrittoma. Ogni trascrittoma ha una composizione complessa, con migliaia di mrna diversi, ciascuno
SAGE: Serial Analysis of Gene Expression L insieme di tutti gli mrna presenti in una cellula si definisce trascrittoma. Ogni trascrittoma ha una composizione complessa, con migliaia di mrna diversi, ciascuno
LA REAZIONE A CATENA DELLA POLIMERASI PCR
 LA REAZIONE A CATENA DELLA POLIMERASI PCR INTRODUZIONE Tecnica ideata da Mullis e collaboratori nel 1984 La possibilita' di disporre di quantità virtualmente illimitate di un determinato frammento di DNA,
LA REAZIONE A CATENA DELLA POLIMERASI PCR INTRODUZIONE Tecnica ideata da Mullis e collaboratori nel 1984 La possibilita' di disporre di quantità virtualmente illimitate di un determinato frammento di DNA,
scaricato da www.sunhope.it LA TECNOLOGIA DEI MICROARRAYS
 LA TECNOLOGIA DEI MICROARRAYS 1 8 anni dopo: 4162 riferimenti bibliografici sui microarrays I microarrays misurano il livello di espressione degli mrna trascritti dai geni del sistema biologico di interesse
LA TECNOLOGIA DEI MICROARRAYS 1 8 anni dopo: 4162 riferimenti bibliografici sui microarrays I microarrays misurano il livello di espressione degli mrna trascritti dai geni del sistema biologico di interesse
ZytoLight SPEC ERG Dual Color Break Apart Probe
 ZytoLight SPEC ERG Dual Color Break Apart Probe IVD Dispositivo medico-diagnostico in vitro Produttore: ZytoVision GmbH Codice: Z-2138-200 (0.2ml).. Per l identificazione della traslocazione che coinvolge
ZytoLight SPEC ERG Dual Color Break Apart Probe IVD Dispositivo medico-diagnostico in vitro Produttore: ZytoVision GmbH Codice: Z-2138-200 (0.2ml).. Per l identificazione della traslocazione che coinvolge
La possibilita di conoscere i geni deriva dalla capacita di manipolarli:
 La possibilita di conoscere i geni deriva dalla capacita di manipolarli: -isolare un gene (enzimi di restrizione) -clonaggio (amplificazione) vettori -sequenziamento -funzione Il gene o la sequenza
La possibilita di conoscere i geni deriva dalla capacita di manipolarli: -isolare un gene (enzimi di restrizione) -clonaggio (amplificazione) vettori -sequenziamento -funzione Il gene o la sequenza
PCR (Polymerase Chain Reaction)
 PCR (Polymerase Chain Reaction) Metodo enzimatico estremamente rapido e semplice per produrre una quantità illimitata di copie della sequenza di un singolo gene Sometime a good idea comes to yow when you
PCR (Polymerase Chain Reaction) Metodo enzimatico estremamente rapido e semplice per produrre una quantità illimitata di copie della sequenza di un singolo gene Sometime a good idea comes to yow when you
SINTESI DELL RNA. Replicazione. Trascrizione. Traduzione
 SINTESI DELL RNA Replicazione Trascrizione Traduzione L RNA ha origine da informazioni contenute nel DNA La TRASCRIZIONE permette la conversione di una porzione di DNA in una molecola di RNA con una sequenza
SINTESI DELL RNA Replicazione Trascrizione Traduzione L RNA ha origine da informazioni contenute nel DNA La TRASCRIZIONE permette la conversione di una porzione di DNA in una molecola di RNA con una sequenza
Analisi molecolare dei geni
 Analisi molecolare dei geni Denaturazione e rinaturazione di una molecola di DNA Si rompono i legami idrogeno 100 C Denaturazione del DNA Rinaturazione per riassociazione delle sequenze complementari Ogni
Analisi molecolare dei geni Denaturazione e rinaturazione di una molecola di DNA Si rompono i legami idrogeno 100 C Denaturazione del DNA Rinaturazione per riassociazione delle sequenze complementari Ogni
Amplificazione del DNA tramite reazione a catena della polimerasi (POLYMERASE CHAIN REACTION; PCR) e sue applicazioni in ambito biomedico
 Amplificazione del DNA tramite reazione a catena della polimerasi (POLYMERASE CHAIN REACTION; PCR) e sue applicazioni in ambito biomedico Dottoressa Camerin Consuelo Laboratorio Oncoematologia Pediatrica
Amplificazione del DNA tramite reazione a catena della polimerasi (POLYMERASE CHAIN REACTION; PCR) e sue applicazioni in ambito biomedico Dottoressa Camerin Consuelo Laboratorio Oncoematologia Pediatrica
DNA - RNA. Nucleotide = Gruppo Fosforico + Zucchero Pentoso + Base Azotata. Le unità fondamentali costituenti il DNA e l RNA sono i Nucleotidi.
 DNA - RNA Le unità fondamentali costituenti il DNA e l RNA sono i Nucleotidi. Nucleotide = Gruppo Fosforico + Zucchero Pentoso + Base Azotata. Esistono 4 basi azotate per il DNA e 4 per RNA Differenze
DNA - RNA Le unità fondamentali costituenti il DNA e l RNA sono i Nucleotidi. Nucleotide = Gruppo Fosforico + Zucchero Pentoso + Base Azotata. Esistono 4 basi azotate per il DNA e 4 per RNA Differenze
immagine Biologia applicata alla ricerca bio-medica Materiale Didattico Docente: Di Bernardo
 Esperto in processi innovativi di sintesi biomolecolare applicata a tecniche di epigenetica Materiale Didattico Biologia applicata alla ricerca bio-medica immagine Docente: Di Bernardo TECNICHE PER L ANALISI
Esperto in processi innovativi di sintesi biomolecolare applicata a tecniche di epigenetica Materiale Didattico Biologia applicata alla ricerca bio-medica immagine Docente: Di Bernardo TECNICHE PER L ANALISI
La farmacogeneticanella gestione del paziente con tumore colorettale, l esperienza traslazionaleal CRO di Aviano
 SOC di Farmacologia Sperimentale e Clinica VI CONGRESSO NAZIONALE FITeLab Slow Medicine Laboratory: IT s the Future 1-2-3 Ottobre 2015 Ospedale Borgo Roma (Verona) La farmacogeneticanella gestione del
SOC di Farmacologia Sperimentale e Clinica VI CONGRESSO NAZIONALE FITeLab Slow Medicine Laboratory: IT s the Future 1-2-3 Ottobre 2015 Ospedale Borgo Roma (Verona) La farmacogeneticanella gestione del
Quantificazione di. legionella pneumophila. mediante metodo biomolecolare
 Quantificazione di legionella pneumophila mediante metodo biomolecolare Laboratorio di Epidemiologia Genetica e Genomica di Sanità Pubblica Istituto di Igiene LABORATORIO DI EPIDEMIOLOGIA GENETICA: ATTIVITA
Quantificazione di legionella pneumophila mediante metodo biomolecolare Laboratorio di Epidemiologia Genetica e Genomica di Sanità Pubblica Istituto di Igiene LABORATORIO DI EPIDEMIOLOGIA GENETICA: ATTIVITA
Polimorfismi LEZIONE 6. By NA 1
 Polimorfismi LEZIONE 6 By NA 1 * Polimorfismo Variazione presente nella popolazione con una frequenza superiore a 1% Variazioni nell aspetto By NA 2 Polimorfismo proteico Variazione presente nella popolazione
Polimorfismi LEZIONE 6 By NA 1 * Polimorfismo Variazione presente nella popolazione con una frequenza superiore a 1% Variazioni nell aspetto By NA 2 Polimorfismo proteico Variazione presente nella popolazione
RNA polimerasi operone. L operatore è il tratto
 La regolazione genica nei procarioti Alcune proteine vengono prodotte dalla cellula ad un ritmo relativamente costante e l attività dei geni che codificano queste proteine non è regolata in modo sofisticato.
La regolazione genica nei procarioti Alcune proteine vengono prodotte dalla cellula ad un ritmo relativamente costante e l attività dei geni che codificano queste proteine non è regolata in modo sofisticato.
ABI-7700 User Bulletin #5
 ABI-7700 User Bulletin #5 1. halogen tungsten lamp 2b. emission filters 3. intensifier 5. ccd detector 350,000 pixels 2a. excitation filters 4. sample plate www.biorad.com 3 Real-time qpcr - La fluorescenza
ABI-7700 User Bulletin #5 1. halogen tungsten lamp 2b. emission filters 3. intensifier 5. ccd detector 350,000 pixels 2a. excitation filters 4. sample plate www.biorad.com 3 Real-time qpcr - La fluorescenza
LA GENETICA: DNA e RNA LA GENETICA. DNA e RNA. Prof. Daniele Verri
 LA GENETICA DNA e RNA Prof. Daniele Verri L'acido desossiribonucleico o deossiribonucleico (DNA) è un acido nucleico che contiene le informazioni necessarie per la formazione di RNA e proteine. LA GENETICA:
LA GENETICA DNA e RNA Prof. Daniele Verri L'acido desossiribonucleico o deossiribonucleico (DNA) è un acido nucleico che contiene le informazioni necessarie per la formazione di RNA e proteine. LA GENETICA:
Identificazione dei microrganismi mediante tecniche di biologia molecolare Esercitazione n 3. Criteri di identificazione
 Identificazione dei microrganismi mediante tecniche di biologia molecolare Esercitazione n 3 Criteri di identificazione Tradizionale (fenotipo) Tecniche di biologia molecolare Il livello di risoluzione
Identificazione dei microrganismi mediante tecniche di biologia molecolare Esercitazione n 3 Criteri di identificazione Tradizionale (fenotipo) Tecniche di biologia molecolare Il livello di risoluzione
METODI DI MARCATURA DEGLI ACIDI NUCLEICI
 METODI DI MARCATURA DEGLI ACIDI NUCLEICI Marcatura di acidi nucleici Una sonda per ibridazione è una molecola di DNA marcata, con una sequenza complementare al DNA bersaglio da individuare. Poiché la sonda
METODI DI MARCATURA DEGLI ACIDI NUCLEICI Marcatura di acidi nucleici Una sonda per ibridazione è una molecola di DNA marcata, con una sequenza complementare al DNA bersaglio da individuare. Poiché la sonda
PROGETTO DNA chiavi in mano. Le Biotecnologie in classe e in laboratorio 11/03/2015 Prof.ssa Paola Cazzani I.T.E. A. Bassi - Lodi
 PROGETTO DNA chiavi in mano Le Biotecnologie in classe e in laboratorio 11/03/2015 Prof.ssa Paola Cazzani I.T.E. A. Bassi - Lodi PROGETTO DNA chiavi in mano PROGETTO DNA chiavi in mano IFOM PROGETTO DNA
PROGETTO DNA chiavi in mano Le Biotecnologie in classe e in laboratorio 11/03/2015 Prof.ssa Paola Cazzani I.T.E. A. Bassi - Lodi PROGETTO DNA chiavi in mano PROGETTO DNA chiavi in mano IFOM PROGETTO DNA
Real Time PCR: Principi e Chimiche Fluorogeniche
 Real Time PCR: Principi e Chimiche Fluorogeniche M. Favarato Medicina di Laboratorio UOS Biologia Molecolare - Ulss13 Mirano Cenni Storici Prima dell avvento della PCR l analisi molecolare si avvaleva
Real Time PCR: Principi e Chimiche Fluorogeniche M. Favarato Medicina di Laboratorio UOS Biologia Molecolare - Ulss13 Mirano Cenni Storici Prima dell avvento della PCR l analisi molecolare si avvaleva
PROGETTO BIOFORM Corso didattico sperimentale. Esercizio. Tipizzazione del gene PV92
 PROGETTO BIOFORM Corso didattico sperimentale Esercizio Tipizzazione del gene PV92 Elementi trasponibili Che cosa sono gli elementi trasponibili? Sono segmenti di DNA che sono in grado di trasferirsi in
PROGETTO BIOFORM Corso didattico sperimentale Esercizio Tipizzazione del gene PV92 Elementi trasponibili Che cosa sono gli elementi trasponibili? Sono segmenti di DNA che sono in grado di trasferirsi in
SELEZIONE ASSISTITA PER LA RESISTENZA patogeni in orzo
 C.R.A. Consiglio per la Ricerca in Agricoltura Centro di ricerca per la genomica Fiorenzuola d Arda (Piacenza) SELEZIONE ASSISTITA PER LA RESISTENZA patogeni in orzo Tutor: Dott. Gianni TACCONI Studente:
C.R.A. Consiglio per la Ricerca in Agricoltura Centro di ricerca per la genomica Fiorenzuola d Arda (Piacenza) SELEZIONE ASSISTITA PER LA RESISTENZA patogeni in orzo Tutor: Dott. Gianni TACCONI Studente:
La tecnica Real-Time PCR nelle analisi alimentari: Sicurezza e prevenzione delle frodi
 La tecnica Real-Time PCR nelle analisi alimentari: Sicurezza e prevenzione delle frodi -Dr. Matteo D Andrea- -Product Specialist PCR, R-Biopharm Italia- Scandali alimentari: Sempre maggiore attenzione
La tecnica Real-Time PCR nelle analisi alimentari: Sicurezza e prevenzione delle frodi -Dr. Matteo D Andrea- -Product Specialist PCR, R-Biopharm Italia- Scandali alimentari: Sempre maggiore attenzione
REPLICAZIONE DEL DNA
 REPLICAZIONE DEL DNA La replicazione (o anche duplicazione) è il meccanismo molecolare attraverso cui il DNA produce una copia di sé stesso. Ogni volta che una cellula si divide, infatti, l'intero genoma
REPLICAZIONE DEL DNA La replicazione (o anche duplicazione) è il meccanismo molecolare attraverso cui il DNA produce una copia di sé stesso. Ogni volta che una cellula si divide, infatti, l'intero genoma
PCR LIMITI. PCR Quantitativa
 PCR QUANTITATIVA PCR LIMITI -Falsi Positivi -Analisi Qualitativa NUOVE PROSPETTIVE PCR Quantitativa PCR QUANTITATIVA Misura l'amplificazione in tempo reale durante la fase esponenziale della PCR, quando
PCR QUANTITATIVA PCR LIMITI -Falsi Positivi -Analisi Qualitativa NUOVE PROSPETTIVE PCR Quantitativa PCR QUANTITATIVA Misura l'amplificazione in tempo reale durante la fase esponenziale della PCR, quando
Immagine di una sequenza ben riuscita. Sequences troubleshooting
 Immagine di una sequenza ben riuscita. Sequences troubleshooting Sequenza fallita Reazione fallita: non presenta picchi definiti e ha un alto rumore di fondo. il primer non trova sito di annealing il DNA
Immagine di una sequenza ben riuscita. Sequences troubleshooting Sequenza fallita Reazione fallita: non presenta picchi definiti e ha un alto rumore di fondo. il primer non trova sito di annealing il DNA
Come funzionano gli oligo Antisenso? RNA WORLD. mrna. Regolare l espressione genica tramite molecole di RNA. Come funzionano gli oligo antisenso?
 RNA WORLD RNA Come funzionano gli oligo Antisenso? mrna Non coding RNA AAAAAAA rrna trna snrna snorna RNA Antisenso sirna Arresto della traduzione Proteina incompleta o nessuna sintesi MECCANISMO PASSIVO
RNA WORLD RNA Come funzionano gli oligo Antisenso? mrna Non coding RNA AAAAAAA rrna trna snrna snorna RNA Antisenso sirna Arresto della traduzione Proteina incompleta o nessuna sintesi MECCANISMO PASSIVO
Analisi qualitativa con Agilent BioAnalyzer. cdna, RNA Totale e Messaggero e small RNA
 Il Servizio di Biologia Molecolare si è di recente dotato di uno strumento per l analisi qualitativa e quantitativa degli acidi nucleici Agilent Bioanalyzer 2100 e ha implementato tale tecnologia nell
Il Servizio di Biologia Molecolare si è di recente dotato di uno strumento per l analisi qualitativa e quantitativa degli acidi nucleici Agilent Bioanalyzer 2100 e ha implementato tale tecnologia nell
DOMANDA FREQUENTE: QUALE E LA FUNZIONE DI UNA CERTA PROTEINA? SI AUMENTA O SI DIMINUISCE L ESPRESSIONE DELLA PROTEINA
 DOMANDA FREQUENTE: QUALE E LA FUNZIONE DI UNA CERTA PROTEINA? OVERESPRESSIONE DELLA PROTEINA ESPRESSIONE ECTOPICA CON UN VETTORE DI ESPRESSIONE ABOLIZIONE DELLA ESPRESSIONE DELLA PROTEINA INTERFERENZA
DOMANDA FREQUENTE: QUALE E LA FUNZIONE DI UNA CERTA PROTEINA? OVERESPRESSIONE DELLA PROTEINA ESPRESSIONE ECTOPICA CON UN VETTORE DI ESPRESSIONE ABOLIZIONE DELLA ESPRESSIONE DELLA PROTEINA INTERFERENZA
ELETTROFORESI SU GEL
 ELETTROFORESI SU GEL Permette la separazione di frammenti di DNA/RNA da una miscela complessa E una tecnica fondamentale per: l analisi (elettroforesi analitica) la purificazione degli acidi nucleici (elettroforesi
ELETTROFORESI SU GEL Permette la separazione di frammenti di DNA/RNA da una miscela complessa E una tecnica fondamentale per: l analisi (elettroforesi analitica) la purificazione degli acidi nucleici (elettroforesi
LA DIAGNOSTICA MOLECOLARE E I TUMORI DEL SANGUE
 LA DIAGNOSTICA MOLECOLARE E I TUMORI DEL SANGUE UNA NUOVA FRONTIERA NELLA DIAGNOSI DI ALCUNI TUMORI La diagnostica molecolare ha l obiettivo di accertare un ampia varietà di patologie (infettive, oncologiche
LA DIAGNOSTICA MOLECOLARE E I TUMORI DEL SANGUE UNA NUOVA FRONTIERA NELLA DIAGNOSI DI ALCUNI TUMORI La diagnostica molecolare ha l obiettivo di accertare un ampia varietà di patologie (infettive, oncologiche
TECNICHE DI BIOLOGIA MOLECOLARE. LA REAZIONE POLIMERASICA A CATENA Principi teorici e aspetti pratici
 TECNICHE DI BIOLOGIA MOLECOLARE LA REAZIONE POLIMERASICA A CATENA Principi teorici e aspetti pratici POLYMERASE CHAIN REACTION (PCR) 1955 A. Kronembreg e coll. (Stanford University) scoprono la DNA-polimerasi
TECNICHE DI BIOLOGIA MOLECOLARE LA REAZIONE POLIMERASICA A CATENA Principi teorici e aspetti pratici POLYMERASE CHAIN REACTION (PCR) 1955 A. Kronembreg e coll. (Stanford University) scoprono la DNA-polimerasi
METODI ALTERNATIVI. PCR digitale per la rilevazione e quantificazione. assoluta del DNA
 METODI ALTERNATIVI PCR digitale per la rilevazione e quantificazione assoluta del DNA Roma, 25 settembre 2013 Giuseppina Buonincontro IZS PLV- S.S. Controllo Alimenti La prima generazione di PCR consente
METODI ALTERNATIVI PCR digitale per la rilevazione e quantificazione assoluta del DNA Roma, 25 settembre 2013 Giuseppina Buonincontro IZS PLV- S.S. Controllo Alimenti La prima generazione di PCR consente
ZytoLight SPEC ALK Dual Color Break Apart Probe
 ZytoLight SPEC ALK Dual Color Break Apart Probe Z-2124-200 20 (0.2 ml) Z-2124-50 5 (0.05 ml) Per la rilevazione della traslocazione che coinvolge il gene ALK a 2p23 mediante ibridazione in situ fluorescente
ZytoLight SPEC ALK Dual Color Break Apart Probe Z-2124-200 20 (0.2 ml) Z-2124-50 5 (0.05 ml) Per la rilevazione della traslocazione che coinvolge il gene ALK a 2p23 mediante ibridazione in situ fluorescente
Lezione IX-X martedì 25-X-2011
 Lezione IX-X martedì 25-X-2011 corso di genomica laurea magistrale Biotecnologia Industriale aula 8 orario : Martedì ore 14.00-16.00 Giovedì ore 13.00-15.00 non ci sarà lezione martedì 1 e giovedì 3 Novembre
Lezione IX-X martedì 25-X-2011 corso di genomica laurea magistrale Biotecnologia Industriale aula 8 orario : Martedì ore 14.00-16.00 Giovedì ore 13.00-15.00 non ci sarà lezione martedì 1 e giovedì 3 Novembre
Dott.ssa Quintarelli Concetta
 Dott.ssa Quintarelli Concetta Estrazione e quantizzazione degli acidi nucleici Pre-PCR Accetazione Post-PCR Refertazione Area PCR GUANTI MONOUSO PUNTALI CON FILTRO CESTELLO PER GHIACCIO TUBINI PCR Materiale
Dott.ssa Quintarelli Concetta Estrazione e quantizzazione degli acidi nucleici Pre-PCR Accetazione Post-PCR Refertazione Area PCR GUANTI MONOUSO PUNTALI CON FILTRO CESTELLO PER GHIACCIO TUBINI PCR Materiale
Dott.ssa Maria Antonietta Lozzi Dipartimento di sanità Pubblica e Malattie Infettive Sapienza Università di Roma
 DAGLI ESORDI DELLA MEDICINA MOLECOLARE ALL EVOLUZIONE DELL AUTOMAZIONE Dott.ssa Maria Antonietta Lozzi Dipartimento di sanità Pubblica e Malattie Infettive Sapienza Università di Roma La scoperta che il
DAGLI ESORDI DELLA MEDICINA MOLECOLARE ALL EVOLUZIONE DELL AUTOMAZIONE Dott.ssa Maria Antonietta Lozzi Dipartimento di sanità Pubblica e Malattie Infettive Sapienza Università di Roma La scoperta che il
Analisi di sequenziamento degli acidi nucleici
 Analisi di sequenziamento degli acidi nucleici In questa lezione darò qualche breve cenno sui metodi di sequenziamento del DNA e specialmente quelli con marcatura fluorescente che attualmente vengono effettuati
Analisi di sequenziamento degli acidi nucleici In questa lezione darò qualche breve cenno sui metodi di sequenziamento del DNA e specialmente quelli con marcatura fluorescente che attualmente vengono effettuati
ANALISI DI MUTAZIONI PUNTIFORMI NON NOTE ANALISI DI SEQUENZA.
 ANALISI DI MUTAZIONI PUNTIFORMI NON NOTE Margherita Vinciguerra U.O. Ematologia II Laboratorio per lo Studio e la Diagnosi Molecolare Prenatale di Talassemia A.O. V. Cervello, Palermo. Analisi di sequenza
ANALISI DI MUTAZIONI PUNTIFORMI NON NOTE Margherita Vinciguerra U.O. Ematologia II Laboratorio per lo Studio e la Diagnosi Molecolare Prenatale di Talassemia A.O. V. Cervello, Palermo. Analisi di sequenza
Metodi per il rilevamento degli OGM in matrici alimentari: principi ed i metodi di analisi basati sulla ricerca del DNA e delle proteine
 Università degli Studi del Piemonte Orientale A. Avogadro CORSO DI ALTA FORMAZIONE IN LEGISLAZIONE ALIMENTARE Metodi per il rilevamento degli OGM in matrici alimentari: principi ed i metodi di analisi
Università degli Studi del Piemonte Orientale A. Avogadro CORSO DI ALTA FORMAZIONE IN LEGISLAZIONE ALIMENTARE Metodi per il rilevamento degli OGM in matrici alimentari: principi ed i metodi di analisi
Campione sciolto in un solvente (deuterato) e. posto in un tubo. di vetro a pareti sottili di diametro di 5 mm e lungo circa 20 cm
 posto in un tubo Campione sciolto in un solvente (deuterato) e di vetro a pareti sottili di diametro di 5 mm e lungo circa 20 cm o spettrometro NMR è formato da alcuni mponenti fondamentali: un magnete,
posto in un tubo Campione sciolto in un solvente (deuterato) e di vetro a pareti sottili di diametro di 5 mm e lungo circa 20 cm o spettrometro NMR è formato da alcuni mponenti fondamentali: un magnete,
eaction A very efficient method for IN VITRO REPLICATION of DNA
 1 olymerase hain What is it? eaction A very efficient method for IN VITRO REPLICATION of DNA What is for? Synthesis of several million copies of a specific DNA sequence within a few hours 2 PCR INGREDIENTS
1 olymerase hain What is it? eaction A very efficient method for IN VITRO REPLICATION of DNA What is for? Synthesis of several million copies of a specific DNA sequence within a few hours 2 PCR INGREDIENTS
( x) ( x) 0. Equazioni irrazionali
 Equazioni irrazionali Definizione: si definisce equazione irrazionale un equazione in cui compaiono uno o più radicali contenenti l incognita. Esempio 7 Ricordiamo quanto visto sulle condizioni di esistenza
Equazioni irrazionali Definizione: si definisce equazione irrazionale un equazione in cui compaiono uno o più radicali contenenti l incognita. Esempio 7 Ricordiamo quanto visto sulle condizioni di esistenza
PCR. Polymerase Chain Reaction
 PCR Polymerase Chain Reaction PCR o Tecnica della reazione a catena della DNA polimerasi o PCR (Polymerase Chain Reaction) o Introdotta da Kary B. Mullis alla metà degli anni 80 ha rivoluzionato la genetica
PCR Polymerase Chain Reaction PCR o Tecnica della reazione a catena della DNA polimerasi o PCR (Polymerase Chain Reaction) o Introdotta da Kary B. Mullis alla metà degli anni 80 ha rivoluzionato la genetica
DNA BARCODE: ALLESTIRE UNA BANCA DATI PER TUTELARE LE NOSTRE RISORSE E GARANTIRE LA TRACCIABILITA.
 DNA BARCODE: ALLESTIRE UNA BANCA DATI PER TUTELARE LE NOSTRE RISORSE E GARANTIRE LA TRACCIABILITA. Ogni regione italiana vanta una quantità notevole di prodotti agroalimentari ed animali tipici e caratteristici.
DNA BARCODE: ALLESTIRE UNA BANCA DATI PER TUTELARE LE NOSTRE RISORSE E GARANTIRE LA TRACCIABILITA. Ogni regione italiana vanta una quantità notevole di prodotti agroalimentari ed animali tipici e caratteristici.
Dal DNA all RNA. La trascrizione nei procarioti e negli eucarioti
 Dal DNA all RNA La trascrizione nei procarioti e negli eucarioti DOGMA CENTRALE DELLA BIOLOGIA MOLECOLARE Gene Regione di DNA che porta l informazione (= che CODIFICA) per una catena polipeptidica o per
Dal DNA all RNA La trascrizione nei procarioti e negli eucarioti DOGMA CENTRALE DELLA BIOLOGIA MOLECOLARE Gene Regione di DNA che porta l informazione (= che CODIFICA) per una catena polipeptidica o per
Tecniche di sequenziamento del DNA
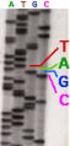 Tecniche di sequenziamento del DNA -Metodo di Maxam e Gilbert (della degradazione chimica del DNA) -Metodo di Sanger (a terminazione di catena) Metodo di Maxam-Gilbert Questo metodo, basato sulla degradazione
Tecniche di sequenziamento del DNA -Metodo di Maxam e Gilbert (della degradazione chimica del DNA) -Metodo di Sanger (a terminazione di catena) Metodo di Maxam-Gilbert Questo metodo, basato sulla degradazione
ARCHITETTURA DI RETE FOLEGNANI ANDREA
 ARCHITETTURA DI RETE FOLEGNANI ANDREA INTRODUZIONE È denominata Architettura di rete un insieme di livelli e protocolli. Le reti sono organizzate gerarchicamente in livelli, ciascuno dei quali interagisce
ARCHITETTURA DI RETE FOLEGNANI ANDREA INTRODUZIONE È denominata Architettura di rete un insieme di livelli e protocolli. Le reti sono organizzate gerarchicamente in livelli, ciascuno dei quali interagisce
Maria Antonietta Lepore. Principali tecniche di biologia molecolare clinica
 Maria Antonietta Lepore Principali tecniche di biologia molecolare clinica Copyright MMIX ARACNE editrice S.r.l. www.aracneeditrice.it info@aracneeditrice.it via Raffaele Garofalo, 133 a/b 00173 Roma (06)
Maria Antonietta Lepore Principali tecniche di biologia molecolare clinica Copyright MMIX ARACNE editrice S.r.l. www.aracneeditrice.it info@aracneeditrice.it via Raffaele Garofalo, 133 a/b 00173 Roma (06)
Verifiche qualitative dell RNA e cdna in ambito dei trials BCR/ABL e AML translocation programme. Massimo Degan, CRO Aviano (PN)
 e cdna in ambito dei trials BCR/ABL e AML translocation programme Massimo Degan, CRO Aviano (PN) perchè è importante verificare l RNA La verifica della qualità dell RNA nei saggi diagnostico-molecolari
e cdna in ambito dei trials BCR/ABL e AML translocation programme Massimo Degan, CRO Aviano (PN) perchè è importante verificare l RNA La verifica della qualità dell RNA nei saggi diagnostico-molecolari
Energia nelle reazioni chimiche. Lezioni d'autore di Giorgio Benedetti
 Energia nelle reazioni chimiche Lezioni d'autore di Giorgio Benedetti VIDEO Introduzione (I) L energia chimica è dovuta al particolare arrangiamento degli atomi nei composti chimici e le varie forme di
Energia nelle reazioni chimiche Lezioni d'autore di Giorgio Benedetti VIDEO Introduzione (I) L energia chimica è dovuta al particolare arrangiamento degli atomi nei composti chimici e le varie forme di
LE MOLECOLE INFORMAZIONALI. Lezioni d'autore Treccani
 LE MOLECOLE INFORMAZIONALI Lezioni d'autore Treccani Introduzione (I) I pionieri della biologia molecolare, scoperta la struttura degli acidi nucleici, pensarono di associare al DNA una sequenza di simboli,
LE MOLECOLE INFORMAZIONALI Lezioni d'autore Treccani Introduzione (I) I pionieri della biologia molecolare, scoperta la struttura degli acidi nucleici, pensarono di associare al DNA una sequenza di simboli,
REAZIONI ORGANICHE Variazioni di energia e velocità di reazione
 REAZIONI ORGANICHE Variazioni di energia e velocità di reazione Abbiamo visto che i composti organici e le loro reazioni possono essere suddivisi in categorie omogenee. Per ottenere la massima razionalizzazione
REAZIONI ORGANICHE Variazioni di energia e velocità di reazione Abbiamo visto che i composti organici e le loro reazioni possono essere suddivisi in categorie omogenee. Per ottenere la massima razionalizzazione
Polymerase chain reaction - PCR. Biotecnologie applicate all ispezione degli alimenti di origine animale
 Prof.ssa Tiziana Pepe Polymerase chain reaction - PCR Biotecnologie applicate all ispezione degli alimenti di origine animale Dip. di Medicina Veterinaria e Produzioni animali tiziana.pepe@unina.it Metodologia
Prof.ssa Tiziana Pepe Polymerase chain reaction - PCR Biotecnologie applicate all ispezione degli alimenti di origine animale Dip. di Medicina Veterinaria e Produzioni animali tiziana.pepe@unina.it Metodologia
Diagnostica Biomolecolare: Tecnologie e Applicazioni
 Diagnostica Biomolecolare: Tecnologie e Applicazioni Preparazione dei campioni: (Estrazione del DNA o dell RNA dal tessuto di interesse) Analisi delle mutazioni: SSCP DHPLC Dot blot - Southern - PCR (ARMS
Diagnostica Biomolecolare: Tecnologie e Applicazioni Preparazione dei campioni: (Estrazione del DNA o dell RNA dal tessuto di interesse) Analisi delle mutazioni: SSCP DHPLC Dot blot - Southern - PCR (ARMS
DNA Memory. Approfondimento del corso di Bioinformatica. prof.ssa Cocco. Sebastiano Vascon
 DNA Memory Approfondimento del corso di Bioinformatica prof.ssa Cocco DNA Memory (Outline) Nested PCR NPMM (Nested Primer Molecular Memory) Gerarchie di memoria Accesso ai dati Spazio di memoria Vincoli
DNA Memory Approfondimento del corso di Bioinformatica prof.ssa Cocco DNA Memory (Outline) Nested PCR NPMM (Nested Primer Molecular Memory) Gerarchie di memoria Accesso ai dati Spazio di memoria Vincoli
Modulo di GENETICA APPLICATA. Esame integrato di METODOLOGIE BIOTECNOLOGICHE CORSO DI LAUREA IN BIOTECNOLOGIE. Docente: FLAVIA CERRATO
 Modulo di GENETICA APPLICATA Esame integrato di METODOLOGIE BIOTECNOLOGICHE CORSO DI LAUREA IN BIOTECNOLOGIE Docente: FLAVIA CERRATO a. a. 2008-2009 2009 PROGRAMMA 1. Tecniche di base. Taglio e saldatura
Modulo di GENETICA APPLICATA Esame integrato di METODOLOGIE BIOTECNOLOGICHE CORSO DI LAUREA IN BIOTECNOLOGIE Docente: FLAVIA CERRATO a. a. 2008-2009 2009 PROGRAMMA 1. Tecniche di base. Taglio e saldatura
La PCR e le sue applicazioni. La PCR di base L RT-PCR Applicazioni mediche e forensi
 La PCR e le sue applicazioni La PCR di base L RT-PCR Applicazioni mediche e forensi Polymerase Chain Reaction e sue applicazioni La polymerase chain reaction o PCR è una tecnica relativamente recente che
La PCR e le sue applicazioni La PCR di base L RT-PCR Applicazioni mediche e forensi Polymerase Chain Reaction e sue applicazioni La polymerase chain reaction o PCR è una tecnica relativamente recente che
Capitolo 1 Introduzione alla PCR
 Capitolo 1 Introduzione alla PCR La tecnologia della PCR ha rivoluzionato l attività dei laboratori di ricerca e di diagnostica trovando applicazioni ed impieghi in svariati campi della medicina e della
Capitolo 1 Introduzione alla PCR La tecnologia della PCR ha rivoluzionato l attività dei laboratori di ricerca e di diagnostica trovando applicazioni ed impieghi in svariati campi della medicina e della
lindab we simplify construction Lindab Solus Semplicemente, la scelta naturale
 lindab we simplify construction Lindab Solus Semplicemente, la scelta naturale Semplicemente, la scelta naturale Immagina una soluzione a travi fredde con bilanciamento della temperatura, dove riscaldamento
lindab we simplify construction Lindab Solus Semplicemente, la scelta naturale Semplicemente, la scelta naturale Immagina una soluzione a travi fredde con bilanciamento della temperatura, dove riscaldamento
