Corso di Bioinformatica. Docente: Dr. Antinisca DI MARCO
|
|
|
- Luciano Marchetti
- 9 anni fa
- Просмотров:
Транскрипт
1 Corso di Bioinformatica Docente: Dr. Antinisca DI MARCO
2 Analisi Filogenetica Gene Ancestrale duplicazione genica La filogenesi è lo studio delle relazioni evolutive tra entità biologiche (non solo specie) che condividono antenati comuni Gene A Gene A1 Gene B1 Gene B speciazione ortologhi parologhi ortologhi Gene A2 Gene B2 Specie 1 Specie 2
3 Analisi Filogenetica La sua rappresentazione grafica è l albero filogenetico L albero filogenetico contiene i tempi e gli schemi temporali dei processi di divergenza Tutti gli organismi hanno un unico antenato comune nel passato Ogni coppia di organismi ha un antenato comune nel passato Eventi di speciazione si susseguono nel tempo creando nuove specie
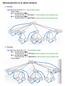
4 Analisi Filogenetica Nodo Radice Ricostruzione di Filogenesi Una albero evolutivo, o filogenesi, è un albero con radice o senza radice i cui nodi interni hanno almeno grado 3 (ad eccezione della radice che ha grado 2) e rappresentano specie progenitrici, mentre le foglie rappresentano specie attuali. Gli archi dell albero solitamente rappresentano la distanza temporale tra due specie (nodi). Nodo Radice Nodo Antenato Nodo Antenato Orango Gorilla Uomo Scimpanzé
5
6
7
8
9
10
11 Analisi Filogenetica Nodo Radice Problema della Ricostruzione di Filogenesi Istanza: un insieme di specie S (es. S = {Orango, Gorilla, }) Questione: trovare la filogenesi T che rappresenta l evoluzione delle specie in S Nodo Radice Nodo Antenato Nodo Antenato Orango Gorilla Uomo Scimpanzé
12 Analisi Filogenetica Nodo Radice Proteine o acidi nucleici? In filogenesi vengono utilizzati entrambi: Sequenze proteiche - necessitano di matrici si sostituzione 20x20, molto complesse da trattare. - sono espressione di sole regioni codificanti. - aminoacidi identici possono essere espressione di più codoni
13 Analisi Filogenetica Nodo Radice Proteine o acidi nucleici? In filogenesi vengono utilizzati entrambi: Sequenze proteiche - necessitano di matrici si sostituzione 20x20, molto complesse da trattare. - sono espressione di sole regioni codificanti. - aminoacidi identici possono essere espressione di più codoni Sequenze nucleotidiche - sono descrivibili con matrici 4x4. - possono essere estratte da sequenze genomiche non codificanti, quindi con una tendenza alla variazione più ampia - non hanno degenerazione né ridondanza.
14 Analisi Filogenetica Nodo Radice Proteine o acidi nucleici? In filogenesi vengono utilizzati entrambi: Sequenze proteiche - necessitano di matrici si sostituzione 20x20, molto complesse da trattare. - sono espressione di sole regioni codificanti. - aminoacidi identici possono essere espressione di più codoni Sequenze nucleotidiche - sono descrivibili con matrici 4x4. - possono essere estratte da sequenze genomiche non codificanti, quindi con una tendenza alla variazione più ampia - non hanno degenerazione né ridondanza. Per la filogenesi molecolare è preferibile utilizzare sequenze nucleotidiche
15 Analisi Filogenetica Nodo Radice Assunzioni a priori Per calcolare una distanza evolutiva è necessario formulare un modello evolutivo: è quindi necessario considerare alcuni aspetti generali che possono essere considerati assunzioni a priori del modello: 1. tutti i siti evolvono in modo indipendente 2. tutti i siti mutano con la stessa probabilità 3. tutte le sostituzioni sono ugualmente probabili 4. la velocità di sostituzione è costante nel tempo 5. la composizione delle basi è costante maggiore è il numero di assunzioni a priori - maggiore è la semplicità del modello - minore è l attendibilità dei risultati
16 Analisi Filogenetica Nodo Radice Topologia Si definisce TOPOLOGIA la struttura generale di un albero. Se ai rami non si dà valenza di distanza evolutiva, ho un CLADOGRAMMA, altrimenti ho un FILOGRAMMA. Alberi CON RADICE accettano come vera l ipotesi dell orologio molecolare* e i nodi stanno in un preciso ordine temporale. UOMO MUCCA TOPO Alberi SENZA RADICE Non prevedono significati evolutivi in termini temporali e descrivono semplicemente le relazioni tra le sequenze * L evoluzione è un processo inevitabilmente divergente e il numero di mutazioni che si accumulano nel tempo è direttamente proporzionale al tempo intercorso dalla divergenza delle sequenze in analisi. Se questo è vero, data una distanza genetica calcolata osservando le divergenze, è possibile ottenere il tempo trascorso dal momento in cui due sequenze hanno cominciato a divergere. B A 1 2 C D 3 E
17 Analisi Filogenetica Nodo Radice Topologia Si definisce TOPOLOGIA la struttura generale di un albero. Se ai rami non si dà valenza di distanza evolutiva, ho un CLADOGRAMMA, altrimenti ho un FILOGRAMMA. Alberi CON RADICE accettano come vera l ipotesi dell orologio molecolare* e i nodi stanno in un preciso ordine temporale. Alberi SENZA RADICE Non prevedono significati evolutivi in termini temporali e descrivono semplicemente le relazioni tra le sequenze Il numero complessivo di alberi che si possono costruire con N sequenze (denominate OTU, cioè Operational Taxonomic Units) è dato da: Rooted N R = (2N - 3)! / (2 N-3 )*(N-3)! UnRooted N U = (2N - 5)! / (2 N-3 )*(N-3)! * L evoluzione è un processo inevitabilmente divergente e il numero di mutazioni che si accumulano nel tempo è direttamente proporzionale al tempo intercorso dalla divergenza delle sequenze in analisi. Se questo è vero, data una distanza genetica calcolata osservando le divergenze, è possibile ottenere il tempo trascorso dal momento in cui due sequenze hanno cominciato a divergere.
18 Analisi Filogenetica Nodo Radice Metodi per la creazione degli alberi I sistemi per costruire gli alberi possono essere distinti secondo due tipi di raggruppamenti, a seconde delle metodologie: Algoritmi di clusterizzazione (Unweighted Pair Group Method with Aritmetic mean (UPMGA), Neighbour Joining(NJ)): si basano sull osservazione delle distanze genetiche calcolate su allineamenti multipli. Algoritmi di ottimizzazione (Minima evoluzione): ottimizzazione degli alberi in base a criteri obiettivi di qualità. Oppure in base all origine dei dati Distanze genetiche pre-calcolate: tempi di calcolo minori. Sequenze omologhe multiallineate: tempi di calcolo molto superiori.
19 Analisi Filogenetica Nodo Radice MEGA: Per maggiori dettagli sugli algoritmi per studio filogenetico è possibile fare riferimento al file AlgoritmiPhylogenesis.pdf
20
21
22
23
24
25
26 Neighbour Joining Algorithm The Neighbour Joining method is a method for re-constructing phylogenetic trees, and computing the lengths of the branches of this tree. In each stage, the two nearest nodes of the tree are chosen and defined as neighbours in our tree. This is done recursively until all of the nodes are paired together. Neighbours are defined as a pair of OTU's (OTU=operational taxonomic units, or in other words leaves of the tree), who have one node connecting them. For instance, in the tree in figure 1, nodes A and B are neighbours (connected by only one internal node), and nodes C and D are neighbours, whereas nodes A and C (for example) are not neighbours.
27 Neighbour Joining Algorithm How do we find neighbours, and how de we construct our tree? 1. We start off with a star tree: 2. We define some kind of distance parameter between our nodes (1 through 5), and enter this parameter into a distance matrix. The columns and rows of the matrix represent nodes, and the value i,j of the matrix represent the distance between node i and node j. Note that the matrix is symmetric, and that the diagonal is irrelevant, therefore only the top half (or lower half) are enough. 3. We pick the two nodes with the lowest value in the matrix defined in step 2. These are defined as neighbours. For example, assuming nodes 1 and 2 are the nearest, we define them as neighbours
28 Neighbour Joining Algorithm Figure 2(b)
29
30
31 sostituzioni. L algoritmo ha due componenti
32
33
34
Filogenesi molecolare
 Filogenesi molecolare Geni ortologhi e geni paraloghi Geni ortologhi: geni simili riscontrabili in organismi correlati tra loro. Il fenomeno della speciazione porta alla divergenza dei geni e quindi delle
Filogenesi molecolare Geni ortologhi e geni paraloghi Geni ortologhi: geni simili riscontrabili in organismi correlati tra loro. Il fenomeno della speciazione porta alla divergenza dei geni e quindi delle
Filogenesi molecolare
 Filogenesi molecolare Evoluzione dei geni Gene ancestrale Gene duplicazione genica Gene speciazione Gene 1 Gene 1 ortologhi paraloghi ortologhi Gene 2 Gene 2 Specie 1 Specie 2 Proteine o acidi nucleici?
Filogenesi molecolare Evoluzione dei geni Gene ancestrale Gene duplicazione genica Gene speciazione Gene 1 Gene 1 ortologhi paraloghi ortologhi Gene 2 Gene 2 Specie 1 Specie 2 Proteine o acidi nucleici?
Alberi filogenetici. File: alberi_filogenetici.odp. Riccardo Percudani 02/03/04
 Alberi filogenetici The tree of life Albero filogenetico costruito con le sequenze della subunità piccola dell RNA ribosomale. Tutte le forme viventi condividono un comune ancestore (LCA, last common ancestor
Alberi filogenetici The tree of life Albero filogenetico costruito con le sequenze della subunità piccola dell RNA ribosomale. Tutte le forme viventi condividono un comune ancestore (LCA, last common ancestor
Algoritmi di Allineamento
 Algoritmi di Allineamento CORSO DI BIOINFORMATICA Corso di Laurea in Biotecnologie Università Magna Graecia Catanzaro Outline Similarità Allineamento Omologia Allineamento di Coppie di Sequenze Allineamento
Algoritmi di Allineamento CORSO DI BIOINFORMATICA Corso di Laurea in Biotecnologie Università Magna Graecia Catanzaro Outline Similarità Allineamento Omologia Allineamento di Coppie di Sequenze Allineamento
Riconoscimento e recupero dell informazione per bioinformatica
 Riconoscimento e recupero dell informazione per bioinformatica Filogenesi Manuele Bicego Corso di Laurea in Bioinformatica Dipartimento di Informatica - Università di Verona Sommario Introduzione alla
Riconoscimento e recupero dell informazione per bioinformatica Filogenesi Manuele Bicego Corso di Laurea in Bioinformatica Dipartimento di Informatica - Università di Verona Sommario Introduzione alla
EVOLUZIONE MOLECOLARE. Silvia Fuselli
 EVOLUZIONE MOLECOLARE Silvia Fuselli [email protected] TESTI Organizzazione del corso Graur and Li, Fundamentals of molecular evolution, Sinauer 2000 Michael Lynch, The Origins of Genome Architecture,
EVOLUZIONE MOLECOLARE Silvia Fuselli [email protected] TESTI Organizzazione del corso Graur and Li, Fundamentals of molecular evolution, Sinauer 2000 Michael Lynch, The Origins of Genome Architecture,
SAGA: sequence alignment by genetic algorithm. ALESSANDRO PIETRELLI Soft Computing
 SAGA: sequence alignment by genetic algorithm ALESSANDRO PIETRELLI Soft Computing Bologna, 25 Maggio 2007 Multi Allineamento di Sequenze (MSAs) Cosa sono? A cosa servono? Come vengono calcolati Multi Allineamento
SAGA: sequence alignment by genetic algorithm ALESSANDRO PIETRELLI Soft Computing Bologna, 25 Maggio 2007 Multi Allineamento di Sequenze (MSAs) Cosa sono? A cosa servono? Come vengono calcolati Multi Allineamento
Genomica Evoluzione e cambiamenti dei genomi. Dott.ssa Inga Prokopenko
 Genomica Evoluzione e cambiamenti dei genomi Dott.ssa Inga Prokopenko Sistematica in biologia La varietà degli organismi viventi richiede organizzaione delle nostre osservazioni Tassonomia in biologia
Genomica Evoluzione e cambiamenti dei genomi Dott.ssa Inga Prokopenko Sistematica in biologia La varietà degli organismi viventi richiede organizzaione delle nostre osservazioni Tassonomia in biologia
Metodi di Distanza. G.Allegrucci riproduzione vietata
 Metodi di Distanza La misura più semplice della distanza tra due sequenze nucleotidiche è contare il numero di siti nucleotidici che differiscono tra le due sequenze Quando confrontiamo siti omologhi in
Metodi di Distanza La misura più semplice della distanza tra due sequenze nucleotidiche è contare il numero di siti nucleotidici che differiscono tra le due sequenze Quando confrontiamo siti omologhi in
Filogenesi e alberi filogenetici. Darwin, 1837
 Filogenesi e alberi filogenetici Darwin, 1837 Definizione di filogenesi La filogenesi è lo studio delle relazioni evolutive tra entità biologiche (non solo specie) che condividono antenati comuni La sua
Filogenesi e alberi filogenetici Darwin, 1837 Definizione di filogenesi La filogenesi è lo studio delle relazioni evolutive tra entità biologiche (non solo specie) che condividono antenati comuni La sua
Genomics Session. Lezione 6. Filogenomica
 Genomics Session Filogenomica Filogenetica Filogenesi: Ricostruzione della storia evolutiva Obiettivo: inferire la storia evolutiva fra entità biologiche mediante una serie di caratteri moderni osservati
Genomics Session Filogenomica Filogenetica Filogenesi: Ricostruzione della storia evolutiva Obiettivo: inferire la storia evolutiva fra entità biologiche mediante una serie di caratteri moderni osservati
Allineamento multiplo
 Allineamento multiplo Allineamenti multipli Il modo migliore per conoscere le caratteristiche di una determinata famiglia è allineare molte proteine a funzione analoga. I siti funzionalmente o strutturalmente
Allineamento multiplo Allineamenti multipli Il modo migliore per conoscere le caratteristiche di una determinata famiglia è allineare molte proteine a funzione analoga. I siti funzionalmente o strutturalmente
Ortologhi e paraloghi
 Ortologhi e paraloghi Similarità e distanza Sequenza originaria GHSVLIWETS Gene Gene uplicazione Eventi di sostituzione: vvenuti = 12 Osservabili = 3 Speciazione Gene 1 Gene 2 Geni Ortologhi uplicazione
Ortologhi e paraloghi Similarità e distanza Sequenza originaria GHSVLIWETS Gene Gene uplicazione Eventi di sostituzione: vvenuti = 12 Osservabili = 3 Speciazione Gene 1 Gene 2 Geni Ortologhi uplicazione
ALBERI FILOGENETICI. Genetica delle popolazioni a.a. 11-12 prof. S. Presciuttini
 ALBERI FILOGENETICI Questo documento è pubblicato sotto licenza Creative Commons Attribuzione Non commerciale Condividi allo stesso modo http://creativecommons.org/licenses/by-nc-sa/2.5/deed.it Che cosa
ALBERI FILOGENETICI Questo documento è pubblicato sotto licenza Creative Commons Attribuzione Non commerciale Condividi allo stesso modo http://creativecommons.org/licenses/by-nc-sa/2.5/deed.it Che cosa
Il progetto Genoma Umano è iniziato nel E stato possibile perchè nel 1986 era stato sviluppato il sequenziamento automatizzato del DNA.
 Il progetto Genoma Umano è iniziato nel 1990. E stato possibile perchè nel 1986 era stato sviluppato il sequenziamento automatizzato del DNA. Progetto internazionale finanziato da vari paesi, affidato
Il progetto Genoma Umano è iniziato nel 1990. E stato possibile perchè nel 1986 era stato sviluppato il sequenziamento automatizzato del DNA. Progetto internazionale finanziato da vari paesi, affidato
GENOMA. Analisi di sequenze -- Analisi di espressione -- Funzione delle proteine CONTENUTO FUNZIONE. Progetti genoma in centinaia di organismi
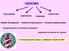 GENOMA EVOLUZIONE CONTENUTO FUNZIONE STRUTTURA Analisi di sequenze -- Analisi di espressione -- Funzione delle proteine Progetti genoma in centinaia di organismi Importante la sintenia tra i genomi The
GENOMA EVOLUZIONE CONTENUTO FUNZIONE STRUTTURA Analisi di sequenze -- Analisi di espressione -- Funzione delle proteine Progetti genoma in centinaia di organismi Importante la sintenia tra i genomi The
Graphs: Cycles. Tecniche di Programmazione A.A. 2012/2013
 Graphs: Cycles Tecniche di Programmazione Summary Definitions Algorithms 2 Definitions Graphs: Cycles Cycle A cycle of a graph, sometimes also called a circuit, is a subset of the edge set of that forms
Graphs: Cycles Tecniche di Programmazione Summary Definitions Algorithms 2 Definitions Graphs: Cycles Cycle A cycle of a graph, sometimes also called a circuit, is a subset of the edge set of that forms
Indice generale. Nozioni fondamentali. Prefazione XIII
 Prefazione XIII A Nozioni fondamentali CAPITOLO 1 La biologia essenziale 3 1.1 Genomi, genomica e avvento della Bioinformatica 3 1.2 Genoma dei procarioti 5 1.2.1 Struttura e dimensioni 5 1.2.2 Proprietà
Prefazione XIII A Nozioni fondamentali CAPITOLO 1 La biologia essenziale 3 1.1 Genomi, genomica e avvento della Bioinformatica 3 1.2 Genoma dei procarioti 5 1.2.1 Struttura e dimensioni 5 1.2.2 Proprietà
BLAST. W = word size T = threshold X = elongation S = HSP threshold
 BLAST Blast (Basic Local Aligment Search Tool) è un programma che cerca similarità locali utilizzando l algoritmo di Altschul et al. Anche Blast, come FASTA, funziona: 1. scomponendo la sequenza query
BLAST Blast (Basic Local Aligment Search Tool) è un programma che cerca similarità locali utilizzando l algoritmo di Altschul et al. Anche Blast, come FASTA, funziona: 1. scomponendo la sequenza query
Informatica e Bioinformatica A. A
 Purtroppo non esiste un modo univoco per indicare un gene. Ad esempio abbiamo visto che il gene tcap a seconda del record è riportato come titin-cap protein o telethonin. Questo crea confusione e non facilita
Purtroppo non esiste un modo univoco per indicare un gene. Ad esempio abbiamo visto che il gene tcap a seconda del record è riportato come titin-cap protein o telethonin. Questo crea confusione e non facilita
RELAZIONE di BIOLOGIA MOLECOLARE
 NOME: Marini Selena MATRICOLA: 592330 RELAZIONE di BIOLOGIA MOLECOLARE CHE ORGANISMO MODELLO È DICTYOSTELIUM? CHE RISORSE BIOINFORMATICHE AGEVOLANO I RICERCATORI CHE LO STUDIANO? Dictyostelium è un genere
NOME: Marini Selena MATRICOLA: 592330 RELAZIONE di BIOLOGIA MOLECOLARE CHE ORGANISMO MODELLO È DICTYOSTELIUM? CHE RISORSE BIOINFORMATICHE AGEVOLANO I RICERCATORI CHE LO STUDIANO? Dictyostelium è un genere
TASSONOMIA E FILOGENESI
 TASSONOMIA E FILOGENESI Evoluzione e filogenesi EVOLUZIONE rappresenta il cambiamento di una linea di discendenti che, nel tempo, porta alla formazione di nuove specie. FILOGENESI: studia le connessioni,
TASSONOMIA E FILOGENESI Evoluzione e filogenesi EVOLUZIONE rappresenta il cambiamento di una linea di discendenti che, nel tempo, porta alla formazione di nuove specie. FILOGENESI: studia le connessioni,
Allineamenti multipli
 Allineamenti multipli Allineamenti multipli Finora ci siamo occupati di allineamenti a coppie (pairwise), ma il modo migliore per conoscere le caratteristiche di una determinata famiglia è allineare molte
Allineamenti multipli Allineamenti multipli Finora ci siamo occupati di allineamenti a coppie (pairwise), ma il modo migliore per conoscere le caratteristiche di una determinata famiglia è allineare molte
A.A. 2006/2007 Laurea di Ingegneria Informatica. Fondamenti di C++ Horstmann Capitolo 3: Oggetti Revisione Prof. M. Angelaccio
 A.A. 2006/2007 Laurea di Ingegneria Informatica Fondamenti di C++ Horstmann Capitolo 3: Oggetti Revisione Prof. M. Angelaccio Obbiettivi Acquisire familiarità con la nozione di oggetto Apprendere le proprietà
A.A. 2006/2007 Laurea di Ingegneria Informatica Fondamenti di C++ Horstmann Capitolo 3: Oggetti Revisione Prof. M. Angelaccio Obbiettivi Acquisire familiarità con la nozione di oggetto Apprendere le proprietà
07/01/2015. Come si ferma una macchina in corsa? Il terminatore. Terminazione intrinseca (rho-indipendente)
 Come si ferma una macchina in corsa? Il terminatore Terminazione intrinseca (rho-indipendente) Terminazione dipendente dal fattore Rho (r) 1 Operoni: gruppi di geni parte di una unica unità trascrizionale
Come si ferma una macchina in corsa? Il terminatore Terminazione intrinseca (rho-indipendente) Terminazione dipendente dal fattore Rho (r) 1 Operoni: gruppi di geni parte di una unica unità trascrizionale
Espressioni aritmetiche
 Espressioni aritmetiche Consideriamo espressioni costruite a partire da variabili e costanti intere mediante applicazione delle operazioni di somma, sottrazione, prodotto e divisione (intera). Ad esempio:
Espressioni aritmetiche Consideriamo espressioni costruite a partire da variabili e costanti intere mediante applicazione delle operazioni di somma, sottrazione, prodotto e divisione (intera). Ad esempio:
Lezione 7. Allineamento di sequenze biologiche
 Lezione 7 Allineamento di sequenze biologiche Allineamento di sequenze Determinare la similarità e dedurre l omologia Allineare Definire il numero di passi necessari per trasformare una sequenza nell altra
Lezione 7 Allineamento di sequenze biologiche Allineamento di sequenze Determinare la similarità e dedurre l omologia Allineare Definire il numero di passi necessari per trasformare una sequenza nell altra
Quarta lezione. 1. Ricerca di omologhe in banche dati. 2. Programmi per la ricerca: FASTA BLAST
 Quarta lezione 1. Ricerca di omologhe in banche dati. 2. Programmi per la ricerca: FASTA BLAST Ricerca di omologhe in banche dati Proteina vs. proteine Gene (traduzione in aa) vs. proteine Gene vs. geni
Quarta lezione 1. Ricerca di omologhe in banche dati. 2. Programmi per la ricerca: FASTA BLAST Ricerca di omologhe in banche dati Proteina vs. proteine Gene (traduzione in aa) vs. proteine Gene vs. geni
Tesi di Laurea Specialistica. Laureando: Silvio Zennaro. Accordo tra alberi filogenetici: dalla teoria allo sviluppo web 2.0
 UNIVERSITÀ CA FOSCARI DI VENEZIA Facoltà di Scienze Matematiche, Fisiche e Naturali Corso di Laurea Specialistica in Informatica Tesi di Laurea Specialistica Laureando: Silvio Zennaro Accordo tra alberi
UNIVERSITÀ CA FOSCARI DI VENEZIA Facoltà di Scienze Matematiche, Fisiche e Naturali Corso di Laurea Specialistica in Informatica Tesi di Laurea Specialistica Laureando: Silvio Zennaro Accordo tra alberi
Si faccia riferimento all Allegato A - OPS 2016, problema ricorrente REGOLE E DEDUZIONI, pagina 2.
 Scuola Sec. SECONDO Grado Gara 2 IND - 15/16 ESERCIZIO 1 Si faccia riferimento all Allegato A - OPS 2016, problema ricorrente REGOLE E DEDUZIONI, pagina 2. Sono date le seguenti regole: regola(1,[a],b)
Scuola Sec. SECONDO Grado Gara 2 IND - 15/16 ESERCIZIO 1 Si faccia riferimento all Allegato A - OPS 2016, problema ricorrente REGOLE E DEDUZIONI, pagina 2. Sono date le seguenti regole: regola(1,[a],b)
Botanica (CFU 5+1) Martedì 11:00-13:00 Venerdì. scienza della diversità I turno 14:00-16:00 2 turno 16:00-18:00. aa
 Botanica (CFU 5+1) Botanica o Biologia vegetale: Lezioni Morfologia vegetale Anatomia vegetale * Citologia vegetale * Martedì 11:00-13:00 Venerdì Fisiologia vegetale * Genetica dei vegetali Biologia molecolare
Botanica (CFU 5+1) Botanica o Biologia vegetale: Lezioni Morfologia vegetale Anatomia vegetale * Citologia vegetale * Martedì 11:00-13:00 Venerdì Fisiologia vegetale * Genetica dei vegetali Biologia molecolare
Attraversamento di un albero (binario)
 Attraversamento di un albero (binario) 1) Preordine Algorithm binarypreorder( T, v) //caso di albero binario Visita il nodo v; binarypreorder( T, T.leftChild(v)); //Attraversamento ricorsivo sottoalbero
Attraversamento di un albero (binario) 1) Preordine Algorithm binarypreorder( T, v) //caso di albero binario Visita il nodo v; binarypreorder( T, T.leftChild(v)); //Attraversamento ricorsivo sottoalbero
Introduzione all analisi di arrays: clustering.
 Statistica per la Ricerca Sperimentale Introduzione all analisi di arrays: clustering. Lezione 2-14 Marzo 2006 Stefano Moretti Dipartimento di Matematica, Università di Genova e Unità di Epidemiologia
Statistica per la Ricerca Sperimentale Introduzione all analisi di arrays: clustering. Lezione 2-14 Marzo 2006 Stefano Moretti Dipartimento di Matematica, Università di Genova e Unità di Epidemiologia
Patologie da analizzare
 Fasi cruciali Scelta della patologia da analizzare Scelta del campione da analizzare Scelta dell approccio da utilizzare Scelta della tecnica da utilizzare Analisi statistica del dati Conferme con approcci
Fasi cruciali Scelta della patologia da analizzare Scelta del campione da analizzare Scelta dell approccio da utilizzare Scelta della tecnica da utilizzare Analisi statistica del dati Conferme con approcci
scaricato da I peptidi risultano dall unione di due o più aminoacidi mediante un legame COVALENTE
 Legame peptidico I peptidi risultano dall unione di due o più aminoacidi mediante un legame COVALENTE tra il gruppo amminico di un aminoacido ed il gruppo carbossilico di un altro. 1 Catene contenenti
Legame peptidico I peptidi risultano dall unione di due o più aminoacidi mediante un legame COVALENTE tra il gruppo amminico di un aminoacido ed il gruppo carbossilico di un altro. 1 Catene contenenti
Allineamenti di sequenze: concetti e algoritmi
 Allineamenti di sequenze: concetti e algoritmi 1 globine: a- b- mioglobina Precoce esempio di allineamento di sequenza: globine (1961) H.C. Watson and J.C. Kendrew, Comparison Between the Amino-Acid Sequences
Allineamenti di sequenze: concetti e algoritmi 1 globine: a- b- mioglobina Precoce esempio di allineamento di sequenza: globine (1961) H.C. Watson and J.C. Kendrew, Comparison Between the Amino-Acid Sequences
Data Alignment and (Geo)Referencing (sometimes Registration process)
 Data Alignment and (Geo)Referencing (sometimes Registration process) All data aquired from a scan position are refered to an intrinsic reference system (even if more than one scan has been performed) Data
Data Alignment and (Geo)Referencing (sometimes Registration process) All data aquired from a scan position are refered to an intrinsic reference system (even if more than one scan has been performed) Data
Algoritmi Priority-Driven RT. Corso di Sistemi RT Prof. Davide Brugali Università degli Studi di Bergamo
 Algoritmi Priority-Driven RT Corso di Sistemi RT Prof. Davide Brugali Università degli Studi di Bergamo 2 Algoritmi Real Time Earliest Due Date (statico) Seleziona il task con la deadline relativa più
Algoritmi Priority-Driven RT Corso di Sistemi RT Prof. Davide Brugali Università degli Studi di Bergamo 2 Algoritmi Real Time Earliest Due Date (statico) Seleziona il task con la deadline relativa più
TASSONOMIA O SISTEMATICA
 TASSONOMIA O SISTEMATICA È la branca della batteriologia responsabile della caratterizzazione degli organismi ed organizzazione in gruppi affini (TAXA). NOMENCLATURA CLASSIFICAZIONE IDENTIFICAZIONE taxon
TASSONOMIA O SISTEMATICA È la branca della batteriologia responsabile della caratterizzazione degli organismi ed organizzazione in gruppi affini (TAXA). NOMENCLATURA CLASSIFICAZIONE IDENTIFICAZIONE taxon
LA BIOLOGIA MOLECOLARE E UNA BRANCA DELLA BIOLOGIA CHE STUDIA LE BASI MOLECOLARI DELLE FUNZIONI BIOLOGICHE, PONENDO UNA PARTICOLARE ATTENZIONE A QUEI
 CONCETTI DI BASE LA BIOLOGIA MOLECOLARE E UNA BRANCA DELLA BIOLOGIA CHE STUDIA LE BASI MOLECOLARI DELLE FUNZIONI BIOLOGICHE, PONENDO UNA PARTICOLARE ATTENZIONE A QUEI PROCESSI CHE COINVOLGONO GLI ACIDI
CONCETTI DI BASE LA BIOLOGIA MOLECOLARE E UNA BRANCA DELLA BIOLOGIA CHE STUDIA LE BASI MOLECOLARI DELLE FUNZIONI BIOLOGICHE, PONENDO UNA PARTICOLARE ATTENZIONE A QUEI PROCESSI CHE COINVOLGONO GLI ACIDI
