Lezione 6. Lo string matching
|
|
|
- Clementina Porta
- 8 anni fa
- Просмотров:
Транскрипт
1 Lezione 6 Lo string matching
2 String matching Date due stringhe (sequenze di caratteri) vogliamo stabilire se sono uguali Nel caso dello string matching, due stringhe sono uguali se... sono uguali ( DNA e RNA non sono uguali) Noi tratteremo string matching approssimato ( DNA è omologo a RNA )
3 Alfabeti L'alfabeto nucleotidico (standard IUPAC): A: Adenina C: Citosina T: Timina G: Guanina A=T C=G L'Uracile (U) sostituisce la T nell'rna (non la useremo). IUPAC è l'acronimo di International Union of Pure and Applied Chemistry (Unione Internazionale di Chimica Pura ed Applicata)
4 Alfabeti Alfabeto aminoacidico (standard IUPAC) A Alanina C Cisteina D Acido aspartico E Acido glutammico F Fenilalanina G Glicina H Istidina I Isoleucina K Lisina L Leucina M Metionina N Asparagina P Prolina Q Glutammina R Arginina S Serina T Treonina V Valina W Triptofano Y Tirosina
5 String matching tctgtagaaggctcctaacgatg tctcctgtaggaggctcctgatg
6 String matching tctgtagaaggctcctaacgatg tctcctgtaggaggctcctgatg
7 String matching tct---gtagaaggctcctaacgatg tctcctgtaggaggctcct---gatg
8 Metrica Vogliamo avere una misura della differenza (distanza) fra due stringe studio strutturale/funzionale/evoluzionistico di stringhe biologiche confronto con database di sequenze note in ambito non biologico: correzione degli errori ortografici Esistono diversi modi per formalizzare la distanza fra due stringhe, noi ci concentreremo sulla EDIT DISTANCE che si focalizza sulla trasformazione di singoli caratteri
9 Edit distance Le operazioni permesse sono: I: insert (inserimento, inserzione) D: delete (cancellazione, delezione, rimozione) R: replacement (substition, sostituzione) M: match (corrispondenza, accoppiamento, uguaglianza) v-intner- RIMDMDMMI wri-t-ers
10 Esempio tct---gtagaaggctcctaacgatg MMMIIIMMMMRMMMMMMMMDDDMMMM tctcctgtaggaggctcct---gatg
11 Edit transcript Definizione Una stringa su un alfabeto {I,D,R,M} che descrive una trasformazione da una stringa ad un'altra e' detta edit transcript (trascrizione) delle due stringhe. Date due stringhe A e B, sia T la trascrizione da A a B. Se in T sostituiamo le I con D e contemporaneamente le D con le I otteniamo una trascrizione T' da B ad A.
12 Esempio di commutatività A T B RIMDMDMMI wri-t-ers T' RDMIMIMMD A v-intner- v-intner-
13 Edit distance Definizione La edit distance fra due stringhe e' definita come il minimo numero di operazione di edit (inserzioni, delezioni e sostituzioni) necessarie a trasformare una stringa nell'altra. NOTA BENE: i match non sono contati! La edit distance e' conosciuta anche come Levenshtein distance
14 Edit distance problem L'edit distance problem e' computare la edit distance fra due stringhe date, in modo che l'edit transcript sia ottimale Traduzione: trovare il trascritto che minimizza la distanza. Molto spesso si usa come sinonimo problema dell'allineamento (globale)
15 Problemi le sequenze di interesse possono variare da poche basi (~700pb, reads di un Whole Genome Shotgun Project) fino a milioni di basi (un cromosoma) si vuole sapere se una sequenza e' gia' stata scoperta e caratterizzata (o una sua omologa) dalla comunita' scientifica (NCBI, National Center for Biotechnology Information) si vuole sapere se una sequenza e' parte di un'altra sequenza...
16 Soluzioni gia' pronte BLAST (Basic Local Alignment Search Tool) linea di comando (blastall) Dotter programma visuale
17 Input per BLAST BLAST può prendere in input una o più sequenze nucleotidiche o aminoacidiche Bisogna specificare un database di confronto che può essere nucleotidico o aminoacidico Quando si confrontano gli alfabeti nucleotidici con quelli aminoacidici bisogna traslare le sequenze nucleotidiche nei sei diversi modi (frame di lettura) e convertire i codoni
18 Codoni A GCT, GCC, GCA, GCG L TTA, TTG, CTT, CTC, CTA, CTG R CGT, CGC, CGA, CGG, AGA, AGG K AAA, AAG N AAT, AAC M ATG D GAT, GAC F TTT, TTC C TGT, TGC P CCT, CCC, CCA, CCG Q CAA, CAG S TCT, TCC, TCA, TCG, AGT, AGC E GAA, GAG T ACT, ACC, ACA, ACG G GGT, GGC, GGA, GGG W TGG H CAT, CAC Y TAT, TAC I ATT, ATC, ATA V GTT, GTC, GTA, GTG start ATG, GTG stop TAG, TGA, TAA
19 Open Reading Frame (ORF)
20 BLAST Query Sequence nucleotide Database type nucleotide Algorithm for comparison blastn nucleotide (translated) protein blastx protein nucleotide (translated) tblastn nucleotide (translated) nucleotide (translated) tblastx protein protein blastp
21 MEGABLAST Esiste una versione greedy di BLAST Serve per cercare piccole differenze fra sequenze nucleotidiche (es. differenze derivante da errori di sequenziamento) E' 10 volte più veloce di BLAST
22 PSI-BLAST e PHI-BLAST PSI-BLAST cerca membri di una famiglia di proteine oppure costruisce una matrice di costi specifica PHI-BLAST cerca similarità con la proteina di riferimento usando un pattern specificato
23 Query
24 Database
25 Informazioni generali
26 Distribuzione
27 Riassunto
28 E-Value L'E-Value (Expect Value) è un parametro che descrive il numero di hits con punteggio uguale o migliore di quello osservato che ci si aspetta di vedere in un database della stessa dimensione di quello in esame. Descresce esponenzialmente rispetto allo Score Per esempio, E=1 si può interpretare come il fatto che ci si può aspettare di vedere 1 match con punteggio uguale o superiore Più il valore è vicino a zero e più l'hit è significativo
29 L'allineamento migliore
30 Allineamento con gaps
31 BLASTX (TBLASTN)
32 BLASTP
33 TBLASTN
34 BL2SEQ Serve per fare l'allineamento fra due sequenze particolari invece che fra una sequenza e un database
35 Dotter Dotter è un programma dotplot per la comparazione grafica di due (o più) sequenze. Ogni base di una sequenza è comparata con ogni base delle altre sequenze. il valore di una determinata base dipende anche dalle basi che gli stanno attorno (è un valore locale) viene usata una finestra di lettura che scorre fra le due sequenze da allineare
36 Dotter Genera una matrice, ogni punto della matrice rappresenta il valore dell'omologia per la coppia di basi con quelle coordinate Le regioni omologhe si riconoscono da linee diagonali Se si compara una sequenza contro se stessa la diagonale principale avrà un allineamento del 100%
37 Esempio Esempio con una sliding window di 3 Matrice dei costi: DNA+5/-4 t c t g t a a c a a t g t c a c
38 BLOSUM62 A R N D C Q E G H I L K M F P S T W Y V B Z X * A R N D C Q E G H I L K M F P S T W Y V B Z X *
39 A cosa serve DOTTER? vedere l'omologia fra regioni diverse es. riconoscere se una regione di un sequenza è presente in una regione di un'altra sequenza riconoscere e identificare regioni ripetute in una singola sequenza ricerca delle LTR (Long Terminal Repeat) e delle TIR (Terminal Inverted Repeat) di elementi trasponibili
40 Come si legge Dotter?
41 Dotter e Edit trascript M R I D
42 Grayramp
43 Grayramp
44 Grayramp
45 Zoom
46 Tandem Repeats
47 Match sullo strand opposto
48 Piu' sequenze
49 Proteine Dotter puo' fare l'allinemaneto fra sequenze aminoacidiche Non si puo' fare nucleotidi vs aminoacidi e viceversa Strand unico Viene utilizzata una matrice di costi (BLOSUM62) per calcolare l'omologia
50 BLAST pro: è disponibile online e non richiede risorse di calcolo locali è di facile lettura e interpretazione da linea di comando è facilmente automatizzabile contro: non è interattivo si vedono solo le omologie migliori (scelte da lui) non è lo strumento adeguato per cercare sequenze ripetute
51 DOTTER pro: è disponibile per diverse architetture è visuale e interattivo si può osservare tutto l'allineamento utilissimo per cercare sequenze ripetute contro: richiede risorse di calcolo locali si possono osservare poche sequenze alla volta non è automatizzabile
52 BLAST vs DOTTER Si usa BLAST per cercare omologie con proteine o sequenze note in grandi database Si usa Dotter per cercare le zone ripetute o per cercare omologie con altre sequenze (poche)
COME CALCOLARE IL PUNTEGGIO DI UN ALLINEAMENTO? Il problema del calcolo del punteggio di un allineamento può essere considerato in due modi diversi
 COME CALCOLARE IL PUNTEGGIO DI UN ALLINEAMENTO? Il problema del calcolo del punteggio di un allineamento può essere considerato in due modi diversi che, però, sono le due facce di una stessa medaglia al
COME CALCOLARE IL PUNTEGGIO DI UN ALLINEAMENTO? Il problema del calcolo del punteggio di un allineamento può essere considerato in due modi diversi che, però, sono le due facce di una stessa medaglia al
TRADUZIONE. 2. Transfer (legato agli aminoacidi) 3. Ribosomale (associato a proteine nei ribosomi)
 enhancer promotore regione trascritta TATA trascrizione 5 3 splicing mrna 5 3 traduzione Proteina NH2 COOH Funzione biologica TRADUZIONE I tre ruoli svolti dall RNA: 1. Messaggero 2. Transfer (legato agli
enhancer promotore regione trascritta TATA trascrizione 5 3 splicing mrna 5 3 traduzione Proteina NH2 COOH Funzione biologica TRADUZIONE I tre ruoli svolti dall RNA: 1. Messaggero 2. Transfer (legato agli
Classificazione. I complessi. Le pietre miliari della tassonomia. Tassonomia del genere Mycobacterium. Pietre miliari nella tassonomia dei micobatteri
 Le pietre miliari della tassonomia Tassonomia del genere Mycobacterium Enrico Tortoli Centro Regionale di Riferimento per i Micobatteri Firenze Adamo è autorizzato da Dio a dare un nome a tutti gli esseri
Le pietre miliari della tassonomia Tassonomia del genere Mycobacterium Enrico Tortoli Centro Regionale di Riferimento per i Micobatteri Firenze Adamo è autorizzato da Dio a dare un nome a tutti gli esseri
Edit distance. v intner RIMDMDMMI wri t ers
 L'allineamento Edit distance Le operazioni permesse sono: I: insert (inserimento, inserzione) D: delete (cancellazione, delezione, rimozione) R: replacement (substition, sostituzione) M: match (corrispondenza,
L'allineamento Edit distance Le operazioni permesse sono: I: insert (inserimento, inserzione) D: delete (cancellazione, delezione, rimozione) R: replacement (substition, sostituzione) M: match (corrispondenza,
Proficiency test soia Roundup Ready (GTS 40-3-2)
 ISTITUTO ZOOPROFILATTICO SPERIMENTALE DELLE REGIONI LAZIO E TOSCANA (D.L.vo 30.06.1993 n. 270) SEDE CENTRALE - 00178 Roma/Capannelle- Via Appia Nuova, 1411 Tel. (06) 79099.1 (centralino) - Fax (06) 79340724
ISTITUTO ZOOPROFILATTICO SPERIMENTALE DELLE REGIONI LAZIO E TOSCANA (D.L.vo 30.06.1993 n. 270) SEDE CENTRALE - 00178 Roma/Capannelle- Via Appia Nuova, 1411 Tel. (06) 79099.1 (centralino) - Fax (06) 79340724
BLAST. W = word size T = threshold X = elongation S = HSP threshold
 BLAST Blast (Basic Local Aligment Search Tool) è un programma che cerca similarità locali utilizzando l algoritmo di Altschul et al. Anche Blast, come FASTA, funziona: 1. scomponendo la sequenza query
BLAST Blast (Basic Local Aligment Search Tool) è un programma che cerca similarità locali utilizzando l algoritmo di Altschul et al. Anche Blast, come FASTA, funziona: 1. scomponendo la sequenza query
PROBLEMI CONNESSI ALL USO DI PESTICIDI IN AGRICOLTURA
 PROBLEMI CONNESSI ALL USO DI PESTICIDI IN AGRICOLTURA COSTI DI PRODUZIONE SVILUPPO DI POPOLAZIONI DI INSETTI RESISTENTI NON SPECIFICITÀ DEGRADO AMBIENTALE DANNI ALLA SALUTE DELL UOMO PROTEASI Enzimi che
PROBLEMI CONNESSI ALL USO DI PESTICIDI IN AGRICOLTURA COSTI DI PRODUZIONE SVILUPPO DI POPOLAZIONI DI INSETTI RESISTENTI NON SPECIFICITÀ DEGRADO AMBIENTALE DANNI ALLA SALUTE DELL UOMO PROTEASI Enzimi che
A cosa serve la mutagenesi del DNA?
 MUTAGENESI DEL DNA A cosa serve la mutagenesi del DNA? 1. Studio delle sequenze nucleotidiche, delle funzioni dei geni e di particolari aminoacidi nelle proteine. 2. Ingegnerizzazione di proteine in modo
MUTAGENESI DEL DNA A cosa serve la mutagenesi del DNA? 1. Studio delle sequenze nucleotidiche, delle funzioni dei geni e di particolari aminoacidi nelle proteine. 2. Ingegnerizzazione di proteine in modo
COREA DI HUNTINGTON. Dott.ssa Silvia Battista Scuola di Specializzazione in Psichiatria
 COREA DI HUNTINGTON Dott.ssa Silvia Battista Scuola di Specializzazione in Psichiatria George Huntington (1850-1916) DESCRIZIONE Disordine genetico neurodegenerativo progressivo A trasmissione autosomica
COREA DI HUNTINGTON Dott.ssa Silvia Battista Scuola di Specializzazione in Psichiatria George Huntington (1850-1916) DESCRIZIONE Disordine genetico neurodegenerativo progressivo A trasmissione autosomica
 Patologia autosomico recessiva Malattia metabolica ereditaria Terapia dietetica Segni caratteristici : capelli biondi,cute chiara, ritardo mentale Rischi in gravidanza di malformazioni www.fisiokinesiterapia.biz
Patologia autosomico recessiva Malattia metabolica ereditaria Terapia dietetica Segni caratteristici : capelli biondi,cute chiara, ritardo mentale Rischi in gravidanza di malformazioni www.fisiokinesiterapia.biz
Bioinformatica. Analisi del genoma
 Bioinformatica Analisi del genoma GABRIELLA TRUCCO CREMA, 5 APRILE 2017 Cosa è il genoma? Insieme delle informazioni biologiche, depositate nella sequenza di DNA, necessarie alla costruzione e mantenimento
Bioinformatica Analisi del genoma GABRIELLA TRUCCO CREMA, 5 APRILE 2017 Cosa è il genoma? Insieme delle informazioni biologiche, depositate nella sequenza di DNA, necessarie alla costruzione e mantenimento
FASTA: Lipman & Pearson (1985) BLAST: Altshul (1990) Algoritmi EURISTICI di allineamento
 Algoritmi EURISTICI di allineamento Sono nati insieme alle banche dati, con lo scopo di permettere una ricerca per similarità rapida anche se meno accurata contro le migliaia di sequenze depositate. Attualmente
Algoritmi EURISTICI di allineamento Sono nati insieme alle banche dati, con lo scopo di permettere una ricerca per similarità rapida anche se meno accurata contro le migliaia di sequenze depositate. Attualmente
UNIVERSITÁ POLITECNICA DELLE MARCHE FACOLTÁ DI MEDICINA E CHIRURGIA
 UNIVERSITÁ POLITECNICA DELLE MARCHE FACOLTÁ DI MEDICINA E CHIRURGIA Dottorato di Ricerca X ciclo- Nuova serie Curriculum Oncologia MUTAZIONI GERMINALI DI GENI CORRELATI ALLA SINDROME DI LYNCH Tesi di Dottorato
UNIVERSITÁ POLITECNICA DELLE MARCHE FACOLTÁ DI MEDICINA E CHIRURGIA Dottorato di Ricerca X ciclo- Nuova serie Curriculum Oncologia MUTAZIONI GERMINALI DI GENI CORRELATI ALLA SINDROME DI LYNCH Tesi di Dottorato
Quarta lezione. 1. Ricerca di omologhe in banche dati. 2. Programmi per la ricerca: FASTA BLAST
 Quarta lezione 1. Ricerca di omologhe in banche dati. 2. Programmi per la ricerca: FASTA BLAST Ricerca di omologhe in banche dati Proteina vs. proteine Gene (traduzione in aa) vs. proteine Gene vs. geni
Quarta lezione 1. Ricerca di omologhe in banche dati. 2. Programmi per la ricerca: FASTA BLAST Ricerca di omologhe in banche dati Proteina vs. proteine Gene (traduzione in aa) vs. proteine Gene vs. geni
Z-score. lo Z-score è definito come: Z-score = (opt query - M random)/ deviazione standard random
 Z-score lo Z-score è definito come: Z-score = (opt query - M random)/ deviazione standard random è una misura di quanto il valore di opt si discosta dalla deviazione standard media. indica di quante dev.
Z-score lo Z-score è definito come: Z-score = (opt query - M random)/ deviazione standard random è una misura di quanto il valore di opt si discosta dalla deviazione standard media. indica di quante dev.
- PROGETTO DI LABORATORIO - PCR
 - PROGETTO DI LABORATORIO - PCR 1 DIFFERENZIAMENTO DEI SUBSET CELLULARI Th1, Th2, Th17 e Treg Controllo/eradicazione di tumori e patogeni intracellulari 2 CITOCHINE DELLA FAMIGLIA DI IL-12 3 4 5 PROGETTO
- PROGETTO DI LABORATORIO - PCR 1 DIFFERENZIAMENTO DEI SUBSET CELLULARI Th1, Th2, Th17 e Treg Controllo/eradicazione di tumori e patogeni intracellulari 2 CITOCHINE DELLA FAMIGLIA DI IL-12 3 4 5 PROGETTO
Mutagenesi: introduzione di alterazioni in una sequenza nucleotidica. Mutagenesi random: le mutazioni avvengono a caso su un tratto di DNA.
 Mutagenesi: introduzione di alterazioni in una sequenza nucleotidica Mutagenesi random: le mutazioni avvengono a caso su un tratto di DNA. In genere si ottengono trattando il DNA con agenti chimici (es.
Mutagenesi: introduzione di alterazioni in una sequenza nucleotidica Mutagenesi random: le mutazioni avvengono a caso su un tratto di DNA. In genere si ottengono trattando il DNA con agenti chimici (es.
Bioinformatica (3) Banche dati biologiche. Dott. Alessandro Laganà
 Bioinformatica (3) Banche dati biologiche Dott. Alessandro Laganà Banche dati biologiche Organismi e sequenze biologiche Rappresentazione digitale dei dati biologici e formati Banche dati generiche: NCBI,
Bioinformatica (3) Banche dati biologiche Dott. Alessandro Laganà Banche dati biologiche Organismi e sequenze biologiche Rappresentazione digitale dei dati biologici e formati Banche dati generiche: NCBI,
Il progetto Genoma Umano è iniziato nel E stato possibile perchè nel 1986 era stato sviluppato il sequenziamento automatizzato del DNA.
 Il progetto Genoma Umano è iniziato nel 1990. E stato possibile perchè nel 1986 era stato sviluppato il sequenziamento automatizzato del DNA. Progetto internazionale finanziato da vari paesi, affidato
Il progetto Genoma Umano è iniziato nel 1990. E stato possibile perchè nel 1986 era stato sviluppato il sequenziamento automatizzato del DNA. Progetto internazionale finanziato da vari paesi, affidato
RNA. Uracile al posto della Timina RNA MESSAGGERO. Sempre a SINGOLO FILAMENTO
 DNA 1 RNA Uracile al posto della Timina Sempre a SINGOLO FILAMENTO RNA MESSAGGERO Filamento lineare di sequenze nucleotidiche: copia l informazione presente sul DNA e porta il messaggio a livello dei ribosomi
DNA 1 RNA Uracile al posto della Timina Sempre a SINGOLO FILAMENTO RNA MESSAGGERO Filamento lineare di sequenze nucleotidiche: copia l informazione presente sul DNA e porta il messaggio a livello dei ribosomi
Produzione di proteine eterologhe. Cosa occorre per l espressione l livello di una proteina nella cellula? Trascrizione/traduzione/stabilità
 Cosa occorre per l espressione l ad alto livello di una proteina nella cellula? Trascrizione/traduzione/stabilità Promotore forte (trascrizione) Presenza di segnali per il riconoscimento dell mrna da parte
Cosa occorre per l espressione l ad alto livello di una proteina nella cellula? Trascrizione/traduzione/stabilità Promotore forte (trascrizione) Presenza di segnali per il riconoscimento dell mrna da parte
Allineamenti a coppie
 Laboratorio di Bioinformatica I Allineamenti a coppie Dott. Sergio Marin Vargas (2014 / 2015) ExPASy Bioinformatics Resource Portal (SIB) http://www.expasy.org/ Il sito http://myhits.isb-sib.ch/cgi-bin/dotlet
Laboratorio di Bioinformatica I Allineamenti a coppie Dott. Sergio Marin Vargas (2014 / 2015) ExPASy Bioinformatics Resource Portal (SIB) http://www.expasy.org/ Il sito http://myhits.isb-sib.ch/cgi-bin/dotlet
ISTITUTO SUPERIORE DI SANITÀ
 ISTITUTO SUPERIORE DI SANITÀ Metodi microbiologici tradizionali e metodi molecolari per l analisi degli integratori alimentari a base di o con probiotici per uso umano Paolo Aureli, Alfonsina Fiore, Concetta
ISTITUTO SUPERIORE DI SANITÀ Metodi microbiologici tradizionali e metodi molecolari per l analisi degli integratori alimentari a base di o con probiotici per uso umano Paolo Aureli, Alfonsina Fiore, Concetta
Sequenze nucleotidiche del DNA definite loci costituiscono i geni. Ogni gene codifica per una specifica proteina
 sintesi proteica La sintesi proteica è il processo che porta alla formazione delle proteine da sequenze del DN definite geni. Si tratta di un processo a più fasi Nelle sue linee fondamentali questo processo
sintesi proteica La sintesi proteica è il processo che porta alla formazione delle proteine da sequenze del DN definite geni. Si tratta di un processo a più fasi Nelle sue linee fondamentali questo processo
Amminoacidi. Struttura base di un a-amminoacido
 Amminoacidi Struttura base di un a-amminoacido Forma non ionizzata Forma ionizzata, sale interno (zwitterione) Il carbonio α di tutti gli α-amminoacidi (tranne la glicina) è asimmetrico (=chirale) D-alanina
Amminoacidi Struttura base di un a-amminoacido Forma non ionizzata Forma ionizzata, sale interno (zwitterione) Il carbonio α di tutti gli α-amminoacidi (tranne la glicina) è asimmetrico (=chirale) D-alanina
sono le unità monomeriche che costituiscono le proteine hanno tutti una struttura comune
 AMINO ACIDI sono le unità monomeriche che costituiscono le proteine sono 20 hanno tutti una struttura comune sono asimmetrici La carica di un amino acido dipende dal ph Classificazione amino acidi Glicina
AMINO ACIDI sono le unità monomeriche che costituiscono le proteine sono 20 hanno tutti una struttura comune sono asimmetrici La carica di un amino acido dipende dal ph Classificazione amino acidi Glicina
La sintesi delle proteine
 La sintesi delle proteine Struttura del trna In che modo l informazione contenuta sotto forma di sequenze nucleotidiche nel DNA e nell RNA si traduce nella sequenza amminoacidica delle proteine? Esperimenti
La sintesi delle proteine Struttura del trna In che modo l informazione contenuta sotto forma di sequenze nucleotidiche nel DNA e nell RNA si traduce nella sequenza amminoacidica delle proteine? Esperimenti
Bioinformatica ed applicazioni di bioinformatica strutturale!
 Bioinformatica ed applicazioni di bioinformatica strutturale! Bioinformatica! Le banche dati! Programmi per estrarre ed analizzare i dati! I numeri! Cellule nell uomo! Geni nell uomo! Genoma umano Il dogma
Bioinformatica ed applicazioni di bioinformatica strutturale! Bioinformatica! Le banche dati! Programmi per estrarre ed analizzare i dati! I numeri! Cellule nell uomo! Geni nell uomo! Genoma umano Il dogma
Percorsi di chimica organica - Soluzioni degli esercizi del testo
 ercorsi di chimica organica - Soluzioni degli esercizi del testo AITL 14 1. Il prefisso α negli α-amminoacidi sta ad indicare che il gruppo amminico, - 2, si trova sul carbonio alfa (carbonio legato al
ercorsi di chimica organica - Soluzioni degli esercizi del testo AITL 14 1. Il prefisso α negli α-amminoacidi sta ad indicare che il gruppo amminico, - 2, si trova sul carbonio alfa (carbonio legato al
Ricerche con BLAST (Laboratorio)
 Laboratorio di Bioinformatica I Ricerche con BLAST (Laboratorio) Dott. Sergio Marin Vargas (2014 / 2015) NCBI BLAST BLAST: Basic Local Alignment Search Tool http://blast.ncbi.nlm.nih.gov/blast.cgi NCBI
Laboratorio di Bioinformatica I Ricerche con BLAST (Laboratorio) Dott. Sergio Marin Vargas (2014 / 2015) NCBI BLAST BLAST: Basic Local Alignment Search Tool http://blast.ncbi.nlm.nih.gov/blast.cgi NCBI
Mutazioni. Un cambiamento nel materiale genetico che non venga riparato dai meccanismi di riparo costituisce una mutazione
 Mutazioni Un cambiamento nel materiale genetico che non venga riparato dai meccanismi di riparo costituisce una mutazione Le mutazioni possono essere spontanee oppure causate da agenti fisici, chimici
Mutazioni Un cambiamento nel materiale genetico che non venga riparato dai meccanismi di riparo costituisce una mutazione Le mutazioni possono essere spontanee oppure causate da agenti fisici, chimici
BLAST: Basic Local Alignment Search Tool
 BLAST: Basic Local Alignment Search Tool 1 Outline della lezione di oggi BLAST Uso pratico Algoritmo Strategie Trovare proteine lontanamente legate: PSI-BLAST 2 Problema con gli algoritmi dinamici Gli
BLAST: Basic Local Alignment Search Tool 1 Outline della lezione di oggi BLAST Uso pratico Algoritmo Strategie Trovare proteine lontanamente legate: PSI-BLAST 2 Problema con gli algoritmi dinamici Gli
Martina Torricelli, Elisa Pierboni, Gloria Raquel Tovo, Cristina Rondini
 1 Biblioteca Istituto Zooprofilattico Sperimentale dell'umbria e delle Marche Webzine Sanità Pubblica Veterinaria: Numero 87, Dicembre 2014 [http://spvet.it/] ISSN 1592-1581 Confronto quali-quantitativo
1 Biblioteca Istituto Zooprofilattico Sperimentale dell'umbria e delle Marche Webzine Sanità Pubblica Veterinaria: Numero 87, Dicembre 2014 [http://spvet.it/] ISSN 1592-1581 Confronto quali-quantitativo
Sperimenta il BioLab Attività di Bioinformatica Caccia al gene
 Sperimenta il BioLab Attività di Bioinformatica Caccia al gene Università degli Studi di Milano Settore Didattico, via Celoria 20, Milano Laboratorio 105 INTRODUZIONE Questa attività pratica ha come scopo
Sperimenta il BioLab Attività di Bioinformatica Caccia al gene Università degli Studi di Milano Settore Didattico, via Celoria 20, Milano Laboratorio 105 INTRODUZIONE Questa attività pratica ha come scopo
REPLICAZIONE DEL DNA
 REPLICAZIONE DEL DNA La replicazione (o anche duplicazione) è il meccanismo molecolare attraverso cui il DNA produce una copia di sé stesso. Ogni volta che una cellula si divide, infatti, l'intero genoma
REPLICAZIONE DEL DNA La replicazione (o anche duplicazione) è il meccanismo molecolare attraverso cui il DNA produce una copia di sé stesso. Ogni volta che una cellula si divide, infatti, l'intero genoma
Amminoacidi (1) Acido 2-ammino propanoico (acido α-ammino propionico) α * NH 2 CH 3 COOH
 Amminoacidi (1) Presentano un gruppo amminico ( N 2 ) ed un gruppo carbossilico ( OO) nella stessa molecola 3 N 2 α * OO Acido 2-ammino propanoico (acido α-ammino propionico) STPA-himica Organica 1 Amminoacidi
Amminoacidi (1) Presentano un gruppo amminico ( N 2 ) ed un gruppo carbossilico ( OO) nella stessa molecola 3 N 2 α * OO Acido 2-ammino propanoico (acido α-ammino propionico) STPA-himica Organica 1 Amminoacidi
MUTAGENESI DEL DNA. A cosa serve la mutagenesi del DNA?
 A cosa serve la mutagenesi del DNA? MUTAGENESI DEL DNA 1. Studio delle sequenze nucleotidiche, delle funzioni dei geni e di particolari aminoacidi nelle proteine. 2. Ingegnerizzazione di proteine in modo
A cosa serve la mutagenesi del DNA? MUTAGENESI DEL DNA 1. Studio delle sequenze nucleotidiche, delle funzioni dei geni e di particolari aminoacidi nelle proteine. 2. Ingegnerizzazione di proteine in modo
Allineamento e similarità di sequenze
 Allineamento e similarità di sequenze Allineamento di Sequenze L allineamento tra due o più sequenza può aiutare a trovare regioni simili per le quali si può supporre svolgano la stessa funzione; La similarità
Allineamento e similarità di sequenze Allineamento di Sequenze L allineamento tra due o più sequenza può aiutare a trovare regioni simili per le quali si può supporre svolgano la stessa funzione; La similarità
Proteine strutturali Sostegno meccanico Cheratina: costituisce i capelli Collagene: costituisce le cartilagini Proteine di immagazzinamento
 Tipo Funzione Esempi Enzimi Accelerano le reazioni chimiche Saccarasi: posiziona il saccarosio in modo che possa essere scisso nelle due unità di glucosio e fruttosio che lo formano Ormoni Messaggeri chimici
Tipo Funzione Esempi Enzimi Accelerano le reazioni chimiche Saccarasi: posiziona il saccarosio in modo che possa essere scisso nelle due unità di glucosio e fruttosio che lo formano Ormoni Messaggeri chimici
Amminoacidi. Struttura base di un a-amminoacido
 Amminoacidi Struttura base di un a-amminoacido Forma non ionizzata Forma ionizzata, sale interno (zwitterione) Il carbonio α di tutti gli α-amminoacidi (tranne la glicina) è asimmetrico (=chirale) D-alanina
Amminoacidi Struttura base di un a-amminoacido Forma non ionizzata Forma ionizzata, sale interno (zwitterione) Il carbonio α di tutti gli α-amminoacidi (tranne la glicina) è asimmetrico (=chirale) D-alanina
Prof. Giorgio Sartor. Sintesi proteica. Trasmissione dell informazione
 rof. Giorgio Sartor Sintesi proteica Copyright 2001-2013 by Giorgio Sartor. All rights reserved. B15 -Versione 1.0 nov2013 Trasmissione dell informazione L informazione è contenuta nel DA ed è trasferita
rof. Giorgio Sartor Sintesi proteica Copyright 2001-2013 by Giorgio Sartor. All rights reserved. B15 -Versione 1.0 nov2013 Trasmissione dell informazione L informazione è contenuta nel DA ed è trasferita
MACROMOLECOLE. Polimeri (lipidi a parte)
 MACROMOLECOLE Monomeri Polimeri (lipidi a parte) Le caratteristiche strutturali e funzionali di una cellula o di un organismo sono determinate principalmente dalle sue proteine. Ad esempio: Le proteine
MACROMOLECOLE Monomeri Polimeri (lipidi a parte) Le caratteristiche strutturali e funzionali di una cellula o di un organismo sono determinate principalmente dalle sue proteine. Ad esempio: Le proteine
Algoritmi di Allineamento
 Algoritmi di Allineamento CORSO DI BIOINFORMATICA Corso di Laurea in Biotecnologie Università Magna Graecia Catanzaro Outline Similarità Allineamento Omologia Allineamento di Coppie di Sequenze Allineamento
Algoritmi di Allineamento CORSO DI BIOINFORMATICA Corso di Laurea in Biotecnologie Università Magna Graecia Catanzaro Outline Similarità Allineamento Omologia Allineamento di Coppie di Sequenze Allineamento
α-amminoacidi O α O α R CH C O - NH 3 forma ionizzata sale interno (zwitterione) OH NH 2 forma non ionizzata (non esistente in realtà)
 Amminoacidi 2 forma non ionizzata (non esistente in realtà) 3 forma ionizzata sale interno (zwitterione) In soluzione acquosa c'è equilibrio tra tre forme 3 forma cationica p molto acidi 3 forma zwitterionica
Amminoacidi 2 forma non ionizzata (non esistente in realtà) 3 forma ionizzata sale interno (zwitterione) In soluzione acquosa c'è equilibrio tra tre forme 3 forma cationica p molto acidi 3 forma zwitterionica
DNA E PROTEINE IL DNA E RACCHIUSO NEL NUCLEO, MENTRE LA SINTESI PROTEICA SI SVOLGE NEL CITOPLASMA: COME VIENE TRASPORTATA L INFORMAZIONE?
 DNA E PROTEINE NUMEROSI DATI SUGGERISCONO CHE IL DNA SVOLGA IL SUO RUOLO GENETICO CONTROLLANDO LA SINTESI DELLE PROTEINE, IN PARTICOLARE DETERMINANDONE LA SEQUENZA IN AMINOACIDI E NECESSARIO RISPONDERE
DNA E PROTEINE NUMEROSI DATI SUGGERISCONO CHE IL DNA SVOLGA IL SUO RUOLO GENETICO CONTROLLANDO LA SINTESI DELLE PROTEINE, IN PARTICOLARE DETERMINANDONE LA SEQUENZA IN AMINOACIDI E NECESSARIO RISPONDERE
Allineamento dei 2 RNA
 La traduzione 2 codone Allineamento dei 2 RNA anticodone Studi Molecolari hanno dimostrato che: 3 residui nucleotidici del mrna sono necessari per codificare ciascun amminoacido Il linguaggio contenuto
La traduzione 2 codone Allineamento dei 2 RNA anticodone Studi Molecolari hanno dimostrato che: 3 residui nucleotidici del mrna sono necessari per codificare ciascun amminoacido Il linguaggio contenuto
Codice Genetico (segue)
 CODICE GENETICO Nucleotidi, acidi nucleici CODICE GENETICO Codice mediante il quale la sequenza nucleotidica di una molecola di DNA o di RNA specifica la sequenza amminoacidica di un polipeptide. Consiste
CODICE GENETICO Nucleotidi, acidi nucleici CODICE GENETICO Codice mediante il quale la sequenza nucleotidica di una molecola di DNA o di RNA specifica la sequenza amminoacidica di un polipeptide. Consiste
Amminoacidi (1) Acido 2-ammino propanoico (acido α-ammino propionico) α * NH 2 CH 3 COOH. ) ed un gruppo carbossilico ( COOH) nella stessa molecola
 Amminoacidi (1) Presentano un gruppo amminico ( NH 2 ) ed un gruppo carbossilico ( COOH) nella stessa molecola CH 3 NH 2 C H α * COOH Acido 2-ammino propanoico (acido α-ammino propionico) 1 Amminoacidi
Amminoacidi (1) Presentano un gruppo amminico ( NH 2 ) ed un gruppo carbossilico ( COOH) nella stessa molecola CH 3 NH 2 C H α * COOH Acido 2-ammino propanoico (acido α-ammino propionico) 1 Amminoacidi
RNA polimerasi II precursori mrna snrna
 RNA polimerasi II trascrive i geni per la sintesi dei precursori degli mrna, molti snrna (U1, U2, U3, U4, U5, ), un gran numero di long non coding RNA mrna di Eucarioti e Procarioti alla fine si lega
RNA polimerasi II trascrive i geni per la sintesi dei precursori degli mrna, molti snrna (U1, U2, U3, U4, U5, ), un gran numero di long non coding RNA mrna di Eucarioti e Procarioti alla fine si lega
Nel codice genetico, una tripletta di nucleotidi codifica per un aminoacido
 Il codice genetico: Come triplette dei quattro nucleotidi specificano 20 aminoacidi, rendendo possibile la traduzione dell informazione da catena nucleotidica a sequenza di aminoacidi. Come le mutazioni
Il codice genetico: Come triplette dei quattro nucleotidi specificano 20 aminoacidi, rendendo possibile la traduzione dell informazione da catena nucleotidica a sequenza di aminoacidi. Come le mutazioni
InfoBioLab I ENTREZ. ES 1: Ricerca di sequenze di aminoacidi in banche dati biologiche
 InfoBioLab I ES 1: Ricerca di sequenze di aminoacidi in banche dati biologiche Esercizio 1 - obiettivi: Ricerca di 2 proteine in ENTREZ Salva i flat file che descrivono le 2 proteine in formato testo Importa
InfoBioLab I ES 1: Ricerca di sequenze di aminoacidi in banche dati biologiche Esercizio 1 - obiettivi: Ricerca di 2 proteine in ENTREZ Salva i flat file che descrivono le 2 proteine in formato testo Importa
Informatica e biotecnologie II parte
 Informatica e biotecnologie II parte Analisi di sequenze: allineamenti CGCTTCGGACGAAATCGCATCAGCATACGATCGCATGCCGGGCGGGATAAC CGAAATCGCATCAGCATACGATCGCATGC Bioinformatica La Bioinformatica è una disciplina
Informatica e biotecnologie II parte Analisi di sequenze: allineamenti CGCTTCGGACGAAATCGCATCAGCATACGATCGCATGCCGGGCGGGATAAC CGAAATCGCATCAGCATACGATCGCATGC Bioinformatica La Bioinformatica è una disciplina
ISTITUTO SUPERIORE DI SANITÀ
 ISTITUTO SUPERIORE DI SANITÀ Metodi microbiologici tradizionali e metodi molecolari per l analisi degli integratori alimentari a base di o con probiotici per uso umano Paolo Aureli, Alfonsina Fiore, Concetta
ISTITUTO SUPERIORE DI SANITÀ Metodi microbiologici tradizionali e metodi molecolari per l analisi degli integratori alimentari a base di o con probiotici per uso umano Paolo Aureli, Alfonsina Fiore, Concetta
Caratterizzazione molecolare di antiche cultivar di melo del Cilento (Salerno)
 Delpinoa, n.s. 46: 117-122. 2004 Caratterizzazione molecolare di antiche cultivar di melo del Cilento (Salerno) M. D. MoCCIA 1, R. DI NoVeLLA 2, P. De LuCA 2 1 Dipartimento delle Scienze Biologiche, Sezione
Delpinoa, n.s. 46: 117-122. 2004 Caratterizzazione molecolare di antiche cultivar di melo del Cilento (Salerno) M. D. MoCCIA 1, R. DI NoVeLLA 2, P. De LuCA 2 1 Dipartimento delle Scienze Biologiche, Sezione
Amminoacidi (1) Acido 2-ammino propanoico (acido α-ammino propionico) α * NH 2 CH 3 COOH
 Amminoacidi (1) Presentano un gruppo amminico ( N 2 ) ed un gruppo carbossilico ( COO) nella stessa molecola C 3 N 2 C α * COO Acido 2-ammino propanoico (acido α-ammino propionico) STPA-Chimica Organica
Amminoacidi (1) Presentano un gruppo amminico ( N 2 ) ed un gruppo carbossilico ( COO) nella stessa molecola C 3 N 2 C α * COO Acido 2-ammino propanoico (acido α-ammino propionico) STPA-Chimica Organica
PROTEINA GREGGIA (P.G.)
 PROTEINA GREGGIA (P.G.) Il contenuto proteico di un alimento è valutato dal suo tenore in azoto, determinato con il metodo Kjeldahl modificato. Il metodo Kjeldahl valuta la maggior parte dell azoto presente
PROTEINA GREGGIA (P.G.) Il contenuto proteico di un alimento è valutato dal suo tenore in azoto, determinato con il metodo Kjeldahl modificato. Il metodo Kjeldahl valuta la maggior parte dell azoto presente
Struttura degli amminoacidi
 AMMINOACIDI, PEPTIDI E PROTEINE AMMINOACIDI, PEPTIDI E PROTEINE AMMINOACIDI, PEPTIDI E PROTEINE Le proteine sono macromolecole costituite dall unione di un grande numero di unità elementari: gli amminoacidi
AMMINOACIDI, PEPTIDI E PROTEINE AMMINOACIDI, PEPTIDI E PROTEINE AMMINOACIDI, PEPTIDI E PROTEINE Le proteine sono macromolecole costituite dall unione di un grande numero di unità elementari: gli amminoacidi
Una proteina nella rete: Caccia al tesoro bioinformatica
 Una proteina nella rete: Caccia al tesoro bioinformatica Nel corso di questa attivita utilizzeremo alcune delle piu importanti banche dati disponibili in rete per cercare informazioni su una proteina.
Una proteina nella rete: Caccia al tesoro bioinformatica Nel corso di questa attivita utilizzeremo alcune delle piu importanti banche dati disponibili in rete per cercare informazioni su una proteina.
La chimica della vita si basa sui composti del carbonio e dipende da reazioni chimiche che avvengono in soluzione acquosa.
 La chimica della vita si basa sui composti del carbonio e dipende da reazioni chimiche che avvengono in soluzione acquosa. Le cellule contengono 4 famiglie principali di piccole molecole organiche: Amminoacidi
La chimica della vita si basa sui composti del carbonio e dipende da reazioni chimiche che avvengono in soluzione acquosa. Le cellule contengono 4 famiglie principali di piccole molecole organiche: Amminoacidi
ALLINEAMENTO DI SEQUENZE
 ALLINEAMENTO DI SEQUENZE Procedura per comparare due o piu sequenze, volta a stabilire un insieme di relazioni biunivoche tra coppie di residui delle sequenze considerate che massimizzino la similarita
ALLINEAMENTO DI SEQUENZE Procedura per comparare due o piu sequenze, volta a stabilire un insieme di relazioni biunivoche tra coppie di residui delle sequenze considerate che massimizzino la similarita
amminico è legato all atomo di carbonio immediatamente adiacente al gruppo carbonilico e hanno la seguente
 Gli amminoacidi naturali sono α-amminoacidi : il gruppo amminico è legato all atomo di carbonio immediatamente adiacente al gruppo carbonilico e hanno la seguente formula generale: gruppo funzionale carbossilico
Gli amminoacidi naturali sono α-amminoacidi : il gruppo amminico è legato all atomo di carbonio immediatamente adiacente al gruppo carbonilico e hanno la seguente formula generale: gruppo funzionale carbossilico
Corso di Genetica -Lezione 12- Cenci
 Corso di Genetica -Lezione 12- Cenci Il codice genetico: Come triplette dei quattro nucleotidi specificano 20 aminoacidi, rendendo possibile la traduzione dell informazione da catena nucleotidica a sequenza
Corso di Genetica -Lezione 12- Cenci Il codice genetico: Come triplette dei quattro nucleotidi specificano 20 aminoacidi, rendendo possibile la traduzione dell informazione da catena nucleotidica a sequenza
emulsione per infusione 4 sacche excel multicompartimentate da 1206 ml emulsione per infusione 4 sacche biofine multicompartimentate da 1206 ml
 Autorizzazione all immissione in commercio del medicinale «Perismofven» Estratto determinazione n. 408/2012 del 4 giugno 2012 MEDICINALE PERISMOFVEN TITOLAREAIC: FreseniusKabiItaliaS.r.l. ViaCamagre,41
Autorizzazione all immissione in commercio del medicinale «Perismofven» Estratto determinazione n. 408/2012 del 4 giugno 2012 MEDICINALE PERISMOFVEN TITOLAREAIC: FreseniusKabiItaliaS.r.l. ViaCamagre,41
Vittoria Patti MACROMOLECOLE BIOLOGICHE. 4. proteine
 Vittoria Patti MACROMOLECOLE BIOLOGICHE 4. proteine 1 Funzioni principali delle proteine funzione cosa significa esempi ENZIMATICA STRUTTURALE TRASPORTO MOVIMENTO DIFESA IMMUNITARIA ORMONALE catalizzare
Vittoria Patti MACROMOLECOLE BIOLOGICHE 4. proteine 1 Funzioni principali delle proteine funzione cosa significa esempi ENZIMATICA STRUTTURALE TRASPORTO MOVIMENTO DIFESA IMMUNITARIA ORMONALE catalizzare
Corso di. Giandomenico Corrado Dipartimento di Scienze del Suolo, della Pianta e dell Ambiente : [email protected] : 081.25.39446
 Corso di Giandomenico Corrado Dipartimento di Scienze del Suolo, della Pianta e dell Ambiente : [email protected] : 081.25.39446 Oultine della lezione Introduzione alla base genetica della diversità DNA,
Corso di Giandomenico Corrado Dipartimento di Scienze del Suolo, della Pianta e dell Ambiente : [email protected] : 081.25.39446 Oultine della lezione Introduzione alla base genetica della diversità DNA,
Allineamento locale: BLAST
 Allineamento locale: BLAST BLAST (Basic Local Alignment Search Tool) è il più diffuso programma di allineamento locale delle sequenze. Per vari anni il metodo FASTA (da non confondere con l omonimo formato)
Allineamento locale: BLAST BLAST (Basic Local Alignment Search Tool) è il più diffuso programma di allineamento locale delle sequenze. Per vari anni il metodo FASTA (da non confondere con l omonimo formato)
Confezione G13%E emulsione per infusione 10 sacche da 300 ml a 3 camere non PVC AIC n /M (in base 10) 16WBCU (in base 32)
 Autorizzazione all immissione in commercio del medicinale «Numeta» Estratto determinazione n. 2473/2011 MEDICINALE NUMETA TITOLARE AIC: BAXTER S.P.A. Piazzale dell Industria, 20 00144 ROMA G13%E emulsione
Autorizzazione all immissione in commercio del medicinale «Numeta» Estratto determinazione n. 2473/2011 MEDICINALE NUMETA TITOLARE AIC: BAXTER S.P.A. Piazzale dell Industria, 20 00144 ROMA G13%E emulsione
INTERAZIONE TRA mrna, trna e RIBOSOMI
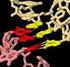 INTERAZIONE TRA mrna, trna e RIBOSOMI mrna: porta l'informazione della sequenza degli aminoacidi di una determinata proteina. trna: ogni trna è specifico per il trasporto di un determinato aminoacido Ribosoma:
INTERAZIONE TRA mrna, trna e RIBOSOMI mrna: porta l'informazione della sequenza degli aminoacidi di una determinata proteina. trna: ogni trna è specifico per il trasporto di un determinato aminoacido Ribosoma:
