RISOLUZIONE OIV-OENO
|
|
|
- Luigi Pellegrini
- 9 anni fa
- Просмотров:
Транскрипт
1 RISOLUZIONE OIV-OENO STRUMENTI DI BIOLOGIA MOLECOLARE PER L'IDENTIFICAZIONE DEL LIEVITO VINARIO SACCHAROMYCES CEREVISIAE E DI ALTRE SPECIE DI LIEVITI RELATIVE ALLA VINIFICAZIONE L ASSEMBLEA GENERALE Visto l'articolo 2 paragrafo 2, n. IV dell'accordo del 3 aprile 2001 che istituisce l'organizzazione Internazionale della Vigna e del Vino, Su proposta del gruppo di esperti di Microbiologia DECIDE di adottare i seguenti strumenti di biologia molecolare per l'identificazione del lievito vinario Saccharomyces cerevisiae e di altre specie di lieviti relative alla vinificazione DECIDE, inoltre, di includere le seguenti Premesse nel promuovere gli strumenti di biologia molecolare per l'identificazione del lievito vinario Saccharomyces cerevisiae e di altre specie di lieviti legate alla vinificazione, nonché gli strumenti di biologia molecolare per l'identificazione dei batteri lattici [Oeno-MICRO ] sull uva e nel vino Premessa [ad Oeno-MICRO ed Oeno-MICRO ] L'origine, lo sviluppo, i cambiamenti e la successione delle varie specie di lievito possono essere seguiti utilizzando specifiche tecniche molecolari che permettono la differenziazione e la tipizzazione dei ceppi di lievito. Recentemente, nello studio della microbiologia della vinificazione sono state impiegate diverse tecniche. Tali metodi sono sensibili e specifici, essendo volti a rispondere alle diverse esigenze, oltre ad essere semplici, rapidi, riproducibili, efficaci, affidabili e non costosi. L applicazione di metodi molecolari di identificazione può essere effettuata senza una previa coltura, oppure a seguito di arricchimento o anche a seguito di isolamento dei microrganismi. Ciò permette di conoscere meglio il sistema microbico che si sviluppa sulla superficie dell uva o del vino. La presente guida ha lo scopo di assistere i laboratori che svolgono analisi microbiologiche nel loro approccio all identificazione del lievito Saccharomyces cerevisiae e di altre specie di lieviti [Oeno-MICRO ] relative alla vinificazione, nonché nell identificazione dei batteri lattici [Oeno-MICRO ] presenti sull uva e nel vino. Le tecniche riportate trattano i principi generali delle tecniche molecolari disponibili. Per i metodi dettagliati si rimanda alla bibliografia. 1
2 Strumenti molecolari per l'identificazione del lievito vinario Saccharomyces cerevisiae e di altre specie di lieviti relative alla vinificazione Per l'identificazione e la caratterizzazione dei lieviti vinari in diverse fasi della vinificazione, dell invecchiamento e della conservazione possono essere utilizzati metodi coltura-dipendenti o coltura-indipendenti. METODI COLTURA-DIPENDENTI IDENTIFICAZIONE DI LIEVITI A LIVELLO DI SPECIE rdna PCR-RFLP (restriction fragments length polymorphism) Si tratta di un metodo coltura-dipendente, poiché richiede l'estrazione del DNA da una coltura pura. Tale metodo si basa sull'amplificazione di regioni specifiche di unità ripetute di rdna (tra cui gli spaziatori interni trascritti ITS1 e ITS2 e il gene 5.8S rrna integrato o il gene 265 rrna). Tali regioni hanno sequenze altamente conservate e sequenze che mostrano un alto grado di variabilità genetica tra lieviti di specie differenti. Nella maggioranza dei casi, i prodotti della PCR amplificati da ceppi della stessa specie e dello stesso genere presentano dimensioni molecolari identiche, e le specie dello stesso genere hanno dimensioni simili. Anche se della stessa dimensione, la sequenza di tali regioni amplificate differisce secondo le specie. Pertanto, la differenza di sequenza è messa in evidenza mediante l analisi di restrizione utilizzando differenti endonucleasi di restrizione come ad esempio: CfoI HaeIII, HinfI, DdeI, MboI. I profili di restrizione differiscono secondo le specie. L enzima DdeI è necessario per la differenziazione tra H. uvarum e H. Guilliermondii, come riportato da Esteve-Zarzoso et al. (1999) e Cadez et al., 2002, mentre l'enzima MboI è necessario per distinguere C. zemplinina da C. stellata (Sipicki, 2004). Inoltre, per differenziare le specie del genere Saccharomyces e i relativi ibridi dovrebbero essere utilizzati altri enzimi di restrizione (Gonzales et al., 2006). Questa metodologia è già stata utilizzata per identificare circa 145 specie di lieviti appartenenti a 26 generi di lievito differenti e i profili di restrizione della maggior parte delle specie identificate sono riportati da Esteve-Zarzoso et al. (1999) e Zanol et al. (2010). Dati relativi all ITS-5.8S sono disponibili online ( Esteve-Zarzoso et al., (1999) Identification of yeasts by RFLP analysis of the 5.8 S rrna gene and the two ribosomal internal transcribed spacers. Int. J. Syst. Bacteriolo. 49, 329-2
3 337. Fernández-Espinar et al. (2000) RFLP analysis of the ribosomal transcribed spacers and the 5.8 S rrna gene region of the genus Saccharomyces: a fast method for species identification and the differentiation of flor yeasts.. Antoine Van Leeuwenhoek 78: De Llanos et al. (2004) Identification of species of genus Candida by RFLP analysis of the 5.8 S rrna gene and the two ribosomal internal transcribed spacers.. Antoine Van Leeuwenhoek 85: Baleiras Couto et al. (2005) Partial 26S rdna restriction analysis as a tool to characterise non-saccharomyces yeasts present during red wine fermentations. Int. J. Food Microbiol 102, Zanol G., Baleiras-Couto M.M., Duarte F.L. (2010) Restriction profiles of 26S rdna as a molecular approach for wine yeasts identification. Ciência e Técnica Vitivinícola 25: Cadez N., Raspor P., de Cock A.W.A.M., Boekhout T., Smith M.Th. (2002) Molecular identification and genetic diversity within species of the genera Hanseniaspora and Kloeckera. FEMS Yeast Research 1, Sipiczki M. (2004) Species identification and comparative molecular and physiological analysis of Candida zemplinina and Candida stellata. J. Basic Microbiol. 44 (6), González S.S., Barrio E., Gafner J., Querol A. (2006) Natural hybrids from Saccharomyces cerevisiae, Saccharomyces bayanus and Saccharomyces kudriavzevii in wine fermentations. FEMS Yeast Res 6, Sequenziamento della regione D1/D2 dopo amplificazione PCR Si tratta di un metodo coltura-dipendente, poiché richiede l estrazione del DNA da una coltura pura. Si basa sull amplificazione della regione D1/D2 del gene 26S rrna e sul successivo sequenziamento dell amplicone ottenuto. La sequenza della regione D1/D2 differisce più dell 1% tra specie diverse e meno dell 1% tra ceppi appartenenti alla stessa specie. La sequenza della regione D1/D2 del gene 26S rrna consente di compiere una differenziazione all interno dell ampia varietà di specie di lieviti conosciute. La sequenza della regione D1/D2 del gene 26S rrna permette la classificazione e l identificazione filogenetica degli isolati incogniti, giacché il database esistente è di gran lunga il più grande tra i geni dei lieviti. 3
4 Kurtzman e Robnett (1997) Identification of clinically important ascomycetous yeasts based on nucleotide divergence in the 5' end of the large-subunit (26S) ribosomal DNA gene. J Clin Microbiol. 35, 5 :: Kurtzman e Robnett (1998) Identification and phylogeny of ascomycetous yeasts from analysis of nuclear large subunit (26S) ribosomal DNA partial sequences. Antonie Van Leeuwenhoek. 73, 4,: Baleiras Couto et al. (2005) Partial 26S rdna restriction analysis as a tool to characterise non-saccharomyces yeasts present during red wine fermentations. Int. J. Food Microbiol 102, IDENTIFICAZIONE DEI LIEVITI VINARI A LIVELLO DI CEPPO RFLP (restriction fragments length polymorphism) del DNA mitocondriale (mtdna) Il DNA mitocondriale (mtdna) del S. cerevisiae è una piccola molecola di Kb il cui grado di variabilità può essere osservato mediante l analisi di restrizione. L alto grado di polimorfismo del mtdna consente di analizzare la variabilità di specifici ceppi vinari di S. cerevisiae. Si tratta di uno dei metodi più utilizzati al fine di caratterizzare i lieviti vinari isolati durante la fermentazione alcolica. Querol et al (1992) e López et al (2001) hanno semplificato il metodo d analisi: è richiesta soltanto l estrazione del DNA totale da un isolato in coltura pura e l analisi di restrizione con gli enzimi di restrizione Hinf I o Rsa I (Guillamón et al., 1994, Schuller et al 2004; Lopes et al 2006). La presente tecnica permette un alta capacità d identificazione del ceppo in tempi brevi. Può essere utilizzata dall industria vinicola, poiché è una tecnica rapida, sicura e non necessita di strumentazione PCR. Querol et al (1992) A comparative study of different methods of yeast strain characterization. Syst. Appl. Microbiol. 15: Guillamón et al (1994) Rapid characterization of four species of the Saccharomyces sensu stricto complex according to mitochondrial DNA patterns. Int. J. Bacteriol. 44: López et al (2001) A simplified procedure to analyse mtdna from industrial yeast. Int. J. Food Microbiology 68: Schuller D, Valero E., Dequin S., Casal (2004) Survey of molecular methods for the typing of wine yeast strains. FEMS Microbiology Letters 231,
5 Lopes C.A, Lavalle T.L, Querol A., Caballero A.C. (2006) Combined use of killer biotype and mtdna-rflp patterns in a Patagonian wine Saccharomyces cerevisiae diversity study. Antonie van Leeuwenhoek 89, Amplificazione delle sequenze Delta (δ) Le sequenze Delta sono elementi di 0,3 Kb (334 bp) che affiancano i retrotrasposoni Ty1 in S. cerevisiae. All interno del genoma del lievito sono state trovate tra 35 e 55 copie di sequenze delta, come parte dei retrotrasposoni Ty1 o come elementi isolati. Tuttavia, tali sequenze delta sono concentrate nelle regioni genomiche che si legano ai geni trna. Il numero e l ubicazione di questi elementi presentano una certa variabilità intraspecifica che Ness et al (1993) hanno utilizzato per l elaborazione di primer specifici: δ 1 e δ 2 utili per la differenziazione del ceppo S. cerevisiae. Legras e Karts (2003) hanno ottimizzato questa tecnica mediante la progettazione di due nuovi primer: δ 12 e δ 21 collocati accanto a δ 1 e δ 2. L utilizzo di δ 12 e δ 21 o di δ 12 con δ 2 rivela maggiori polimorfismi che si riflettono in più bande sul gel dell elettroforesi. Legras e Karts (2003) hanno identificato 53 ceppi commerciali utilizzando la combinazione di δ 12 e δ 21 o δ 12 con δ 2. Shuller et al. (2004) sono stati in grado di differenziare un gran numero di ceppi di lieviti vinari mediante l utilizzo dei primer δ 12 e δ 2. Ness et al, (1993) Identification of yeast strains using the polymerase chain reaction. J. Sci. Food Agric. 62: Legras e Karst (2003) Optimisation of interdelta for Saccharomyces cerevisiae strain characterization. FEMS Microbiol. Lett. 221 : Schuller et al, (2004) Survey of molecular methods for the typing of wine yeast strains. FEMS Microbiol. Lett. 231: Genotipizzazione per mezzo di microsatelliti I microsatelliti sono brevi sequenze nucleotidiche ripetute in tandem lunghe da 1 a 10 pb. Tali sequenze sono diffuse in tutto il genoma del lievito, sia nelle regioni di codificazione sia in quelle di non codificazione ma con una percentuale più bassa nelle regioni di codificazione. I marker microsatellitari sono dei loci polimorfi per i quali la diversità degli 5
6 alleli permette di differenziare i ceppi di una stessa specie di lieviti. I vari loci sono noti e possono essere usati per tipizzare ceppi di S. cerevisiae (Legras et al. 2005). I profili ottenuti da una combinazione di almeno sei microsatelliti permettono un efficace differenziazione di ceppi di S. cerevisiae. I marker microsatelliti sono frequentemente usati come marker genetici in studi di mappatura genetica e di genetica della popolazione. La combinazione di sei loci microsatelliti è indicata come una tecnica altamente discriminante e riproducibile, in grado di rivelare al tempo stesso relazioni geografiche e tecnologiche tra ceppi. Questi loci polimorfici possono essere facilmente usati per determinare il profilo dei ceppi di S. cerevisiae durante la fermentazione. Schuller et al. (2004) Survey of molecular methods for the typing of wine yeast strains. FEMS Microbiol. Lett. 231: Legras et al. (2005) Selection of hypervariable microsatellite loci for the characterization of Saccharomyces cerevisiae strains. Int J Food Microbiol. 102: Schuller e Casal (2007) The genetic structure of fermentative vineyard-associated Saccharomyces cerevisiae populations revealed by microsatellite analysis. Antonie van Leeuwenhoek 91: METODI COLTURA-INDIPENDENTI PCR QUANTITATIVA (qpcr) OBIETTIVO Individuazione e quantificazione rapida dei lieviti a livello di specie nel mosto o nel vino. Questo metodo si basa sull uso di primer per lieviti universali disegnati sui domini variabili D1/D2 del gene 26S rrna. Si tratta di una delle poche sequenze di geni disponibili per tutte le specie di lieviti ascomiceti conosciute. La quantificazione è possibile a partire dalla determinazione del numero di cicli di polimerizzazione necessario per superare il segnale soglia. Più la concentrazione di DNA della specie bersaglio è elevata nel campione, meno il numero di cicli necessari per superare il segnale soglia è elevato. Le curve di calibrazione permettono una determinazione precisa. 6
7 La presente tecnica è stata usata per la quantificazione delle cellule di Candida stellata, Dekkera bruxellensis, Hanseniaspora uvarum, e Saccharomyces cerevisiae in fermentazione mista sia in un mezzo sintetico sia nel vino. L analisi è risultata lineare su 5 ordini di grandezza e il limite di rivelazione è stato di circa 10 2 CFU/ml. La presenza di altri microrganismi vinari non-target (sia lieviti sia batteri) nei campioni non ha influito significativamente sull analisi qpcr. Un metodo rapido qpcr è stato sviluppato per individuare e quantificare i diversi lieviti non Saccharomyces, utilizzando primers specie-specifici per C. zemplinina, T.delbrueckii, I. orientalis e M. pulcherrima (Zott et al., 2010). Hierro, Esteve-Zarzoso, Gonzalez, Mas and Guillamon et al. (2006) Real-Time Quantitative PCR (qpcr) and Reverse Transcription-qPCR for Detection and Enumeration of Total Yeasts in Wine. Appl. Environ. Microbiol. 72(11): Zott K, Claisse O, Lucas P, Coulon J, Lonvaud-Funel A, Masneuf-Pomarede I (2010) Characterization of the yeast ecosystem in grape must and wine using real-time PCR. Food Microbiology 27: PCR-DGGE (denaturing gradient gel electrophoresis) OBIETTIVO Identificazione dei lieviti a livello di specie nel mosto o nel vino Il presente metodo si basa sull amplificazione dei lieviti 26S rdna utilizzando primer universali U1 ( contenente una coda GC clamp) e U2. I frammenti di amplificazione sono separati sulla base della lunghezza e della composizione nucleotidica in un gel denaturante di poliacrilammide (gradiente da 20 a 60% di urea e formammide). I frammenti di amplificazione che presentano un certo interesse sono asportati direttamente dal gel e sequenziati per l identificazione delle specie microbiche facendo riferimento alla banda di sequenza 26S rdna dei lieviti. Uno dei vantaggi è la possibilità di identificare lieviti vitali ma non coltivabili per i quali il DNA è amplificato. La presente tecnica è stata utilizzata per l identificazione di popolazioni microbiche sia in campioni di uva sia di vino ed ha portato all identificazione di varie specie di lieviti (Candida diversa, Candida sorboxylosa, Candida stellata, Dekkera bruxellensis, 7
8 Hanseniaspora occidentalis, Hanseniaspora uvarum, Issatchenkia hanoiensis, Issatchenkia occidentalis, Issatchenkia orientalis, Issatchenkia terricola, Kluyveromyces thermotolerans, Metschnikowia pulcherrima, Pichia kluyveri, Saccharomyces cerevisiae, Saccharomycodes ludwigii, Torulaspora delbrueckii, Zygosaccharomyces bailii). Popolazioni di lieviti vinari superiori a 10 3 cellule/ml sono state adeguatamente rivelate e identificate mediante PCR-DGGE. La PCR-DGGE non è uno strumento quantitativo. Cocolin L, Heisey A, and Mills D.A. et al. (2001) Direct Identification of the Indigenous Yeasts in Commercial Wine Fermentations. Am. J. Enol. Vitic. 52:1:
Metodi molecolari per l identificazione di lieviti isolati dalle paste acide siciliane **
 Metodi molecolari per l identificazione di lieviti isolati dalle paste acide siciliane ** P. Giudici 1, A. Pulvirenti 1 1 Università degli Studi di Modena e Reggio Emilia, Via Kennedy, 17-42100 Reggio
Metodi molecolari per l identificazione di lieviti isolati dalle paste acide siciliane ** P. Giudici 1, A. Pulvirenti 1 1 Università degli Studi di Modena e Reggio Emilia, Via Kennedy, 17-42100 Reggio
Metodologie citogenetiche. Metodologie molecolari. Formulare la domanda Utilizzare la metodica appropriata
 In base al potere di risoluzione della tecnica Metodologie citogenetiche Metodologie molecolari Formulare la domanda Utilizzare la metodica appropriata 1 DNA RNA PROTEINE DNA Cromosomi (cariotipo, FISH,
In base al potere di risoluzione della tecnica Metodologie citogenetiche Metodologie molecolari Formulare la domanda Utilizzare la metodica appropriata 1 DNA RNA PROTEINE DNA Cromosomi (cariotipo, FISH,
Differenti tipi di PCR
 Differenti tipi di PCR Colony PCR Nested PCR Multiplex PCR AFLP PCR Hot start PCR In situ PCR Inverse PCR Asymmetric PCR Long PCR Long accurate PCR Reverse transcriptase PCR Allele Specific PCR Real time
Differenti tipi di PCR Colony PCR Nested PCR Multiplex PCR AFLP PCR Hot start PCR In situ PCR Inverse PCR Asymmetric PCR Long PCR Long accurate PCR Reverse transcriptase PCR Allele Specific PCR Real time
PROBIOTICI: UNA VISIONE MOLECOLARE. Maria Luisa Callegari
 PROBIOTICI: UNA VISIONE MOLECOLARE Maria Luisa Callegari Health and Nutritional Properties of of Probiotics in in Food including Powder Milk with Live Lactic Acid Bacteria Report of a Joint FAO/WHO Expert
PROBIOTICI: UNA VISIONE MOLECOLARE Maria Luisa Callegari Health and Nutritional Properties of of Probiotics in in Food including Powder Milk with Live Lactic Acid Bacteria Report of a Joint FAO/WHO Expert
SPECIE MICROBICHE DOMINANTI NEL VINO
 SPECIE MICROBICHE DOMINANTI NEL VINO FERMENTAZIONE ALCOLICA (FA) E FERMENTAZIONE MALOLATTICA (FML) SONO PROCESSI POLIMICROBICI NELLE VARIE FASI DELLA VINIFICAZIONE LO SVILUPPO DELLE SPECIE FERMENTANTI
SPECIE MICROBICHE DOMINANTI NEL VINO FERMENTAZIONE ALCOLICA (FA) E FERMENTAZIONE MALOLATTICA (FML) SONO PROCESSI POLIMICROBICI NELLE VARIE FASI DELLA VINIFICAZIONE LO SVILUPPO DELLE SPECIE FERMENTANTI
PCR allele-specifica Ibridazione con sonde allele-specifiche (ASO) PCR Real-time con sonde TaqMan Saggio OLA (Oligo Ligation Assay)
 Tecniche per l analisi di singole variazioni: PCR allele-specifica Ibridazione con sonde allele-specifiche (ASO) PCR Real-time con sonde TaqMan Saggio OLA (Oligo Ligation Assay) alcuni SNP (ca. 10%) sono
Tecniche per l analisi di singole variazioni: PCR allele-specifica Ibridazione con sonde allele-specifiche (ASO) PCR Real-time con sonde TaqMan Saggio OLA (Oligo Ligation Assay) alcuni SNP (ca. 10%) sono
La variabilità genetica: tipi e metodi per studiarla e misurarla
 La variabilità genetica: tipi e metodi per studiarla e misurarla La variabilità genetica (V.G.) 1. V.G. somatica 2. V.G. gametica intraindividuo 3. V.G. gametica intrapopolazione (polimorfismo) 4. V.G.
La variabilità genetica: tipi e metodi per studiarla e misurarla La variabilità genetica (V.G.) 1. V.G. somatica 2. V.G. gametica intraindividuo 3. V.G. gametica intrapopolazione (polimorfismo) 4. V.G.
Banca dati genetica per l identificazione rapida dei microorganismi nella filiera viticolo enologica Acronimo: SEQVINO
 SEDE LEGALE Via Po, 14-00198 Roma T +39 06 478361 CF 97231970589 PI 08183101008 Progetto di ricerca Banca dati genetica per l identificazione rapida dei microorganismi nella filiera viticolo enologica
SEDE LEGALE Via Po, 14-00198 Roma T +39 06 478361 CF 97231970589 PI 08183101008 Progetto di ricerca Banca dati genetica per l identificazione rapida dei microorganismi nella filiera viticolo enologica
Le biotecnologie. Sadava et al. Biologia La scienza della vita Zanichelli editore 2010
 Le biotecnologie 1 Cosa sono le biotecnologie? Le biotecnologie sono tutte quelle tecniche utilizzate (fin dall antichità) per produrre sostanze specifiche a partire da organismi viventi o da loro derivati.
Le biotecnologie 1 Cosa sono le biotecnologie? Le biotecnologie sono tutte quelle tecniche utilizzate (fin dall antichità) per produrre sostanze specifiche a partire da organismi viventi o da loro derivati.
Marcatori molecolari per l analisi genica, genetica e genomica
 Marcatori molecolari per l analisi genica, genetica e genomica (RFLP e PCR-derivati, inclusi SSR e SNP) DNA fingerprinting DNA genotyping DNA haplotyping cp/mtdna barcoding MG/QTL mapping MAS breeding
Marcatori molecolari per l analisi genica, genetica e genomica (RFLP e PCR-derivati, inclusi SSR e SNP) DNA fingerprinting DNA genotyping DNA haplotyping cp/mtdna barcoding MG/QTL mapping MAS breeding
Origine e valutazione della qualità percepibile dei vini
 Workshop su: Origine e valutazione della qualità percepibile dei vini in collaborazione con la Società Italiana di Scienze Sensoriali Firenze, 28 maggio 2007 Iolanda Rosi* Microrganismi e proprietà sensoriali:
Workshop su: Origine e valutazione della qualità percepibile dei vini in collaborazione con la Società Italiana di Scienze Sensoriali Firenze, 28 maggio 2007 Iolanda Rosi* Microrganismi e proprietà sensoriali:
Marcatori molecolari
 Marcatori molecolari Caratteristiche e applicazioni Luca Gianfranceschi e Rosanna Marino 1 I marcatori molecolari Strumento per l analisi genetica Strumento Molecolari Analisi genetica Marcatori non oggetto
Marcatori molecolari Caratteristiche e applicazioni Luca Gianfranceschi e Rosanna Marino 1 I marcatori molecolari Strumento per l analisi genetica Strumento Molecolari Analisi genetica Marcatori non oggetto
UNIVERSITÀ DEGLI STUDI DI NAPOLI FEDERICO II DIPARTIMENTO DI AGRARIA Via Università, PORTICI (NA) Italia RELAZIONE FINALE
 RELAZIONE FINALE Convenzione di Ricerca: ACCERTAMENTO, MEDIANTE METODI MOLECOLARI, DELLA DIVERSITÀ MICROBICA RICORRENTE IN IMPASTI ACIDI IMPIEGATI PER LA PRODUZIONE DI PRODOTTI DA FORNO A LIEVITAZIONE
RELAZIONE FINALE Convenzione di Ricerca: ACCERTAMENTO, MEDIANTE METODI MOLECOLARI, DELLA DIVERSITÀ MICROBICA RICORRENTE IN IMPASTI ACIDI IMPIEGATI PER LA PRODUZIONE DI PRODOTTI DA FORNO A LIEVITAZIONE
Cenni di genetica di popolazione delle specie native
 Cenni di genetica di popolazione delle specie native prof. Pallavicini dott. Victoria Bertucci 27 gen 2012 1 Biodiversità L'espressione italiana è un calco linguistico derivante dal termine inglese biodiversity.
Cenni di genetica di popolazione delle specie native prof. Pallavicini dott. Victoria Bertucci 27 gen 2012 1 Biodiversità L'espressione italiana è un calco linguistico derivante dal termine inglese biodiversity.
Tecnologia del DNA ricombinante
 Tecnologia del DNA ricombinante Scoperte rivoluzionarie che hanno permesso lo studio del genoma e della funzione dei singoli geni Implicazioni enormi nel progresso della medicina: comprensione malattie
Tecnologia del DNA ricombinante Scoperte rivoluzionarie che hanno permesso lo studio del genoma e della funzione dei singoli geni Implicazioni enormi nel progresso della medicina: comprensione malattie
TASSONOMIA O SISTEMATICA
 TASSONOMIA O SISTEMATICA È la branca della batteriologia responsabile della caratterizzazione degli organismi ed organizzazione in gruppi affini (TAXA). NOMENCLATURA CLASSIFICAZIONE IDENTIFICAZIONE taxon
TASSONOMIA O SISTEMATICA È la branca della batteriologia responsabile della caratterizzazione degli organismi ed organizzazione in gruppi affini (TAXA). NOMENCLATURA CLASSIFICAZIONE IDENTIFICAZIONE taxon
Corso di laurea in Viticoltura ed enologia a.a MICROBIOLOGIA GENERALE ED ENOLOGICA (MICROGE 006GG)
 Corso di laurea in Viticoltura ed enologia a.a. 2015-2016 MICROBIOLOGIA GENERALE ED ENOLOGICA (MICROGE 006GG) Docente: Annita TOFFANIN, Dip. Scienze Agrarie Alimentari e Agro-ambientali Via del Borghetto
Corso di laurea in Viticoltura ed enologia a.a. 2015-2016 MICROBIOLOGIA GENERALE ED ENOLOGICA (MICROGE 006GG) Docente: Annita TOFFANIN, Dip. Scienze Agrarie Alimentari e Agro-ambientali Via del Borghetto
VALUTAZIONE DELLA BIODIVERSITÀ MICROBICA MEDIANTE L UTILIZZO DI TECNICHE MOLECOLARI
 VALUTAZIONE DELLA BIODIVERSITÀ MICROBICA MEDIANTE L UTILIZZO DI TECNICHE MOLECOLARI Laboratorio di Genetica dei Microrganismi (Responsabile attività: Prof. Giovanni Salzano; Tutor: Dr.ssa Maria Grazia
VALUTAZIONE DELLA BIODIVERSITÀ MICROBICA MEDIANTE L UTILIZZO DI TECNICHE MOLECOLARI Laboratorio di Genetica dei Microrganismi (Responsabile attività: Prof. Giovanni Salzano; Tutor: Dr.ssa Maria Grazia
Patologie da analizzare
 Fasi cruciali Scelta della patologia da analizzare Scelta del campione da analizzare Scelta dell approccio da utilizzare Scelta della tecnica da utilizzare Analisi statistica del dati Conferme con approcci
Fasi cruciali Scelta della patologia da analizzare Scelta del campione da analizzare Scelta dell approccio da utilizzare Scelta della tecnica da utilizzare Analisi statistica del dati Conferme con approcci
CLASSIFICAZIONE DEI LIEVITI
 CLASSIFICAZIONE DEI LIEVITI funghi unicellulari che si moltiplicano per gemmazione o scissione, appartenenti a ascomiceti e basidiomiceti (il gruppo deuteromiceti, anamorfi, è stato soppresso) lieviti
CLASSIFICAZIONE DEI LIEVITI funghi unicellulari che si moltiplicano per gemmazione o scissione, appartenenti a ascomiceti e basidiomiceti (il gruppo deuteromiceti, anamorfi, è stato soppresso) lieviti
RISOLUZIONE OIV-OENO MONOGRAFIA SUL GLUTATIONE
 RISOLUZIONE OIV-OENO 571-2017 MONOGRAFIA SUL GLUTATIONE L ASSEMBLEA GENERALE, Visto l'articolo 2, paragrafo 2 iv dell'accordo del 3 aprile 2001 che istituisce l'organizzazione internazionale della vigna
RISOLUZIONE OIV-OENO 571-2017 MONOGRAFIA SUL GLUTATIONE L ASSEMBLEA GENERALE, Visto l'articolo 2, paragrafo 2 iv dell'accordo del 3 aprile 2001 che istituisce l'organizzazione internazionale della vigna
ANALISI MOLECOLARE DEL GENOMA
 ANALISI MOLECOLARE DEL GENOMA Come sono disposti i geni nel genoma? MAPPA GENETICA: un set ordinato di geni sul cromosoma, la distanza tra i quali è espressa in unità di ricombinazione genetica (centimorgan)
ANALISI MOLECOLARE DEL GENOMA Come sono disposti i geni nel genoma? MAPPA GENETICA: un set ordinato di geni sul cromosoma, la distanza tra i quali è espressa in unità di ricombinazione genetica (centimorgan)
Polimorfismi LEZIONE 3. By NA 1
 Polimorfismi LEZIONE 3 By NA 1 Polimorfismo Variazione presente nella popolazione con una frequenza superiore a 1% Variazioni nell aspetto By NA 2 Polimorfismo proteico Variazione presente nella popolazione
Polimorfismi LEZIONE 3 By NA 1 Polimorfismo Variazione presente nella popolazione con una frequenza superiore a 1% Variazioni nell aspetto By NA 2 Polimorfismo proteico Variazione presente nella popolazione
Microbiologia applicata al settore enologico
 Microbiologia applicata al settore enologico Emilia Garcia-Moruno, Enrico Vaudano Consiglio per la Ricerca e Sperimentazione in Agricoltura Centro di Ricerca per l Enologia -ASTI LA FERMENTAZIONE ALCOLICA
Microbiologia applicata al settore enologico Emilia Garcia-Moruno, Enrico Vaudano Consiglio per la Ricerca e Sperimentazione in Agricoltura Centro di Ricerca per l Enologia -ASTI LA FERMENTAZIONE ALCOLICA
Graziella Bongioni, Sabina Arabi e Rossana Capoferri. Istituto Spallanzani
 Utilizzo di metodi molecolari per l identificazione di specie microalgali Rivolta d Adda, 22 giugno 2017 Graziella Bongioni, Sabina Arabi e Rossana Capoferri Istituto Spallanzani Progetto finanziato da:
Utilizzo di metodi molecolari per l identificazione di specie microalgali Rivolta d Adda, 22 giugno 2017 Graziella Bongioni, Sabina Arabi e Rossana Capoferri Istituto Spallanzani Progetto finanziato da:
Tecniche molecolari in uso per la caratterizzazione ed identificazione di artropodi di interesse economico
 Tecniche molecolari in uso per la caratterizzazione ed identificazione di artropodi di interesse economico Perché identificare insetti con tecniche molecolari? Identificazione morfologica Identificazione
Tecniche molecolari in uso per la caratterizzazione ed identificazione di artropodi di interesse economico Perché identificare insetti con tecniche molecolari? Identificazione morfologica Identificazione
VINIFICAZIONE SPONTANEA: ASPETTI MICROBIOLOGICI
 VINIFICAZIONE SPONTANEA: ASPETTI MICROBIOLOGICI uve sane e mature presentano molte specie di lieviti (alcune a metabolismo ossidativo, altre anche fermentativo) Lieviti non-saccharomyces Hanseniaspora
VINIFICAZIONE SPONTANEA: ASPETTI MICROBIOLOGICI uve sane e mature presentano molte specie di lieviti (alcune a metabolismo ossidativo, altre anche fermentativo) Lieviti non-saccharomyces Hanseniaspora
Il progetto Genoma Umano è iniziato nel E stato possibile perchè nel 1986 era stato sviluppato il sequenziamento automatizzato del DNA.
 Il progetto Genoma Umano è iniziato nel 1990. E stato possibile perchè nel 1986 era stato sviluppato il sequenziamento automatizzato del DNA. Progetto internazionale finanziato da vari paesi, affidato
Il progetto Genoma Umano è iniziato nel 1990. E stato possibile perchè nel 1986 era stato sviluppato il sequenziamento automatizzato del DNA. Progetto internazionale finanziato da vari paesi, affidato
USO DEI MARCATORI MOLECOLARI A DNA PER LA TRACCIABILITÀ DEI VITIGNI NEI VINI
 USO DEI MARCATORI MOLECOLARI A DNA PER LA TRACCIABILITÀ DEI VITIGNI NEI VINI CLAUDIO D ONOFRIO*, FABIOLA MATESE*, ELEONORA DUCCI E GIUSEPPE CELANO *UNIVERSITÀ DI PISA, DIPARTIMENTO DI SCIENZE AGRARIE,
USO DEI MARCATORI MOLECOLARI A DNA PER LA TRACCIABILITÀ DEI VITIGNI NEI VINI CLAUDIO D ONOFRIO*, FABIOLA MATESE*, ELEONORA DUCCI E GIUSEPPE CELANO *UNIVERSITÀ DI PISA, DIPARTIMENTO DI SCIENZE AGRARIE,
Lieviti autoctoni: genius loci del territorio?
 Lieviti autoctoni: genius loci del territorio? Giovanna Suzzi e Rosanna Tofalo Università degli Studi di Teramo Facoltà di Bioscienze e Tecnologie Agro-Alimentari e Ambientali La spumantizzazione come
Lieviti autoctoni: genius loci del territorio? Giovanna Suzzi e Rosanna Tofalo Università degli Studi di Teramo Facoltà di Bioscienze e Tecnologie Agro-Alimentari e Ambientali La spumantizzazione come
Biologia Molecolare e nuove tecnologie. M.Favarato ULSS13 Mirano (Ve) Medicina di Laboratorio Biologia Molecolare
 Biologia Molecolare e nuove tecnologie M.Favarato ULSS13 Mirano (Ve) Medicina di Laboratorio Biologia Molecolare Identificazione, virulenza, resistenza antibiotici Resistenza antibiotici (4-5 gg) Tipizzazione,
Biologia Molecolare e nuove tecnologie M.Favarato ULSS13 Mirano (Ve) Medicina di Laboratorio Biologia Molecolare Identificazione, virulenza, resistenza antibiotici Resistenza antibiotici (4-5 gg) Tipizzazione,
LA REAZIONE A CATENA DELLA POLIMERASI PCR
 LA REAZIONE A CATENA DELLA POLIMERASI PCR INTRODUZIONE Tecnica ideata da Mullis e collaboratori nel 1984 La possibilita' di disporre di quantità virtualmente illimitate di un determinato frammento di DNA,
LA REAZIONE A CATENA DELLA POLIMERASI PCR INTRODUZIONE Tecnica ideata da Mullis e collaboratori nel 1984 La possibilita' di disporre di quantità virtualmente illimitate di un determinato frammento di DNA,
CONOSCENZE / COMPETENZE STRUMENTI E METODI LABORATORIO COLLEGAMENTI VERIFICHE ORE
 PROGRAMMAZIONE DIDATTICA DEL CORSO DI BIOLOGIA,MICROBIOLOGIA E TECNOLOGIE DI CONTROLLO SANITARIO CLASSE 5 D ANNO SCOLASTICO 2015-2016 Proff ELENA ZACCHIA, RAFFAELE FIORINI MODULI MODULO 1 Modulo di raccordo
PROGRAMMAZIONE DIDATTICA DEL CORSO DI BIOLOGIA,MICROBIOLOGIA E TECNOLOGIE DI CONTROLLO SANITARIO CLASSE 5 D ANNO SCOLASTICO 2015-2016 Proff ELENA ZACCHIA, RAFFAELE FIORINI MODULI MODULO 1 Modulo di raccordo
RISOLUZIONE OIV-OENO 576A-2017
 RISOLUZIONE OIV-OENO 576A-2017 MONOGRAFIA SUI LIEVITI SACCHAROMYCES L ASSEMBLEA GENERALE, Visto l articolo 2, paragrafo 2 iv dell'accordo del 3 aprile 2001 che istituisce l Organizzazione internazionale
RISOLUZIONE OIV-OENO 576A-2017 MONOGRAFIA SUI LIEVITI SACCHAROMYCES L ASSEMBLEA GENERALE, Visto l articolo 2, paragrafo 2 iv dell'accordo del 3 aprile 2001 che istituisce l Organizzazione internazionale
Confronto dei metodi di tipizzazione molecolare per la caratterizzazione di ceppi di Listeria monocytogenes circolanti in Italia
 Confronto dei metodi di tipizzazione molecolare per la caratterizzazione di ceppi di Listeria monocytogenes circolanti in talia Progetto ricerca corrente MSRCTE0212 Patrizia Centorame Laboratorio Nazionale
Confronto dei metodi di tipizzazione molecolare per la caratterizzazione di ceppi di Listeria monocytogenes circolanti in talia Progetto ricerca corrente MSRCTE0212 Patrizia Centorame Laboratorio Nazionale
Tassonomia. - Classificazione. - Nomenclatura. - identificazione
 Tassonomia - Classificazione - Nomenclatura - identificazione Definizione di specie Criterio biologico: Gruppo di popolazioni naturali interfertili che sono incapaci di incrociarsi o riprodursi con successo
Tassonomia - Classificazione - Nomenclatura - identificazione Definizione di specie Criterio biologico: Gruppo di popolazioni naturali interfertili che sono incapaci di incrociarsi o riprodursi con successo
I marcatori molecolari. Dipartimento di Scienze Agronomiche e Genetica Vegetale Agraria Corso di Genetica Agraria Giovanna Attene
 I marcatori molecolari Dipartimento di Scienze Agronomiche e Genetica Vegetale Agraria Corso di Genetica Agraria Giovanna Attene Marcatori molecolari del DNA I marcatori molecolari sono sequenze di DNA
I marcatori molecolari Dipartimento di Scienze Agronomiche e Genetica Vegetale Agraria Corso di Genetica Agraria Giovanna Attene Marcatori molecolari del DNA I marcatori molecolari sono sequenze di DNA
La mappatura dei geni umani. SCOPO conoscere la localizzazione dei geni per identificarne la struttura e la funzione
 La mappatura dei geni umani SCOPO conoscere la localizzazione dei geni per identificarne la struttura e la funzione Un grande impulso alla costruzione di mappe genetiche è stato dato da le tecniche della
La mappatura dei geni umani SCOPO conoscere la localizzazione dei geni per identificarne la struttura e la funzione Un grande impulso alla costruzione di mappe genetiche è stato dato da le tecniche della
CORSO INTEGRATO DI GENETICA a.a. 2011-2012. Genetica molecolare in medicina: Analisi di Mutazioni. Cristina Bombieri 7 dicembre 2011
 CORSO INTEGRATO DI GENETICA a.a. 2011-2012 Genetica molecolare in medicina: Analisi di Mutazioni Cristina Bombieri 7 dicembre 2011 GENETICA MOLECOLARE IN MEDICINA SVILUPPI SCIENTIFICI Mappatura gene Identificazione
CORSO INTEGRATO DI GENETICA a.a. 2011-2012 Genetica molecolare in medicina: Analisi di Mutazioni Cristina Bombieri 7 dicembre 2011 GENETICA MOLECOLARE IN MEDICINA SVILUPPI SCIENTIFICI Mappatura gene Identificazione
USO DEI LIEVITI SELEZIONATI E BIODIVERSITÀ
 VALERO ET AL., USO DI LIEVITI SELEZIONATI E BIODIVERSITÀ, PAG. 1 USO DEI LIEVITI SELEZIONATI E BIODIVERSITÀ Eva VALERO 1, Dorit SCHULLER 2, Brigitte CAMBON 1, Margarida CASAL 2 and Sylvie DEQUIN 1 (1)
VALERO ET AL., USO DI LIEVITI SELEZIONATI E BIODIVERSITÀ, PAG. 1 USO DEI LIEVITI SELEZIONATI E BIODIVERSITÀ Eva VALERO 1, Dorit SCHULLER 2, Brigitte CAMBON 1, Margarida CASAL 2 and Sylvie DEQUIN 1 (1)
Reg. (CE) 2073, punto 24 delle considerazioni preliminari
 I risultati delle analisi dipendono dal metodo analitico utilizzato; pertanto occorre associare ad ogni criterio microbiologico un metodo di riferimento specifico. Tuttavia, gli operatori del settore alimentare
I risultati delle analisi dipendono dal metodo analitico utilizzato; pertanto occorre associare ad ogni criterio microbiologico un metodo di riferimento specifico. Tuttavia, gli operatori del settore alimentare
Dr.ssa Francesca Ciampini. ISVEA - Le tecniche analitiche di monitoraggio del Brettanomyces
 Le Tecniche Analitiche di monitoraggio del Brettanomyces Dr.ssa Francesca Ciampini Brettanomyces sp. La scoperta e le prime classificazioni dalle fermentazioni secondarie della birra (N.H. Claussen 1904).
Le Tecniche Analitiche di monitoraggio del Brettanomyces Dr.ssa Francesca Ciampini Brettanomyces sp. La scoperta e le prime classificazioni dalle fermentazioni secondarie della birra (N.H. Claussen 1904).
METODO RAPIDO PER DETERMINARE IL CARATTERE BRETT NEI VINI
 TOFALO ET AL., METODO RAPIDO PER DETERMINARE IL CARATTERE BRETT NEI VINI, PAG. 1 METODO RAPIDO PER DETERMINARE IL CARATTERE BRETT NEI VINI TOFALO Rosanna, SCHIRONE Maria, PERPETUINI Giorgia, CORSETTI Aldo,
TOFALO ET AL., METODO RAPIDO PER DETERMINARE IL CARATTERE BRETT NEI VINI, PAG. 1 METODO RAPIDO PER DETERMINARE IL CARATTERE BRETT NEI VINI TOFALO Rosanna, SCHIRONE Maria, PERPETUINI Giorgia, CORSETTI Aldo,
Enzimi di Restrizione
 Enzimi di Restrizione Origine e Funzione Sono proteine di origine batterica che tagliano il DNA esogeno Sistema di difesa: proteggono i batteri dai batteriofagi danneggiandone il DNA I batteri proteggono
Enzimi di Restrizione Origine e Funzione Sono proteine di origine batterica che tagliano il DNA esogeno Sistema di difesa: proteggono i batteri dai batteriofagi danneggiandone il DNA I batteri proteggono
Caratterizzazione genetica ed assegnazione geografica di testuggini (Testudo hermanni) di origine ignota
 Caratterizzazione genetica ed assegnazione geografica di testuggini (Testudo hermanni) di origine ignota Scopo: caratterizzare geneticamente testuggini provenienti da sequestri per identificare animali
Caratterizzazione genetica ed assegnazione geografica di testuggini (Testudo hermanni) di origine ignota Scopo: caratterizzare geneticamente testuggini provenienti da sequestri per identificare animali
LA REAZIONE A CATENA DELLA POLIMERASI
 Polymerase Chain Reaction LA REAZIONE A CATENA DELLA POLIMERASI e LE SUE APPLICAZIONI Prima diagnosi molecolare sul DNA 1978 *Primo ormone umano ricombinante (insulina) *Premio Nobel agli scopritori degli
Polymerase Chain Reaction LA REAZIONE A CATENA DELLA POLIMERASI e LE SUE APPLICAZIONI Prima diagnosi molecolare sul DNA 1978 *Primo ormone umano ricombinante (insulina) *Premio Nobel agli scopritori degli
Southern blot. !Per. determinare la presenza o assenza di specifici frammenti genici. !Studio. della struttura e dell organizzazione di un gene
 Southern blot!per determinare la presenza o assenza di di specifici frammenti genici!studio della struttura e dell organizzazione di di un gene Southern blot Procedura Isolare DNA genomico Digerirlo con
Southern blot!per determinare la presenza o assenza di di specifici frammenti genici!studio della struttura e dell organizzazione di di un gene Southern blot Procedura Isolare DNA genomico Digerirlo con
Polymerase chain reaction - PCR. Biotecnologie applicate all ispezione degli alimenti di origine animale
 Prof.ssa Tiziana Pepe Polymerase chain reaction - PCR Biotecnologie applicate all ispezione degli alimenti di origine animale Dip. di Medicina Veterinaria e Produzioni animali [email protected] Metodologia
Prof.ssa Tiziana Pepe Polymerase chain reaction - PCR Biotecnologie applicate all ispezione degli alimenti di origine animale Dip. di Medicina Veterinaria e Produzioni animali [email protected] Metodologia
GENOMA. Analisi di sequenze -- Analisi di espressione -- Funzione delle proteine CONTENUTO FUNZIONE. Progetti genoma in centinaia di organismi
 GENOMA EVOLUZIONE CONTENUTO FUNZIONE STRUTTURA Analisi di sequenze -- Analisi di espressione -- Funzione delle proteine Progetti genoma in centinaia di organismi Importante la sintenia tra i genomi The
GENOMA EVOLUZIONE CONTENUTO FUNZIONE STRUTTURA Analisi di sequenze -- Analisi di espressione -- Funzione delle proteine Progetti genoma in centinaia di organismi Importante la sintenia tra i genomi The
I MICRORGANISMI DEL VINO
 UNIVERSITA DEGLI STUDI DELLA BASILICATA POTENZA I MICRORGANISMI DEL VINO Adriano Sofo 1 Indice Introduzione 3 Importanza dei lieviti nel processo di vinificazione 4 I lieviti coinvolti nella vinificazione..
UNIVERSITA DEGLI STUDI DELLA BASILICATA POTENZA I MICRORGANISMI DEL VINO Adriano Sofo 1 Indice Introduzione 3 Importanza dei lieviti nel processo di vinificazione 4 I lieviti coinvolti nella vinificazione..
Dipartimento DEMETRA
 Dipartimento DEMETRA Dottorato di ricerca in Frutticoltura Mediterranea XXII ciclo (SSD AGR/16-Microbiologia Agraria) - TESI DI DOTTORATO DI RICERCA - Ecologia microbica del vitigno Grillo e selezione
Dipartimento DEMETRA Dottorato di ricerca in Frutticoltura Mediterranea XXII ciclo (SSD AGR/16-Microbiologia Agraria) - TESI DI DOTTORATO DI RICERCA - Ecologia microbica del vitigno Grillo e selezione
Mappe fisiche. Si basano sulla localizzazione fisica delle molecole di DNA
 Mappe fisiche Si basano sulla localizzazione fisica delle molecole di DNA Costruzione di una mappa fisica diversi metodi - Mappe a bassa risoluzione - Mappe ad alta risoluzione Risoluzione= distanza a
Mappe fisiche Si basano sulla localizzazione fisica delle molecole di DNA Costruzione di una mappa fisica diversi metodi - Mappe a bassa risoluzione - Mappe ad alta risoluzione Risoluzione= distanza a
Benedetta Turchetti Dipartimento di Biologia Applicata Università degli Studi di Perugia Curatore della Collezione dei Lieviti Industriali DBVPG
 Benedetta Turchetti Dipartimento di Biologia Applicata Università degli Studi di Perugia Curatore della Collezione dei Lieviti Industriali DBVPG ICLAVA Risultati progetto MIPAF - OIGA 18829/2009 Partecipanti
Benedetta Turchetti Dipartimento di Biologia Applicata Università degli Studi di Perugia Curatore della Collezione dei Lieviti Industriali DBVPG ICLAVA Risultati progetto MIPAF - OIGA 18829/2009 Partecipanti
MARCATORI MOLECOLARI
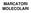 MARCATORI MOLECOLARI MARCATORI ENZIMATICI A B D E C Marcatori biochimici: (A) fosfo-gluco-mutasi (PGM); (B) lipoossigenasi (LOX) in soia; (C) esterasi (EXT) in poa pratense; (D,E) rappresentazioni schematiche
MARCATORI MOLECOLARI MARCATORI ENZIMATICI A B D E C Marcatori biochimici: (A) fosfo-gluco-mutasi (PGM); (B) lipoossigenasi (LOX) in soia; (C) esterasi (EXT) in poa pratense; (D,E) rappresentazioni schematiche
MIGLIORAMENTO QUALITATIVO DEI VINI ROSSI TRAMITE L IMPIEGO IN CANTINA DI CEPPI DI CANDIDA ZEMPLININA ISOLATI IN SICILIA
 CANDIDA ZEMPLININA ISOLATI IN SICILIA, PAG. 1 MIGLIORAMENTO QUALITATIVO DEI VINI ROSSI TRAMITE L IMPIEGO IN CANTINA DI CEPPI DI CANDIDA ZEMPLININA ISOLATI IN SICILIA Giovanna PONTICELLO a, Pieramaria GIARAMIDA
CANDIDA ZEMPLININA ISOLATI IN SICILIA, PAG. 1 MIGLIORAMENTO QUALITATIVO DEI VINI ROSSI TRAMITE L IMPIEGO IN CANTINA DI CEPPI DI CANDIDA ZEMPLININA ISOLATI IN SICILIA Giovanna PONTICELLO a, Pieramaria GIARAMIDA
Ecologia dei lieviti vinari a cura di Maurizio Donadi
 Associazione culturale senza fini di lucro Ecologia dei lieviti vinari a cura di Maurizio Donadi seminario Bologna, 11 giugno 2010 Premessa I lieviti sono microrganismi essenziali per lo svolgimento della
Associazione culturale senza fini di lucro Ecologia dei lieviti vinari a cura di Maurizio Donadi seminario Bologna, 11 giugno 2010 Premessa I lieviti sono microrganismi essenziali per lo svolgimento della
SAFE - SCUOLA DI SCIENZE AGRARIE, FORESTALI, ALIMENTARI ED AMBIENTALI
 Programma di insegnamento per l anno accademico 2013/2014 Programma dell insegnamento di: MICROBIOLOGIA DELLE BEVANDE FERMENTATE (italiano) Course title: Microbiology of fermented beverages (inglese) Corso/i
Programma di insegnamento per l anno accademico 2013/2014 Programma dell insegnamento di: MICROBIOLOGIA DELLE BEVANDE FERMENTATE (italiano) Course title: Microbiology of fermented beverages (inglese) Corso/i
