UNIVERSITÀ DEGLI STUDI DI SASSARI
|
|
|
- Uberto Franchi
- 10 anni fa
- Просмотров:
Транскрипт
1 UNIVERSITÀDEGLISTUDIDISASSARI SCUOLADIDOTTORATOIN SCIENZEBIOMOLECOLARIEBIOTECNOLOGICHE INDIRIZZOMICROBIOLOGIAMOLECOLAREECLINICA IDENTIFICAZIONEECARATTERIZZAZIONEDIUNA PUTATIVAPATHWAYDIRNAINTERFERENCENEL PROTOZOOATRASMISSIONESESSUALETRICHOMONAS VAGINALIS Relatore: Dott.DanieleDessì XXIICiclo TesidiDottoratodi: FedericaRiu FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.1
2 FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.2
3 SOMMARIO RIASSUNTO INTRODUZIONE Trichomonasvaginalis... 2 Morfologia... 2 Metabolismo... 3 Epidemiologia,manifestazioniclinicheediagnosi RNAinterferenza... 6 Scopertadell RNAinterferenza... 6 Meccanismodell RNAinterferenza... 8 Componentidell RNAi:siRNA,Dicer,RISC Micro interferencerna Rimodellamentocromatinico Applicazionibiotecnologicheebiomedichedell RNAi RNAineiprotozoi IlsequenziamentodelgenomadiT.vaginalis Strutturadelgenoma,processamentodell RNA,trasferimentogenico laterale Repeats,elementitrasponibiliedespansionegenomica Metabolismo,stressossidativo,trasporto Famigliegenicheespanse Meccanismimolecolaridipatogenicità Materialiemetodi AnalisidellasequenzadelgenomadiT.vaginalis FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.3
4 Celluleelorocoltivazione EstrazioneDNA Estrazioneedanalisidell RNA Sintesidell RNAdoublestranded(dsRNA)omologoall α actinina ElettroporazionedidsRNAinT.vaginalis Analisidelleproteine Anticorpianti enzimamalico Costruzionedeivettoriperl espressionedidsrna RISULTATI RicostruzionediunaputativaviadiRNAiinT.vaginalis SintesiedelettroporazionedidsRNAinT.vaginalis WesternblottingeRT PCR Costruzionedivettoriperl espressionedidsrna DISCUSSIONE BIBLIOGRAFIA FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.4
5 FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.5
6 RIASSUNTO T. vaginalis è il protozoo responsabile della malattia a trasmissione sessuale non viralepiùdiffusaalmondo,latricomoniasi.ilrecentecompletamentodelgenomadi T.vaginaliscihapermessodiricostruireperviabioinformaticailbackbonegenetico di una putativa via di RNA interferenza. L RNAi è un meccanismo di regolazione dell espressionegenicaposttrascrizionalesequenza specificopresenteneglieucarioti ed attivato da dsrna. I due componenti chiave dell RNAi sono Dicer, appartenente allafamigliadellernaseiii,elafamigliadelleproteineargonaute,necessarieperla formazionedelcomplessoeffettorecheguidaladegradazionedell RNAmessaggero. L analisidisequenzaeseguitasulgenomat.vaginalishaportatoall identificazionedi geni predetti per una putativa Dicer, due putative Argonaute e 41 DEAD/DEAH box elicasi, tutti trascrizionalmente attivi. Per poter valutare se T. vaginalis possieda un attivitàdisilenziamentogenicopost trascrizionaleindottodadsrna,ilprotozooè statotrasfettatoconundsrnasinteticoomologoall α actinina.irisultatideidiversi esperimentisisonomostraticontraddittori,didifficileinterpretazioneeconproblemi di riproducibilità che hanno impedito di trarre conclusioni. Il sistema sperimentale stesso di trasfezione di dsrna sintetico può non essere e il più adatto, almeno nel casodit.vaginalis,permonitorareunaeventualeattivitàdirnai.infattiinizialmente èstatopossibileosservareunsilencingdell α actinina,maesperimentisuccessivinon hannocondottoallostessorisultato.peraggirareiproblemiinsitinell utilizzazionedi dsrna sintetico è stato messo a punto un sistema plasmidico per l espressione stabile e inducibile di dsrna stem loop in vivo, la cu itrasfezione in T. vaginalis potrebbeportareallaverificadell esistenzaomenodiun attivitàrnainelprotozoo. LadimostrazionediunaviadiRNAiinT.vaginalispotrebbeportareallamessaputno di un potente strumento di genetica inversa per questo protozoo, nonché gettare nuovalucesullacomparsadiquestomeccanismoneglieucarioti. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.1
7 1.INTRODUZIONE 1.1Trichomonasvaginalis Morfologia T. vaginalis è un protozoo appartenente alla classe dei Flagellati e all ordine dei Trichomonadida, descritto per la prima volta da Donnè nel T. vaginalis non formacisti,eilsuociclocellularepresentailsolostadioditrofozoite.ledimensioni del protozoo variano notevolmente, da 7 a 23 µm di lunghezza e da 5 a 15 µm di larghezza 2. T. vaginalis è in genere piriforme, ma può mostrare forme diverse a seconda delle condizioni ambientali. Nei terreni di coltura liquidi il protozoo si presenta generalmente con morfologia piriforme, mentre in presenza di agar o di monostrati cellulari assume spesso forma ameboide (Figura. 1). Morfologie particolari sono osservate talvolta nelle secrezioni vaginali e nelle urine. Anche condizionifisico chimichequalilatensioned ossigeno,ilph,latemperatura,possono alterarnelamorfologia 3.Sel ambientediventasfavorevole,adesempio,t.vaginalis può assumere aspetto sferoidale, con internalizzazione dei flagelli, senza però che formi alcuna parete. Sono state inoltre osservate forme giganti multinucleate sferoidali,condimensionifinoadiecivolterispettoallacellulanormale 4.Ladivisione cellulare è di tipo criptopleuromitotico, con la formazione di un fuso extranucleare durante la mitosi, senza scomparsa della membrana nucleare 3. Osservazioni di microscopiaelettronicahannoevidenziatodiribosomiedell apparatodelgolgi,che prendeilnomediapparatoparabasale 5. T.vaginalishaquattroflagellianteriori,lunghicirca12µm.Unquintoflagelloorigina dorsalmente in prossimità degli altri quattro e viene incorporato lungo il margine liberodiunamembranaondulantechesiestendepercircadueterzidellalunghezza del protozoo. È presente una struttura chiamata assostile, localizzata lungo l asse anteroposterioredell organismo,eilcuisegmentoterminalesporgeoltrel estremità posteriore del protozoo di circa un terzo, contribuendo alla definizione della sua caratteristica morfologia. Il trofozoite presenta un unico nucleo, disposto anteriormente,diformatipicamenteallungata. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.2
8 Nel citoplasma di T. vaginalis non sono presenti mitocondri, ma altri organuli detti idrogenosomi6,dotatidiunadoppiamembranaecontenentiunamatricegranulare. Questiorganulidevonoilloronomealfattocheproduconoidrogeno7erivestonoun ruolofondamentalenelmetabolismoenergeticodelprotozoo8. Figura1AspettimorfologicidiTrichomonasvaginalis.A)Piriforme;B)Ameboide. Metabolismo T. vaginalis ha un metabolismo tipicamente eucariotico, nonostante alcune importanti differenze per quanto riguarda le esigenze trofiche ed il metabolismo energetico9.difattit.vaginalismancadimolteviebiosinteticheedabbisognadiun apportoesternodiamminoacidi,purineepirimidine,vitamine,acidigrassisaturied insaturi, colesterolo. La fonte energetica primaria è rappresentata da carboidrati quali il glucosio, maltosio e galattosio. T. vaginalis presenta inoltre scorte intracellularidiglicogeno,ilcuiutilizzovieneregolatodalladisponibilitàdeizuccheri sopracitati10.t.vaginalisèunmicroorganismoaerotolleranteingradodicrescerea diversepressioniparzialidio2.ilmetabolismoenergeticoèditipofermentativo,ei prodotti finali sono principalmente glicerolo, lattato, acetato, CO2, ed H2, oltre che malato ed alanina11. In Figura. 2 è possibile osservare come il metabolismo FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.3
9 energetico di T.vaginalis sia ripartito tra citosol ed idrogenosoma, e quali siano le reazionicheportanoallaformazionediatpedeicatabolitidescritti. Figura 2 Mappa metabolica di T. vaginalis. 1) esochinasi; 2) glicogeno fosforilasi; 3) fosfoglucomutasi; 4) fosfoglucoisomerasi; 5) fosfoglucochinasi; 6) aldolasi; 7) trioso fosfato isomerasi; 8) gliceraldeide fosfato isomerasi;9)fosfogliceratochinasi;10)fosfogliceromutasi;11)enolasi;12)piruvatochinasi;13)glicerolo 3 fosfato deidrogenasi, 14) glicerolo 3 fosfatasi; 15) lattato deidrogenasi, 16) alanina amino transferasi; 17) fosfoenolpiruvato chinasi; 18) malato deidrogenasi; 19) piruvato:ferrodossina ossido reduttasi; 20) malato deidrogenasi decarbossilante (enzima malico); 21) NAD ferrodossina ossido reduttasi; 22) idrogenasi; 23) acetato:succinatocoa transferasi;24)succinatotiochinasi. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.4
10 Epidemiologia,manifestazioniclinicheediagnosi T. vaginalis è responsabile della più diffusa malattia a trasmissione sessuale non virale, la tricomoniasi. T. vaginalis infetta 173 milioni di persone ogni anno nel mondo. 12 Latrasmissioneavvieneesclusivamentepercontattosessuale,benchéalcuniabbiano speculatosullapossibilitàdiunatrasmissionenonsessualedell infezione 13 Nelle donne, T. vaginalis infetta principalmente l epitelio squamoso del tratto genitale.ilquadroclinicopuòvariaredaun infezioneasintomaticafinoallavaginite conclamata. Nell infezione sintomatica, la presenza di secrezioni vaginali anomale e di irritazioni vulvovaginali sono i sintomi più frequentemente riportati, e sono presenti dal 50 al 75% dei casi. Le pazienti sintomatiche possono inoltre riportare dispareunia (10 50%), disuria (30 50%), e dolori addominali (5 12%). All esame ginecologico, la vulva presenta un eritema diffuso o escoriazioni in meno del 20% delle pazienti, un infiammazione della parete vaginale (40 75%), e la cosiddetta cerviceafragolache,puressendospessoriportatacomesegnotipicodell infezione da T. vaginalis, è osservata solo nel 2% dei casi 14. I fattori che determinano la presenzaomenodellasintomatologiaedellemanifestazioniclinichenonsononoti, ma si ritiene dipendano da differenze da virulenza fra i diversi isolati del protozoo oppuredaunadiversasuscettibilitàindividualedell ospiteinfettato 15.Èstatainoltre osservata una variabilità nella sintomatologia nelle diverse fasi del ciclo mestruale. Infatti l infezione diventa spesso latente durante la fase follicolare e ovulatoria del ciclomestruale,mentresihageneralmenteunesacerbarsideisintomidurantelafase mestruale. Questo si ritiene correlato al cambiamento di ph che si verifica durante questiperiodi,oltrealdiversoquadroormonale,alqualeilprotozoopotrebbeessere suscettibile. Inoltre, l esacerbarsi dei sintomi potrebbe essere correlato con l ampia disponibilità di ferro durante la fase mestruale, che causa un aumento del metabolismo del protozoo e induce l espressione di alcuni fattori di patogenicità 16. Alcuni studi hanno riportato un aumento delle infezioni sintomatiche durante la gravidanza.questaosservazionepotrebbeesserecorrelataaglistessimotiviriportati perlevariazioniduranteilciclomestruale 17. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.5
11 1.2RNAinterferenza Scopertadell RNAinterferenza Fu Thomas Hunt Morgan, nel 1908, a dare inizio alla selezione basata sulla mutagenesi, isolando decine di mutazioni in D.melanogaster 18. Questo sistema di identificazione genica permise, oltre a costruire una mappa genetica, di arrivare ad un metodo di ''forward screen'' genetico, dando un grosso contributo alla comprensionesullosviluppoedellaregolazionecellulare. Questo tipo di screening genetico permetteva di ottenere informazioni solo utilizzando organismi che presentavano determinate caratteristiche: capacità di ibridizzazioneinlaboratorio,breveciclovitale,abbondanteprole,econunlavorodi mesi o anni per identificare il gene mutato responsabile del relativo fenotipo. Con l'avvento della biologia molecolare i ricercatori hanno iniziato a cercare la funzione biologica di un gene a partire dalle omologie di sequenza o dalle sue funzioni biochimiche,iniziandocosiunapprocciodigeneticainversa:dalgenealfenotipo. Nel 1984 uno passo significativo in questa direzione fu riportato da Izant e Weintraub 19, che trasformarono cellule in coltura con un costrutto che esprimesse RNA antisenso complementare all'mrna della timidina chinasi. L'accumulo della proteinatimidinachinasirisultavacosidrammaticamenteespecificamenteinibito.a questistudiinizialisonoseguitimoltialtri 20,21,22,23 neiqualilastrategiadell'antisenso èstatautilizzataperinibirel'attivitàdigenispecifici. NegliesperimentibasatisuRNAantisensovenivautilizzato,comecontrollonegativo per la specificità, RNA senso. Durante questi esperimenti Guo e Kemphues 24 osservarono che iniettando i filamenti di RNA senso ed antisenso in C.elegans ottenevanofenocopiesimili. Fire,Melloecolleghi 25 inseguitochiamaronoquestofenomenornainterferenceo RNAiperdistinguerlodall'inibizioneindottadalsoloRNAantisenso. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.6
12 Mello e collaboratori però notarono un'altra cosa: il silenziamento avveniva in siti differenti da quello di iniezione suggerendo che l'rna venisse trasportato dal sito iniziale attraverso le cellule e i tessuti del nematode, attivando una risposta sistemica 26,27.Un'altrainteressanteosservazionefattadaFirefuchetransfettandoC. elegans con una miscela di RNA senso ed antisenso ottenevano una degradazione sequenza specifica dell'mrna omologo. Fire infatti ipotizzò che le soluzioni di RNA senso ed antisenso generate mediante trascrizione in vitro fossero contaminate da piccole quantità di RNA di opposta polarità, causata dalla poca fedeltà di RNA polimerasi virale usate durante la trascrizione in vitro. Fu allora che per testare questa ipotesi iniziò ad utilizzare dei dsrna scoprendo cosi che inducevano una rispostaveloceespecificadidegradazionedell'mrnaomologo. Unadellecaratteristichepiùinteressantidell'RNAièchenonsoloinduceunarisposta moltopiùintensamenterispettoaissrna,macheunasolamolecoladidsrnapuò indurreilsilenziamentodidecinedimessaggeri 28.Esperimentidiibridizzazioneinsitu mostrarono che gli mrna di sequenza corrispondente al dsrna non venivano accumulati.infattilaprimaideafucheildsrnainibisseilgenestesso,interferendo con l'inizio o l'allungamento della trascrizione. Questa ipotesi però non trovò riscontro sperimentalmente, infatti il gene target continuava ad essere trascrizionalmente attivo anche in presenza di dsrna: era il messaggero ad essere degradato. 28 Una forma di silenziamento posttrascrizionale era stato precedentemente documentatoinpianteefunghi 29,fuperprimoNapolietall. 28 cercandodiintrodurre in petunie un transgene che iperesprimesse la chalcone sintasi, per ottenere un incremento della pigmentazione del fiore. Inaspettatamente in più del 40% delle piante transgeniche i fiori apparivano bianchi o con variegature di colore rosso. Questo fenotipo risultava sia dal silenziamento, non solo del transgene, ma anche dalle copie endogene della chalcone sintasi quindi fu chiamato cosoppressione. Nel 1992 Romano e Mancino 30 riportarono fenomeni simili in un fungo, la Neurospora crassa,chiamandotaleeffetto''quelling''. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.7
13 InseguitoCogonietall. 31 ottennerofortievidenzecheilquellingneifunghiderivava da alterazioni a livello posttrascrizionale, stabilendo che le molecole effettrici risiedevanonelcitoplasmaemoltoprobabilmenteeranorna.tuttaviainalcunicasi lacosoppressionenellepianterisultavacorrelataconlametilazionedelgenestesso, conducendo ad una downregolazione dell'espressione 32. Waterhouse et all. dimostrarono l'rnai anche nelle piante di tabacco e riso, concludendo quindi che anche due organismi evolutivamente cosi divergenti come piante e nematodi rispondonoallapresenzadidsrnaallostessomodo. Meccanismodell RNAinterferenza Lascopertadell RNAièlamaggioreconquistadellamodernabiologia.L RNAiinfatti influenza la proliferazione cellulare, lo sviluppo, l immunità e la cancerogenesi. Le due maggiori classi di RNAi sono gli small interfering RNA o sirna ed i micro interfering RNA o mirna. Entrambe richiedono il taglio di lunghi RNA a doppio filamento (dsrna) in frammenti di paia di basi, e sono caratterizzate da 2 nucleotidi(nt)protrusialterminale3. IsiRNAsonogeneratidaltagliodidsRNAprecursoriadoperadiDicer,unaRNasedi tipo III, presente nel citoplasma; mentre la via che conduce ai mirna inizia nel nucleo, dove i pri mirna sono processati da un complesso costituito da Drosha, un altra RNaeIII, e DGCR8 per produrre i pre mirna di circa 70 nucleotidi. Questi ultimisonotrasportatinelcitoplasmadovesonotagliatidadicerinmirnamaturi.un filamentodeicortidsrnacosiprodotti,chiamatofilamentoguida,vieneincorporato inuncomplessomultiproteicochiamato RNAinducedsilencingcomplex (RISC)nel qualeleproteineargonauteinduconol appaiamentodelfilamentoguidaconl mrna omologo in modo sequenza specifico. L appaiamento tra il filamento dell sirna e l mrnainduceladegradazionediquest ultimo(figura.3a b).neimirnainvecetale appaiamento porta ad una inibizione della trascrizione. In entrambe i casi sia ha l inibizionedellasintesiproteica(figura.3c) GliRNAattivinell RNAipossonoessereclassificatiinfamiglie: FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.8
14 Small interfering RNA o sirna : sono corti filamenti di dsrna di circa nt omologhi ad un RNA messaggero. Hanno una distinta polarità, essenziale per lo svolgimentodellalorofunzione. sirnaefficientidevonopossedereungruppoossidrilicoe2nucleotidiprotrusial3, ed un gruppo fosfato al 5. I sirna possono derivare da virus a RNA, elementi trasponibilioessereprodottisinteticamente. Micro interfering RNA o mirna: sono oligomeri di 21 nt che si legano al 3 UTR dell RNA messaggero specifico inibendone la traduzione. I mirna derivano da precursori primari endogeni chiamati pri mirna che vengono tagliati da un enzima della famiglia delle RNaseIII chiamata Drosha originando i pre mirna di circa 70 nt che vengono trasportati nel citosol dove le Dicer provvedono a tagliarli in mirna maturianaloghiaisirnaeprocessatiinmodoanalogo 33. Tinynon codingrnaotncrna:sonosimiliaimirnainquantoanch essinelgenoma sonolocalizzatialdifuoridellesequenzecodificantiproteine,sonocompostidacirca nt e mostrano un pattern di espressione temporale ben definito durante lo sviluppo,masidistinguonodaimirnapoichéiprecursorinonpresentanostrutture secondariestemloopcomeimirna.lafunzionedeitncrnanonèancorachiara 34. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.9
15 Figura3 a Smallinterfering(si)RNA.LecaratteristichemolecolarideisiRNAcomprendono:ilterminale5 fosforilato, unaregioneduplexdi19nucleotidi(nt),e2ntprotrusienonfosforilatialterminale3 chesonocaratteristici deiprodottiditagliodellernaseiii b MeccanismodisilenziamentomediatodasiRNA.Ilunghidoublestrand(ds)RNAsonotagliatiadoperadi un membro della famiglia delle RNaseIII, Dicer, in sirna in modo ATP dipendente. Questi sirna sono incorporatinell RNA inducingsilencingcomplex(risc).sebbenelaformazionedelcomplessorisc sirnasia ATP indipendente, l apertura del sirna duplex richiede ATP. Una volta svolto, il filamento antisenso guida RISC sull RNA messaggero con sequenza complementare, portando al taglio endonucleolitico dell mrna target. c Meccanismo di silenziamento mediato da micro (mi)rna. Sebbene originariamente sia stato identificatosullabasedellasuacapacitàdiprocessarelunghidsrna,dicerpuòtagliareancherna hairpindicirca70nt,precursorideimirna 35. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.10
16 Componentidell RNAi:siRNA,Dicer,RISC Iniziali studi su estratti embrionali di D. melanogaster rivelarono la presenza di un attività capace di degradare lunghi dsrna in frammenti di nt chiamati small interfering RNA (sirna) 36. L analisi di questi RNA mostrò che erano RNA a doppio filamento contenenti un gruppo fosfato al 5' 37. L'enzima che inizia la via dell'rnai appartieneallafamigliadellernaseiii,enzimichemostranospecificitàperidsrna. GlienzimidelleRNaseIIIsidividonointreclassi: RNAIII batterici contenenti un singolo dominio catalitico e un dominio di dsrna binding(dsrbd). lafamigliadelledroshacontenente2dominicatalitici 38 laterzafamigliacontiene,oltreaiduedominicatalitici,ancheundominioelicasico edunmotivopaz.membridellaterzaclassesonostaticorrelaticonilprocessamento deldsrnainsirnaall iniziodell'rnai 39.Questafamigliadiproteine,chiamataDicer, possiede dei componenti evolutivamente conservati. Proteine Dicer ottenute da D. melanogaster, C. elegans, eucarioti superiori e neurospora hanno mostrato la capacità di riconoscereeprocessareidsrnainsirnadidimensionicaratteristichedellaspecie. DicerètipicamentecompostodaundominioDExH/DEAHRNAelicasiN terminale,un dominiopaz,duedominirnaseiiiedundominiodsrna binding(dsrbd). IdominiDExH/DEAHsonoRNAelicasiresponsabilidell assemblamentodeisirnanel complessorisc. Il dominio PAZ (piwi argonaute zwille), presente in Dicer, è costituito da circa 130 residuiamminoacidiciepuòlegaresiail3 deissrnaoppurei2ntprotrusial3 dei dsrna. Il dominio dsrbd è presente in molte proteine coinvolte nella trascrizione, nel processamento dell RNA, localizzazione e traduzione degli mrna. Questo dominio riconosce e lega i dsrna aspecificamente, agevolando probabilmente il legame del dsrnaconildominiopaz 40. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.11
17 Funzionalmente i due domini RNaseIII di Dicer si associano a formare un pseudo dimero intramolecolare, creando così un sito attivo in cui ogni dominio idrolizza un singolofilamentodell RNAduplex,generandounnuovoterminale. IlprodottodiDicerèunRNA21nucleotidi.IlnumerodinucleotididelsiRNAderiva dalladistanzatrailterminaleneoformatosull RNAduplexchelegheràPAZ,edilsito attivodell RNaseIII(Figura4). Figura 4 Modello di processamento di dsrna da parte di Dicer di Giardia intestinalis. Dicer riconosce il terminaledeldsrnaattraversoildominiopaz(ingiallo),elotagliaconidominirnasiiii.ladistanzatrapaz eidominirnaseiiideterminalalunghezzadeisirnaprodotti.nelcasodigiardiataledistanzaèdi65å,che 41 corrispondonoa25nt. IlprocessodiRNAivieneportatoaterminedaRISCchericonosceedegradal'mRNA target. Le proteine chiave del RISC sono le proteine Argonaute, inizialmente FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.12
18 identificateinmutantidia.thalianalecuifoglieportavanoun'alteratamorfologia. LeArgonautecostituisconounafamigliaevolutivamenteconservatapresenteinmolti eucarioti. Le Ago sono proteine ubiquitarie in animali e piante, funghi, protisti e archea. Il numerodigeniagotrovatinellediversespecievannodaunocomeins.pombe,a27 in C. elegans. In alcuni casi copie multiple di geni Ago sono funzionalmente ridondanti. Per esempio alg 1 e alg 2 sono sufficienti per compensare un'altra Argonaute,anche sesolitamente i geni Agoin un organismo sono specifici enon si sovrappongono funzionalmente tra di loro. La famiglia di Ago eucariotiche sono classificate in 3 classi principali: il gruppo più grande è chiamato Argonaute (ci si riferisce a questa classe come Ago), e di questo gruppo fanno parte le Ago 1 di Arabidopsis. AlivellocellulareleAgosilocalizzanoprincipalmentenelcitoplasmaenelnucleo. Il secondo gruppo è Piwi (P element Induced Wimpy Testis), molto abbondanti in cellule della linea germinale dove agiscono per silenziare i trasposoni. Nel genoma umanocisono4copiesiadiagochedipiwi. LaterzaclassecomprendegeniArgonautespecificideinematodi,chiamatiWAGO. Nel gruppo Ago i sirna sono prodotti da Dicer nel citoplasma, mentre nel gruppo Piwi il filamento guida si forma attraverso un meccanismo nel quale l'rna target è tagliatodaunaproteinapiwidiventandoilfilamentoguidadiun'altrapiwi.questa cascata è generalmente iniziata da pirna (piwi interacting RNA) ereditati per via materna. Le Argonaute della terza classe ottengono il filamento guida mediante il clivaggiodilunghidsrnaesogenioendogeniadoperadidicer. Strutturalmente le proteine Argonaute sono composte da 4 domini: un dominio N terminale,undominiopaz,undominiocentralemid,edildominiopiwi. IdominiN terminale,midepazsidispongonoaformareunincavoincuisitrovail dominiopiwi.ildominiopiwisiripiegainmodosimileallernaseh,unendonucleasi chetaglial RNAibridiRNA/DNA. IlloboN terminalecontieneundominiopaz,ilqualelegail3'finaledeldnaguida, mentreilloboc terminalecontieneildominiocentralemidchelegail5'fosfatodel FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.13
19 DNAguidaeildominioPIWI,ilcuigruppocarbossiterminaleinteragisceconilgruppo fosfatoal5'delfilamentoguida. Il 5' fosfato del DNA guida è tenuto in una tasca tra il dominio Mid e Piwi, i quali agisconocomepuntodiancoraggioperildnanellaproteina.ilprimonucleotideal5' del filamento guida si infila in una piccola tasca permettendo alla proteina un contatto base specifico che spiega perché alcune Argonaute eucariotiche hanno preferenze per alcune basi al 5' e perché solitamente il nucleotide al 5' non contribuiscasignificativamentealriconoscimentodeltarget.le2basiprotruseal3' sono invece legate al dominio PAZ mentre il resto della molecola è relativamente libera, in modo da accomodarsi nell incavo dell Argonaute, permettendo cosi la sistemazioneanchedifilamentididifferentilunghezze. Dopoillegameconl'RNAtarget,idominidilegamedell'Argonautesiapronoinmodo dafarappoggiareilfilamentotargetedilfilamentoguida. Iduefilamentisonounitineinucleotidida2a8medianteappaiamentodiWatson Crick. Le basi da 2 a 6 del filamento guida si trovano esposte nella parte esterna del complesso e questo è molto importante in quanto sono le responsabili del riconoscimento della sequenza target. Questa porzione del filamento guida viene chiamata"seedregion".talemodellospiegherebbeanchel'elevataefficienzaconcui RISClocalizzaimessaggeritarget. Il riconoscimento dell'mrna target da parte del complesso RISC filamento guida è l'idrolisidelmrna,o"slicing".leduecaratteristichenecessarieperloslicingsonola presenza di proteine Ago cataliticamente attive, ed un appaiamento quasi perfetto trafilamentoguidaernatarget,perassicurarechesoloilmessaggerospecificosia degradate. L'attività RNasica del dominio Piwi di Argonaute catalizza la reazione di taglio dell'rna target mediante idrolisi, e il conseguente silenziamento dell espressione dellaproteina. 39 FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.14
20 Figura5 a. Le proteine Argonaute possiedono quattro domini: il dominio amminoterminale (N), PAZ, MID e PIWI. Ogni proteina Argonaute lega una corta molecola di RNA (in rosso), la quale funziona da templato per il legameconl RNAtarget(inblu).Ilterminale5 fosfato(5 P)dell RNAèancoratoaldominioMID,mentreil terminale3 ossidrilico(3 OH)sitrovaancoratoaldominioPAZ. b. StudistrutturalidiWangecolleghimostranocheilcomplessoArgonautelegal RNAtarget,iniziandocon laformazionediunadoppiaelicaderivantedall appaiamentodelfilamentoguidaconl RNAtarget. c. Il movimento necessario di Argonaute permette l estensione delle doppia elica mentre il l RNA guida è ancoratoinentrambeleestremità.il3 OHdelfilamentoguidaèrilasciatodaldominioPAZpermettendola rotazione. d. Tale cambio conformazionale favorisce l esatto posizionamento del sito di taglio dell RNA target in prossimitàdeldominiopiwi.gliionimagnesiofacilitanolaprecisioneditaglionell RNAtarget 42. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.15
21 Micro interferencerna Negli eucarioti il meccanismo prevalente di silenziamento mediato da RISC è la repressionedellatraduzioneguidatadaimirna.questirappresentanounaclassedi corti RNA regolatori presenti in piante e animali. I mirna derivano da trascritti endogeni a doppio filamento con struttura a forcina (stem loop), e che sono processatidalleproteineago. Adifferenzadellereazionidislicing,larepressionedellatraduzionenonrichiedeuna estesacomplementarietàdisequenzatrafilamentoguidaetarget.ingeneralesolole basida2a7delfilamentoguidasononecessarieperappaiarsiconiltargeteiniziare la repressione della trascrizione. Esistono diversi meccanismi di repressione della traduzione da parte di RISC. La repressione della traduzione è stata studiata approfonditamente in D. melanogaster, che possiede almeno due distinti RISC e ognunomedialarepressioneattraversomeccanismidifferenti.piùprecisamenterisc formatodaago 2bloccal'interazioneproteina proteinatraeif4eeeif4g,necessari perlaformazionediuncomplessopre inizialesulmrnatarget. Ago 1 di D.melanogaster, invece, promuove la repressione della traduzione tramite deadenilazione e degradazione dell'mrna. Infatti nel complesso Ago1 RISC è presente anche la proteina GW182, che ha la funzione di reclutare il complesso di poli deadenilazione costituito da Ccr4 Not, e il complesso di mrna decapping costituitodadcp1edcp2 39 FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.16
22 Rimodellamentocromatinico Generalmente nei sistemi eucariotici le modifiche negli istoni inducono il passaggio da eterocromatina, non trascrivibile, ad una forma altamente trascritta come l eucromatina. Una volta formata l eterocromatina l effetto di blocco della trascrizione, viene propagatoanotevoledistanza,graziealleinterazioniproteina proteinatraifattoridi rimodellamentocromatinico.questeproteinesonogeneralmenteposteinprossimità di sequenze di DNA ripetute, come per esempio centromeri, telomeri e locus mating 43.QuestotipodisequenzesonoresponsabilidellaproduzionedidsRNA,che diconseguenzavengonoprocessatemediantelaviadirnai. In S.pombe è stata osservata un elevata quantità di sirna derivanti da sequenze centromeriche ripetute 44 ; inoltre, mutanti di S.pombe per dcr1, ago1, rdrp1, presentano degli accumuli di lunghi RNA non codificanti (ncrna) omologhi alle sequenzecentromeriche 45. In organismi wild type un filamento della regione centromerica è costitutivamente espresso, mentre il filamento complementare, soggetto a repressione eterocromatinica, viene trascritto solo occasionalmente 46, e proprio tale trascritto guiderà a formazione di dsrna poi processato mediante RNAi. Questo processo potrebbe avvenire nel nucleo, infatti un componente di tale complesso, RdRP, è fisicamente legato alle sequenze ripetute centromeriche più esterne 42. Questo complesso potrebbe essere guidato da determinate regioni di DNA, in seguito ad appaiamentodna RNA. Laconseguenzaèchel istoneh3 K9vienemetilatoeacetilato,condizionenecessaria per la formazione dell eterocromatina. Inoltre in N.crassa e A.thaliana è stato osservato che la metilazione di H3 K9 dirige la metilazione del DNA, e di conseguenza, consente il legame di proteine che legano i gruppi metilici al DNA metilato 47. A seguito di questi eventi la cromatina rimane estremamente compattata e quindi trascrizionalmenteinattiva 48. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.17
23 Applicazionibiotecnologicheebiomedichedell RNAi L RNAièunpotentemezzoperl inibizionedellafunzionegenicainmodosequenzaspecifico.leapplicazionidisilenziamentoindottedarnaisistannofacendostradain campobiotecnologicoebiomedico. PeresempioincampoagricoloisiRNAsonostatiutilizzatipercrearemaschisterilidi parassiti nocivi, utilizzando come target geni legati alla fertilità. Sono state create pianteadaltopotenzialecommercialeincuil RNAiinduceresistenzaavirusobatteri. Anche in campo terapeutico l RNAi possiede un elevato potenziale. Attualmente le applicazioni dell RNAi includono terapie antivirali, come nel caso del papilloma virus 49,virusdell epatiteb 50 ec 51,gammaherpesvirusmurinoeHIVditipo1 52.Anche se, nonostante il primo successo un ostacolo importante è rappresentato dalle strategiechealcunivirushannoevolutoperevaderel RNAi. Moltigruppidiricercaeaziendefarmaceutichehannoutilizzatol RNAiperscopriree validarenuovitargetperlosviluppodifarmaci. Uno degli studi più interessanti è rappresentato dal silenziamento di un oncogene chetrascriveperlaproteinasurvivina,iper espressaincelluletumoralidelcolon,in cuic èstatadiminuzionedellacrescitatumoraleinseguitoaterapiadirnai 53. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.18
24 RNAineiprotozoi Nei protozoi il fenomeno dell RNAi è stato per la prima volta descritto in TrypanosomabruceidaUlluetall.nel IlmeccanismodiRNAiinT.bruceiha molte caratteristiche in comune con le altre vie di RNAi conosciute, inclusa la formazionedisirna 55 elapresenzadeigeniargonauteedicer 56,57,58. Il lavoro iniziato in T.bruceipotrebbe proseguireinvestigando su quali altri protozoi parassiti abbiano una via attiva di RNAi, ottenendo un potente tool per la manipolazione genica di queste specie. Sono state impiegate molte strategie per accertarequaliprotozoipossedesserounarnaiattiva.laprimaèstatalagenomica comparativamediantericercadiomologiedisequenzaperidentificaregeniortologhi codificantiperargonauteedicer. Losvantaggiodell approcciobioinformaticoècheortologhimoltodistantinonsono facilmente identificabili, specialmente se i dati dei sequenziamenti non sono completi. Ortologhi di Argonaute e Dicer sono stati identificati in Trypanosoma congolense 59, Leishmania braziliensis 60, Giardia intestinalis 61,62,63, Entamoeba histolytica 56,57,64,Toxoplasmagondii 65. Mentre non sono stati identificati nel genoma di Leishmania major, Leishmania infantum,trypanosomacruzi,eplasmodiumspp 56,57. Sono stati analizzati anche i genomi di Cryptosporidium spp, Theileria spp., Babesia bovis e Eimeria tenella alla ricerca di omologhi di Dicer e Argonaute, mediante TBLASTN e confrontando le sequenze Argonaute e Dicer umani, e non sono stati trovati omologhi. Alcuni, ma non tutti, i protozoi sono dotati dei tradizionali componentidell RNAi.LasuddivisionetralespecieRNA+eRNA nonsembraseguire la filogenesi, un ipotesi è che l RNAi possa essere stata persa ripetutamente presumibilmenteperl assenzadiunapressioneselettiva.èinteressantenotarechel. major e L. infantum posseggono una sequenza Argonaute degenerata nella regione sintenicaall ortologaputativainl.braziliensis. 66 Nei parassiti in cui sono presenti i componenti dell RNAi, la genomica comparativa dovrebbeesserecomplementataconanalisifunzionali,determinandocosiqualidegli FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.19
25 ortologhi identificati, spesso altamente divergenti, sono funzionali in una via tradizionaledirnai. La strategia adeguata per determinare se i protozoi parassiti possiedano una via di RNAi attiva è l approccio funzionale. Lunghi dsrna e sirna sono stati utilizzati per silenziare l espressione di trascritti endogeni, e l efficienza è stata mostrata misurandoladegradazionedeltrascrittoomologo.ilpuntodebolediquestastrategia èlanonfacilitàdicorrelazionedirisultatipositiviconlapresenzadiunaviadirnai dipendentedadsrna,sirna,edegradazionedeltarget.quindisisonocercati,edin seguito caratterizzati, sia sirna derivanti da dsrna, che sirna omologhi a geni potenzialmenteregolaticonl RNAi. Quest ultima strategia supporta, ma non sostituisce, la strategia funzionale prima descritta. Infatti i sirna possono essere presenti a bassi livelli, e potrebbe essere difficile differenziare i sirna endogeni derivanti da corti trascritti, dai corti RNA risultantidallanormaledegradazionedeglimrna. Esistono forti evidenze funzionali per la presenza di un RNAi attiva nel parassita correlatot.congolense 67.D altrapartestudisistematicidirnaidimostranochenéi dsrnaenéisirnahannolacapacitàdisilenziarel espressionegenicainl.majore T.cruzi.Noncisonofinoradatirelativiallafunzionalitàdell RNAiinL.braziliensis 68, 69. Perciòikinetoplastidisonoapparentementedivisiinbaseadunefficaceutilizzodei dsrnanell RNAi.Quindibasandosisuanalisibioinformaticheefunzionalidell RNAi,i kinetoplastidipossonoesseredivisiintregruppi: 1. organismi in cui la presenza di RNAi è supportata sia da analisi bioinformatichechefunzionali,enelqualeormail RNAièutilizzatadiroutine; 2. organismi in cui non c è stato riscontro né a livello bioinformatico né funzionale; 3. organismi che presentano delle evidenze bioinformatiche o strutturali dell RNAi,maneiqualil RNAinonèutilizzatodiroutine. Poiché T.brucei reca numerose componenti della tradizionale via di RNAi, inclusi omologhifunzionalicomeargonauteedicer,sirnaendogeni,edatidifunzionalità, nonpuòcheessereinseritonelprimogruppo.insiemeat.congolese,incuil RNAiè FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.20
26 supportata da dati bioinformatici ed un singolo, forte studio funzionale. Finora T.cruzi, L. major e L. infantum non è stata supportata da dati né funzionali né bioinformatici e di conseguenza sono stati inseriti nel secondo gruppo. Per L. braziliensis invece ci sono evidenze bioinformatiche ma non funzionali quindi attualmenteènelterzogruppo. I dati derivanti da G.intestinalis e E. histolytica sembrano essere coerenti quando vengono confrontati gli studi funzionali e bioinformatici. Inoltre la presenza di ortologhididicereargonauteèstataosservataing.intestinalis;ulluetall.hanno identificatornaduplexdi25ntderivantidalretrotrasposoneendogenogilt/genie 1,suggerendo,manonprovandolapresenzadiunaRNAiattivainquestoorganismo. In E. histolytica, nel quale sono codificati ortologhi di componenti noti dell RNAi, ci sonoevidenzecheindicanosilenziamentogenicoinseguitoatrattamentoconsirna o di shrna espressi da un plasmide. L attività di silencing è limitata a due soli geni target γ tubulina e EhDia e non c è ad oggi un uso sistematico dell RNAi in E. histolyticapereffettuaregenesilencing. LapossibilepresenzadiRNAinegliapicomplexahageneratoenormeinteresse,anche se continua a rimanere controversa. Oltre alle evidenze bioinformatiche già citate, dsrnaesirnasonostatiutilizzatinellaboratoriodiananvoranichperridurreilivelli ditrascrittoint.gondii,stabilendoun evidenzafunzionaleperl RNAi 70,71,72.Moltidei lavori si sono basati sul silenziamento della ipoxantina xantina guanina fosforibosiltrasferasi(hxgprt)edellauracilfosforibosiltrasferasi(uprt),ilivellidei quali vengono poi misurati valutandone l attività metabolica. I parassiti con ridotti livelliditgago(argonaute PIWIortholog)daRNAi,possiedonounaridottacapacità di silenziamento mediata da RNAi per i trascritti HXGPRT e UPRT, suggerendo un ruolo funzionale per questi ortologhi. Tuttavia la produzione di sirna non è stata dimostrataenonèdiffusol usodell RNAiinT.gondii. La presenza di un attiva via di RNAi in Plasmodium spp., è ugualmente dibattuta. Sebbene non siano stati trovati ortologhi della via di RNAi durante gli studi di genomicacomparativa,cisonocinquestudifunzionalichesuggerisconolapresenza di una via di RNAi in Plasmodium spp. In ogni caso successivamente non sono stati FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.21
27 fattialtristudiesonostatiinoltreriportaticasidifallimentodiesperimentisimili 73,74,. InpiùèfallitoancheunostudioperidentificaresiRNAendogeniinP.falciparum 75, cheinconseguenzadituttiquestiesperimentièstatoposizionatoneliiigruppo.non sono stati osservati ortologhi di componenti dell RNAi né sono stati effettuati studi funzionalisucryptosporidiumspp.,theileriaspp.,e.tenella,eb.bovis,chesonostati tuttiinseritineliiigruppo. L RNAi, quando presente e funzionale, gioca un ruolo importante nella biologia dei protozoiparassiti. GliesperimentisuT.bruceisuggerisconochel RNAipuòaveremoltiruoliendogeni. T. brucei difettivi nel meccanismo di RNAi presentano elevati livelli di trascritti dei trasposonislacseingi,ebassilivellidisirnaderivantidaslacseingi 54,76,77,78 Lafunzionesembraesserealmenoparzialmenteilcontrollodeiretrotrasposonicome èstatoosservatoinorganisminonprotozoari.iretrotrasposonisonostatiidentificati in molti protozoi parassiti che possiedono una putativa via di RNAi oltre a T.brucei, inclusi L. braziliensis, E. histolytica, e Giardia lamblia, e sirna derivanti da retrotrasposoni sono stati identificati in G. intestinalis. Tuttavia la presenza di retrotrasposoninonèstatastrettamentecorrelataconlapresenzadiunaviadirnai, comet.cruziperesempiochepresentadeitrasposonimanonfarnai 79.Mentrein P.falciparumeT.gondiineiqualièancoracontroversalapresenzadiun attivarnai, nonsonopresentiretrotrasposoni 80.Rimanedachiariresel RNAivengausatacome difesa contro virus a dsrna, sebbene siano stati identificati virus in alcuni protozoi comeg.lamblia 81 et.vaginalis 82. Leprovedicomel'RNAineiprotozoicontrollil'espressioneendogenadisiRNAsono attualmente poche, eccetto che per T. brucei e G. intestinalis, nei quali sono stati trovaticortirnaomologhiamessaggeri 56,83. Resta il dubbio se questi RNA siano effettivamente sirna oppure derivino dalla normaledegradazionedirna. L'analisi di sequenza di questi corti RNA, sia in wild type che in mutanti Dicer ha chiarito questo dilemma,anche grazie al legame di sirna alle Argonaute che permette l'isolamento e la caratterizzazione dei relativi RNA. Portando alla FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.22
28 conclusionecheicortirnanonsonocorrelaticonladegradazionedell'rna,maconi sirna. Poiché i mutanti nella via dell'rnai presentano alti livelli di trascrizione dei retrotrasposoni, è anche possibile che la via dell'rnai possieda un ruolo, diretto o indiretto, nel silenziamento trascrizionale nel nucleo come osservato nell'uomo, piantees.pombe 84,85,86.Un'ipotesièchel'RNAisianecessariaperilsilenziamentoe spegnimento di antigeni, poiché questo processo è regolato dalla trascrizione e potenzialmentedarimodellamentocromatinico. Nonostante studi funzionali suggeriscano la presenza dell'rnai in molti protozoi patogeni, ancora l'rnai non è stato adottato come metodo diffuso di genetica inversa,trannechepert.brucei. Èchiaroilmotivodiciòperiprotozoineiqualinonc'èstatoriscontrobioinformatico ofunzionale. Per quanto invece riguarda il terzo gruppo è possibile che questi protozoi non posseggano una via classica di RNAi, e i risultati ottenuti finora rappresentino degli artefatti. Per esempio è stato osservato che alti livelli di oligonucleotidi possono causare inibizionedellacrescitainp.falciparum 87,88,89.Intalmodo,quandoelevatequantità didsrnavengonoutilizzateinesperimentidisilenziamento,bloccandolacrescitain modononspecificobloccandolatrascrizione,iltassoditurnoverdeterminaillivello di RNA e proteine prodotte per il target preso in esame. RNA con emivita breve appaionosilenziati,mentrernaconlungaemivita,sembranononessereinfluenzati. MoltistudispecialmentequelliinPlasmodiumspp.,eT.gondii,nonhannomostrato in modo diretto una specifica riduzione di RNA e proteine, ma piuttosto sono stati valutatialtrifenotipi,comevariazioninellacrescitaonelmetabolismo. Conl ormairoutinarioutilizzodell'rnaiint.brucei,usarelamanipolazionegenetica perricostruireun'attivaviadirnaiinorganismichenonlapossiedonosembrauna possibilitàallettanteanchesepotenzialmenteirraggiungibile. È stato dimostrato come in T.brucei, che la proteina Ago2 di origine umana complementi TbAgo1, dando la prima dimostrazione che le proteine Argonaute FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.23
29 possano essere intercambiabili e funzionali anche in organismi evolutivamente distanti 90. InoltreRivasetall.hannodimostratocheAgo2umanaricombinantepuòcombinarsi consirnapertagliarespecificamenternainunsistemainvitro,definendocosìun RISCminimale. Consideratiinsieme,questirisultatisembranosuggerirelapossibilitàdirestaurarela funzionalità dell RNAi mediante knocking in del RISC minimale seguito dall introduzione di sirna. Per ottenere un sistema funzionale in vivo il RISC ha bisogno di altre proteine; per esempio è stato dimostrato che in vitro l'atp non è necessarioinquantoilcomplessoriscnonrilascial'rnadopoaverlodegradato,step crucialeinvivoperilriciclodelrisc. 91 Inoltre la ricostituzione di una funzionale via di RNAi richiederebbe precisa coordinazione della localizzazione così come dell'espressione dei componenti necessari, incluso il trascritto target, cosa che potrebbe rivelarsi difficoltosa, specialmente se la ricostituzione richiede più della sola reintroduzione di una Argonaute. l'rnairappresentaunmezzoottimaleperavereinformazionisullafunzionegenicain modo veloce e facile. In molti parassiti metodi efficienti per il silenziamento genico non sono disponibili, e il lavoro si complica se si parla di geni correlati, duplicati o interefamigliedigeni. Risulta difficile l applicazione dei classici metodi utilizzati in altri organismi, ad esempio se il ciclo sessuale non è stato completamente identificato, oppure lo sviluppoècomplessoosperimentalmenteimpraticabile. L'RNAipotrebbeaveremolteapplicazioninellacaratterizzazionefunzionaledisingoli geni. La regolazione dell'induzione dell'rnai e le inerenti variazioni nell'efficienza dell'interferenzapermetterebbeairicercatoridianalizzarefenotipiderivantidalivelli differentidiespressionegenica.moltigeninoncorrelatipossonoesserestudiaticon poco sforzo, permettendo analisi di epistasi e di processi multipli. L'RNAi può produrre cellule con ridotta espressione di geni essenziali, portando a fenotipi che FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.24
30 non potrebbero essere studiati con la completa eliminazione del gene. Inoltre gli effettidell'rnaisonoreversibilipermettendounostudioapprofonditodellafunzione genica.inorganismidoveladelezionegenicaèlaboriosaodifficoltosa,eisistemidi regolazione dell espressione sono limitati, questo approccio risulta estremamente promettente. Poichél'RNAièunsistemadisilenziamentobasatosullaspecificitàdisequenzapuò essere utilizzato a livello di intere famiglie geniche. Nei tripanosomi, infatti, è stata fattainterferenzasimultaneadimembriomologhidiunafamigliautilizzandounsolo dsrna. Al contrario, in Drosophila, sono stati utilizzati una combinazione di dsrna per silenziare una famiglia di geni. Nonostante l'interpretazione dei dati sia da trattareconattenzione,l'rnairestaunmetodomigliorerispettoallacostruzionedi knock outmultipli 92. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.25
31 1.3IlsequenziamentodelgenomadiT.vaginalis Negliultimianni,lacomunitàdeiricercatorichehannocomeoggettodeilorostudiT. vaginalis ha creato un consorzio con lo scopo di esercitare pressioni sui National Institutes of Health americani al fine di finanziare il sequenziamento del genoma di questomicroorganismo.glisforzisonostatipremiatieilt.vaginalisgenomeproject ha iniziato le proprie attività presso il TIGR (The Institute of Genomic Research, Rockville,MD,USA),sottoladirezionediJaneCarlton. 93 Strutturadelgenoma,processamentodell RNA,trasferimentogenicolaterale LasequenzadelgenomadiT.vaginalisèstatagenerataconlametodologiawholegenome shotgun, e contiene 1,4 milioni di reads shotgun assemblate in scaffoldsperunacoperturastimatadi7.2x.almenoil65%delgenomadit.vaginalis è costituito da sequenze ripetute. Nonostante siano state sviluppate diverse procedure per implementare l assemblaggio, la sovrabbondanza di repeats ha prodotto una sequenza frammentata, impedendo lo studio dell architettura del genoma di T. vaginalis. Questa caratteristica ha anche reso difficoltosa la determinazione delle dimensioni del genoma stesso, che sono state comunque stimateincirca160mb.e statoidentificatounsetdibasedi60.000genicodificanti proteine,unadellecifrepiùaltetraglieucarioti.sonostatiidentificatiintroniin65 geni,compresii20incuieranostatiprecedentementedimostrati.sonostatitrovati trnapertuttie20gliaminoacidi,esonostateinoltreidentificatecirca250unitàdi DNAribosomale(rDNA),tuttelocalizzatesuunodeiseicromosomidiT.vaginalis.Da sottolineare come l apparato di trascrizione di T. vaginalis, nel suo assortimento di fattori di trascrizione e di subunità delle RNA polimerasi, appaia più simile a quello dei metazoi che non tipicamente protista. Durante l annotazione del genoma sono statetrovate152possibilicasiditrasferimentolateralegenico(lgt)daprocarioti.le funzioniputativediquestigenisonodiverse,einfluenzanodiverseviemetabolichee FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.26
32 quindi influenzando l evoluzione del metaboloma di T. vaginalis. La maggior parte (65%)deigeniputativamentederivatidaLGTcodificanoperenzimimetabolici,piùdi unterzodeiqualisonocoinvoltinelmetabolismodeicarboidratiedegliaminoacidi. Diversi dei geni acquisiti per LGT potrebbero essere derivati da batteri del genere Bacteroides, che sono abbondanti nella flora intestinaledeivertebrati(tab1). Tabella1.TabellariassuntivadellecaratteristichedelgenomadiT.vaginalisilnumerodigenipredetti potrebbeincludererepeatsabassacomplessitàonuovielementitrasponibilipiuttostocheverigenidi T.vaginalis,mainassenzadidecisiveproverestal attualesetdigeni. Repeats,elementitrasponibiliedespansionegenomica Le 59 famiglie più comuni di repeats identificate nella sequenza assemblata costituisconocirca39mbdelgenomaepossonoesserecosìclassificate:(i)virus like; (ii) transposon like, comprese le circa 1000 copie del primo elemento trasponibile mariner identificato al di fuori degli animali; (iii) retrotransposon like; (iv) non classificati. La maggior parte dei 59 repeats sono presenti in centinaia di copie (numeromediodicopie:660),eognifamigliadirepeatsapparestraordinariamente omogenea, con un polimorfismo medio del 2.5%. La mancanza di una forte correlazione tra numero delle copie e differenze medie di appaiamento tra copie, FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.27
33 suggeriscechevisiastataunaimprovvisaespansionedeirepeats.perdareunastima delperiododiespansione,sonostaticomparatiigradidipolimorfismotrairepeatsdi T. vaginalis con la divergenza tra diversi loci codificanti proteine in T. vaginalis e la specie correlata T. tenax, ottenendo l indicazione che l espansione dei repeats sia avvenuta dopo la separazione tra le due specie. Sono state inoltre ottenute indicazioni di come diverse famiglie di repeats siano andate incontro a successive espansioni. Le famiglie di repeats di T. vaginalis sono assenti in T. tenax, ma sono presentiinisolatidit.vaginaliscondiversaprovenienzageografica,inaccordocon l ipotesi che l espansione sia avvenuta dopo la speciazione ma prima della diversificazione di T. vaginalis. Le grandi dimensioni del genoma, l alto numero di copie di repeats, il basso polimorfismo dei repeats e le evidenze di una espansione dei repeats dopo la separazione tra T. vaginalis e T. tenax, suggeriscono che recentemente T. vaginalis è andato incontro a un sostanziale aumento delle dimensionidelgenoma. Metabolismo,stressossidativo,trasporto T. vaginalis utilizza I carboidrati come principale fonte di energia, attraverso un metabolismo fermentativo in condizioni sia aerobiche che anaerobiche. Il protozoo utilizza inoltre diversi aminoacidi come substrati energetici, con la via dell arginina diidrolasicomeunadelleprincipaliviediproduzionediatp.l analisidellasequenza delgenomahaconfermatounruolocentraleperleaminotransferasielaglutammato deidrogenasi: queste vie sono presumibilmente cataboliche, ma potrebbero essere reversibili e consentire al parassita di sintetizzare glutammato, aspartato, glutammina, alanina e glicina. Son ostati identificati i geni necessari alla sintesi di prolina,argininaetreonina.e stataancheidentificataunaviaperlasintesidenovo di cisteina, attraverso la cisteina sintasi, un candidato LGT, nonché I geni per il metabolismodellametionina,inclusiquellicoinvoltinellasuapossibilerigenerazione. Studi precedenti indicano che la sintesi de novo di lipidi sia limitata alla fosfatidiletanolammina,mentrealtrilipidi,inclusoilcolesterolo,sonoprobabilmente FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.28
34 acquisti da fonti esterne. L analisi del genoma ha confermato l assenza di geni codificanti per gli enzimi coinvolti nelle vie di sintesi degradazione di quasi tutti I lipidi. Sono stati identificati geni codificanti per superossido dismutasi, tioredoxina reduttasi,perossiredoxinaeruberitrina,inaccordoconlostiledivitamicroaerofilico di T. vaginalis, che richiede sistemi redox e antiossidanti per contrastare gli effetti tossicidell ossigeno. T.vaginalisdimostranotevolicapacitàditrasporto,comeevidenziatodall espansione difamiglieditrasportatori,comeadesempioquelliperglizuccheriegliaminoacidi. Possiede inoltre il maggior numero di componenti della famiglia di cotrasportatori cationeclorurodituttiglieucariotidicuièstatosequenziatoilgenoma,cheriflettela capacità del protozoo di adattarsi ai cambiamenti osmotici presenti nell ambiente mucosale. Famigliegenicheespanse MoltefamigliegenichenelgenomadiT.vaginalissonoandateincontroaespansione aunlivellomaiosservatoprimaneglieucariotiunicellulari(tab.2).questasortadi espansione conservativa di famiglie geniche potrebbero aumentare le capacità adattative di un microorganismo al proprio ambiente. Da sottolineare come l espansione selettiva di componenti del macchinario di membrane trafficking, fondamentale per la secrezione di effettori di patogenicità, per l endocitosi di proteine dell ospite, e per la fagocitosi di batteri e cellule dell ospite, correli con l intensaattivitàendociticaefagociticadit.vaginalis. Alcune delle famiglie geniche espanse fanno parte del kinoma di T. vaginalis, che comprendecirca880genichecodificanopertipichechinasieucariotiche,ecirca40 chinasiatipiche,cosachelorendeunodeikinomieucarioticipiùgrandiecomplessi. L espansione genica ha riguardato anche proteine del citoscheletro. T. vaginalis possiedediversestrutturecitoscheletricheinsolite(lapelta,l assostile,lacosta).son presenti molti elementi citoscheletrici correlati con l actina e la tubulina, con FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.29
35 l eccezione della miosina. In contrasto, gli omologhi del motore microtubulare dineinaekinesinasonoabbondantiinmodoinusuale.perciò,iltrafficointracellulare in T. vaginalis potrebbe essere mediato essenzialmente dalla dineina e kinesina citoplasmatiche, come già osservato per Dictyostelium e per i funghi filamentosi. Si potrebbeipotizzarechelaperditadiuntraffickingintracellularemediatodamiosina possaessereuneventocomunetraglieucariotiunicellulari.rimanedachiariresela trasformazione morfologica in senso ameboide osservata durante la colonizzazione dell ospite sia mediata dall actina o se sia determinata da riarrangiamenti citoscheletricialternativi.sonostatiidentificatiomologhidiproteinecoinvoltenella risposta al danneggiamento e riparo del DNA, rimodellamento cromatinico e nella meiosi, nonostante T. vaginalis abbia una riproduzione asessuata. Dei 29 geni che fannopartedelcorredobasemeiotico,diversisonoproteineconfunzionediriparo generalenecessarieperlameiosiinaltriorganismi,mentre8sonomeiosi specifici.si può concludere che T. vaginalis possiede dei recenti relitti evoluzionistici di un macchinario meiotico, oppure dei geni funzionali in un processo meiotico di ricombinazioneinunciclosessualenonancoradescritto. Tabella2 IntabellasonoriportatelefamiglieoigruppidifamigliegenichediT.vaginalischemediano processi, nei quali sono coinvolte più di 30 proteine alle quali sono state assegnate delle putative funzioni.gtpasessonolasommasolodellegtpaserabearf;abc:atp bindingcassette;msf:major facilitatorsuperfamily;mopmulti drug/oligosaccharidyl lipid/polysaccharide;aaap,aminoacid/auxin permease. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.30
36 Meccanismimolecolaridipatogenicità Uno step cruciale nell inizio e nel mantenimento dell infezione è l adesione alle cellule dell ospite da parte di T. vaginalis. Sono state identificate otto famiglie contenenti circa 800 candidate proteine di superficie, che includono anche 650 putativebspa likeproteinscaratterizzatedaleucine rich repeats(lrr).lebspa like proteinssonoespressesullasuperficiedimoltibatteripatogeniemedianol adesione cellulare. L unico altro eucariote che esprime BspA like proteins è Entamoeba histolytica. T. vaginalis possiede 75 geni che codificano per GP63 like proteins, omologhi delle proteine di superficie più abbondanti di Leishmania major, le leishmanolisine. La maggior parte delle GP63 like proteins predette possiede i domini necessari per un attività metallopeptidasica. Sono stati inoltre identificati dei geni codificanti per putativi effettori citolitici, che potrebbero essere rilasciati dopo il contatto con le cellule ospiti. Si tratta di 12 geni (TvSaplip1 12) contenenti dei domini saposin like, che sono ritenuti mediare un attività formante poro. Questi domini mostrano un tipico pattern di sei residui di cisteina, abbondanti residui idrofobici in posizioni conservate.questecandidateproteineformantiporosonosimilialleamoebapores, proteine ad attività citolitica secrete da E. histolytica, e possono essere ritenute le candidatetrichopores. L analisi della sequenza del genoma di T. vaginalis ha consentito inoltre di avere nuoveeimportantiinformazionisuldegradoma,evidenziandoancheinquestocaso unamassicciaespansionechehaportatoilprotozooapossederepiùdi400peptidasi. Ciòsottolineal importanzadiquestaclassedimolecolenellabiologiadelparassita. Grazie al progetto genoma è stato possibile identificare nuove vie metaboliche e gettarelucesulprocessopatogenetico,fornendocosìpotenzialinuovoapprocciper lo sviluppo di innovativi strumenti diagnostici e nuove terapie. Le analisi condotte sono state sicuramente ostacolate dal gran numero di repeats molto simili e di elementitrasponibili.leragionidiquestodrammaticoaumentonelledimensionidel FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.31
37 genomapotrebberoesserelepiùvarie.e statoipotizzatocheunantenatocomunedi T. vaginalis sia andato incontro a un effetto collo di bottiglia durante un ipotetico passaggiodall ambienteintestinale(l habitattipicodimoltespecieditrichomonas)a quello urogenitale. In questo passaggio una diminuita selezione potrebbe essere risultatanell accumulodirepeatsenell espansioneselettivadideterminatefamiglie geniche.poichéledimensionidelgenomaequellecellularisonocorrelate,l aumento del genoma potrebbe avere avuto come effetto anche l aumento delle dimensioni della cellula. L aumento delle dimensioni potrebbe avvantaggiato T. vaginalis da un lato aumentandone le capacità fagocitiche nei confronti dei batteri della flora vaginale,daunaltrolatorendendopiùdifficoltosal ingestionedapartedeifagociti dell ospite e fornendo una maggiore area di contatto per la colonizzazione della mucosavaginale. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.32
38 2.Materialiemetodi AnalisidellasequenzadelgenomadiT.vaginalis Sonostateeffettuatericerchediomologianeldatabasedellasequenzadelgenomadi T. vaginalis( per l identificazione di putativi componenti della via di RNAi. Le queries utilizzate per l analisi BLAST erano le sequenze aminoacidiche:drospophilamelanogasterdicer(accnoq9vcu9);t.bruceitbago 1 (acc no EAN78475), D. melanogaster Armitage (acc no AAT12000). L analisi è stata effettuata mediante TBLASTN usando l assembly 7.2X del genoma come subject. L attività trascrizionale delle putative ORF trovate mediante analisi di omologia è stata valutata mediante analisi BLAST di EST (expressed sequence tags) nel databasechanggungtrichomonasvaginalisexpressedsequencetag(tvxpressdb; I geni predetti che non sono stati confermati come trascrittiinquestomodosonostatianalizzatisperimentalmentemediantert PCR.Le sequenzeaminoacidicheottenutepertraduzioneconcettualedeigenipredettisono state analizzate per la ricerca di domini funzionali conservati mediante il software SMART (Simple Modular Architecure Research Tool Celluleelorocoltivazione L isolatodit.vaginalisss30,naturalmenteprivodimycoplasmahominis 94, 95 etvv 96, è stato ottenuto da tampone vaginale di donna affetta da tricomoniasi. I protozoi sono stati coltivati mediante diluizioni giornaliere 1:16 in terreno Diamond s TYM supplementatoconsierobovinofetale(fbs)al10%.lecolturesonostateincubatea 37 C.Lavitalitàdeiprotozoièstatamonitoratavalutandonelamotilità. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.33
39 EstrazioneDNA 10 7 cellulesonostatecentrifugatea1500gperallontanareilterrenodicoltura;sono statieffettuatiduelavaggiinpbs.lecellulesonostaterisospesein318μlditampone TEpH8,80μldiSDSal10%,2μldiproteinasiKesonostateincubatea65 Cper30 minuti.sonostatiaggiunti200μldifenolosaturatointris HCl,200μldicloroformioalcolisoamilico24:1.E statafattaun ulteriorecentrifugazionea12000xgper10.e stataraccoltalafaseacquosachehasubitoaltredueestrazioniinfenolo CIA25:24:1. È stato fatto precipitare il DNA aggiungendo 0.8 ml di etanolo al 100% e 40 μl di acetatodisodio3maph5.2eincubandoper1orae45 a 80 C.E statafattauna centrifugazione a 12000xg per 15 a 4 C, il sopranatante è stato scartato e il pellet lavatocon1mldietanoloal70%.unavoltaasciugatoall ariaildnaèstatorisospeso in30µlditeph8. Ilciclodiamplificazioneutilizzatovariavaasecondadellacoppiadiprimersutilizzata. 1)DENATURAZIONEa94 Cper5minuti. 2)AMPLIFICAZIONE,ripetutaper35cicli 94 Cper45 temperaturadiannealing45 72 Cper30 3)POLIMERIZZAZIONEa72 Cper5minuti. Estrazioneedanalisidell RNA L RNA totale è stato estratto con Trizol(Invitrogen) in accordo con le istruzioni del produttore. Brevemente, alle cellule risospese in Trizol sono stati aggiunti 200 µl di cloroformio, seguiti da agitazione per 15, 3 a T ambiente, e centrifuga per 10. L RNAnellafaseacquosaèstatoprecipitatocon500µldiisopropanolo,incubato10 atambienteecentrifugato.ilpelletdirnaèstatolavatoconetanoloal70%,eduna volta asciugato è stato risospeso in opportuno volume di acqua trattata con DEPC (dietilpirocarbonato)allo0,01%. Tuttelecentrifugatesonostateeffettuatea4 Ce12000xg. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.34
40 Laconcentrazionedell RNAèstatadeterminatainspettrofotometriaUVa260nme la qualità valutata con l elettroforesi su gel d agarosio all 1%. Per la RT PCR semiquantitativa un eventuale DNA genomico contaminante è stato eliminato mediantetrattamentocondnasei(invitrogen),el assenzadidnaèstataconfermata dapcrconvenzionale. IcDNAsonostatiretrotrascrittiapartireda500ngdiRNAtotale,0,5µgdiOligo(dT), 1 µl di dntps 10 mm, 4 µl di first strand 5X, 2 µl di DTT 0,1 M, ed 200 unità di SuperScriptIIreversetrascriptase(Invitrogen)secondoleistruzionidelproduttore. PerognireazionediqRT PCRconidiversicDNAsonostateeffettuatecurvestandard condiluizioniserialidicdna. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.35
41 Tabella3Elencodeiprimersutilizzati: ATGAACGAGGCTCATGC TvAA TCTCCTTCTTGGCGTTGA 63 TT TvME CCAGACACTCCCAGTCC 58 CT FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.36
42 AT TGTCTCGCCAAAGACTT CCT Sintesidell RNAdoublestranded(dsRNA)omologoall α actinina. GliRNAsensoedantisensosonotrascrittiapartireda2DNAidenticiomologhialla regionecentraledi700paiadibasi(bp)dell α actinina(geneidxm tvag ),marecantiilpromotoreT7indirezioniopposte,inseritomediantePCR. α actsenso: ForTAATACGACTCACTATAGGGACTCCGTCAACCGCCACCACTCC RevCGGGCCTTGCGCTCTTCTTCCT α actantisenso: ForACTCCGTCAACCGCCACCACTCC RevTAATACGACTCACTATAGGGCGGGCCTTGCGCTCTTCTTCCT). Ogni DNA templato viene trascritto in una singola reazione di trascrizione in vitro, originandocosiiduefilamentissrnacomplementari.lereazionisonostateeseguite come da protocollo l unica variazione è stata l aggiunta alla miscela di reazione di fluorescein 12 uridine 5 trifosfato (UTP FITC) (Roche, Mannheim, Germany), in quantitàtalecheilrapportoutp FITC/UTPfosse3,5mM/6,5mM.IssRNA FITCsono statipurificati,quantificatiequantitàequimolaridirna sensoerna antisensosono stati incubati per 5 a 75 C e lasciati a temperatura ambiente fino a completo raffreddamento (circa 4 ore.). la qualità del dsrna FITC è stata valutata mediante elettroforesisugeld agarosio. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.37
43 ElettroporazionedidsRNAinT.vaginalis. 2,5x10 8 cellule di T. vaginalis SS 30 sono state centrifugate a 1500xg per 10, e il pelletèstatorisospesoin300µldidiamondfreddo.allasospensionecellularesono stati aggiunti 35 µg di dsrna FITC o una quantità equivalente di poly(ic) come controllo.l elettroporazioneèstataeffettuataa350voltse960µfdinmicrocuvette da0,4cmutilizzandolostrumentobio Radgenepulser.Lecelluleelettroporatesono stateimmediatamenterisospesein50mldidiamonda37 C. Apartiredall elettroporazione(tempo0)sonostatieffettuatiprelieviconsecutiviper l estrazionediproteineerna,rispettivamenteda5x10 5 e1x10 7 cellule. Analisidelleproteine. 5x10 5 cellule (trattate e controllo) sono state raccolte mediante centrifugazione e lavate 2 volte con PBS. Il pellet è stato risospeso in Laemmli e bollito per 3. Per il Western blotting proteine estratte da 5x10 4 cellule sono state separate mediante SDS PAGEinungelall 8%,etrasferitesumembranadinitrocellulosa.Lemembrane sonostatesaturateinpbscontenenteil0,05%ditween20eil3%dialbuminaserica bovina(sigma Aldrich).LemembranesonostateincubateconanticorpipoliclonaliĀα actininaeā enzimamalico. Anticorpianti enzimamalico. Per valutare la possibile variazione dell espressione dell α actinina in seguito alla transfezione con dsrna FITC, i livelli di espressione dell enzima malico sono stati utilizzaticomeloadingcontrol.perfareciòstatonecessarioprodurreanticorpicontro taleproteina.laporzionedelgenedell enzimamalicocompresatrailresiduo230e 1810(geneIDXM TVAG_267870)èstataamplificatamediatePCR(TvMEclon for: CGGGATCCGCTAAGGTCCCAACC. TvMEclon rev: AACTGCAGATAGAGTTGCTCGTA) eclonatanelvettorediespressionepqe30(qiagen),chepermettedisintetizzarela FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.38
44 proteina di interesse fusa con una coda N terminale di 6 residui di istidina, consentendo perciò la purificazione della proteina mediante cromatografia per affinitàconionidinichel. La proteina ricombinante è stata purificata e quantificata mediante Bradford s reagent(sigma Aldrich) 40 µg di antigene addizionati con 500 µl di PBS e 500 µl di adiuvante di Freund completo(sigma Aldrich)sonostatiinoculatiintopo(BALB C). Dopo15giornièstatainoculatalastessaquantitàdiantigenemiscelatacon500µldi PBSe500µldiadiuvantediFreundincompleta. Ilterzoinoculoèstatoeffettuatodopocirca22giornielamiscelacomprendeva30 µgdiantigenerisospesiin1mldipbs. Ilbleedingdeltopoèstatoeffettuatodopounasettimanadall ultimoinoculo. Iltitolodell anticorpoèstatovalutatomedianteelisa. Costruzionedeivettoriperl espressionedidsrna Per ottenere un vettore che esprima in modo inducibile dsrna in T. vaginalis, abbiamo utilizzato il vettore ptv94tet neo, precedentemente messo a punto per l espressione di geni esogeni in T. vaginalis. (gentilmente fornito da P.J. Johnson, UCLA, Los Angeles, USA 97 ). Il vettore ptv94tet neo è stato messo a punto sullo scheletro del pbluescript (Stratagene), in cui è stato inserito, tra il 5 UTR ed il 3 dell α succinyl CoA sintetase B (5 3 α SCS), il gene CAT (cloramfenicolo acetil trasferasi),lasequenzadell operatoretet(teto,freccianera)èstatainseritaavalle del sito di inizio della trascrizione Inr(freccia bianca). La cassetta Neo, che codifica perlaneomicinafosfotransferasi,èstataposizionatatrail3 e5 dellaregioneutr del gene della tubulina. TetR, anch essa inserita tra il 3 e il 5 dell UTR dell α SCS, esprimeperilrepressorediteto. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.39
45 L obiettivoèl espressionedidsrnastem loop,incuiiduessrnasianoseparatida una sequenza spaziatrice non correlata con T. vaginalis. Questa sequenza è necessaria per la propagazione nei batteri del plasmide, che senza risulterebbe instabileacausadellesequenzeripetuteinvertite. NelplasmidepTV94Tet neoèstatosostituitocatconlaporzionedell α actinina α actbamhi5 CGGGATCCTGCATGGACATCATCAACAA3 ; α actkpni 5 GGTACCCAACCTGAGCCTTGACTGC 3 ) di 700 bp orientata in direzione antisensoutilizzandokpniebamhi.ilplasmideèstatochiamatoptvαact. L α actininaindirezionesensoamplificatamediantepcr (α actsmai5 CCCCCGGGGGTGCATGGACATCATCAACAA3 ; α actpsti 5 GGTACCCAACCTGAGCCTTGACTGC 3 ) è stata inserita mediante SmaI e PstIavalledelgeneDHFRdelplasmidepQE40 FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.40
46 Il plasmide cosi ottenuto è stato utilizzato come templato per amplificare in PCR (DHFBamHI for5 CGCGGATCCGCGAAGAATGACCACAACCTCTTCAG3 ; DHFBamHI rev5 CGCGGATCCGCGCTGCAGCAGCATCTCCTG3 )500ntdelgeneDHFR (spaziatore)el α actininaindirezionesenso. L amplificato ottenuto è stato inserito in ptvαact originando il plasmide definitivo pfrαacttet neo. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.41
47 3.RISULTATI RicostruzionediunaputativaviadiRNAiinT.vaginalis. Duefamigliegenicheconservatesonoicomponentiuniversalidell RNAieriflettonoi due step principali di questa via: la famiglia Dicer, caratterizzata da un attività RNasicaditipoIII,elafamigliaArgonaute(AGO).L analisidellasequenzadelgenoma hapermessol identificazionediunaputativarnasiiii(tvdsrnase)ediduegeniago (TvAgo 1 e 2). Tutti e tre i geni hanno attività trascrizionale, come dimostrato mediante RT PCR. In figura 6 è possibile osservare l organizzazione in domini di TvdsRNAseconfrontataconquellediproteineDicerdiD.melanogastereC.elegans, econladsrnasedie.hystolytica. Figura 6 Comparazione dell organizzazione in domini delle dsrnasi di diversi organismi. Dm: Drososphila melanogaster;ce:caenorhabditiselegans;tv:trichomonasvaginalis;eh:entamoebahystolytica. TvdsRNAse differisce dalle proteine Dicer nell assenza dei domini helicase, PAZ e dsrna binding.dsrnasedie.histolyticamostraun attivitàdicer like,anchesemanca della tipica organizzazione in domini delle proteine Dicer, e il dominio RNaseIII è tipicamente procariotico. Al contrario di EhdsRNase e analogamente alle Dicer, TvdsRNasepossiededuedominiRNaseIIItipicamenteeucarioticiripetutiintandem. LesequenzeaminoacidichediTvAgo 1e 2mostranoinvecelatipicaorganizzazione della famiglia AGO, con un dominio PAZ e uno PIWI (Figura. 7). In particolare la sequenza piwi box, che interagisce con Dicer e lega i sirna, sembra altamente conservata(figura.7). FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.42
48 Figura7OrganizzazioneindominidelleproteineTvAGO 1e 2confrontateconquelladelleproteineAGOdi altriprotozoipatogeni(t.brucei,e.histolytica,giardiaintestinalis) Figura 8 Allinemento delle sequenze dei piwi box di proteine Argonaute di T. vaginalis, T. brucei, E. histolytica,g.intestinalis,d.melanogaster,a.thaliana. StudiinmoltiorganismihannodimostratochediverseRNAelicasisonocoinvoltenei meccanismi di silencing post trascrizionale. In particolare si ritiene che le DEAD/DEAH box helicase siano coinvolte nello srotolamento dei sirna nel RISC. Ad esempioladead boxhelicasearmitageèessenzialeperl assemblaggiodelriscind. melanogster.dall analisidellasequenzadelgenomadit.vaginalissonostatiinoltre FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.43
49 predetti 41 geni DEAD/DEAH box helicase, la cui attività trascrizionale è stata confermatasiatramitericercainunabancaestchetramitert PCR. SintesiedelettroporazionedidsRNAinT.vaginalis Per valutare l eventuale attività di RNAi in T. vaginalis, è stato prodotto, mediante trascrizioneinvitro,undsrnadicirca700bpomologoallaregionecentraledell αactinina. 2,5x10 8 cellule sono state elettroporate con 35 µg di dsrna FITC. Il controllo è rappresentatoda2,5x10 8 celluletrasfettatecondsrnaaspecifico,poly(ic) Pervalutarel efficienzadielettroporazioneun aliquotadicelluletrattatecondsrna FITC e di cellule trattate con poly(ic) sono state osservate in microscopia a fluorescenza.(figura.9) FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.44
50 Figura 9 2,5 x 10 8 cellule sono state elettroporate con 35 µg di dsrna FITC omologo alla regione centrale dell α actinina. Il controllo è rappresentato dallo stesso numero di cellule elettroporate con poly(ic). È possibileosservareinbchelecellulecontrollononemettonoalcuntipodifluorescenzasesottoposteadluce a480nm,mentreindèpossibileosservarelafluorescenzaemessadacelluletransfettatecondsrna FITC. WesternblottingeRT PCR Leproteineestratteda5x10 4 celluletransfettatecondsrna FITCeconpoly(IC)sono state analizzate in Western blot. Sono stati effettuati diversi esperimenti mantenendo le stesse condizioni (numero di cellule, quantità di dsrna FITC, FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.45
51 condizionideiprelievi)mairisultatisonodiscordantifraloro,comesipuòosservare nei due esempi rappresentativi di tutti gli esperimenti. Infatti nell esperimento A (Figura 9A) è possibile osservare una diminuzione della proteina α actinina nelle cellule trattate con dsrna, se confrontata sia con l enzima malico utilizzato come loadingcontrol,siaconl espressionedell α actininanellecelluletrattateconpoly(ic). Mentre nell esperimento B (Figura. 9B) non si osserva alcuna variazione dell espressionedell α actininaconlecelluleelettroporateconpoly(ic). A B Figura 10 5x10 5 cellule sono state separate su gel di acrilammide 8%, elettrotrasferite su nitrocellulosa e incubate con Ā α actinina e Ā enzima malico. Le corsie contrassegnate con K rappresentano le cellule elettroporateconpoly(ic),mentrelecorsietsonolecelluleelettroporatecondsrna FITC.0,2,8sonoleore FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.46
52 trascorse dall elettroporazione. Nella figura A è possibile osservare la completa scomparsa dell α actinina dopo 2 e 8 ore dalla transfezione. La ripetizione dell esperimento non ha evidenziato alcuna variazione tra l espressionedell α actininatralecorsieketcomemostratoinfigurab. OgniqRT PCRèstataeffettuataconiprimersperl α actininaenormalizzatasulgene housekeeping dell enzima malico Per valutare le variazioni RNA messaggeri dell αactinina.idatiottenutisonostatinormalizzatiutilizzandocomegenehousekeeping l enzimamalico. I risultati ottenuti non hanno mostrato una significativa variazione tra cellule di controlloetrattate. Costruzionedivettoriperl espressionedidsrna. Ilvettoreperl espressionedidsrnastemloopèstatocostruitoutilizzandoilvettore ptv94tet neo. A valle del promotore tetraciclina inducibile sono state inserite due sequenzedidnaugualimaorientateinsensooppostoeseparatedaunasequenza spaziatricenoncorrelatacont.vaginalis. La selezione e l induzione, rispettivamente ad opera di gentamicina e tetraciclina permetteranno l espressione di un dsrna haipin. Attualmente si sta portando a terminel ultimapartedilavoropermettereapuntoilplasmidedefinitivo. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.47
53 4.DISCUSSIONE Gli ultimi 10 anni hanno visto la ricerca biologica arricchirsi di un nuovo campo di studi, da quando sono stati osservati e descritti in diversi eucarioti fenomeni di regolazione post trascrizionale dell espressione genica indotti e guidati da corti duplexdirna:l RNAinterference. Questa scoperta ha portato in dote alla comunità scientifica una tecnologia rivoluzionaria per gli studi di funzione genica, che hanno consentito notevoli passi avanti nella comprensione della biologia degli organismi in cui questa tecnologia è stataapplicataconsuccesso. La relativa rapidità e facilità di esecuzione, ovvero l introduzione di molecole di dsrna omologhe al gene di cui si vuole silenziare l espressione, e la specificità ne fannounatecnicaestremamenteversatileealtamenteinformativa. Perquantoriguardaiprotozoipatogeniperl uomo,sièappenainiziatoascoprirele potenzialità dell applicazione di questa tecnologia. Difatti, solo per T. brucei l RNAi vieneormaiutilizzataroutinariamenteperstudidifunzionegenicacheprevedonoil silenziamentopost trascrizionaledell espressionegenica.recentistudi,siafunzionali chedidatabasemininginseguitoaiprogettidisequenziamentogenomicodidiverse specieprotozarie,stannosuggerendol esistenzadiunapathwaydirnaifunzionalein microorganismicomet.gondii,e.histolytica,g.intestinalis. Tra i microorganismi di cui è stato recentemente effettuato il sequenziamento del genoma,c èt.vaginalis.ilt.vaginalisgenomeproject,acuihapartecipatoancheil nostrogruppodiricerca,hafornitonuoveprospettiveperstudiarelabiologiadiun microorganismo, la cui importanza a livello di salute pubblica continua a essere ignorata,nonostantel elevatonumerodicasiditricomoniasichevengonoriscontrati ogniannointuttoilmondo. ScopodellavorosvoltoduranteilCorsodiDottoratoèstatoquellodiricercarenella sequenza del genoma di T. vaginalis geni omologhi a quelli che costituiscono i passaggi chiave della via di RNAi negli eucarioti, tentare una preliminare FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.48
54 caratterizzazione funzionale di un ipotetico silenziamento genico dsrna indotto, e sviluppare un efficiente sistema di espressione di dsrna in questo protozoo, che potesseconsentirediaggirareiproblemitipicamenteincontratinell introduzionedi dsrnasinteticiperottenereungenesilencing.iduepassaggichiavedelpathwaydi RNAi sono la produzione di sirna, mediata dalla RNasi di tipo III Dicer, e l appaiamento degli sirna con il mrna omologo, che porta alla degradazione sequenza specifica di quest ultimo, mediati dal RISC, il cui core catalitico è rappresentato da proteine della famiglia Argonaute (AGO). L analisi della sequenza delgenomahaportatoallaricostruzionedelbackbonegeneticodiunaviadirnaiin T. vaginalis. In particolare, è stata identificata una Dicer like protein (TvDicer), due Ago like proteins e un corredo di 41 putative DEAD/DEAH RNA helicases. Proteine appartenentiaquestaclassesonostatevisteavereunruolochiavenellosvolgimento degli sirna e nell assemblaggio del RISC, in altri organismi come D. melanogaster. Mentre le due putative Argonaute(TvAgo 1 e 2) mostrano la tipica organizzazione delle proteine appartenenti a questa famiglia, con un dominio PAZ e un dominio PIWI,laTvDicer likeproteinmostraun organizzazionemenocomplessarispettoalle Dicer dei metazoi. Difatti, manca dei domini dsrna binding, PAZ e RNA helicase, mentrepresentaduetipicidominirnaseiiiripetutiintandem.ciòpotrebberiflettere l origine evolutivamente antica di T. vaginalis e della sua putativa RNAi pathway; si potrebbe difatti ipotizzare che le RNasiIII coinvolte nell RNAi si siano, nel corso dell evoluzione, arricchite di altri domini funzionali aggiuntivi, sino ad arrivare all assettodelledicer.e dasottolinearecomeancheladicer likedit.brucei,dicuiè stata dimostrata l attività di produzione di sirna a partire da lunghi dsrna, sia organizzata in due domini RNasiIII in tandem, analogamente a TvDicer. E' interessantenotarecomet.vaginalispossaessereinfettatodadiversivirusadsrna (T.vaginalisvirus TVV) 98.Ciòpotrebbeessereun'indicazionedicomeilmeccanismo dirnainonsiaattivoint.vaginalis,echel'ipoteticomacchinariodigenesilencing manchi di un qualche componente fondamentale. In alternativa potrebbe essere ipotizzato che TVV ha evoluto delle strategie di evasione per aggirare l'attività antiviraledell'rnai.infattimoltivirussiaanimalichevegetalicodificanoperproteine FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.49
55 cheinibisconol'rnai,sequestrandosiaidsrnacheglisirna,quindiinibendol'azione di Dicer e del RISC 99. L'identificazione di un gene Dicer like, 2 geni AGO e 41 DEAD/DEAH boxelicasisonounaforteindicazionedellapresenzadiunaviadirnai in T. vaginalis, o quantomeno di un sofisticato macchinario di processamento del dsrna.gliesempidiknock outgenicoint.vaginalissonorarielimitatiaunoscarso numero di geni (16), mostrandosi uno strumento limitato per gli studi di funzione genicainquestomicroorganismo. Se tutte queste proteine predette sulla base di analisi bioinformatiche siano effettivamente coinvolte in un ipotetico fenomeno di RNAi in T. vaginalis, deve essereconfermatosperimentalmenteconstudifunzionali. LasecondafasedellavorosvoltoduranteilCorsodiDottoratoèstatoimprontatoal tentativodidimostrarefunzionalmentel esistenzadiunfenomenodisilenziamento genico post trascrizionale specificamente indotto da dsrna. La strategia sperimentaleseguitaharicalcatoquellapresenteinletteraturapert.brucei,ovvero l introduzione di lunghi dsrna sintetici (700 bp) in T. vaginalis. Il gene target presceltoperquestostudioèstatal α actinina,unaactin bindingproteinstudiatain dettaglioinannipassatineinostrilaboratori.oltreapossederetools,qualianticorpi specifici, che consentono il monitoraggio dell espressione di questo gene, il suo coinvolgimento in fenomeni di transizione morfologica legati alla virulenza lo rendono un bersaglio interessante, il cui fenotipo knockdown potrebbe essere facilmente monitorabile e di sicuro interesse. Un primo gruppo di esperimenti ha dato risultati incoraggianti, ovvero è stata osservata una netta downregolazione dell α actininaseriferitaall enzimamalicodicontrolloeacelluledit.vaginalisincui veniva introdotto un dsrna aspecifico. Successivamente, è stato impossibile riprodurre i dati ottenuti: l espressione del gene target non variava in seguito all introduzionedidsrnaomologo.dasottolineare,inoltre,l estremavariabilitànella vitalità delle cellule protozoarie in seguito all elettroporazione. Nonostante la costanza delle condizioni sperimentali usate, la vitalità osservata variava enormementedaesperimentoaesperimento,rendendodifficoltosaepocoaffidabile un interpretazionecoerentedeidati. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.50
56 Lamancatariproducibilitàdeidatiottenutiinunprimomomento,lavariabilitàdella vitalità cellulare post elettroporazione ci ha indotto ad avanzare diverse ipotesi di naturaprettamentespeculativa. 1. T. vaginalis è RNAi negativo. La prima conclusione che si può trarre è che il macchinariodirnaidit.vaginalispredettoconl analisidellasequenzadelgenoma nonsiafunzionale,echeigeniidentificatiabbianofunzionidiversedalgenesilencing. L apparenteknockdowndell α actininaottenutoinunprimotempopotrebbeessere unartefattoequindinonriproducibile. 2. Diluizione delsilenziamento:unapossibileinterpretazionedeidaticheindicano l assenzadiuneffettodiknockdown,potrebbeessereunamancatarivelazionediun possibileeffettodiknockdown.difatti,basticonsiderareche: l efficienzaditransfezionedeldsrnanonèmaistatadel100%(intornoall 80%) l efficienza di downregolazione dell espressione genica mediata da RNAi ha una variabilitànotevole,epuòesserebassafinoancheal40%. T. vaginalis replica in vitro ogni 6 ore, cosa che porta quindi ogni 6 ore a un dimezzamentodiunipoteticogenesilencing Ciò considerato, si potrebbe ipotizzare che un eventuale diminuzione dell espressionedell α actininanonèstatarivelataperchétroppoesigua,acausadei limitidelsistemasperimentaleadottato. 3. Il fenotipo α actinina knock down potrebbe essere se non letale quantomeno svantaggiato rispetto al wild type, e potrebbe subire quindi una selezione negativa rispetto alle cellule non trasfettate, o molto semplicemente avere un tasso di replicazione inferiore rispetto a queste ultime. Anche in questo caso un ipotetico effetto knockdown non sarebbe rilevabile, portando cosi ad una sottostima dell effettodisilencing. Inconclusione,ilsistemasperimentalerappresentatodall introduzioneincelluledi.t vaginalis di dsrna omologo all α actinina non rappresenta il modello di studio ottimale per caratterizzare una possibile attività di gene silencing. Si è quindi reso FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.51
57 necessarioricercareunanuovastrategiadiapprocciocheconsentissediaggiraretutti gliinconvenientisopracitati. Laterzafasedellavorosvolto,ancorainprogress,sièfocalizzatasullacostruzionedi un sistema plasmidico di espressione inducibile di dsrna. Sulla base di un sistema inducibile di espressione di proteine eterologhe in T. vaginalis, è stato costruito un vettoreplasmidicocheconsentalasintesiinvivodidsrna.e statoclonatoeposto sotto il controllo del sistema inducibile Tet un inserto di DNA che codifica per un lungo RNA dalla struttura stem loop, che verrà presumibilmente riconosciuto dalla putativamachinerydell RNAidiT.vaginalis.Essendoilplasmideselezionabile,cisarà la possibilità di isolare cloni stabili di T. vaginalis che in condizioni di induzione esprimerannodsrnasottoilcontrollodiunpromotoreforte. Ciò consentirà di aggirare gli inconvenienti incontrati finora nei tentativi di caratterizzazionefunzionalediun ipoteticarnaiint.vaginalis. Inoltre, la dimostrazione di una via funzionale di RNAi in un protozoo filogeneticamente antico come T. vaginalis potrebbe gettare nuova luce sulla comparsa di questo meccanismo negli eucarioti. Inoltre, la dimostrazione e la caratterizzazionedell'rnaiint.vaginalispotràessereconsideratalabasedipartenza per lo sviluppo di nuove strategie di intervento contro le malattie di origine protozoaria. L'RNAi viene attualmente largamente sfruttata come innovativo approccioditerapiagenicapertrattareimportantimalattieumanecomeitumorioi disordini neurodegenerativi. L'RNAi potrebbe essere considerata una potenziale e importantealternativaalleclassicheterapiefarmacologicheantiprotozoarie.infattiil continuoaumentodellacircolazionediceppidit.vaginalismetronidazolo resistenti rendelaricercadinuoviapprocciterapeuticiunaimportanteesigenza,considerando anche che limitare la diffusione della tricomoniasi potrebbe significare limitare la diffusionedihiv,soprattuttoneipaesiinviadisviluppo. FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.52
58 Bibliografia 1 DonnéA.(1836)Animaliculesobservédanslesmatièrespurulentesetleproduitdessécrétionsdesorganes génitauxdel hommeetdelafemme.crsciparis3: HonigbergB.M.,KingV.M.(1964)StructureofTrichomonasvaginalisDonné.JParassitol50: HonigbergB.M.,BrugerolleG.(1990)Structurepp.5 35In:Trichomonadsparasiticinhumans.Ed.Springer Verlag,NewYorkUSA. 4 MatternC.T.F.,HonigbergB.M.,DanielW.A.(1973)Finestructuralchangesassociatedwithpseudocyst formationintrichomitusbatrachorum.jprotozool20: WartonA.,HonigbergB.M.(1979)StructureofTrichomonasasrevealedbyscannincelectronmicroscopy.J Protozool26: MullerM.(1993)Thehydrogenosome.JGenMicrobiol139: LindmarkD.G.,MullerM.(1974)Hydrogenosome,acytoplasmaticorganelleoftheanaerobicflagellate Trichomonasfoetusanditsroleinpyruvatemetabolism.JBiolChem248: LindmarkD.G.,MullerM.,ShioH.(1975)HydrogenosomeinTrichomonasvaginalis.JParasitol61: MullerM(1990)BiochemistryofTrichomonasvaginalisp.53 83In:Trichomonasparasiticinhumans. Ed.Springer Verlag,NewYorkUSA. 10 TerKuileBH(1995)AdaptationofthecarbonmetabolismofTrichomonasvaginalistothenatureand availabilityofthecarbonsource.microbiology140: MackS.R.,MullerM.(1980)EndproductsofcarbohydratemetabolisminTrichomonasvaginalis.Comp. Biochem.Physiol.67: WorldHealthOrganization(WHO).Globalprevalenceandincidenceofselectedcurablesexually transmitteddiseases:overviewandestimates.geneva:who, WorldHealtorganization(2001)Trichomoniasisp InGlobalprevalenceandincidenceofselected curablesexuallytransmittedinfections,.worldhealthorganization,geneva,switzerland. 14 Su LinKE(1982)AntibodytoTrichomonasvaginalisinhumancervicovaginalsecretions.Infect.Immun. 37: ReinMF(1990)Clinicalmanifestationofurogenitaltrichomoniasisinwomen.In:Trichmonadsparasiticin humans.ed.springer Verlag,NewYorkUSA 16 KriegerJN(1981)Urologicaspectsoftrichomoniasis.Invest.Urol.18: LehkerMW,AldereteJF(1992)IronregulatesgrowthofTrichomonasvaginalisandtheexpressionof immunogenictrichomonadproteins.mol.microbiol.6: FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.53
59 18 Kohler,R.(1994)LordsoftheFly:DrosophilaGeneticsandtheExperimentalLife.UniversityofChicago Press,Chicago. 19 Izant,J.G.andWeintraub,H.(1984)Inhibitionofthymidinekinasegeneexpressionbyanti senserna:a molecularapproachtogeneticanalysis.cell36, Rosenberg,U.B.,Preiss,A.,Seifert,E.,Jackle,H.,andKnipple,D.C.(1985)Productionofphenocopiesby KruppelantisenseRNAinjectionintoDrosophilaembryos.Nature313, Harland,R.andWeintraub,H.(1985)TranslationofmRNAinjectedintoXenopusoocytesisspecifically inhibitedbyantisenserna.j.cellbiol.101, Melton,D.A.(1985)Injectedanti sensernasspecificallyblockmessengerrnatranslationinvivo.proc. Natl.Acad.Sci.USA82, Fire,A.,Albertson,D.,Harrison,S.W.,andMoerman,D.G.(1991)ProductionofantisenseRNAleadsto effectiveandspecificinhibitionofgeneexpressioninc.elegansmuscle.development113, Guo,S.andKemphues,K.J.(1995)par 1,agenerequiredforestablishingpolarityinC.elegansembryos, encodesaputativeser/thrkinasethatisasymmetricallydistributed.cell81, Rocheleau,C.E.,Downs,W.D.,Lin,R.,Wittmann,C.,Bei,Y.,Cha,Y.H.,Ali,M.,Priess,J.R.,andMello,C.C. (1997)WntsignalingandanAPC relatedgenespecifyendoderminearlyc.elegansembryos.cell90, Fire,A.,Xu,S.,Montgomery,M.K.,Kostas,S.A.,Driver,S.E.,andMello,C.C.(1998)Potentandspecific geneticinterferencebydouble strandedrnaincaenorhabditiselegans.nature391, Montgomery,M.K.,Xu,S.,andFire,A.(1998)RNAasatargetofdoublestrandedRNA mediatedgenetic interferenceincaenorhabditiselegans.proc.natl.acad.sci.usa95,15,502 15, Napoli,C.,Lemieux,C.,andJorgensen,R.(1990)Introductionofachimericchalconesynthasegeneinto petuniaresultsinreversibleco suppressionofhomologousgenesintrans.plantcell2, Romano,N.andMacino,G.(1992)Quelling:transientinactivationofgeneexpressioninNeurosporacrassa bytransformationwithhomologoussequences.mol.microbiol.6, Cogoni,C.,Irelan,J.T.,Schumacher,M.,Schmidhauser,T.J.,Selker,E.U.,andMacino,G.(1996)Transgene silencingoftheal 1geneinvegetativecellsofNeurosporaismediatedbyacytoplasmiceffectoranddoesnot dependondna DNAinteractionsorDNAmethylation.EMBOJ.15, Matzke,M.A.andMatzke,A.(1995)Howandwhydoplantsinactivatehomologous(trans)genes?Plant Physiol.107, Montgomery,M.K.andFire,A.(1998)Double strandedrnaasamediatorinsequence specificgenetic silencingandco suppression.trendsgenet.14, MarcinNowotnyandWeiYang(2009)StructuralandfunctionalmodulesinRNAinterference.Current OpinioninStructuralBiology19: FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.54
60 34 Ambros,V.,Lee,R.C.,Lavanway,A.,Williams,P.T.andJewell,D.(2003b).microRNAsandothertiny endogenousrnasinc.elegans.currentbiology,13, D.M.Dykxhoorn,C.D.NovinaandP.A.Sharp.(2003)Killingthemessenger:shortRNAsthatsilencegene expression.naturereviewsvol.4: Zamore,P.D.,Tuschl,T.,Sharp,P.A.&Bartel,D.P.RNAi:double strandedrnadirectstheatpdependent cleavageofmrnaat21to23nucleotideintervals.cell101,25 33(2000). 37 Elbashir,S.M.,Martinez,J.,Patkaniowska,A.,Lendeckel,W.&Tuschl,T.FunctionalanatomyofsiRNAsfor mediatingefficientrnaiindrosophilamelanogasterembryolysate.emboj.20, (2001) Filippov,V.,Solovyev,V.,Filippova,M.&Gill,S.S.(2000).AnoveltypeofRNaseIIIfamilyproteinsin eukaryotes.gene245, Bernstein,E.,Caudy,A.A.,Hammond,S.M.&Hannon,G.J.(2001).Roleforabidentateribonucleaseinthe initiationstepofrnainterference.nature409, HannonJ.Gregory.(2002).Nature418, J.Macrae,F.Li,K.Zhou,W.Z.Cande,AndJ.A.Doudn.2006.StructureofDicerandMechanistic ImplicationsforRNAi.ColdSpringHarborSymposiaonQuantitativeBiology,VolumeLXXI: S.Bouasker,M.J.Simard.(2009)TracingArgonautebinding.NatureVol.461: Allshire,R.2002.Molecularbiology.RNAiandheterochromatin ahushed upaffair.science297: Reinhart,B.J.,andD.P.Bartel.2002.SmallRNAscorrespondtocentromereheterochromaticrepeats. Science297: Volpe,T.A.,C.Kidner,I.M.Hall,G.Teng,S.L.S.Grewal,andR.A.Martienssen.2003.Regulationof heterochromaticsilencingandhistoneh3lysine 9methylationbyRNAi.Science297: Dernburg,A.F.,andG.H.Karpen.2002.AchromosomeRNAissance.Cell111: Jackson,J.P.,A.M.Lindroth,X.Cao,andS.E.Jacobsen.2002.ControlofCpNpGDNAmethylationbythe KRYPTONITEhistoneH3methyltransferase.Nature416: Tamaru,H.,andE.U.Selker.2001.AhistoneH3methyltransferasecontrolsDNAmethylationin Neurosporacrassa.Nature414: Jiang,M.andMilner,J.(2002)SelectivesilencingofviralgeneexpressioninHPV positivehumancervical carcinomacellstreatedwithsirna,aprimerofrnainterference.oncogene21, Shlomai,A.andShaul,Y.(2003)InhibitionofhepatitisBvirusexpressionandreplicationbyRNA interference.hepatology37, Kapadia,S.B.,Brideau Andersen,A.,andChisari,F.V.(2003)InterferenceofhepatitisCvirusRNA replicationbyshortinterferingrnas.proc.natl.acad.sci.usa100, FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.55
61 52 Yamamoto,T.,Omoto,S.,Mizuguchi,M.,Mizukami,H.,Okuyama,H.,Okada,N.,Saksena,N.K.,Brisibe,E. A.,Otake,K.,andFuji,Y.R.(2002)Double strandednefrnainterfereswithhumanimmunodeficiencyvirus type1replication.microbiol.immunol.46, Williams,N.S.,Gaynor,R.B.,Scoggin,S.,Verma,U.,Gokaslan,T.,Simmang,C.,Fleming,J.,Tavana,D., Frenkel,E.,andBecerra,C.(2003)Identificationandvalidationofgenesinvolvedinthepathogenesisof colorectalcancerusingcdnamicroarraysandrnainterference.clin.cancerres.9, NgoH,TschudiC,GullK,etal.Double strandedrnainducesmrnadegradationintrypanosomabrucei. ProcNatlAcadSciUSA1998;95: NgoH,TschudiC,GullK,etal.Double strandedrnainducesmrnadegradationintrypanosomabrucei. ProcNatlAcadSciUSA1998;95: ShiH,TschudiC,UlluE.AnunusualDicer like1proteinfuelsthernainterferencepathwayintrypanosoma brucei.rna2006;12: ShiH,UlluE,TschudiC.FunctionoftheTrypanosomeArgonaute1proteininRNAinterferencerequiresthe N terminalrggdomainandarginine735inthepiwidomain.jbiolchem2004;279: ShiH,DjikengA,TschudiC,etal.ArgonauteproteinintheearlydivergenteukaryoteTrypanosomabrucei: controlofsmallinterferingrnaaccumulationandretroposontranscriptabundance.molcellbiol 2004;24: Durand DubiefM,BastinP.TbAGO1,anargonauteproteinrequiredforRNAinterference,isinvolvedin mitosisandchromosomesegregationintrypanosomabrucei.bmcbiol2003;1:2 60 PeacockCS,SeegerK,HarrisD,etal.ComparativegenomicanalysisofthreeLeishmaniaspeciesthatcause diversehumandisease.natgenet2007;39: UlluE,TschudiC,ChakrabortyT.RNAinterferenceinprotozoanparasites.CellMicrobiol2004;6: CeruttiH,Casas MollanoJA.OntheoriginandfunctionsofRNAmediatedsilencing:fromprotiststoman. CurrGenet2006;50: MacraeIJ,ZhouK,LiF,etal.Structuralbasisfordouble strandedrnaprocessingbydicer.science 2006;311: AbedM,AnkriS.MolecularcharacterizationofEntamoebahistolyticaRNaseIIIandAGO2,twoRNA interferencehallmarkproteins.expparasitol2005;110: AlRiyahiA,Al AnoutiF,Al RayesM,etal.SingleargonauteproteinfromToxoplasmagondiiisinvolvedin thedouble strandedrnainducedgenesilencing.intjparasitol2006;36: PeacockCS,SeegerK,HarrisD,etal.ComparativegenomicanalysisofthreeLeishmaniaspeciesthatcause diversehumandisease.natgenet2007;39: InoueN,OtsuK,FerraroDM,etal.Tetracycline regulatedrnainterferenceintrypanosomacongolense. MolBiochemParasitol2002;120: FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.56
62 68 RobinsonKA,BeverleySM.ImprovementsintransfectionefficiencyandtestsofRNAinterference(RNAi) approachesintheprotozoanparasiteleishmania.molbiochemparasitol2003;128: DaRochaWD,OtsuK,TeixeiraSM,etal.TestsofcytoplasmicRNAinterference(RNAi)andconstructionofa tetracycline induciblet7promotersystemintrypanosomacruzi.molbiochemparasitol2004;133: Al AnoutiF,AnanvoranichS.ComparativeanalysisofantisenseRNA,double strandedrna,anddelta ribozyme mediatedgeneregulationintoxoplasmagondii.antisensenucleicaciddrugdev2002;12: Al AnoutiF,TomavoS,ParmleyS,etal.Theexpressionoflactatedehydrogenaseisimportantforthecell cycleoftoxoplasmagondii.jbiolchem2004;279: AnanvoranichS,AlRayesM,AlRiyahiA,etal.RNAsilencingofglycolysispathwayinToxoplasmagondii.J EukaryotMicrobiol2006;53(Suppl.1):S McRobertL,McConkeyGA.RNAinterference(RNAi)inhibitsgrowthofPlasmodiumfalciparum.Mol BiochemParasitol2002;119: MohmmedA,DasaradhiPV,BhatnagarRK,etal.InvivogenesilencinginPlasmodiumberghei amouse malariamodel.biochembiophysrescommun2003;309: RathjenT,NicolC,McConkeyG,etal.AnalysisofshortRNAsinthemalariaparasiteanditsredbloodcell host.febslett2006;580: ShiH,DjikengA,TschudiC,etal.ArgonauteproteinintheearlydivergenteukaryoteTrypanosomabrucei: controlofsmallinterferingrnaaccumulationandretroposontranscriptabundance.molcellbiol 2004;24: JanzenCJ,vanDeursenF,ShiH,etal.Expressionsitesilencingandlifecycleprogressionappearnormalin Argonaute1 deficienttrypanosomabrucei.molbiochemparasitol2006;149: ShiH,ChamondN,TschudiC,etal.SelectionandcharacterizationofRNAinterference deficient trypanosomesimpairedintargetmrnadegradation.eukaryotcell2004;3: El SayedNM,MylerPJ,BartholomeuDC,etal.ThegenomesequenceofTrypanosomacruzi,etiologicagent ofchagasdisease.science2005;309: WicksteadB,ErsfeldK,GullK.Repetitiveelementsingenomesofparasiticprotozoa.MicrobiolMolBiolRev 2003;67: WangAL,WangCC.Discoveryofaspecificdouble strandedrnavirusingiardialamblia.molbiochem Parasitol1986;21: WangAL,WangCC.Thedouble strandedrnaintrichomonasvaginalismayoriginatefromvirus like particles.procnatlacadsciusa1986;83: UlluE,LujanHD,TschudiC.SmallsenseandantisenseRNAsderivedfromatelomericretroposonfamilyin Giardiaintestinalis.EukaryotCell2005;4: FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.57
63 84 MetteMF,AufsatzW,vanderWindenJ,etal.Transcriptionalsilencingandpromotermethylationtriggered bydouble strandedrna.emboj2000;19: WeinbergMS,VilleneuveLM,EhsaniA,etal.TheantisensestrandofsmallinterferingRNAsdirectshistone methylationandtranscriptionalgenesilencinginhumancells.rna2006;12: VolpeTA,KidnerC,HallIM,etal.RegulationofheterochromaticsilencingandhistoneH3lysine 9 methylationbyrnai.science2002;297: WanidworanunC,NagelRL,ShearHL.Antisenseoligonucleotidestargetingmalarialaldolaseinhibitthe asexualerythrocyticstagesofplasmodiumfalciparum.molbiochemparasitol1999;102: BarkerJrRH,MetelevV,RapaportE,etal.InhibitionofPlasmodiumfalciparummalariausingantisense oligodeoxynucleotides.procnatlacadsciusa1996;93: RapaportE,MisiuraK,AgrawalS,etal.Antimalarialactivitiesofoligodeoxynucleotidephosphorothioatesin chloroquine resistantplasmodiumfalciparum.procnatlacadsciusa1992;89: ShiH,TschudiC,UlluE.FunctionalreplacementofTrypanosomabruceiArgonautebythehumanslicer Argonaute2.RNA2006;12: RivasFV,ToliaNH,SongJJ,etal.PurifiedArgonaute2andansiRNAformrecombinanthumanRISC.Nat StructMolBiol2005;12: Silenceofthestrands:RNAinterferenceineukaryoticpathogens.TriciaR.CottrellandTamaraL.Doering. TRENDSinMicrobiologyVol.11No.1January Carlton,J.M.,Hirt,R.P.,Silva,J.C.,Delcher,A.L.,Schatz,M.,Zhao,Q.,Wortman,J.R.,Bidwell,S.L.,Alsmark,U.C., Besteiro,S.etal.(2007)DraftgenomesequenceofthesexuallytransmittedpathogenTrichomonasvaginalis. Science,315, DessiD,DeloguG,EmonteE,CataniaMR,FioriPL,RappelliP(2005)Long termsurvivalandintracellular replicationofmycoplasmahominisintrichomonasvaginaliscells:potentialroletheprotozoonin transmittingbacterialinfection.infectimmun.73: RappelliP,AddisMF,CartaF,FioriPL(1998)MycoplasmahominisparasitismofTrichomonasvaginalis. Lancet352: VirusinTrichomonas anultrastructuralstudymarlenebenchimola,sandrapachecomonteirob,t. H. Changc,JohnF.Alderete.ParasitologyInternational51(2002) DianaOrtiz,PatriciaJ.Johnson.(2003).Tetracycline induciblegeneexpressionintrichomonasvaginalis. Molecular&BiochemicalParasitology128(2003) A.Khoshnan,J.F.Alderete,(1993).MultipledoublestrandedRNAsegmentsareassociatedwithvirus particleinfectingtrichomonasvaginalis.jvirol67, O.Voinnet.(2005)InductionandsuppressionofRNAsilencing:insightsfromviralinfections.Nat.Rev. Genet.6, FedericaRiu IdentificazioneecaratterizzazionediunaputativapathwaydiRNAinterferencenel protozooatrasmissionesessualetrichomonasvaginalis TesidiDottoratoinScienzeBiomolecolari ebiotecnologiche UniversitàdegliStudidiSassari.58
Come funzionano gli oligo Antisenso? RNA WORLD. mrna. Regolare l espressione genica tramite molecole di RNA. Come funzionano gli oligo antisenso?
 RNA WORLD RNA Come funzionano gli oligo Antisenso? mrna Non coding RNA AAAAAAA rrna trna snrna snorna RNA Antisenso sirna Arresto della traduzione Proteina incompleta o nessuna sintesi MECCANISMO PASSIVO
RNA WORLD RNA Come funzionano gli oligo Antisenso? mrna Non coding RNA AAAAAAA rrna trna snrna snorna RNA Antisenso sirna Arresto della traduzione Proteina incompleta o nessuna sintesi MECCANISMO PASSIVO
RNA non codificanti ed RNA regolatori
 RNA non codificanti ed RNA regolatori RNA non codificanti ed RNA regolatori Piccoli RNA non codificanti RNA regolatore microrna RNAi e sirna Piccoli RNA non codificanti Gli RNA non codificanti (ncrna)
RNA non codificanti ed RNA regolatori RNA non codificanti ed RNA regolatori Piccoli RNA non codificanti RNA regolatore microrna RNAi e sirna Piccoli RNA non codificanti Gli RNA non codificanti (ncrna)
Controllo post-trascrizionale dell espressione genica
 Controllo post-trascrizionale dell espressione genica Livelli di controllo dell espressione genica Rivisitazione del concetto di gene Per gli organismi eucariotici più evoluti il dogma un gene = una proteina
Controllo post-trascrizionale dell espressione genica Livelli di controllo dell espressione genica Rivisitazione del concetto di gene Per gli organismi eucariotici più evoluti il dogma un gene = una proteina
RNA interference. La tecnologia dell RNAi è basata su un processo di inattivazione genica post-trascrizionale, altamente specifico
 RNA interference Tecnica che permette di interferire con l espressione di alcuni geni mediante la trasfezione di piccoli frammenti di RNA a doppio filamento in grado di antagonizzare l RNA messaggero corrispondente.
RNA interference Tecnica che permette di interferire con l espressione di alcuni geni mediante la trasfezione di piccoli frammenti di RNA a doppio filamento in grado di antagonizzare l RNA messaggero corrispondente.
Il nobel per l interferenza dell RNA
 Il nobel per l interferenza dell RNA Andrew Fire e Craig Mello, i due vincitori del Premio Nobel 2006 per la Medicina e la Fisiologia. I due biologi molecolari vengono premiati per aver scoperto uno dei
Il nobel per l interferenza dell RNA Andrew Fire e Craig Mello, i due vincitori del Premio Nobel 2006 per la Medicina e la Fisiologia. I due biologi molecolari vengono premiati per aver scoperto uno dei
Regolazione dell espressione genica imputabile esclusivamente a regolatori di natura proteica?
 Regolazione dell espressione genica imputabile esclusivamente a regolatori di natura proteica? 18 1 Watson-Baker-Bell-Gann-Levine-Losick Biologia molecolare del gene Gli RNA regolatori Già gli studi di
Regolazione dell espressione genica imputabile esclusivamente a regolatori di natura proteica? 18 1 Watson-Baker-Bell-Gann-Levine-Losick Biologia molecolare del gene Gli RNA regolatori Già gli studi di
Dal DNA all RNA. La trascrizione nei procarioti e negli eucarioti
 Dal DNA all RNA La trascrizione nei procarioti e negli eucarioti DOGMA CENTRALE DELLA BIOLOGIA MOLECOLARE Gene Regione di DNA che porta l informazione (= che CODIFICA) per una catena polipeptidica o per
Dal DNA all RNA La trascrizione nei procarioti e negli eucarioti DOGMA CENTRALE DELLA BIOLOGIA MOLECOLARE Gene Regione di DNA che porta l informazione (= che CODIFICA) per una catena polipeptidica o per
sirna Strategie di silenziamento genico post-trascrizionale
 sirna Strategie di silenziamento genico post-trascrizionale RNAi Introduction RNAi = RNA interference Il termine è utilizzato per descrivere l interferenza dell RNA come meccanismo naturale e anche come
sirna Strategie di silenziamento genico post-trascrizionale RNAi Introduction RNAi = RNA interference Il termine è utilizzato per descrivere l interferenza dell RNA come meccanismo naturale e anche come
Il genoma dinamico: gli elementi trasponibili
 Il genoma dinamico: gli elementi trasponibili Anni trenta: studi sul mais ribaltano la visione classica secondo cui i geni si trovano solo in loci fissi sul cromosoma principale Esistono elementi genetici
Il genoma dinamico: gli elementi trasponibili Anni trenta: studi sul mais ribaltano la visione classica secondo cui i geni si trovano solo in loci fissi sul cromosoma principale Esistono elementi genetici
Struttura e funzione dei geni. Paolo Edomi - Genetica
 Struttura e funzione dei geni 1 Il DNA è il materiale genetico La molecola di DNA conserva l informazione genetica: topi iniettati con solo DNA di batteri virulenti muoiono 2 Proprietà del DNA Il DNA presenta
Struttura e funzione dei geni 1 Il DNA è il materiale genetico La molecola di DNA conserva l informazione genetica: topi iniettati con solo DNA di batteri virulenti muoiono 2 Proprietà del DNA Il DNA presenta
DNA non codificante ncdna
 DNA non codificante ncdna Teorie sul ruolo genetico RNAi e mirna Liberamente tratto dalla tesina del Dr. Emiliano Mancini ncdna Per ncdna si intende il DNA intronico, intergenico e altre zone non codificanti
DNA non codificante ncdna Teorie sul ruolo genetico RNAi e mirna Liberamente tratto dalla tesina del Dr. Emiliano Mancini ncdna Per ncdna si intende il DNA intronico, intergenico e altre zone non codificanti
LA GENETICA: DNA e RNA LA GENETICA. DNA e RNA. Prof. Daniele Verri
 LA GENETICA DNA e RNA Prof. Daniele Verri L'acido desossiribonucleico o deossiribonucleico (DNA) è un acido nucleico che contiene le informazioni necessarie per la formazione di RNA e proteine. LA GENETICA:
LA GENETICA DNA e RNA Prof. Daniele Verri L'acido desossiribonucleico o deossiribonucleico (DNA) è un acido nucleico che contiene le informazioni necessarie per la formazione di RNA e proteine. LA GENETICA:
SINTESI DELL RNA. Replicazione. Trascrizione. Traduzione
 SINTESI DELL RNA Replicazione Trascrizione Traduzione L RNA ha origine da informazioni contenute nel DNA La TRASCRIZIONE permette la conversione di una porzione di DNA in una molecola di RNA con una sequenza
SINTESI DELL RNA Replicazione Trascrizione Traduzione L RNA ha origine da informazioni contenute nel DNA La TRASCRIZIONE permette la conversione di una porzione di DNA in una molecola di RNA con una sequenza
A che servono le piante transgeniche?
 A che servono le piante transgeniche? Ricerca di base Applicazioni Ricerca di base Favorire la comprensione e lo studio del ruolo fisiologico di molti geni Effetti correlati alla sovraespressione o alla
A che servono le piante transgeniche? Ricerca di base Applicazioni Ricerca di base Favorire la comprensione e lo studio del ruolo fisiologico di molti geni Effetti correlati alla sovraespressione o alla
Indice dell'opera. Prefazione. Capitolo 1 Introduzione alla genetica Genetica classica e moderna Genetisti e ricerca genetica Sommario
 Indice dell'opera Prefazione Capitolo 1 Introduzione alla genetica Genetica classica e moderna Genetisti e ricerca genetica Capitolo 2 DNA: il materiale genetico La ricerca del materiale genetico La composizione
Indice dell'opera Prefazione Capitolo 1 Introduzione alla genetica Genetica classica e moderna Genetisti e ricerca genetica Capitolo 2 DNA: il materiale genetico La ricerca del materiale genetico La composizione
Regolazione dell espressione genica EUCARIOTI
 Regolazione dell espressione genica EUCARIOTI Regolazione della espressione genica Molte proteine sono comuni a tutte le cellule RNA polimerasi, proteine ribosomali, enzimi che regolano il metabolismo,
Regolazione dell espressione genica EUCARIOTI Regolazione della espressione genica Molte proteine sono comuni a tutte le cellule RNA polimerasi, proteine ribosomali, enzimi che regolano il metabolismo,
Il metabolismo dell RNA. Prof. Savino; dispense di Biologia Molecolare, Corso di Laurea in Biotecnologie
 Il metabolismo dell RNA I vari tipi di RNA Il filamento di DNA che dirige la sintesi dello mrna è chiamato filamento stampo o filamento antisenso. L altro filamento che ha sequenza identica a quella dello
Il metabolismo dell RNA I vari tipi di RNA Il filamento di DNA che dirige la sintesi dello mrna è chiamato filamento stampo o filamento antisenso. L altro filamento che ha sequenza identica a quella dello
La regolazione genica nei eucarioti
 La regolazione genica nei eucarioti Lic. Scientifico A. Meucci Aprilia Prof. Rolando Neri Differenziamento negli eucarioti pluricellulari Negli eucarioti le cellule specializzate dei vari tessuti contengono
La regolazione genica nei eucarioti Lic. Scientifico A. Meucci Aprilia Prof. Rolando Neri Differenziamento negli eucarioti pluricellulari Negli eucarioti le cellule specializzate dei vari tessuti contengono
Macromolecole Biologiche. I domini (III)
 I domini (III) Domini α/β La cross over connection è l unità costitutiva su cui si basa la topologia di 3 tipi di domini α/β osservati nelle proteine: - α/β barrel - motivi ricchi di Leu (fold a ferro
I domini (III) Domini α/β La cross over connection è l unità costitutiva su cui si basa la topologia di 3 tipi di domini α/β osservati nelle proteine: - α/β barrel - motivi ricchi di Leu (fold a ferro
REGOLAZIONE DELL'ESPRESSIONE GENICA
 REGOLAZIONE DELL'ESPRESSIONE GENICA Con ESPRESSIONE GENICA si intende quella serie di eventi che dall'attivazione della trascrizione di un gene, conducono alla produzione della proteina corrispondente.
REGOLAZIONE DELL'ESPRESSIONE GENICA Con ESPRESSIONE GENICA si intende quella serie di eventi che dall'attivazione della trascrizione di un gene, conducono alla produzione della proteina corrispondente.
Diapositiva 3: CASPASI IAP inibitor of apoptosis
 Diapositiva 1: Diapositiva 2: Nella presente presentazione vengono trattate le correlazioni scoperte e studiate tra la tecnica dei microrna e l apoptosi. Innanzitutto l apoptosi è il processo che porta
Diapositiva 1: Diapositiva 2: Nella presente presentazione vengono trattate le correlazioni scoperte e studiate tra la tecnica dei microrna e l apoptosi. Innanzitutto l apoptosi è il processo che porta
GENOMA. c varia da pochi kb nei virus a milioni di kb in piante e animali
 GENOMA Insieme del materiale genetico presente in una cellula (DNA nucleare, plastidiale e mitocondriale) Contiene tutte le informazioni necessarie per consentire la vita alla cellula e all individuo Nei
GENOMA Insieme del materiale genetico presente in una cellula (DNA nucleare, plastidiale e mitocondriale) Contiene tutte le informazioni necessarie per consentire la vita alla cellula e all individuo Nei
Dal DNA alle proteine: La trascrizione e la traduzione
 Dal DNA alle proteine: La trascrizione e la traduzione DNA RNA Trascrizione RNA PROTEINE Traduzione Dove avvengono? GLI EUCARIOTI I PROCARIOTI Cambell, Reece Biologia ZANICHELLI Trascrizione Sintesi di
Dal DNA alle proteine: La trascrizione e la traduzione DNA RNA Trascrizione RNA PROTEINE Traduzione Dove avvengono? GLI EUCARIOTI I PROCARIOTI Cambell, Reece Biologia ZANICHELLI Trascrizione Sintesi di
LE MOLECOLE INFORMAZIONALI. Lezioni d'autore Treccani
 LE MOLECOLE INFORMAZIONALI Lezioni d'autore Treccani Introduzione (I) I pionieri della biologia molecolare, scoperta la struttura degli acidi nucleici, pensarono di associare al DNA una sequenza di simboli,
LE MOLECOLE INFORMAZIONALI Lezioni d'autore Treccani Introduzione (I) I pionieri della biologia molecolare, scoperta la struttura degli acidi nucleici, pensarono di associare al DNA una sequenza di simboli,
Piccoli RNA non codificanti RNA regolatore microrna RNAi e sirna
 Piccoli RNA non codificanti RNA regolatore microrna RNAi e sirna Gli RNA non codificanti (ncrna) giocano un ruolo fondamentale nei sistemi biologici complessi, pur non codificando alcuna proteina. Tra
Piccoli RNA non codificanti RNA regolatore microrna RNAi e sirna Gli RNA non codificanti (ncrna) giocano un ruolo fondamentale nei sistemi biologici complessi, pur non codificando alcuna proteina. Tra
Il flusso dell informazione genetica. DNA -->RNA-->Proteine
 Il flusso dell informazione genetica DNA -->RNA-->Proteine Abbiamo visto i principali esperimenti che hanno dimostrato che il DNA è la molecola depositaria dell informazione genetica nella maggior parte
Il flusso dell informazione genetica DNA -->RNA-->Proteine Abbiamo visto i principali esperimenti che hanno dimostrato che il DNA è la molecola depositaria dell informazione genetica nella maggior parte
Figura 1. Rappresentazione della doppia elica di DNA e struttura delle differenti basi.
 Sommario La molecola di DNA è deputata a conservare le informazioni genetiche necessarie per lo sviluppo ed il funzionamento degli organismi viventi. Poiché contiene le istruzioni per la costruzione delle
Sommario La molecola di DNA è deputata a conservare le informazioni genetiche necessarie per lo sviluppo ed il funzionamento degli organismi viventi. Poiché contiene le istruzioni per la costruzione delle
DNA - RNA. Nucleotide = Gruppo Fosforico + Zucchero Pentoso + Base Azotata. Le unità fondamentali costituenti il DNA e l RNA sono i Nucleotidi.
 DNA - RNA Le unità fondamentali costituenti il DNA e l RNA sono i Nucleotidi. Nucleotide = Gruppo Fosforico + Zucchero Pentoso + Base Azotata. Esistono 4 basi azotate per il DNA e 4 per RNA Differenze
DNA - RNA Le unità fondamentali costituenti il DNA e l RNA sono i Nucleotidi. Nucleotide = Gruppo Fosforico + Zucchero Pentoso + Base Azotata. Esistono 4 basi azotate per il DNA e 4 per RNA Differenze
RNA polimerasi operone. L operatore è il tratto
 La regolazione genica nei procarioti Alcune proteine vengono prodotte dalla cellula ad un ritmo relativamente costante e l attività dei geni che codificano queste proteine non è regolata in modo sofisticato.
La regolazione genica nei procarioti Alcune proteine vengono prodotte dalla cellula ad un ritmo relativamente costante e l attività dei geni che codificano queste proteine non è regolata in modo sofisticato.
SUPERAVVOLGIMENTO DEL DNA (ORGANIZZAZIONE TERZIARIA DEL DNA)
 SUPERAVVOLGIMENTO DEL DNA (ORGANIZZAZIONE TERZIARIA DEL DNA) ORGANIZZAZIONE TERZIARIA DEL DNA Il DNA cellulare contiene porzioni geniche e intergeniche, entrambe necessarie per le funzioni vitali della
SUPERAVVOLGIMENTO DEL DNA (ORGANIZZAZIONE TERZIARIA DEL DNA) ORGANIZZAZIONE TERZIARIA DEL DNA Il DNA cellulare contiene porzioni geniche e intergeniche, entrambe necessarie per le funzioni vitali della
Regolazione genica post- trascrizionale
 18. L RNA regolatore contiene materiale protetto da copyright, ad esclusivo uso personale; non è consentita diffusione ed utilizzo di tipo commerciale Regolazione genica post- trascrizionale L espressione
18. L RNA regolatore contiene materiale protetto da copyright, ad esclusivo uso personale; non è consentita diffusione ed utilizzo di tipo commerciale Regolazione genica post- trascrizionale L espressione
www.fisiokinesiterapia.biz TRASCRIZIONE
 www.fisiokinesiterapia.biz TRASCRIZIONE TRASCRIZIONE Processo mediante il quale una sequenza di DNA (un gene) viene copiata in una sequenza di RNA Dalla trascrizione derivano gli mrna, che verranno tradotti
www.fisiokinesiterapia.biz TRASCRIZIONE TRASCRIZIONE Processo mediante il quale una sequenza di DNA (un gene) viene copiata in una sequenza di RNA Dalla trascrizione derivano gli mrna, che verranno tradotti
La traduzione: dall mrna alle proteine
 La traduzione: dall mrna alle proteine Le infezioni batteriche sono una grave causa di malattie e morte in Europa e negli USA. Le infezioni batteriche si curano con antibiotici che colpiscono l espressione
La traduzione: dall mrna alle proteine Le infezioni batteriche sono una grave causa di malattie e morte in Europa e negli USA. Le infezioni batteriche si curano con antibiotici che colpiscono l espressione
La possibilita di conoscere i geni deriva dalla capacita di manipolarli:
 La possibilita di conoscere i geni deriva dalla capacita di manipolarli: -isolare un gene (enzimi di restrizione) -clonaggio (amplificazione) vettori -sequenziamento -funzione Il gene o la sequenza
La possibilita di conoscere i geni deriva dalla capacita di manipolarli: -isolare un gene (enzimi di restrizione) -clonaggio (amplificazione) vettori -sequenziamento -funzione Il gene o la sequenza
SEQUENZIAMENTO DEL DNA
 SEQUENZIAMENTO DEL DNA Il metodo di Sanger per determinare la sequenza del DNA Il metodo manuale La reazione enzimatica Elettroforesi in gel denaturante di poliacrilammide Autoradiografia Il metodo automatico
SEQUENZIAMENTO DEL DNA Il metodo di Sanger per determinare la sequenza del DNA Il metodo manuale La reazione enzimatica Elettroforesi in gel denaturante di poliacrilammide Autoradiografia Il metodo automatico
Regolazione della trascrizione. Operoni catabolici nei procarioti (controllo negativo)
 Regolazione della trascrizione Operoni catabolici nei procarioti (controllo negativo) I geni possono essere accesi e spenti In un organismo pluricellulare adulto, vi sono molti tipi di cellule differenti,
Regolazione della trascrizione Operoni catabolici nei procarioti (controllo negativo) I geni possono essere accesi e spenti In un organismo pluricellulare adulto, vi sono molti tipi di cellule differenti,
TEST BIOLOGIA 1 ANNO ABEI Da inviare a [email protected] entro e non oltre il 6 novembre 2015
 1) I batteri sono organismi: a- bicellulari b- monocellulari c- pluricellulari 2) I virus: a- possono riprodursi solo nell acqua b- possono riprodursi solo sulla superficie di una cellula c- possono riprodursi
1) I batteri sono organismi: a- bicellulari b- monocellulari c- pluricellulari 2) I virus: a- possono riprodursi solo nell acqua b- possono riprodursi solo sulla superficie di una cellula c- possono riprodursi
Biosintesi non ribosomiale di metaboliti peptidici bioattivi
 Biosintesi non ribosomiale di metaboliti peptidici bioattivi Principali bersagli degli antibiotici Gli antibiotici derivano per la maggior parte da composti naturali Strutture di alcuni peptidi bioattivi
Biosintesi non ribosomiale di metaboliti peptidici bioattivi Principali bersagli degli antibiotici Gli antibiotici derivano per la maggior parte da composti naturali Strutture di alcuni peptidi bioattivi
L adattamento dei batteri. Strategie di adattamento
 L adattamento dei batteri Strategie di adattamento mutazione trasferimento genico orizzontale regolazione dell espressione genica regolazione della trascrizione regolazione della traduzione regolazione
L adattamento dei batteri Strategie di adattamento mutazione trasferimento genico orizzontale regolazione dell espressione genica regolazione della trascrizione regolazione della traduzione regolazione
immagine Biologia applicata alla ricerca bio-medica Materiale Didattico Docente: Di Bernardo
 Esperto in processi innovativi di sintesi biomolecolare applicata a tecniche di epigenetica Materiale Didattico Biologia applicata alla ricerca bio-medica immagine Docente: Di Bernardo Per animali transgenici
Esperto in processi innovativi di sintesi biomolecolare applicata a tecniche di epigenetica Materiale Didattico Biologia applicata alla ricerca bio-medica immagine Docente: Di Bernardo Per animali transgenici
RNA interference e sue applicazioni
 RNA interference e sue applicazioni Cosa è l RNA interference Come funziona Funzione biologica nei diversi organismi Come può essere utilizzata per fini applicativi e di genetica funzionale Che cosa è
RNA interference e sue applicazioni Cosa è l RNA interference Come funziona Funzione biologica nei diversi organismi Come può essere utilizzata per fini applicativi e di genetica funzionale Che cosa è
Lo sviluppo del cancro è un processo complesso che coinvolge parecchi cambiamenti nella stessa cellula staminale. Poiché tutte le cellule staminali
 Tumore Cos è il tumore? Il tumore o neoplasia (dal greco neo,, nuovo, e plasìa,, formazione), o cancro se è maligno, è una classe di malattie caratterizzate da una incontrollata riproduzione di alcune
Tumore Cos è il tumore? Il tumore o neoplasia (dal greco neo,, nuovo, e plasìa,, formazione), o cancro se è maligno, è una classe di malattie caratterizzate da una incontrollata riproduzione di alcune
Il termine connettiviti indica un gruppo di malattie reumatiche, caratterizzate dall infiammazione cronica del tessuto connettivo, ossia di quel
 Il termine connettiviti indica un gruppo di malattie reumatiche, caratterizzate dall infiammazione cronica del tessuto connettivo, ossia di quel complesso tessuto con funzione di riempimento, sostegno
Il termine connettiviti indica un gruppo di malattie reumatiche, caratterizzate dall infiammazione cronica del tessuto connettivo, ossia di quel complesso tessuto con funzione di riempimento, sostegno
SAGE: Serial Analysis of Gene Expression
 SAGE: Serial Analysis of Gene Expression L insieme di tutti gli mrna presenti in una cellula si definisce trascrittoma. Ogni trascrittoma ha una composizione complessa, con migliaia di mrna diversi, ciascuno
SAGE: Serial Analysis of Gene Expression L insieme di tutti gli mrna presenti in una cellula si definisce trascrittoma. Ogni trascrittoma ha una composizione complessa, con migliaia di mrna diversi, ciascuno
I marcatori molecolari. Dipartimento di Scienze Agronomiche e Genetica Vegetale Agraria Corso di Genetica Agraria Giovanna Attene
 I marcatori molecolari Dipartimento di Scienze Agronomiche e Genetica Vegetale Agraria Corso di Genetica Agraria Giovanna Attene Marcatori molecolari del DNA I marcatori molecolari sono sequenze di DNA
I marcatori molecolari Dipartimento di Scienze Agronomiche e Genetica Vegetale Agraria Corso di Genetica Agraria Giovanna Attene Marcatori molecolari del DNA I marcatori molecolari sono sequenze di DNA
Protocollo dei saperi imprescindibili
 Protocollo dei saperi imprescindibili Ordine di scuola:professionale DISCIPLINA: Scienze integrate( Scienze della Terra e Biologia) RESPONSABILE: Meri Teti CLASSI SECONDE SEZIONE B INDIRIZZO: Grafico CONOSCENZE/CONTENUTI:
Protocollo dei saperi imprescindibili Ordine di scuola:professionale DISCIPLINA: Scienze integrate( Scienze della Terra e Biologia) RESPONSABILE: Meri Teti CLASSI SECONDE SEZIONE B INDIRIZZO: Grafico CONOSCENZE/CONTENUTI:
PCR. PCR o reazione di polimerizzazione a catena. Amplificazione esponenziale di DNA. Puo amplificare un tratto di DNA per piu di 1 milione di volte
 PCR Prof.ssa Flavia Frabetti PCR o reazione di polimerizzazione a catena Fine anni 80 Amplificazione esponenziale di DNA. Puo amplificare un tratto di DNA per piu di 1 milione di volte Permette di estrarre
PCR Prof.ssa Flavia Frabetti PCR o reazione di polimerizzazione a catena Fine anni 80 Amplificazione esponenziale di DNA. Puo amplificare un tratto di DNA per piu di 1 milione di volte Permette di estrarre
Isolamento e purificazione di DNA e RNA. -Separare gli acidi nucleici da altri componenti cellulari (lipidi e proteine)
 Isolamento e purificazione di DNA e RNA -Rompere la membrana cellulare -Separare gli acidi nucleici da altri componenti cellulari (lipidi e proteine) -Separare gli acidi nucleici tra loro -Rompere la membrana
Isolamento e purificazione di DNA e RNA -Rompere la membrana cellulare -Separare gli acidi nucleici da altri componenti cellulari (lipidi e proteine) -Separare gli acidi nucleici tra loro -Rompere la membrana
I mirna NEI MECCANISMI ANTIVIRALI
 Davide Schiavone Biochimica A.A. 2004-2005 I mirna NEI MECCANISMI ANTIVIRALI I processi di difesa antivirale operati da RNA sfruttano diversi meccanismi che sono raggruppati sotto il nome di RNA silencing.
Davide Schiavone Biochimica A.A. 2004-2005 I mirna NEI MECCANISMI ANTIVIRALI I processi di difesa antivirale operati da RNA sfruttano diversi meccanismi che sono raggruppati sotto il nome di RNA silencing.
Vettori di espressione
 Vettori di espressione Vengono usati per: 1.Generare sonde di RNA 2.Produrre la proteina codificata Per fare questo viene utilizzato un promotore che risiede sul vettore, modificato per ottimizzare l interazione
Vettori di espressione Vengono usati per: 1.Generare sonde di RNA 2.Produrre la proteina codificata Per fare questo viene utilizzato un promotore che risiede sul vettore, modificato per ottimizzare l interazione
Carpire il segreto della vita con l informatica Giosuè Lo Bosco Dipartimento di Matematica e Informatica, Università di Palermo, ITALY.
 Carpire il segreto della vita con l informatica Giosuè Lo Bosco Dipartimento di Matematica e Informatica, Università di Palermo, ITALY. Lezioni Lincee Palermo, 26 Febbraio 2015 Alla base della vita degli
Carpire il segreto della vita con l informatica Giosuè Lo Bosco Dipartimento di Matematica e Informatica, Università di Palermo, ITALY. Lezioni Lincee Palermo, 26 Febbraio 2015 Alla base della vita degli
Scuola Media Piancavallo 2
 LA CELLULA Una caratteristica di quasi tutti gli esseri viventi è quella di possedere una struttura più o meno complessa in cui parti diverse, gli organi, sono adatte a svolgere funzioni specifiche. Il
LA CELLULA Una caratteristica di quasi tutti gli esseri viventi è quella di possedere una struttura più o meno complessa in cui parti diverse, gli organi, sono adatte a svolgere funzioni specifiche. Il
GLUCONEOGENESI. Sintesi (GENESI) di nuove (NEO) molecole di glucosio
 GLUCONEOGENESI Sintesi (GENESI) di nuove (NEO) molecole di glucosio CATABOLISMO ANABOLISMO OSSIDAZIONI Produzione di ATP RIDUZIONI Consumo di ATP La GLUCONEOGENESI è un PROCESSO ANABOLICO La gluconeogenesi
GLUCONEOGENESI Sintesi (GENESI) di nuove (NEO) molecole di glucosio CATABOLISMO ANABOLISMO OSSIDAZIONI Produzione di ATP RIDUZIONI Consumo di ATP La GLUCONEOGENESI è un PROCESSO ANABOLICO La gluconeogenesi
VALORE DELLE MERCI SEQUESTRATE
 La contraffazione in cifre: NUOVA METODOLOGIA PER LA STIMA DEL VALORE DELLE MERCI SEQUESTRATE Roma, Giugno 2013 Giugno 2013-1 Il valore economico dei sequestri In questo Focus si approfondiscono alcune
La contraffazione in cifre: NUOVA METODOLOGIA PER LA STIMA DEL VALORE DELLE MERCI SEQUESTRATE Roma, Giugno 2013 Giugno 2013-1 Il valore economico dei sequestri In questo Focus si approfondiscono alcune
Nei sistemi modello approcci di modificazione genetica che producono o sequenze genetiche alterate o espressione genetica alterata fenotipo alterato.
 Nei sistemi modello approcci di modificazione genetica che producono o sequenze genetiche alterate o espressione genetica alterata fenotipo alterato. Correlazione tra fenotipo alterato, o a livello cellulare,
Nei sistemi modello approcci di modificazione genetica che producono o sequenze genetiche alterate o espressione genetica alterata fenotipo alterato. Correlazione tra fenotipo alterato, o a livello cellulare,
Mediatore chimico. Recettore. Trasduzione del segnale. Risposta della cellula
 Mediatore chimico Recettore Trasduzione del segnale Risposta della cellula I mediatori chimici sono prodotti da cellule specializzate e sono diffusi nell organismo da apparati di distribuzione Sistemi
Mediatore chimico Recettore Trasduzione del segnale Risposta della cellula I mediatori chimici sono prodotti da cellule specializzate e sono diffusi nell organismo da apparati di distribuzione Sistemi
Che cosa è l RNA interference?
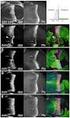 Che cosa è l RNA interference? L RNA interference (RNAi) è un processo naturale di silenziamento dell espressione genica post-trascrizionale iniziato da RNA a doppio filamento (dsrna) di sequenza omologa
Che cosa è l RNA interference? L RNA interference (RNAi) è un processo naturale di silenziamento dell espressione genica post-trascrizionale iniziato da RNA a doppio filamento (dsrna) di sequenza omologa
COME VIENE REALIZZATA UNA RICERCA SPERIMENTALE IN BIOLOGIA MOLECOLARE?
 COME VIENE REALIZZATA UNA RICERCA SPERIMENTALE IN BIOLOGIA MOLECOLARE? A Flusso di attività B - INPUT C Descrizione dell attività D RISULTATO E - SISTEMA PROFESSIONALE 0. RICHIESTA DI STUDIARE E/O INDIVIDUARE
COME VIENE REALIZZATA UNA RICERCA SPERIMENTALE IN BIOLOGIA MOLECOLARE? A Flusso di attività B - INPUT C Descrizione dell attività D RISULTATO E - SISTEMA PROFESSIONALE 0. RICHIESTA DI STUDIARE E/O INDIVIDUARE
MANIPOLAZIONE GENETICA DEGLI ANIMALI
 MANIPOLAZIONE GENETICA DEGLI ANIMALI Perché creare animali transgenici Per studiare la funzione e la regolazione di geni coinvolti in processi biologici complessi come lo sviluppo di un organismo e l insorgenza
MANIPOLAZIONE GENETICA DEGLI ANIMALI Perché creare animali transgenici Per studiare la funzione e la regolazione di geni coinvolti in processi biologici complessi come lo sviluppo di un organismo e l insorgenza
Negli eucarioti, per la maggior parte dei geni, entrambe le copie sono espresse dalla cellula, ma una piccola classe di geni è espressa
 Epigenetica ed espressione genica monoallelica Negli eucarioti, per la maggior parte dei geni, entrambe le copie sono espresse dalla cellula, ma una piccola classe di geni è espressa monoallelicamente,
Epigenetica ed espressione genica monoallelica Negli eucarioti, per la maggior parte dei geni, entrambe le copie sono espresse dalla cellula, ma una piccola classe di geni è espressa monoallelicamente,
LEUCEMIE tessuto ematopoieitico MIELOMI. più precisamente!
 LEUCEMIE tessuto ematopoieitico MIELOMI più precisamente! TUMORI EVOLUZIONE E SELEZIONE CLONALE Cambiano: Velocita proliferazione Velocità di mutazione Stabilità genetica Attività telomerasica Vantaggi
LEUCEMIE tessuto ematopoieitico MIELOMI più precisamente! TUMORI EVOLUZIONE E SELEZIONE CLONALE Cambiano: Velocita proliferazione Velocità di mutazione Stabilità genetica Attività telomerasica Vantaggi
Sensori a effetto Hall bipolari con ritenuta stabilizzati e non stabilizzati con circuito chopper
 Sensori a effetto Hall bipolari con ritenuta stabilizzati e non stabilizzati con circuito chopper I risultati dei test mostrano che è possibile ottenere prestazioni significativamente maggiori impiegando
Sensori a effetto Hall bipolari con ritenuta stabilizzati e non stabilizzati con circuito chopper I risultati dei test mostrano che è possibile ottenere prestazioni significativamente maggiori impiegando
KIR EVOLUZIONE RAPIDA E DIVERSIFICATA DEI RECETTORI DELL IMMUNITA INNATA E ADATTATIVA
 KIR EVOLUZIONE RAPIDA E DIVERSIFICATA DEI RECETTORI DELL IMMUNITA INNATA E ADATTATIVA C.Vilches, P. Parham Natural Killer Cellule di origine linfoide la cui funzione è lisare le cellule infettate da virus
KIR EVOLUZIONE RAPIDA E DIVERSIFICATA DEI RECETTORI DELL IMMUNITA INNATA E ADATTATIVA C.Vilches, P. Parham Natural Killer Cellule di origine linfoide la cui funzione è lisare le cellule infettate da virus
INDICE. VOLUME 1 Cellula. VOLUME 2 Genetica. Capitolo 9 Comunicazione cellulare 181. Capitolo 1 Introduzione alla biologia 1
 00PrPag_Vol_02_BROOKER 30/07/10 11:22 Pagina V VOLUME 1 Cellula Capitolo 1 Introduzione alla biologia 1 PARTE I Capitolo 2 Chimica Basi chimiche della vita I: atomi, molecole e acqua 19 Capitolo 3 Basi
00PrPag_Vol_02_BROOKER 30/07/10 11:22 Pagina V VOLUME 1 Cellula Capitolo 1 Introduzione alla biologia 1 PARTE I Capitolo 2 Chimica Basi chimiche della vita I: atomi, molecole e acqua 19 Capitolo 3 Basi
ncdna Per ncdna si intende il DNA intronico, intergenico e altre zone non codificanti del genoma.
 ncdna Per ncdna si intende il DNA intronico, intergenico e altre zone non codificanti del genoma. ncdna è caratteristico degli eucarioti: Sequenze codificanti 1.5% del genoma umano Introni in media 95-97%
ncdna Per ncdna si intende il DNA intronico, intergenico e altre zone non codificanti del genoma. ncdna è caratteristico degli eucarioti: Sequenze codificanti 1.5% del genoma umano Introni in media 95-97%
CELLULE EUCARIOTICHE
 CELLULE EUCARIOTICHE Le cellule eucariotiche sono di maggiori dimensioni, rispetto a quelle procariotiche (almeno 10 volte più grandi) Oltre a: membrana plasmatica, citoplasma, DNA e ribosomi (comuni a
CELLULE EUCARIOTICHE Le cellule eucariotiche sono di maggiori dimensioni, rispetto a quelle procariotiche (almeno 10 volte più grandi) Oltre a: membrana plasmatica, citoplasma, DNA e ribosomi (comuni a
DOMANDA FREQUENTE: QUALE E LA FUNZIONE DI UNA CERTA PROTEINA? SI AUMENTA O SI DIMINUISCE L ESPRESSIONE DELLA PROTEINA
 DOMANDA FREQUENTE: QUALE E LA FUNZIONE DI UNA CERTA PROTEINA? OVERESPRESSIONE DELLA PROTEINA ESPRESSIONE ECTOPICA CON UN VETTORE DI ESPRESSIONE ABOLIZIONE DELLA ESPRESSIONE DELLA PROTEINA INTERFERENZA
DOMANDA FREQUENTE: QUALE E LA FUNZIONE DI UNA CERTA PROTEINA? OVERESPRESSIONE DELLA PROTEINA ESPRESSIONE ECTOPICA CON UN VETTORE DI ESPRESSIONE ABOLIZIONE DELLA ESPRESSIONE DELLA PROTEINA INTERFERENZA
Prof.ssa Gamba Sabrina. Lezione 7: IL DNA. Duplicazione e sintesi delle proteine
 Prof.ssa Gamba Sabrina Lezione 7: IL DNA Duplicazione e sintesi delle proteine concetti chiave della lezione Costituzione fisico-chimica del DNA Basi azotate Duplicazione Concetto di geni Rna Trascrizione
Prof.ssa Gamba Sabrina Lezione 7: IL DNA Duplicazione e sintesi delle proteine concetti chiave della lezione Costituzione fisico-chimica del DNA Basi azotate Duplicazione Concetto di geni Rna Trascrizione
Applicazioni biotecnologiche in systems biology
 Applicazioni biotecnologiche in systems biology Lezione #6 Dr. Marco Galardini AA 2012/2013 Gene regulation analysis Lezione #6 Dr. Marco Galardini AA 2012/2013 Regolazione genica Elementi molecolari e
Applicazioni biotecnologiche in systems biology Lezione #6 Dr. Marco Galardini AA 2012/2013 Gene regulation analysis Lezione #6 Dr. Marco Galardini AA 2012/2013 Regolazione genica Elementi molecolari e
NORMATIVA OGM IN ALIMENTI, SEMENTI E COLTURE AGRARIE
 NORMATIVA OGM IN ALIMENTI, SEMENTI E COLTURE AGRARIE Che cosa sono le piante transgeniche? Transgenesi indica il trasferimento di geni mediante la tecnologia del DNA ricombinante. Il gene viene trasferito
NORMATIVA OGM IN ALIMENTI, SEMENTI E COLTURE AGRARIE Che cosa sono le piante transgeniche? Transgenesi indica il trasferimento di geni mediante la tecnologia del DNA ricombinante. Il gene viene trasferito
Biologia Cellulare e DNA «Bigino»
 Biologia Cellulare e DNA «Bigino» Giulio Barigelletti www.baveno.net Premesse 2 Sempre più frequentemente si sente parlare di DNA, Proteine, Amminoacidi, etc., relazionati all esistenza dell essere umano.
Biologia Cellulare e DNA «Bigino» Giulio Barigelletti www.baveno.net Premesse 2 Sempre più frequentemente si sente parlare di DNA, Proteine, Amminoacidi, etc., relazionati all esistenza dell essere umano.
NUCLEOTIDI e ACIDI NUCLEICI
 NUCLEOTIDI e ACIDI NUCLEICI Struttura dei nucleotidi Il gruppo fosfato conferisce carica negativa e proprietà acide FUNZIONI DEI NUCLEOTIDI MOLECOLE DI RISERVA DI ENERGIA L idrolisi dei nucleosidi trifosfato
NUCLEOTIDI e ACIDI NUCLEICI Struttura dei nucleotidi Il gruppo fosfato conferisce carica negativa e proprietà acide FUNZIONI DEI NUCLEOTIDI MOLECOLE DI RISERVA DI ENERGIA L idrolisi dei nucleosidi trifosfato
DI REGOLAZIONE A DUE COMPONENTI
 LEZIONE 16 Sistemi di regolazione SISTEMI DI REGOLAZIONE A DUE COMPONENTI In che modo un batterio sente e risponde a specifici segnali provenienti dall ambiente? Per esempio, nel caso dell operone lac
LEZIONE 16 Sistemi di regolazione SISTEMI DI REGOLAZIONE A DUE COMPONENTI In che modo un batterio sente e risponde a specifici segnali provenienti dall ambiente? Per esempio, nel caso dell operone lac
SINTESI PROTEICA. Replicazione. Trascrizione. Traduzione
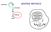 Replicazione SINTESI PROTEICA Trascrizione Traduzione 61 codoni codificanti 3 triplette non senso (STOP) AUG codone di inizio codone per Met Caratteristiche del codice genetico Specificità Il codice genetico
Replicazione SINTESI PROTEICA Trascrizione Traduzione 61 codoni codificanti 3 triplette non senso (STOP) AUG codone di inizio codone per Met Caratteristiche del codice genetico Specificità Il codice genetico
L endocitosi dell EGFR
 L endocitosi dell EGFR IFOM per la scuola Lo Studente Ricercatore 2011 Muzio Giulia Istituto d Istruzione Superiore Maserati Voghera Gruppo di lavoro: Determinanti della trasformazione neoplastica e della
L endocitosi dell EGFR IFOM per la scuola Lo Studente Ricercatore 2011 Muzio Giulia Istituto d Istruzione Superiore Maserati Voghera Gruppo di lavoro: Determinanti della trasformazione neoplastica e della
Organizzazione del genoma umano II
 Organizzazione del genoma umano II Lezione 7 & Pseudogeni I Pseudogeni non processati : convenzionali ed espressi * Copie non funzionali del DNA genomico di un gene. Contengono esoni, introni e spesso
Organizzazione del genoma umano II Lezione 7 & Pseudogeni I Pseudogeni non processati : convenzionali ed espressi * Copie non funzionali del DNA genomico di un gene. Contengono esoni, introni e spesso
PRINCIPALI TIPI DI PCR a) PRINCIPALI TIPI DI PCR b)
 PRINCIPALI TIPI DI PCR a) RT-PCR: serve a valutare l espressione di un gene tramite l amplificazione dell mrna da esso trascritto PCR COMPETITIVA: serve a valutare la concentrazione iniziale di DNA o RNA
PRINCIPALI TIPI DI PCR a) RT-PCR: serve a valutare l espressione di un gene tramite l amplificazione dell mrna da esso trascritto PCR COMPETITIVA: serve a valutare la concentrazione iniziale di DNA o RNA
GENETICA... lessico. Genetica: studio dei geni e dell'ereditarietà
 GENETICA... lessico Genetica: studio dei geni e dell'ereditarietà Geni: porzioni di DNA contenenti un'informazione che permette di decodificare una certa proteina. Es: gene che determina il colore dei
GENETICA... lessico Genetica: studio dei geni e dell'ereditarietà Geni: porzioni di DNA contenenti un'informazione che permette di decodificare una certa proteina. Es: gene che determina il colore dei
Le cellule eucariotiche svolgono durante la loro vita una serie ordinata di eventi che costituiscono il Ciclo Cellulare
 Le cellule eucariotiche svolgono durante la loro vita una serie ordinata di eventi che costituiscono il Ciclo Cellulare Interfase comprende le fasi G 1, S, and G 2 Sintesi di macromolecole durante la
Le cellule eucariotiche svolgono durante la loro vita una serie ordinata di eventi che costituiscono il Ciclo Cellulare Interfase comprende le fasi G 1, S, and G 2 Sintesi di macromolecole durante la
CORSO DI AGGIORNAMENTO PER GLI INSEGNANTI DELLE SCUOLE MEDIE SUPERIORI INGEGNERIA GENETICA E SUE APPLICAZIONI
 CORSO DI AGGIORNAMENTO PER GLI INSEGNANTI DELLE SCUOLE MEDIE SUPERIORI INGEGNERIA GENETICA E SUE APPLICAZIONI mercoledì 5 maggio 2004 La regolazione dell'espressione genica prof. Giovanna Viale - Università
CORSO DI AGGIORNAMENTO PER GLI INSEGNANTI DELLE SCUOLE MEDIE SUPERIORI INGEGNERIA GENETICA E SUE APPLICAZIONI mercoledì 5 maggio 2004 La regolazione dell'espressione genica prof. Giovanna Viale - Università
STUDI SU MATERIALE GENETICO
 Istituto Oncologico Veneto Istituto di Ricovero e Cura a Carattere Scientifico Ospedale Busonera I.O.V. ISTITUTO ONCOLOGICO VENETO I.R.C.C.S. STUDI SU MATERIALE GENETICO Comitato Etico Istituto Oncologico
Istituto Oncologico Veneto Istituto di Ricovero e Cura a Carattere Scientifico Ospedale Busonera I.O.V. ISTITUTO ONCOLOGICO VENETO I.R.C.C.S. STUDI SU MATERIALE GENETICO Comitato Etico Istituto Oncologico
Database. Si ringrazia Marco Bertini per le slides
 Database Si ringrazia Marco Bertini per le slides Obiettivo Concetti base dati e informazioni cos è un database terminologia Modelli organizzativi flat file database relazionali Principi e linee guida
Database Si ringrazia Marco Bertini per le slides Obiettivo Concetti base dati e informazioni cos è un database terminologia Modelli organizzativi flat file database relazionali Principi e linee guida
CONTROLLO ORMONALE DEL METABOLISMO GLUCIDICO DA PARTE DI GLUCAGONE, ADRENALINA E INSULINA
 CONTROLLO ORMONALE DEL METABOLISMO GLUCIDICO DA PARTE DI GLUCAGONE, ADRENALINA E INSULINA QUESTI ORMONI REGOLANO IL FLUSSO DEI METABOLITI NELLA GLICOLISI, NELLA GLICOGENO-SINTESI, NELLA GLIGENO-LISI E
CONTROLLO ORMONALE DEL METABOLISMO GLUCIDICO DA PARTE DI GLUCAGONE, ADRENALINA E INSULINA QUESTI ORMONI REGOLANO IL FLUSSO DEI METABOLITI NELLA GLICOLISI, NELLA GLICOGENO-SINTESI, NELLA GLIGENO-LISI E
Mutagenesi: introduzione di alterazioni in una sequenza nucleotidica. Mutagenesi random: le mutazioni avvengono a caso su un tratto di DNA.
 Mutagenesi: introduzione di alterazioni in una sequenza nucleotidica Mutagenesi random: le mutazioni avvengono a caso su un tratto di DNA. In genere si ottengono trattando il DNA con agenti chimici (es.
Mutagenesi: introduzione di alterazioni in una sequenza nucleotidica Mutagenesi random: le mutazioni avvengono a caso su un tratto di DNA. In genere si ottengono trattando il DNA con agenti chimici (es.
la struttura tridimensionale può essere ottenuta solo per Un intero dominio in genere da 50 a 300 residui
 Durante la traduzione l informazione di ripiegamento codificata nella sequenza aminoacidica diventa disponibile in maniera vettoriale la struttura tridimensionale può essere ottenuta solo per Un intero
Durante la traduzione l informazione di ripiegamento codificata nella sequenza aminoacidica diventa disponibile in maniera vettoriale la struttura tridimensionale può essere ottenuta solo per Un intero
Cosa sono le malattie polyq?
 Novità dalla ricerca sulla Malattia di Huntington In un linguaggio semplice. Scritto da ricercatori. Per la comunità mondiale MH. Ci sono connessioni genetiche tra le malattie neurodegenerative? Evidenze
Novità dalla ricerca sulla Malattia di Huntington In un linguaggio semplice. Scritto da ricercatori. Per la comunità mondiale MH. Ci sono connessioni genetiche tra le malattie neurodegenerative? Evidenze
Corso di Laurea in Farmacia Insegnamento di BIOCHIMICA Angela Chambery
 Corso di Laurea in Farmacia Insegnamento di BIOCHIMICA Angela Chambery Lezione 26 La gluconeogenesi Concetti chiave: Il fegato e il rene possono sintetizzare glucosio da lattato, piruvato e amminoacidi.
Corso di Laurea in Farmacia Insegnamento di BIOCHIMICA Angela Chambery Lezione 26 La gluconeogenesi Concetti chiave: Il fegato e il rene possono sintetizzare glucosio da lattato, piruvato e amminoacidi.
Silenziamento genico sequenza specifico. Pathway di regolazione dell'espressione genica provocato da dsrna.
 ( RNAi ) RNA Interference Silenziamento genico sequenza specifico. Pathway di regolazione dell'espressione genica provocato da dsrna. E un meccanismo naturale in piante, funghi, insetti e mammiferi. Cronologia:
( RNAi ) RNA Interference Silenziamento genico sequenza specifico. Pathway di regolazione dell'espressione genica provocato da dsrna. E un meccanismo naturale in piante, funghi, insetti e mammiferi. Cronologia:
Tasso di occupazione per fasce di età. Provincia di Piacenza, 2009 90,3 83,1 77,7 27,6 16,4. 15-24 anni. 25-34 anni. 45-54 anni.
 La situazione occupazionale dei giovani in provincia di Piacenza Premessa Una categoria di soggetti particolarmente debole nel mercato del lavoro è rappresentata, di norma, dai lavoratori di età più giovane
La situazione occupazionale dei giovani in provincia di Piacenza Premessa Una categoria di soggetti particolarmente debole nel mercato del lavoro è rappresentata, di norma, dai lavoratori di età più giovane
La genetica è la disciplina che si occupa della trasmissione dei caratteri ereditari Si divide in:
 La genetica La genetica è la disciplina che si occupa della trasmissione dei caratteri ereditari Si divide in: 1. Genetica mendeliana 2. Genetica citoplasmatica 3. Citogenetica 4. La genetica delle popolazioni
La genetica La genetica è la disciplina che si occupa della trasmissione dei caratteri ereditari Si divide in: 1. Genetica mendeliana 2. Genetica citoplasmatica 3. Citogenetica 4. La genetica delle popolazioni
Una proteina qualsiasi assume costantemente un unica conformazione ben definita, cui è legata la sua azione biologica.
 Concanavalina A Emoglobina subunità Trioso fosfato isomerasi Una proteina qualsiasi assume costantemente un unica conformazione ben definita, cui è legata la sua azione biologica. 1 La conformazione è
Concanavalina A Emoglobina subunità Trioso fosfato isomerasi Una proteina qualsiasi assume costantemente un unica conformazione ben definita, cui è legata la sua azione biologica. 1 La conformazione è
Biologia Molecolare. CDLM in CTF 2010-2011 La modificazione dell RNA e la traduzione
 Biologia Molecolare CDLM in CTF 2010-2011 La modificazione dell RNA e la traduzione La maturazione del trascritto primario I microrna Le componenti del macchinario di traduzione Il meccanismo della traduzione
Biologia Molecolare CDLM in CTF 2010-2011 La modificazione dell RNA e la traduzione La maturazione del trascritto primario I microrna Le componenti del macchinario di traduzione Il meccanismo della traduzione
Tratto dal libro Come vivere 150 anni Dr. Dimitris Tsoukalas
 1 Tratto dal libro Come vivere 150 anni Dr. Dimitris Tsoukalas Capitolo 7 Enzimi, le macchine della vita Piccole macchine regolano la funzione del corpo umano in un orchestrazione perfetta e a velocità
1 Tratto dal libro Come vivere 150 anni Dr. Dimitris Tsoukalas Capitolo 7 Enzimi, le macchine della vita Piccole macchine regolano la funzione del corpo umano in un orchestrazione perfetta e a velocità
Alberto Viale I CROMOSOMI
 Alberto Viale I CROMOSOMI DA MENDEL ALLA GENETICA AL DNA ALLE MUTAZIONI I cromosomi sono dei particolari bastoncelli colorati situati nel nucleo delle cellule. Sono presenti nelle cellule di ogni organismo
Alberto Viale I CROMOSOMI DA MENDEL ALLA GENETICA AL DNA ALLE MUTAZIONI I cromosomi sono dei particolari bastoncelli colorati situati nel nucleo delle cellule. Sono presenti nelle cellule di ogni organismo
I Papillomavirus sono tutti uguali?
 Cos è il Papillomavirus? Il Papillomavirus è un microscopico nemico della tua salute. Attento, però, a non sottovalutare la pericolosità di questo microrganismo lungo solo 55 milionesimi di millimetro.
Cos è il Papillomavirus? Il Papillomavirus è un microscopico nemico della tua salute. Attento, però, a non sottovalutare la pericolosità di questo microrganismo lungo solo 55 milionesimi di millimetro.
Come si traccia un alimento di origine animale? Dalle lasagne con carne di cavallo. alla realtà di ogni giorno
 Editoriale n.10 Newsletter aprile 2013 Come si traccia un alimento di origine animale? Dalle lasagne con carne di cavallo alla realtà di ogni giorno Identificare la specie, un obiettivo fondamentale quando
Editoriale n.10 Newsletter aprile 2013 Come si traccia un alimento di origine animale? Dalle lasagne con carne di cavallo alla realtà di ogni giorno Identificare la specie, un obiettivo fondamentale quando
L età dei vincitori La presenza femminile. L età dei vincitori La presenza femminile. Confronto tra il concorso ordinario ed il concorso riservato
 Premessa Corso-concorso ordinario L età dei vincitori La presenza femminile Corso-concorso riservato L età dei vincitori La presenza femminile Confronto tra il concorso ordinario ed il concorso riservato
Premessa Corso-concorso ordinario L età dei vincitori La presenza femminile Corso-concorso riservato L età dei vincitori La presenza femminile Confronto tra il concorso ordinario ed il concorso riservato
Determinazione del sesso Cromosomi sessuali
 Determinazione del sesso Cromosomi sessuali Negli Eucarioti un cromosoma del sesso è un cromosoma presente in forme diverse nei due sessi. Uno è un cromosoma "X", l'altro strutturalmente e funzionalmente
Determinazione del sesso Cromosomi sessuali Negli Eucarioti un cromosoma del sesso è un cromosoma presente in forme diverse nei due sessi. Uno è un cromosoma "X", l'altro strutturalmente e funzionalmente
Sommario. Definizione di informatica. Definizione di un calcolatore come esecutore. Gli algoritmi.
 Algoritmi 1 Sommario Definizione di informatica. Definizione di un calcolatore come esecutore. Gli algoritmi. 2 Informatica Nome Informatica=informazione+automatica. Definizione Scienza che si occupa dell
Algoritmi 1 Sommario Definizione di informatica. Definizione di un calcolatore come esecutore. Gli algoritmi. 2 Informatica Nome Informatica=informazione+automatica. Definizione Scienza che si occupa dell
DIFFERENZIAMENTO E COMUNICAZIONE TRA CELLULE - LE CELLULE STAMINALI. www.fisiokinesiterapia.biz
 DIFFERENZIAMENTO E COMUNICAZIONE TRA CELLULE - LE CELLULE STAMINALI www.fisiokinesiterapia.biz sito dell NIH sulle cellule staminali in genere http://stemcells.nih.gov/info/basics/basics4.asp sito completo
DIFFERENZIAMENTO E COMUNICAZIONE TRA CELLULE - LE CELLULE STAMINALI www.fisiokinesiterapia.biz sito dell NIH sulle cellule staminali in genere http://stemcells.nih.gov/info/basics/basics4.asp sito completo
