PCR: Polymerase Chain Reaction
|
|
|
- Taddeo Carletti
- 9 anni fa
- Просмотров:
Транскрипт
1 PCR: Polymerase Chain Reaction Poche invenzioni hanno rivoluzionato in maniera così drastica e repentina il corso della biologia molecolare come la PCR. La tecnica é l approccio per il quale, permettendo l amplificazione in vitro di frammenti di DNA, da modo di analizzare l informazione genetica contenuta nel patrimonio genetico di un individuo, con ricadute fondamentali in campi diversissimi, dai laboratori di ricerca pura, ai centri di diagnostica degli ospedali, fino alle aule dei tribunali. KARY BANKS MULLIS BIBLIOGRAPHY. Nel suo libro del 1998 ("Ballando nudi nel campo della mente, Mullis parla della sua visione del mondo e narra di episodi curiosi ed esperienze alquanto insolite da lui vissute. Parla dell astrologia, della sua partecipazione al processo di O. J. Simpson, del suo uso di droghe. Sostiene che "la scienza dei media è una fesseria" per finire addirittura con l'ammissione di essere stato rapito dagli alieni; gli accadde una notte del 1985, in un bosco nei pressi di Mendocino County in California, poco dopo aver incrociato un procione parlante. Mullis racconta come ai tempi dei suoi studi a Berkeley (1973) mandò all'autorevole rivista inglese Nature un articolo inventato di sana pianta nel quale sosteneva che metà della materia dell'universo andrebbe all'indietro nel tempo. L'articolo beffa fu pubblicato. Un ventennio dopo propose alla stessa rivista un lavoro in cui documentava la tecnica del PCR che gli avrebbe valso il Nobel, e non fu pubblicato; "Questa esperienza mi insegnò un paio di cose e mi fece crescere un bel po'"....potevo letteralmente veder lavorare i singoli polimeri...
2 Polymerase Chain Reaction Powerful technique for amplifying or copying a specific piece of DNA Carried out in vitro (in the lab) Extremely simple technique
3 PCR - REAZIONE a CATENA della POLIMERASI Il principio a cui si ispira la PCR è la replicazione del DNA: REPLICAZIONE Primer a RNA Nuovo filamento DNA polimerasi DNA templato Primers a RNA Nuovo filamento
4 COMPONENTI di una REAZIONE di PCR Stampo DNA a doppio filamento Mg 2+ Primers Oligonucleotidi complementari a regioni dei filamenti opposti che fiancheggiano la sequenza DNA bersaglio Deossiribonucleotidi trifosfati Miscela equimolare di datp, dttp, dgtp, dctp Tampone contenente cloruro di magnesio Lo ione Mg 2+ è essenziale per il funzionamento dell enzima Enzima Tradizionalmente viene usata la Taq polimerasi, enzima termostabile estratto dal batterio termofilo Thermus aquaticus
5 Le FASI della PCR DENATURAZIONE: Il DNA viene denaturato mediante riscaldamento in provetta a ~ C ANNEALING: La miscela viene raffreddata fino a raggiungere la temperatura che garantisce la specifica ibridazione dei primers alle regioni dello stampo ad essi complementari ALLUNGAMENTO: La temperatura della miscela viene portata a C consentendo alla DNA polimerasi termostabile di sintetizzare il filamento complementare allo stampo a partire dall innesco oligonucleotidico
6 Polymerase Chain Reaction: principio CICLI TERMICI: DENATURAZIONE (94-96 C) ANNEALING (50-65 C) EXTENSION (72 C)
7
8
9
10 I primi 4 cicli della PCR in dettaglio Frammento desiderato 2 ciclo 3 ciclo 4 ciclo Amplificazione esponenziale 1 ciclo 35 ciclo DNA stampo Numero di copie di DNA contenenti il frammento desiderato 2 1 = = = = Numero di copie di DNA della corretta lunghezza contenenti il frammento desiderato
11
12 10 12 copies Y = (1+x) n X= mean efficiency of a cycle N= number of cycles Y= fold amplification
13 Per Cycle Efficiency (% ) Extent of amplification (20 cycles) Relative yield
14 What are the factors determining the Plateau Effect???? What is limiting? Template? Primers? dntps? Taq Polymerase?
15 Polymerase Chain Reaction: plateau Resa effettiva: effetto plateau Il processo di duplicazione non procede all infinito, esso è limitato da: Quantità dei primers Attività della Taq polimerasi Reannealing dei filamenti Raggiunto il plateau non si osserva più un incremento nei prodotti
16 Una sequenza di 16 bp sarà statisticamente presente solo una volta ogni 4 16 bp (~ 4 miliardi di basi) corrispondenti circa alla grandezza del genoma umano. Più lungo è il primer e più è stabile, ma > probabilità che formi dimeri T m primer 1 Tm primer 2 La T m dipende dalla lunghezza e dalla sequenza del primer Se la T a dei due primers è molto diversa si possono verificare amplificazioni asimmetriche o a singolo filamento. T m ( C) = 4(G+C)+2(A+T) PCR primer design
17 MG++ Non deve essere limitante: tutto ciò che metabolizza polimeri di nucleotidi necessita di Mg++. Se è largamente eccedente determina inaccuratezza, aumentando la frequenza degli appaiamenti degli oligo con sequenza non omologhe: le 2 cariche positive possono interagire con i fosfati e dare stabilità all appaiamento. Stabilizzando gli omologhi, stabilizzano anche i non omologhi, e questo va evitato. La [Mg++] ottimale si determina tenendo conto che può essere legato sui fosfati di dsdna, Oligo e dntp; sommando queste concentrazioni (conto stechiometrico/spannometrico) più la [compatibile] con l attività enzimatica. Si va a spanne: si guarda l ordine di grandezza molare.
18 Macchine pcr che generano un gradiente termico Aspecifi cità Condizione ideale Specificità e selettività
19
20
21 Riassumendo.in media stat virtus... Mg++ Taq Primers Num. cicli Temp annealing resa specificità Resa e specificità procedono in direzioni opposte. Fattori che favoriscono l una sfavoriscono l altra. Bisogna trovare un equilibrio tra le 2 opposte tendenze
22 Troubleshooting Nessuno o scarso amplificato: Concentrazione reagenti e setup reazione corretti? Disegno Primers corretto? Presenza inibitori T annealing troppo alta Pochi cicli Thermal cycler funziona? Bande aspecifiche: Eccesso reagenti o cicli T annealing troppo bassa Disegno Primers corretto? Sintesi parziale dei primers PCR amplifica solo alcuni campioni: Pulizia e corretto dosaggio DNA templato Presenza polimorfismi che ostacolano annealing di un primer Prodotto dimensioni errate: Appaiamento primers in regioni non corrette (pseudogeni, seq. Ripetute)
23
24
25 STRATEGIE per AUMENTARE la SPECIFICITA PCR CLASSICA TOUCHDOWN PCR Den. iniziale Den. 30 sec 94 C Ann. 30 sec 30 T m (-5 C) cicli All. 1 min/kb 72 C All. finale 3-5 min 94 C 7 min 72 C 1 ciclo 1 ciclo Den. iniziale 3-5 min 94 C Den. 30 sec 94 C Ann. 30 sec T m (+5 C) -1 C/ciclo 10 cicli All. 1 min/kb 72 C Den. 30 sec 94 C Ann. 30 sec T m (-5 C) All. 1 min/kb 72 C 1 ciclo 20 cicli Manteni -mento 4 C All. finale 7 min 72 C 1 ciclo Touch-down: (campioni ricchi di DNA simili al target di amplificazione) Manteni -mento Si parte da cicli con annealing a temperatura superiore a quella prevista per i primer, scendendo gradatamente alla temperatura corretta e poi continuando per gli utimi cicli in condizioni normali. SCOPO: arricchire la miscela del templato voluto a scapito degli omologhi. Touch-up: (campioni molto poveri in templato) Si parte da temperature di annealing basse, per rendere i primers aspecifici e arricchire così la mix, aumentando man mano la temperatura di annealing per recuperare specificità. 4 C
26 ...STRATEGIE per AUMENTARE la SPECIFICITA HOT START Perché realizzare una PCR hot start? Durante l allestimento della reazione di PCR o durante il riscaldamento iniziale del campione si possono verificare situazioni di appaiamento non specifico fra primers e stampo. Fra 40 e 50 C la Taq polimerasi ha un efficiente attività polimerasica e può estendere i primers non correttamente appaiati. La PCR hot start previene la formazione di questi prodotti non specifici in quanto un componente chiave della miscela di reazione (enzima o MgCl 2 ) viene aggiunto dopo lo step di denaturazione iniziale. NOVITA : Enzimi Hot start Gocce di cera NESTED PRIMER PCR Procedura: L amplificazione è realizzata con un set di primers Il prodotto è riamplificato con un set di primers interni ai precedenti I a PCR pr. nested II a PCR pr. nested 3 I prodotti non specifici amplificati nella I a PCR non saranno amplificati nella II a 3 5
27 Con un po di fantasia ;-) PCR asimmetrica Uno dei 2 primers e in eccesso.e una amplificazione lineare. Fra le applicazioni ad es. sequenziamento, oppure se dopo l amplificazione si vuole ibridizzare il prodotto della PCR con una sonda marcata. Impiego di primers degeneri quando si vuole amplificare un gene di una specie, la cui sequenza esatta e conosciuta solo in altre specie (geni omologhi). quando si conosce solo la sequenza aminoacidica della proteina. quando le sequenze target presentano esse stesse eterogeneità, ad es. nel caso dell amplificazione di diversi sottotipi dell HIV. Multiplex PCR Vengono prodotti contemporaneamente e nella stessa provetta diversi amplificati, grazie all utilizzo di diverse coppie di primers (e chiaro che la resa si abbassa). Trova frequente applicazione in problemi diagnostici di routine. Ad es. la fibrosi cistica e causata da determinate mutazioni nel gene CFTR. Se ne conoscono al giorno d oggi più di 100, che si possono distribuire in tutti i 24 esoni. Una situazione analoga si ha per altre malattie genetiche, come la ipercolesterolemiafamiliare, la distrofia muscolare di Duchenne, etc.
28 Mutagenesi in vitro
29 Quantitative aspects of PCR
30 PCR Quantitativa : Real-Time PCR Durante la fase esponenziale della PCR, la quantità di copie prodotte è proporzionale al numero di copie di partenza; ciò è rilevabile grazie alla misurazione in tempo reale della fluorescenza emessa da fluorofori usati durante l amplificazione AMOUNT OF DNA PCR CYCLE NUMBER
31 PCR Quantitativa : Real-Time PCR Principio base: Maggiore è il numero delle molecole stampo presenti all inizio della reazione e minore sarà il numero di cicli necessari per raggiungere un determinato valore minimo di ammontare di prodotto (Cycle threshold (Ct) - ciclo soglia). soglia
32 Real-Time PCR: Detection chemistries. Ovvero i fluorofori che permettono la quantificazione dell amplificato. DNA Binding Dyes. Hybridization Probes. Hydrolisis Probes. Hairpin Probes. Scorpion Probes. FRET Probes. sequenza indipendente sequenza specifiche
33 DNA Binding Dyes: e.g. : SYBR Green molecola fluorescente non specifica che si lega al solco minore del DNA
34 DNA Binding Dyes: e.g. : SYBR Green All inizio del processo di amplificazione, la miscela di reazione contiene DNA denaturato, primers e la molecola fluorescente Dopo l annealing dei primers, si legano poche molecole fluorescenti alla doppia elica Durante l elongazione si verifica un aumento di fluorescenza che corrisponde all aumento del numero di copie dell amplicone
35 Hydrolisis Probes. e.g.: TaqMan Probes Sonda alle cui estremità sono coniugati un reporter al 5 (che emette fluorescenza) ed un quencher al 3 (che blocca l emissione). L idrolisi della sonda ad opera della polimerasi provoca il distacco del reporter dal quencher e la conseguente emissione di energia. 2 primers 1 sonda attività 5 >3 esonucleasica
36 Hairpin Probes: e.g. : LUX Primers Il fluoroforo è integrato in uno dei due primers. Quando non risulta incluso nel dsdna l emissione è minima. Sono sequenza-specifiche. E conveniente verifica (corsa su gel) della presenza di un solo prodotto di PCR. 2 primers (uno dei quali marcato)
37 Real-Time PCR: Quantificazione L approccio quantitativo può essere di due tipi : ASSOLUTO RELATIVO
38 Real-Time PCR: Quantificazione Quantificazione assoluta: Il dato è indicato come valore assoluto (e.g.:copie,ug/ul,etc) Utilizza una retta di calibrazione derivata da diluizioni seriali di uno standard di riferimento. Uno standard di riferimento può essere un frammento di dsdna, o ssdna, o crna prodotti in vitro (tramite vettori plasmidici ad es.) e che ricalchi la sequenza di interesse.
39 Real-Time PCR: Quantificazione Quantificazione relativa: Esprime la variazione nei livelli di espressione dell mrna di un campione TARGET-in relazione ai livelli di un mrna di controllo. I risultati dell elaborazione non sono espressi come quantità di mrna/dna presenti nel campione, ma come RAPPORTO tra TARGET/CONTROLLO.
40 Real-Time PCR: Normalizzazione Come discriminiamo variazioni nei livelli di espressione dalle variazioni nella quantità iniziale di campione? Gene FVII Sample1 NT Ct value: 18 NT Sample2 T Ct value: 29.5 T La variazione tra T e NT è imputabile al trattamento? o era presente in partenza più mrna nel campione NT?
41 Real-Time PCR: Normalizzazione La normalizzazione si pone come obiettivo quello di minimizzare gli errori dovuti a differenti quantità nel materiale di partenza. FVII NT Co-amplificando un gene esogeno (housekeeping) con il nostro target in modo da normalizzarlo. GAPDH T GAPDH NT FVII T
42 Real-Time PCR: Quantificazione Meglio una quantificazione assoluta o relativa? ASSOLUTA: Più impegnativa Richiede costruzione di una curva riproducibile Deve essere ripetuta ad ogni saggio RELATIVA: Valori di Ct applicabili solo ai campioni in esame Non sono dati assoluti Non possono essere considerati per esperimenti svolti nell arco di giorni
43 Digital PCR
44
45
46
47 When the entire set of divided reactions is counted, the total number of positive reactions is equal to the number of original target molecules in the entire volume, and the total number of reactions multiplied by the individual reaction volume equals the total volume assayed. Thus, the absolute concentration of the target is easily calculated as being equal to the total number of target molecules divided by the total measured volume. dpcr platforms which divide the sample into a larger number of compartments will have the highest accuracy, by directly counting single molecules dpcr performed using higher numbers of compartments provides the highest sensitivity with limits of detection approaching 1 in a million
48 It is based on Poisson distribution...suppose someone typically gets 4 pieces of mail per day on average. There will be, however, a certain spread: sometimes a little more, sometimes a little fewer, once in a while nothing at all. Given only the average rate, for a certain period of observation (pieces of mail per day, phonecalls per hour, etc.), and assuming that the process, or mix of processes, that produces the event flow is essentially random, the Poisson distribution specifies how likely it is that the count will be 3, or 5, or 10, or any other number, during one period of observation. That is, it predicts the degree of spread around a known average rate of occurrence.
49 When the number of target molecules is significantly smaller than the number of compartments (low occupancy), the chance of co-compartmentalization is small. Poisson statistics can be used either as a small correction factor (at low occupancy) or it can be used to calculate an estimated concentration (at high occupancy).
50 DNA Sequencing Extremely important technique for understanding organisms Can now determine sequence of whole genomes -including human Technique is based on enzymatic DNA synthesis using dideoxynucleotides
51 DNA Sequencing -Sanger Method Reaction mix: DNA Polymerase Primer Template 2 deoxynucleotides (dntp) 2,3 dideoxynucleotides (ddntp) also used Mix of dntps and ddntp (at lower conc.)
52 Deoxy-and dideoxynucleotides 2,3 -dideoxynucleotide 2 -deoxynucleotide
53 Normal DNA Synthesis Link forms between 3 OH and 5 PO 4
54 Primer Extension during DNA synthesis ds DNA template is denatured temperature lowered to allow basepairing of primer
55 DNA Sequencing Primer GATCACTGTCGACGTAATCGGCATTGCAACGT Template Polymerase extends primer until a ddntp is incorporated CTAGTGACAGCTGCA GATCACTGTCGACGTAATCGGCATTGCAACGT CTAGT GATCACTGTCGACGTAATCGGCATTGCAACGT CTAGTGACAGCTGCATTAGCCGTAAGCTTG GATCACTGTCGACGTAATCGGCATTGCAACGT CTAGTGACTGCAGCATTAGCC GATCACTGTCGACGTAATCGGCATTGCAACGT
56
57 Fluorescent ddntps Plus: a preponderance of dntps
58
59 Automated Fluorescence Sequencing
60 Pyrosequencing Note: No actual houses are burned down in pyrosequencing
61 Pyrosequencing (Life Sciences / Roche 454) A luciferase is an enzyme which emits light in the presence of ATP. Several organisms, such as the American firefly and the poisonous Jack-o-lantern mushroom, produce luciferases.
62 Detecting polymerase activity Recall: Pyrophosphate is also known as PPi, also known as two phosphate groups stuck together. During replication, each addition of a dntp releases pyrophosphate In the reaction mixture, PPi allows adenosine phosphosulfate (APS) to be converted to ATP; this ATP allows luciferase to luciferate (emit light). Measures strand extension as it happens +APS
63 Pyrosequencing cycle Add datp. If light is emitted, your sequence starts with A. If not, the datp is degraded (or elutes past immobilized primer). Add dgtp. If light is emitted, the next base must be a G. Then add T, then C. You now know at least one (maybe more) base of the sequence. Repeat!
64 Pyrosequencing output?
65 Pyrosequencing output AGGCCCCTTTGG
Biotecnologie applicate all ispezione degli alimenti di origine animale
 Prof.ssa Tiziana Pepe Evoluzioni della tecnica PCR Biotecnologie applicate all ispezione degli alimenti di origine animale Dip. di Medicina Veterinaria e Produzioni animali [email protected] Nested
Prof.ssa Tiziana Pepe Evoluzioni della tecnica PCR Biotecnologie applicate all ispezione degli alimenti di origine animale Dip. di Medicina Veterinaria e Produzioni animali [email protected] Nested
PCR. (Reazione a Catena della Polimerasi) Kary Mullis
 POLYMERASE CHAIN REACTION - PCR PCR Polymerase Chain Reaction (Reazione a Catena della Polimerasi) Kary Mullis Premio Nobel per la Chimica nel 1993, Kary Mullis è divenuto una leggenda per la scoperta
POLYMERASE CHAIN REACTION - PCR PCR Polymerase Chain Reaction (Reazione a Catena della Polimerasi) Kary Mullis Premio Nobel per la Chimica nel 1993, Kary Mullis è divenuto una leggenda per la scoperta
ELETTROFORESI SU GEL
 ELETTROFORESI SU GEL ELETTROFORESI SU GEL Metodo per separare le molecole (DNA, RNA, proteine, etc.) sulla base di proprieta fisiche o chimiche quali: (1)dimensioni (2)forma (3)carica elettrica L'AGAROSIO
ELETTROFORESI SU GEL ELETTROFORESI SU GEL Metodo per separare le molecole (DNA, RNA, proteine, etc.) sulla base di proprieta fisiche o chimiche quali: (1)dimensioni (2)forma (3)carica elettrica L'AGAROSIO
LA REAZIONE A CATENA DELLA POLIMERASI PCR
 LA REAZIONE A CATENA DELLA POLIMERASI PCR INTRODUZIONE Tecnica ideata da Mullis e collaboratori nel 1984 La possibilita' di disporre di quantità virtualmente illimitate di un determinato frammento di DNA,
LA REAZIONE A CATENA DELLA POLIMERASI PCR INTRODUZIONE Tecnica ideata da Mullis e collaboratori nel 1984 La possibilita' di disporre di quantità virtualmente illimitate di un determinato frammento di DNA,
Polymerase chain reaction - PCR. Biotecnologie applicate all ispezione degli alimenti di origine animale
 Prof.ssa Tiziana Pepe Polymerase chain reaction - PCR Biotecnologie applicate all ispezione degli alimenti di origine animale Dip. di Medicina Veterinaria e Produzioni animali [email protected] Metodologia
Prof.ssa Tiziana Pepe Polymerase chain reaction - PCR Biotecnologie applicate all ispezione degli alimenti di origine animale Dip. di Medicina Veterinaria e Produzioni animali [email protected] Metodologia
IL SEQUENZIAMENTO DEL DNA. Obiettivo: ottenere la sequenza nucleotidica di un frammento di DNA.
 IL SEQUENZIAMENTO DEL DNA Obiettivo: ottenere la sequenza nucleotidica di un frammento di DNA. Il DNA può essere sequenziato generando frammenti di DNA la cui lunghezza dipende dall ultima base della sequenza.
IL SEQUENZIAMENTO DEL DNA Obiettivo: ottenere la sequenza nucleotidica di un frammento di DNA. Il DNA può essere sequenziato generando frammenti di DNA la cui lunghezza dipende dall ultima base della sequenza.
Si può ottenere un a grande quantità di copie di DNA a partire da una singola molecola di DNA stampo La reazione è semplice ed automatizzabile E
 Si può ottenere un a grande quantità di copie di DNA a partire da una singola molecola di DNA stampo La reazione è semplice ed automatizzabile E possibile scegliere selettivamente cosa amplificare (specificità)
Si può ottenere un a grande quantità di copie di DNA a partire da una singola molecola di DNA stampo La reazione è semplice ed automatizzabile E possibile scegliere selettivamente cosa amplificare (specificità)
PCR - Polymerase Chain Reaction. ideata nel 1983 da Kary B. Mullis il quale ottenne, per questo, il premio Nobel per la chimica (1993).
 End point PCR vs quantitative Real-Time PCR PCR - Polymerase Chain Reaction ideata nel 1983 da Kary B. Mullis il quale ottenne, per questo, il premio Nobel per la chimica (1993). Questa tecnica, utilizzando
End point PCR vs quantitative Real-Time PCR PCR - Polymerase Chain Reaction ideata nel 1983 da Kary B. Mullis il quale ottenne, per questo, il premio Nobel per la chimica (1993). Questa tecnica, utilizzando
PCR - Polymerase Chain Reaction
 PCR - Polymerase Chain Reaction ideata nel 1983 da Kary B. Mullis il quale ottenne, per questo, il premio Nobel per la chimica (1993). Questa tecnica, utilizzando i principi della duplicazione del DNA,
PCR - Polymerase Chain Reaction ideata nel 1983 da Kary B. Mullis il quale ottenne, per questo, il premio Nobel per la chimica (1993). Questa tecnica, utilizzando i principi della duplicazione del DNA,
Analisi degli alimenti tramite PCR Real-Time. Introduzione ad una tecnologia all'avanguardia
 Analisi degli alimenti tramite PCR Real-Time Introduzione ad una tecnologia all'avanguardia Obiettivi Questa presentazione tratterà i seguenti argomenti: Quali sono le applicazioni della PCR Real-time?
Analisi degli alimenti tramite PCR Real-Time Introduzione ad una tecnologia all'avanguardia Obiettivi Questa presentazione tratterà i seguenti argomenti: Quali sono le applicazioni della PCR Real-time?
AMPLIFICAZIONE IN VITRO DEL DNA REAZIONE A CATENA DELLA POLIMERASI (PCR)
 AMPLIFICAZIONE IN VITRO DEL DNA REAZIONE A CATENA DELLA POLIMERASI (PCR) PCR: reazione polimerasica a catena Inventata da Kary Mullis negli anni 80 (premio Nobel 1993) Serve per ottenere una grande quantita
AMPLIFICAZIONE IN VITRO DEL DNA REAZIONE A CATENA DELLA POLIMERASI (PCR) PCR: reazione polimerasica a catena Inventata da Kary Mullis negli anni 80 (premio Nobel 1993) Serve per ottenere una grande quantita
Marcatori molecolari
 Marcatori molecolari Caratteristiche e applicazioni Luca Gianfranceschi e Rosanna Marino 1 I marcatori molecolari Strumento per l analisi genetica Strumento Molecolari Analisi genetica Marcatori non oggetto
Marcatori molecolari Caratteristiche e applicazioni Luca Gianfranceschi e Rosanna Marino 1 I marcatori molecolari Strumento per l analisi genetica Strumento Molecolari Analisi genetica Marcatori non oggetto
La tecnologia Seegene per la diagnosi delle Malattie Sessualmente Trasmesse in Real Time PCR
 La diagnostica molecolare delle malattie sessualmente trasmesse (non HIV): nuovi percorsi di appropriatezza analitica e clinica. La tecnologia Seegene per la diagnosi delle Malattie Sessualmente Trasmesse
La diagnostica molecolare delle malattie sessualmente trasmesse (non HIV): nuovi percorsi di appropriatezza analitica e clinica. La tecnologia Seegene per la diagnosi delle Malattie Sessualmente Trasmesse
PRINCIPALI TIPI DI PCR a) PRINCIPALI TIPI DI PCR b)
 PRINCIPALI TIPI DI PCR a) RT-PCR: serve a valutare l espressione di un gene tramite l amplificazione dell mrna da esso trascritto PCR COMPETITIVA: serve a valutare la concentrazione iniziale di DNA o RNA
PRINCIPALI TIPI DI PCR a) RT-PCR: serve a valutare l espressione di un gene tramite l amplificazione dell mrna da esso trascritto PCR COMPETITIVA: serve a valutare la concentrazione iniziale di DNA o RNA
Metodologie citogenetiche. Metodologie molecolari. Formulare la domanda Utilizzare la metodica appropriata
 In base al potere di risoluzione della tecnica Metodologie citogenetiche Metodologie molecolari Formulare la domanda Utilizzare la metodica appropriata 1 DNA RNA PROTEINE DNA Cromosomi (cariotipo, FISH,
In base al potere di risoluzione della tecnica Metodologie citogenetiche Metodologie molecolari Formulare la domanda Utilizzare la metodica appropriata 1 DNA RNA PROTEINE DNA Cromosomi (cariotipo, FISH,
di Milazzo Gabriele Mangiagli Graziella Paternò Valentina Lomagno Valeria Mangione Enza Prof. C. Di Pietro
 di Milazzo Gabriele Mangiagli Graziella Paternò Valentina Lomagno Valeria Mangione Enza Prof. C. Di Pietro Polymerase Chain Reaction Inventata a metà degli anni 80 da Kary Mullis, è a tutt oggi uno strumento
di Milazzo Gabriele Mangiagli Graziella Paternò Valentina Lomagno Valeria Mangione Enza Prof. C. Di Pietro Polymerase Chain Reaction Inventata a metà degli anni 80 da Kary Mullis, è a tutt oggi uno strumento
La reazione a catena della polimerasi (PCR) di Ofelia Leone e Vincenzo Mandarino
 La reazione a catena della polimerasi (PCR) di Ofelia Leone e Vincenzo Mandarino La Polymerase Chain Reaction (PCR) o reazione di amplificazione a catena è una tecnica che permette di amplificare una specifica
La reazione a catena della polimerasi (PCR) di Ofelia Leone e Vincenzo Mandarino La Polymerase Chain Reaction (PCR) o reazione di amplificazione a catena è una tecnica che permette di amplificare una specifica
eaction A very efficient method for IN VITRO REPLICATION of DNA
 1 olymerase hain What is it? eaction A very efficient method for IN VITRO REPLICATION of DNA What is for? Synthesis of several million copies of a specific DNA sequence within a few hours 2 PCR INGREDIENTS
1 olymerase hain What is it? eaction A very efficient method for IN VITRO REPLICATION of DNA What is for? Synthesis of several million copies of a specific DNA sequence within a few hours 2 PCR INGREDIENTS
LA REAZIONE A CATENA DELLA POLIMERASI
 Polymerase Chain Reaction LA REAZIONE A CATENA DELLA POLIMERASI e LE SUE APPLICAZIONI Prima diagnosi molecolare sul DNA 1978 *Primo ormone umano ricombinante (insulina) *Premio Nobel agli scopritori degli
Polymerase Chain Reaction LA REAZIONE A CATENA DELLA POLIMERASI e LE SUE APPLICAZIONI Prima diagnosi molecolare sul DNA 1978 *Primo ormone umano ricombinante (insulina) *Premio Nobel agli scopritori degli
Lezione 4. Il sequenziamento del DNA, Sanger
 Lezione 4 Il sequenziamento del DNA, Sanger Schema della lezione Polymerase chain reaction (PCR) Dal prodotto di PCR al sequenziamento di Sanger Lettura dei prodotti di sequenziamento con sequenziatori
Lezione 4 Il sequenziamento del DNA, Sanger Schema della lezione Polymerase chain reaction (PCR) Dal prodotto di PCR al sequenziamento di Sanger Lettura dei prodotti di sequenziamento con sequenziatori
Tecnologia del DNA e la genomica
 Tecnologia del DNA e la genomica DNA ricombinante La tecnologia del DNA ricombinante permette di unire in laboratorio il DNA di organismi diversi Permette di manipolare il DNA di un organismo allo scopo
Tecnologia del DNA e la genomica DNA ricombinante La tecnologia del DNA ricombinante permette di unire in laboratorio il DNA di organismi diversi Permette di manipolare il DNA di un organismo allo scopo
Isolamento e purificazione di DNA e RNA. -Separare gli acidi nucleici da altri componenti cellulari (lipidi e proteine)
 Isolamento e purificazione di DNA e RNA -Rompere la membrana cellulare -Separare gli acidi nucleici da altri componenti cellulari (lipidi e proteine) -Separare gli acidi nucleici tra loro -Rompere la membrana
Isolamento e purificazione di DNA e RNA -Rompere la membrana cellulare -Separare gli acidi nucleici da altri componenti cellulari (lipidi e proteine) -Separare gli acidi nucleici tra loro -Rompere la membrana
Il primer utilizzato può essere specifico per il gene che si intende amplificare oppure aspecifico (oligo (dt) oppure random esameri).
 Retrotrascrizione l mrna viene convertito in cdna per mezzo dell enzima trascrittasi inversa (DNA polimerasi RNAdipendenti ricavate dai virus della mieloblastosi aviaria AMV o della leucemia murina di
Retrotrascrizione l mrna viene convertito in cdna per mezzo dell enzima trascrittasi inversa (DNA polimerasi RNAdipendenti ricavate dai virus della mieloblastosi aviaria AMV o della leucemia murina di
Real Time PCR. La PCR Real Time è in grado di misurare in tempo reale la concentrazione iniziale di una sequenza target in un campione biologico.
 eal Time PC La PC eal Time è in grado di misurare in tempo reale la concentrazione iniziale di una sequenza target in un campione biologico. Gli strumenti per PC eal Time, oltre a fungere da termociclatori,
eal Time PC La PC eal Time è in grado di misurare in tempo reale la concentrazione iniziale di una sequenza target in un campione biologico. Gli strumenti per PC eal Time, oltre a fungere da termociclatori,
LA PCR E LE SUE VARIANTI. Quaderno di laboratorio. a cura di PRESS FIRENZE UNIVERSITY
 LA PCR E LE SUE VARIANTI Quaderno di laboratorio a cura di an GE LA scia LP I, ale SSIO me N GO N I FIRENZE UNIVERSITY PRESS manuali scienze 2 pianeta redi comitato scientifico renato fani david caramelli
LA PCR E LE SUE VARIANTI Quaderno di laboratorio a cura di an GE LA scia LP I, ale SSIO me N GO N I FIRENZE UNIVERSITY PRESS manuali scienze 2 pianeta redi comitato scientifico renato fani david caramelli
TECNICHE DI BIOLOGIA MOLECOLARE. LA REAZIONE POLIMERASICA A CATENA Principi teorici e aspetti pratici
 TECNICHE DI BIOLOGIA MOLECOLARE LA REAZIONE POLIMERASICA A CATENA Principi teorici e aspetti pratici POLYMERASE CHAIN REACTION (PCR) 1955 A. Kronembreg e coll. (Stanford University) scoprono la DNA-polimerasi
TECNICHE DI BIOLOGIA MOLECOLARE LA REAZIONE POLIMERASICA A CATENA Principi teorici e aspetti pratici POLYMERASE CHAIN REACTION (PCR) 1955 A. Kronembreg e coll. (Stanford University) scoprono la DNA-polimerasi
Strumenti della Genetica Molecolare Umana (3) Capitoli 6-7-8
 Strumenti della Genetica Molecolare Umana (3) Capitoli 6-7-8 Piccolo test: trova al differenza Gel 2 Gel 1 Gel 1. digestione DNA genomico Gel 2. Digestione inserto cloni genomici BANCHE DI DNA RICOMBINANTE
Strumenti della Genetica Molecolare Umana (3) Capitoli 6-7-8 Piccolo test: trova al differenza Gel 2 Gel 1 Gel 1. digestione DNA genomico Gel 2. Digestione inserto cloni genomici BANCHE DI DNA RICOMBINANTE
PCR (Polymerase Chain Reaction)
 PCR (Polymerase Chain Reaction) Metodo enzimatico estremamente rapido e semplice per produrre una quantità illimitata di copie della sequenza di un singolo gene Sometime a good idea comes to yow when you
PCR (Polymerase Chain Reaction) Metodo enzimatico estremamente rapido e semplice per produrre una quantità illimitata di copie della sequenza di un singolo gene Sometime a good idea comes to yow when you
REAZIONE A CATENA DELLA POLIMERASI. ( PCR =Polymerase Chain Reaction)
 REAZIONE A CATENA DELLA POLIMERASI ( PCR =Polymerase Chain Reaction) Verso la metà degli anni 80, il biochimico Kary Mullis mise a punto un metodo estremamente rapido e semplice per produrre una quantità
REAZIONE A CATENA DELLA POLIMERASI ( PCR =Polymerase Chain Reaction) Verso la metà degli anni 80, il biochimico Kary Mullis mise a punto un metodo estremamente rapido e semplice per produrre una quantità
NEXT- GENERATION DNA SEQUENCING
 NEXT- GENERATION DNA SEQUENCING Introduzione Fino a pochi anni fa i metodi utilizzati per il sequenziamento si basavano sul metodo di Sanger, il quale però risulta avere notevoli svantaggi soprattutto
NEXT- GENERATION DNA SEQUENCING Introduzione Fino a pochi anni fa i metodi utilizzati per il sequenziamento si basavano sul metodo di Sanger, il quale però risulta avere notevoli svantaggi soprattutto
PCR allele-specifica Ibridazione con sonde allele-specifiche (ASO) PCR Real-time con sonde TaqMan Saggio OLA (Oligo Ligation Assay)
 Tecniche per l analisi di singole variazioni: PCR allele-specifica Ibridazione con sonde allele-specifiche (ASO) PCR Real-time con sonde TaqMan Saggio OLA (Oligo Ligation Assay) alcuni SNP (ca. 10%) sono
Tecniche per l analisi di singole variazioni: PCR allele-specifica Ibridazione con sonde allele-specifiche (ASO) PCR Real-time con sonde TaqMan Saggio OLA (Oligo Ligation Assay) alcuni SNP (ca. 10%) sono
Tecnica della reazione a catena della DNA polimerasi o PCR (Polymerase Chain Reaction)
 Tecnica della reazione a catena della DNA polimerasi o PCR (Polymerase Chain Reaction) Una tecnica introdotta da Kary Mullis alla metà degli anni 80 che ha rivoluzionato le tecniche dell ingegneria genetica
Tecnica della reazione a catena della DNA polimerasi o PCR (Polymerase Chain Reaction) Una tecnica introdotta da Kary Mullis alla metà degli anni 80 che ha rivoluzionato le tecniche dell ingegneria genetica
Vettori derivati dal fago λ: batteriofagi filamentosi M13
 Vettori derivati dal fago λ: batteriofagi filamentosi M13 A. Phage display: esibizione della proteina clonata in M13 ed esposta sulla superficie del batteriofago (facile screening dei ricombinanti) mediante
Vettori derivati dal fago λ: batteriofagi filamentosi M13 A. Phage display: esibizione della proteina clonata in M13 ed esposta sulla superficie del batteriofago (facile screening dei ricombinanti) mediante
CORSO INTEGRATO DI GENETICA a.a. 2011-2012. Genetica molecolare in medicina: Analisi di Mutazioni. Cristina Bombieri 7 dicembre 2011
 CORSO INTEGRATO DI GENETICA a.a. 2011-2012 Genetica molecolare in medicina: Analisi di Mutazioni Cristina Bombieri 7 dicembre 2011 GENETICA MOLECOLARE IN MEDICINA SVILUPPI SCIENTIFICI Mappatura gene Identificazione
CORSO INTEGRATO DI GENETICA a.a. 2011-2012 Genetica molecolare in medicina: Analisi di Mutazioni Cristina Bombieri 7 dicembre 2011 GENETICA MOLECOLARE IN MEDICINA SVILUPPI SCIENTIFICI Mappatura gene Identificazione
Quantitative Real-time PCR
 Quantitative Real-time PCR Tecnica che consente la simultanea amplificazione e quantificazione del DNA target AMPLIFICAZIONE: prevede essenzialmente gli step di una classica PCR QUANTIFICAZIONE: effettuata
Quantitative Real-time PCR Tecnica che consente la simultanea amplificazione e quantificazione del DNA target AMPLIFICAZIONE: prevede essenzialmente gli step di una classica PCR QUANTIFICAZIONE: effettuata
DNA revolution. Microsatellites SNPs. Sequenziamento massivo (Next Generation Sequencing NGS)
 DNA revolution Microsatellites SNPs Sequenziamento massivo (Next Generation Sequencing NGS) NGS NGS NGS Non-Sanger-based high-throughput DNA sequencing technology Increasing the throughput Minimizing the
DNA revolution Microsatellites SNPs Sequenziamento massivo (Next Generation Sequencing NGS) NGS NGS NGS Non-Sanger-based high-throughput DNA sequencing technology Increasing the throughput Minimizing the
VET. BIOLOGIA MOLECOLARE CLINICA
 VET. BIOLOGIA MOLECOLARE CLINICA Roberto Giacominelli Stuffler Enzimi di Restrizione Gli enzimi di restrizione sono endonucleasi di origine batterica. Sono stati scoperti con esperimenti di infezione dell
VET. BIOLOGIA MOLECOLARE CLINICA Roberto Giacominelli Stuffler Enzimi di Restrizione Gli enzimi di restrizione sono endonucleasi di origine batterica. Sono stati scoperti con esperimenti di infezione dell
Lezione XLI-XLII martedì 17-1-2012
 Lezione XLI-XLII martedì 17-1-2012 corso di genomica aula 8 orario : Martedì ore 14.00-16.00 Giovedì ore 13.00-15.00 Esami 31- gennaio 2012 7- febbraio 2012 28 - febbraio 2012 D. Frezza Esercitazione II
Lezione XLI-XLII martedì 17-1-2012 corso di genomica aula 8 orario : Martedì ore 14.00-16.00 Giovedì ore 13.00-15.00 Esami 31- gennaio 2012 7- febbraio 2012 28 - febbraio 2012 D. Frezza Esercitazione II
REPLICAZIONE DEL DNA 1
 REPLICAZIONE DEL DNA 1 La replicazione del DNA è semiconservativa: ciascuno dei due filamenti parentali serve da stampo per la sintesi di un nuovo filamento e le due nuove doppie eliche sono costituite
REPLICAZIONE DEL DNA 1 La replicazione del DNA è semiconservativa: ciascuno dei due filamenti parentali serve da stampo per la sintesi di un nuovo filamento e le due nuove doppie eliche sono costituite
Tecnologia del DNA ricombinante
 Tecnologia del DNA ricombinante Scoperte rivoluzionarie che hanno permesso lo studio del genoma e della funzione dei singoli geni Implicazioni enormi nel progresso della medicina: comprensione malattie
Tecnologia del DNA ricombinante Scoperte rivoluzionarie che hanno permesso lo studio del genoma e della funzione dei singoli geni Implicazioni enormi nel progresso della medicina: comprensione malattie
Metodica fu ideata nel 1983
 Metodica fu ideata nel 1983 PCR - Polymerase Chain Reaction ideata nel 1983 da Kary B. Mullis il quale ottenne, per questo, il premio Nobel per la chimica (1993). Questa tecnica, utilizzando i principi
Metodica fu ideata nel 1983 PCR - Polymerase Chain Reaction ideata nel 1983 da Kary B. Mullis il quale ottenne, per questo, il premio Nobel per la chimica (1993). Questa tecnica, utilizzando i principi
Differenti tipi di PCR
 Differenti tipi di PCR Colony PCR Nested PCR Multiplex PCR AFLP PCR Hot start PCR In situ PCR Inverse PCR Asymmetric PCR Long PCR Long accurate PCR Reverse transcriptase PCR Allele Specific PCR Real time
Differenti tipi di PCR Colony PCR Nested PCR Multiplex PCR AFLP PCR Hot start PCR In situ PCR Inverse PCR Asymmetric PCR Long PCR Long accurate PCR Reverse transcriptase PCR Allele Specific PCR Real time
Metodiche Molecolari
 Metodiche Molecolari La rivelazione degli acidi nucleici virali è un altro saggio che può essere utilizzato sia per verificare la presenza di un virus in un determinato campione biologico, sia per studiare
Metodiche Molecolari La rivelazione degli acidi nucleici virali è un altro saggio che può essere utilizzato sia per verificare la presenza di un virus in un determinato campione biologico, sia per studiare
LA REPLICAZIONE DEL DNA
 www.fisiokinesiterapia.biz LA REPLICAZIONE DEL DNA REPLICAZIONE DEL DNA Durante il processo di replicazione la doppia elica del DNA si srotola e ciascuno dei due filamenti funziona da stampo per un nuovo
www.fisiokinesiterapia.biz LA REPLICAZIONE DEL DNA REPLICAZIONE DEL DNA Durante il processo di replicazione la doppia elica del DNA si srotola e ciascuno dei due filamenti funziona da stampo per un nuovo
Quantitative real time Polymerase Chain Reaction
 Quantitative real time Polymerase Chain Reaction sonde TaqMan attività 5 3 esonucleasica della DNA polimerasi Un filamento di DNA polimerizzato = 1 emissione di fluorescenza Permette di vedere cosa succede
Quantitative real time Polymerase Chain Reaction sonde TaqMan attività 5 3 esonucleasica della DNA polimerasi Un filamento di DNA polimerizzato = 1 emissione di fluorescenza Permette di vedere cosa succede
Amplificazione del DNA tramite reazione a catena della polimerasi (POLYMERASE CHAIN REACTION; PCR) e sue applicazioni in ambito biomedico
 Amplificazione del DNA tramite reazione a catena della polimerasi (POLYMERASE CHAIN REACTION; PCR) e sue applicazioni in ambito biomedico Dottoressa Camerin Consuelo Laboratorio Oncoematologia Pediatrica
Amplificazione del DNA tramite reazione a catena della polimerasi (POLYMERASE CHAIN REACTION; PCR) e sue applicazioni in ambito biomedico Dottoressa Camerin Consuelo Laboratorio Oncoematologia Pediatrica
Tecniche molecolari per lo studio degli acidi nucleici
 Tecniche molecolari per lo studio degli acidi nucleici Prof.ssa Flavia Frabetti aa. 2010-11 Estrazione acidi nucleici (DNA o RNA) Verifica tramite elettroforesi su gel di agarosio Amplificazione o clonaggio
Tecniche molecolari per lo studio degli acidi nucleici Prof.ssa Flavia Frabetti aa. 2010-11 Estrazione acidi nucleici (DNA o RNA) Verifica tramite elettroforesi su gel di agarosio Amplificazione o clonaggio
nei tessuti biologici e in varie condizioni sperimentali Prof.ssa: Diana Conte Dott.ssa: Giulia Maria Camerino
 REAL-TIME PCR QUANTIFICAZIONE DELL ESPRESSIONE ESPRESSIONE GENICA Un metodo per misurare l mrnal nei tessuti biologici e in varie condizioni sperimentali Prof.ssa: Diana Conte Dott.ssa: Giulia Maria Camerino
REAL-TIME PCR QUANTIFICAZIONE DELL ESPRESSIONE ESPRESSIONE GENICA Un metodo per misurare l mrnal nei tessuti biologici e in varie condizioni sperimentali Prof.ssa: Diana Conte Dott.ssa: Giulia Maria Camerino
PCR. PCR o reazione di polimerizzazione a catena. Amplificazione esponenziale di DNA. Puo amplificare un tratto di DNA per piu di 1 milione di volte
 PCR Prof.ssa Flavia Frabetti PCR o reazione di polimerizzazione a catena Fine anni 80 Amplificazione esponenziale di DNA. Puo amplificare un tratto di DNA per piu di 1 milione di volte Permette di estrarre
PCR Prof.ssa Flavia Frabetti PCR o reazione di polimerizzazione a catena Fine anni 80 Amplificazione esponenziale di DNA. Puo amplificare un tratto di DNA per piu di 1 milione di volte Permette di estrarre
REAL-TIME PCR QUANTIFICAZIONE DELL ESPRESSIONE GENICA
 REAL-TIME PCR QUANTIFICAZIONE DELL ESPRESSIONE GENICA Un metodo per misurare l mrna nei tessuti biologici e in varie condizioni sperimentali Identificazione del meccanismo di azione dei farmaci Farmaco
REAL-TIME PCR QUANTIFICAZIONE DELL ESPRESSIONE GENICA Un metodo per misurare l mrna nei tessuti biologici e in varie condizioni sperimentali Identificazione del meccanismo di azione dei farmaci Farmaco
Reazione a catena della polimerasi (PCR) ed elettroforesi
 Gioele Casagranda, Camilla Larentis, Emanuele Pallaoro, Filippo Quattrocchi Povo, 1 marzo 2016 P r o g e t t o C L I L - E s p e r i m e n t o f i n a l e Reazione a catena della polimerasi (PCR) ed elettroforesi
Gioele Casagranda, Camilla Larentis, Emanuele Pallaoro, Filippo Quattrocchi Povo, 1 marzo 2016 P r o g e t t o C L I L - E s p e r i m e n t o f i n a l e Reazione a catena della polimerasi (PCR) ed elettroforesi
Il Sequenziamento Tecniche e Strategie
 Il Sequenziamento Tecniche e Strategie Metodi per il sequenziamento del DNA Metodo della degradazione chimica (Maxam & Gilbert, 1977) La sequenza di una molecola di ds DNA viene determinata mediante trattamento
Il Sequenziamento Tecniche e Strategie Metodi per il sequenziamento del DNA Metodo della degradazione chimica (Maxam & Gilbert, 1977) La sequenza di una molecola di ds DNA viene determinata mediante trattamento
Metodi di Quantificazione dell Espressione Genica
 Metodi di Quantificazione dell Espressione Genica Cosa significa quantificare l espressione genica? Alcune tecniche per quantificare l espressione genica Parte I: RT PCR qrt PCR (Real Time) Parte II: Northern
Metodi di Quantificazione dell Espressione Genica Cosa significa quantificare l espressione genica? Alcune tecniche per quantificare l espressione genica Parte I: RT PCR qrt PCR (Real Time) Parte II: Northern
Protocollo di Real-Time RT-PCR per la diagnosi del fitoplasma della Moria del Pero. Claudio Ratti, Chiara Lanzoni e Carlo Poggi Pollini
 Protocollo di Real-Time RT-PCR per la diagnosi del fitoplasma della Moria del Pero Claudio Ratti, Chiara Lanzoni e Carlo Poggi Pollini Moria del pero (Candidatus Phytoplasma pyri) Fitoplasmi: Microrganismi
Protocollo di Real-Time RT-PCR per la diagnosi del fitoplasma della Moria del Pero Claudio Ratti, Chiara Lanzoni e Carlo Poggi Pollini Moria del pero (Candidatus Phytoplasma pyri) Fitoplasmi: Microrganismi
DNA - DENATURAZIONE E RIASSOCIAZIONE
 DNA - DENATURAZIONE E RIASSOCIAZIONE Il doppio strand della molecola di DNA può denaturarsi dando due singoli strand ad alte temperature (>90 C). Due strand di DNA complementari possono accoppiarsi dando
DNA - DENATURAZIONE E RIASSOCIAZIONE Il doppio strand della molecola di DNA può denaturarsi dando due singoli strand ad alte temperature (>90 C). Due strand di DNA complementari possono accoppiarsi dando
Progetto :TRIFOGLIO UNIVERSITA CATTOLICA DEL SACRO CUORE Piacenza. O.G.M. Vegetali
 Progetto :TRIFOGLIO UNIVERSITA CATTOLICA DEL SACRO CUORE Piacenza O.G.M. Vegetali Identificazione di un O.G.M. e metodi di analisi del DNA transgenico Marco Nani 5BL Liceo Scientifico Mattei di Fiorenzuola
Progetto :TRIFOGLIO UNIVERSITA CATTOLICA DEL SACRO CUORE Piacenza O.G.M. Vegetali Identificazione di un O.G.M. e metodi di analisi del DNA transgenico Marco Nani 5BL Liceo Scientifico Mattei di Fiorenzuola
Dott.ssa Quintarelli Concetta
 Dott.ssa Quintarelli Concetta Estrazione e quantizzazione degli acidi nucleici Pre-PCR Accetazione Post-PCR Refertazione Area PCR GUANTI MONOUSO PUNTALI CON FILTRO CESTELLO PER GHIACCIO TUBINI PCR Materiale
Dott.ssa Quintarelli Concetta Estrazione e quantizzazione degli acidi nucleici Pre-PCR Accetazione Post-PCR Refertazione Area PCR GUANTI MONOUSO PUNTALI CON FILTRO CESTELLO PER GHIACCIO TUBINI PCR Materiale
Real-Time RT-PCR (QPCR) quantitativa
 Real-Time RT-PCR (QPCR) quantitativa Metodi in uso comune per rilevare/quantificare trascritti Northern blotting e ibridazione in situ 2. RNAse protection assays 3. cdna microarrays 4. RT-PCR in end-point
Real-Time RT-PCR (QPCR) quantitativa Metodi in uso comune per rilevare/quantificare trascritti Northern blotting e ibridazione in situ 2. RNAse protection assays 3. cdna microarrays 4. RT-PCR in end-point
PRINCIPALI APPLICAZIONI DELLA PCR. PRINCIPALI TIPI DI PCR a) PRINCIPALI TIPI DI PCR b) PRINCIPALI TIPI DI PCR a)
 EAZIONE A CATENA DELLA POLIMEASI (PC) PINCIPALI APPLICAZIONI DELLA PC UPPE primer LOWE primer GENE X 1. Identificazione di agenti patogeni nell uomo, negli animali o negli alimenti (batteri e virus) 2.
EAZIONE A CATENA DELLA POLIMEASI (PC) PINCIPALI APPLICAZIONI DELLA PC UPPE primer LOWE primer GENE X 1. Identificazione di agenti patogeni nell uomo, negli animali o negli alimenti (batteri e virus) 2.
Contenuto di DNA aploide in alcune specie
 Contenuto di DNA aploide in alcune specie 1-10 2 kb 10 3 kb 10 4 kb 10 5-10 8 kb Dimensioni del genoma Paradosso del valore C Non c è una correlazione tra la quantità di DNA e la complessità di un organismo
Contenuto di DNA aploide in alcune specie 1-10 2 kb 10 3 kb 10 4 kb 10 5-10 8 kb Dimensioni del genoma Paradosso del valore C Non c è una correlazione tra la quantità di DNA e la complessità di un organismo
I marcatori molecolari. Dipartimento di Scienze Agronomiche e Genetica Vegetale Agraria Corso di Genetica Agraria Giovanna Attene
 I marcatori molecolari Dipartimento di Scienze Agronomiche e Genetica Vegetale Agraria Corso di Genetica Agraria Giovanna Attene Marcatori molecolari del DNA I marcatori molecolari sono sequenze di DNA
I marcatori molecolari Dipartimento di Scienze Agronomiche e Genetica Vegetale Agraria Corso di Genetica Agraria Giovanna Attene Marcatori molecolari del DNA I marcatori molecolari sono sequenze di DNA
Duplicazione del DNA. 6 Dicembre 2007
 Duplicazione del DNA 6 Dicembre 2007 Duplicazione - Trascrizione - Traduzione DNA Trascrizione DNA - La DUPLICAZIONE è il processo che porta alla formazione di copie delle molecole di DNA ed al trasferimento
Duplicazione del DNA 6 Dicembre 2007 Duplicazione - Trascrizione - Traduzione DNA Trascrizione DNA - La DUPLICAZIONE è il processo che porta alla formazione di copie delle molecole di DNA ed al trasferimento
Ibridazione in situ per mrna: tecnica e interpretazione
 Patologia nodulare della tiroide: focus sugli approcci diagnostici Ibridazione in situ per mrna: tecnica e interpretazione Isabella Giovannoni U.O.C. Anatomia Patologica Ibridazione -> appaiamento di sequenze
Patologia nodulare della tiroide: focus sugli approcci diagnostici Ibridazione in situ per mrna: tecnica e interpretazione Isabella Giovannoni U.O.C. Anatomia Patologica Ibridazione -> appaiamento di sequenze
Tecniche di sequenziamento del DNA
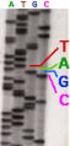 Tecniche di sequenziamento del DNA -Metodo di Maxam e Gilbert (della degradazione chimica del DNA) -Metodo di Sanger (a terminazione di catena) Metodo di Maxam-Gilbert Questo metodo, basato sulla degradazione
Tecniche di sequenziamento del DNA -Metodo di Maxam e Gilbert (della degradazione chimica del DNA) -Metodo di Sanger (a terminazione di catena) Metodo di Maxam-Gilbert Questo metodo, basato sulla degradazione
Dr. Tommaso Giordani SEQUENZIAMENTO SANGER E ANALISI DI SEQUENZE DI DNA
 Dr. Tommaso Giordani SEQUENZIAMENTO SANGER E ANALISI DI SEQUENZE DI DNA OBIETTIVI DELLA GENOMICA MAPPE GENETICHE e FISICHE sempre più accurate SEQUENZIAMENTO GENOMI GENOMICA COMPARATIVA confronto tra genomi
Dr. Tommaso Giordani SEQUENZIAMENTO SANGER E ANALISI DI SEQUENZE DI DNA OBIETTIVI DELLA GENOMICA MAPPE GENETICHE e FISICHE sempre più accurate SEQUENZIAMENTO GENOMI GENOMICA COMPARATIVA confronto tra genomi
Amplificazione mediante PCR (Polymerase Chain Reaction) del DNA estratto dalla saliva.
 OBIETTIVO DEL LAVORO SPERIMENTALE: TIPIZZAZIONE DEI CROMOSOMI SESSUALI X e Y Amplificazione mediante PCR (Polymerase Chain Reaction) del DNA estratto dalla saliva. Cromosoma X Cromosoma y La tipizzazione
OBIETTIVO DEL LAVORO SPERIMENTALE: TIPIZZAZIONE DEI CROMOSOMI SESSUALI X e Y Amplificazione mediante PCR (Polymerase Chain Reaction) del DNA estratto dalla saliva. Cromosoma X Cromosoma y La tipizzazione
