Chimica Farmaceutica. DOCKING and Structure Based Drug Design
|
|
|
- Teodora Antonucci
- 5 anni fa
- Visualizzazioni
Transcript
1 Chimica Farmaceutica DOCKING and Structure Based Drug Design
2 Ricognizione molecolare: Insieme di interazioni tra molecole e macromolecole Modello Lock and key La proteina ha una sua conformazione all interno del quale il ligando fitta perfettamente. Emil Fischer(1890). Modello del fitting indotto Il sito attivo della macromolecola può essere modificato a seconda di come interagisce il ligando. Daniel Koshland Natura delle interazioni? Intensità della ricognizione molecolare? Molecular Docking Pagina 2 Fischer E. (1894). "Einfluss der Configuration auf die Wirkung der Enzyme". Ber. Dt. Chem. Ges. 27 (3):
3 Ricognizione molecolare La complementarità molecolare altamente specifica tra key (ligando) e lock (recettore) gioca un ruolo chiave nei processi biologici. La capacità del recettore di agganciarsi al suo ligando con alta specificità e affinità è dovuta alla formazione di una serie di legami deboli e interazioni favorevoli. Interazioni specifiche ligando-recettore: Interazioni elettrostatiche (Non- Cov) Forze di van der Waals (Non-Cov) Interazioni π - π Coordinazione con Metalli Interazioni idrofobiche Effetti elettromagnetici COMPLEMENTARITA MOLECOLARE Molecular Docking Pagina 3
4 Forze di van der Waals Debole attrazione intermolecolare causata da dipoli molecolari indotti. Es. Interazione tra il ligando Wy-14,643 e il sito attivo della PPARα Ad esempio, se una molecola di ossigeno si avvicina ad una molecola di acqua orientata verso di essa con l'atomo di ossigeno, la frazione di carica negativa presente su quest'ultimo respinge la nuvola elettronica della molecola di ossigeno e attira la carica positiva nucleare. Cio' determina uno spostamento del baricentro della carica negativa rispetto a quello della carica positiva nella molecola di ossigeno e quindi induce una polarita'. Molecular Docking Pagina 4
5 Interazioni Elettrostatiche La legge di Coulomb In un mezzo isolante diverso dall'aria la forza F, a parità di cariche e di distanza, risulta generalmente minore. La forza di Coulomb si scrive allora: dove εr è un numero che prende il nome di costante dielettrica relativa (permittività elettrica relativa). Il prodotto εr x εo si indica con ε, e si chiama costante dielettrica del mezzo (permittività del mezzo). δ+ δ Molecular Docking Pagina 5 δ δ+
6 Interazioni Elettrostatiche Il legame Idrogeno ElegH (solv) ElegH (comp) determina se i legami-h contribuiscono o no all affinità SOLV Es. Legame-H tra l Indinavir, una molecola d acqua e la Ile50 della proteasi dell HIV-1 (1HSG in PDB) LIG LIG REC Molecular Docking Pagina 6
7 Il fattore entropico ed entalpico nel binding SISTEMA: Recettore Ligando Complesso Solvente Solvente La formazione di un complesso è guidata dal cambiamento di ENTALPIA ed ENTROPIA del sistema L equazione fondamentale è: Δ G = ΔH TΔS dove ΔG = variazione energia libera, ΔH = variazione entalpia, ΔS = variazione entropia, T = temperatura (K) Molecular Docking Pagina 7
8 Effetti di solvatazione (Termine Entropico + Entalpico) La ricognizione molecolare tra due molecole avviene in ambiente acquoso Le molecole di acqua mediano l interazione attraverso ponti idrogeno Rottura e formazione di legami-h La desolvatazione del ligando e della proteina attraverso la complessazione è: Sfavorevole(Zone Elettrostatiche) Carica del solvente Screening delle interazioni elettrostatiche sulla superficie della macromolecola Favorevole (zone apolari) Cavità nel sito attivo Riorganizzazione delle molecole d acqua Interazioni di tipo van der Waals tra solvente e ligando Gli effetti di desolvatazione sono proporzionali all area superficiale accessibile Molecular Docking Pagina 8
9 Il fattore entropico nel binding ΔGbinding,solution = ΔGbinding,vacuo + ΔGsolvation(EI) - ΔGsolvation(E+I) La stabilità di un complesso può essere valutata determinando la costante di equilibrio, che è correlata alla variazione di energia libera: ΔG = ΔG0 RT ln Kd dove ΔG0=variazione dell energia libera in condizioni standard, R= costante dei gas,t=temperatura assoluta, Kd = costante di legame espressa come costante di dissociazione con [R] + [L] [RL] reazione di formazione del complesso è: Kd = [R] [L] / [RL] Kd è definita come la concentrazione del ligando per la quale il 50% dei siti del recettore sono occupati. L effetto idrofobico è il termine maggiormente stabilizzante per i complessi biomolecolari, mentre le interazioni coulombiane e i legami idrogeno forniscono specificità alle interazioni proteina-ligando. Molecular Docking Pagina 9
10 Il fattore entropico nel binding Molecular Docking Pagina 10
11 Il fattore entropico nel binding Es. Aricept in soluzione Es. Aricept nel sito attivo della acetilcolinesterasi I gradi di libertà congelati durante la complessazione rendono il ligando sfavorito al binding Molecular Docking Pagina 11
12 Interazioni π 1. Interazioni π-π 2. Interazioni OH-π 3. Interazioni cationi-π Es. Interazioni π tra l Aricept (farmaco anti-alzheimer approvato dalla FDA) e l acetilcolinesterasi Molecular Docking Pagina 12
13 Coordinazione con Metalli Legame covalente di coordinazione O S O S O O S NH 2 NH Dorzolamide: Inibitore dell anidrasi carbonica, approvato dalla FDA come agente anti-glaucoma Molecular Docking Pagina 13
14 DOCKING: Le Scoring Functions Utility? Virtual Screening De novo design Lead optimization Molecular Docking Pagina 14
15 Ligand Docking Posa o Binding Mode: posizione, orientamento e conformazione di un ligando sulla superficie di macromolecole biologiche Binding Mode sperimentale: Estratta da dati cristallografici e stimata come la migliore posa in termini di free binding energy. Docking: Metodo computazionale utilizzato per la predizione di un binding mode il più vicino possibile allo sperimentale (<2 Å) Molecular Docking Pagina 15
16 Ligand Docking L approccio standard: Campionamento dello spazio conformazionale del ligando nel binding site della macromolecola. Scoring di tutte le possibili conformazioni del ligando. Selezione delle pose con il miglior valore di energia (score) rispetto alla posa iniziale. Livelli differenti di approssimazione: La proteina e il ligando sono rigidi. La proteina è rigida e il ligando è flessibile. La proteina e il ligando sono flessibili. Molecular Docking Pagina 16
17 DOCKING Tre tipi ti ricerca conformazionale: 1. Ricerca sistematica (esplorazione combinatoriale dei gradi di libertà, costruzione incrementale) 1. Ricerca stocastica (Monte Carlo, Algoritmo genetico) 2. Ricerca deterministica (Minimizzazione, Dinamica Molecolare) Molecular Docking Pagina 17
18 Details Campionamento dello spazio configurazionale Diversi algoritmi sviluppati per trovare la miglior conformazione del ligando nel sito di legame. Scoring dei complessi proteina-ligando Scopo dello scoring: identificare il modo di binding corretto attraverso la sua minore energia, se la configurazione ad energia minore è assunta essere quella corretta. Sono state sviluppate diverse funzioni per misurare l affinità di binding ligando-recettore negli algoritmi di docking Funzioni di scoring = funzioni designate a classificare complessi proteina-ligando differenti, a seconda delle loro affinità di binding. Molecular Docking Pagina 18
19 Molecular Docking Pagina 19
20 and applications Molecular Docking Pagina 20
21 Workflow del protocollo di allineamento: L allineamento Structure-Based Molecular Docking Pagina 21
22 BD= La conformazione con il minor valore di binding energy generata da Autodock BC= La conformazione a più bassa energia del cluster più popolato BF= La conformazione con il minor valore di rmsd Molecular Docking Pagina 22
23 STRUCTURE-BASED DRUG DESIGN (SBDD). UN EFFICIENTE OTTIMIZZAZIONE MEDIANTE CROSS- DOCKING
24 MOLECULAR DOCKING DOCKING MOLECOLARE SAMPLING SCORING FUNCTION Identificazione di composti di interesse farmaceutico Comprensione meccanismi interazione Ottimizzazione del lead Bioremediation Molecular Docking Pagina 24
25 MOLECULAR DOCKING Docking Rigido Semi-Flessibile Flessibile Molecular Docking Pagina 25
26 VALIDAZIONE Docking Validazione Docking Re Docking Cross Docking Molecular Docking Pagina 26
27 RE-docking (RD) Re Docking Self Re-Docking (ECRD) Re-Docking Modeled (MCRD) Molecular Docking Pagina 27
28 Cross-docking (CD) Cross Docking Self Cross-Docking (ECCD) Cross Docking Modeled (MCCD) Molecular Docking Pagina 28
29 panoramica Surflex DATABASE ORIGINALE SELEZIONE TARGET Training Set Dock TRAINING SET TEST SET Paradocks Autodock pmf04 p-score plp PREPARAZIONI PROTEINE DOCKING CON 9 APPLICAZIONI CONFORMAZIONI Plants chemplp plp95 CLUSTERIZZAZIONE VALUTAZIONE Test Set AutodockVina VALIDAZIONE Molecular Docking Pagina 29
30 Procedura Metodo unificato Automatizzazione Scelta Programma Parametri base Spazio di ricerca 5Å Stesse molecole di partenza Metodica unificata per la valutazione dei risultati ottenuti Molecular Docking Pagina 30
31 Pulizia delle Proteine Eliminazione solvente Eliminazione metalli strutturali Eliminazione catene inutili Ricostruzione amminoacidi tagliati Protonazione Cariche amminoacidi Allineamento Complessi Divisione in Cluster Molecular Docking Pagina 31
32 ALLINEAMENTO/CLUSTER camp-dependent protein Kinase catalytic subunit alpha Cluster 1 Binding site 1 Riunificazione lock/key nel complesso Allineamento Divisione complessi in lock e key Proteine Pulite Binding site 2 Cluster 2 Molecular Docking Pagina 32
33 PROGRAMMI USATI Plants Vina Autodock Surflex Paradocks Dock Molecular Docking Pagina 33
34 Clusterizzazione Predizione Binding mode Clusterizzazione BD (Best Docked) BC (Best Cluster) Rapido Automatizzabile Binding Energy RMSD originale docking Molecular Docking Pagina 34
35 EXPERIMENTAL vs MODELED DA (Docking Accuracy) = f RMSD (f RMSD 3 - f RMSD 2 ) ECRD MCRD ECRD vs MCRD Software DA% DA% Surflex Paradocks pmf Paradocks p-score Vina Dock Autodock Plants chemplp Plants plp Plants plp Media Molecular Docking Pagina 35
36 EXPERIMENTAL vs MODELED DA (Docking Accuracy) = f RMSD (f RMSD 3 - f RMSD 2 ) ECCD MCCD ECCD vs MCCD BD BC BD BC BD Software DA% DA% DA% Surflex Paradocks pmf Paradocks p-score Vina Dock Autodock Plants chemplp Plants plp Plants plp Media Molecular Docking Pagina 36
37 RE-DOCKING vs CROSS-DOCKING DA (Docking Accuracy) = f RMSD (f RMSD 3 - f RMSD 2 ) ECRD vs BD-ECCD MCRD vs BD-MCCD Software DA% Software DA% Surflex Paradocks pmf Paradocks p-score Vina Dock Autodock Plants chemplp Plants plp Plants plp Media Surflex Paradocks pmf Paradocks p-score Vina Dock Autodock Plants chemplp Plants plp Plants plp Media Molecular Docking Pagina 37
38 N complessi Prestazioni singoli programmi Cross-Docking Cross -Docking Modeled RMSD RMSD Molecular Docking Pagina 38
39 Prima scelta RMSD medio Deviazione Standard RMSD Autodock Sperimentale PLANTS chemplp Molecular Docking Pagina 39
40 Prestazioni Prima scelta Cross-Docking Cross -Docking Modeled % complessi 72.47% 68.35% % 81.65% RMSD RMSD Molecular Docking Pagina 40
41 Validazione esterna Validazione Cross Docking Modeled % % complessi % Test 2 molecole % complessi % Test molecola simile Test molecola dissimile RMSD RMSD Molecular Docking Pagina 41
42 conclusioni RD soffre della conformazione di input maggiormente del CD In termini di docking accuracy il CD garantisce prestazioni maggiori di RD La scelta del programma mediante validazione con CD è risultata effettivamente predittiva Limitazioni Ulteriori studi sono in corso su un più vasto numero di complessi al fine di ulteriormente confermare I risultati ottenuti Molecular Docking Pagina 42
Chimica Farmaceutica. DOCKING and Structure Based Drug Design
 Chimica Farmaceutica DOCKING and Structure Based Drug Design Ricognizione molecolare: Insieme di interazioni tra molecole e macromolecole Modello Lock and key La proteina ha una sua conformazione all interno
Chimica Farmaceutica DOCKING and Structure Based Drug Design Ricognizione molecolare: Insieme di interazioni tra molecole e macromolecole Modello Lock and key La proteina ha una sua conformazione all interno
Chimica Farmaceutica. DOCKING and Structure Based Drug Design
 Chimica Farmaceutica DOCKING and Structure Based Drug Design Tipologie di allineamento Scelta del training set Allineamento delle molecole Calcolo del campi di interazione molecolare (MIF) Generazione
Chimica Farmaceutica DOCKING and Structure Based Drug Design Tipologie di allineamento Scelta del training set Allineamento delle molecole Calcolo del campi di interazione molecolare (MIF) Generazione
Le Biomolecole II parte. Lezioni d'autore di Giorgio Benedetti
 Le Biomolecole II parte Lezioni d'autore di Giorgio Benedetti LA STRUTTURA TERZIARIA DI UNA PROTEINA La struttura tridimensionale adottata da una proteina è detta struttura terziaria. Essa prende in considerazione
Le Biomolecole II parte Lezioni d'autore di Giorgio Benedetti LA STRUTTURA TERZIARIA DI UNA PROTEINA La struttura tridimensionale adottata da una proteina è detta struttura terziaria. Essa prende in considerazione
Macromolecole Biologiche Interazioni non covalenti
 Interazioni non covalenti D H A δ - δ + δ - Le interazioni non covalenti Interazioni fra atomi che non sono legati da legami covalenti. Le interazioni non covalenti sono molto meno intense rispetto alle
Interazioni non covalenti D H A δ - δ + δ - Le interazioni non covalenti Interazioni fra atomi che non sono legati da legami covalenti. Le interazioni non covalenti sono molto meno intense rispetto alle
Le interazioni reversibili tra le macromolecole sono mediate da 3 specie di legami non covalenti:
 Le interazioni reversibili tra le macromolecole sono mediate da 3 specie di legami non covalenti: 1) Legami elettrostatici 2) Legami idrogeno 3) Forze di van der Waals Le interazioni deboli tra biomolecole
Le interazioni reversibili tra le macromolecole sono mediate da 3 specie di legami non covalenti: 1) Legami elettrostatici 2) Legami idrogeno 3) Forze di van der Waals Le interazioni deboli tra biomolecole
UNIVERSITÀ DEGLI STUDI DI TERAMO CORSO DI LAUREA IN BIOTECNOLOGIE CORSO MONODISCIPLINARE: BIOCHIMICA (6CFU)
 UNIVERSITÀ DEGLI STUDI DI TERAMO CORSO DI LAUREA IN BIOTECNOLOGIE CORSO MONODISCIPLINARE: BIOCHIMICA (6CFU) Roberto Giacominelli Stuffler IL C.M. BIOCHIMICA È SUDDIVISO IN DUE UNITÀ DIDATTICHE: A) BIOCHIMICA
UNIVERSITÀ DEGLI STUDI DI TERAMO CORSO DI LAUREA IN BIOTECNOLOGIE CORSO MONODISCIPLINARE: BIOCHIMICA (6CFU) Roberto Giacominelli Stuffler IL C.M. BIOCHIMICA È SUDDIVISO IN DUE UNITÀ DIDATTICHE: A) BIOCHIMICA
Le interazioni deboli:
 Le interazioni deboli: sono legami non covalenti sono da 1 a 3 ordini di grandezza più deboli dei legami covalenti sono alcune volte maggiori della tendenza a dissociare dovuta all agitazione termica delle
Le interazioni deboli: sono legami non covalenti sono da 1 a 3 ordini di grandezza più deboli dei legami covalenti sono alcune volte maggiori della tendenza a dissociare dovuta all agitazione termica delle
I Legami intermolecolari
 I Legami intermolecolari Legami tra gli atomi di una molecola riepilogando Ionico D >1,9 Legami forti Covalente D = differenza di elettronegatività tra gli atomi Metallico (dovuto alla dislocazione di
I Legami intermolecolari Legami tra gli atomi di una molecola riepilogando Ionico D >1,9 Legami forti Covalente D = differenza di elettronegatività tra gli atomi Metallico (dovuto alla dislocazione di
Corso di BIOINFORMATICA Applicazioni BIO-Mediche
 Corso di BIOINFORMATICA Applicazioni BIO-Mediche - Introduzione al Molecular Docking (algoritmi di ricerca e Moderni software) Pietro BUFFA Responsabile Unità Operativa di Bioinformatica Dipartimento di
Corso di BIOINFORMATICA Applicazioni BIO-Mediche - Introduzione al Molecular Docking (algoritmi di ricerca e Moderni software) Pietro BUFFA Responsabile Unità Operativa di Bioinformatica Dipartimento di
Legame Covalente Polare e MOT. Polarità del legame aumenta con differenza di elettronegatività.
 Legame Covalente Polare e MOT Polarità del legame aumenta con differenza di elettronegatività. Legame Ionico Se differenza di elettronegatività è molto grande si ottiene un legame ionico. Legame Ionico
Legame Covalente Polare e MOT Polarità del legame aumenta con differenza di elettronegatività. Legame Ionico Se differenza di elettronegatività è molto grande si ottiene un legame ionico. Legame Ionico
FORZE INTERMOLECOLARI
 FORZE INTERMOLECOLARI Oltre alle forze intramolecolari (legami) esistono nella materia forze intermolecolari (tra molecole diverse), anch esse dovute ad interazioni elettrostatiche. Le forze intermolecolari
FORZE INTERMOLECOLARI Oltre alle forze intramolecolari (legami) esistono nella materia forze intermolecolari (tra molecole diverse), anch esse dovute ad interazioni elettrostatiche. Le forze intermolecolari
Chimica Supramolecolare
 Chimica Supramolecolare Core Concepts in Supramolecular Chemistry and Nanochemistry J. W. Steed, D. R. Turner, K. J. Wallace Wiley Chimica Supramolecolare La Chimica oltre le molecole Chimica nella seconda
Chimica Supramolecolare Core Concepts in Supramolecular Chemistry and Nanochemistry J. W. Steed, D. R. Turner, K. J. Wallace Wiley Chimica Supramolecolare La Chimica oltre le molecole Chimica nella seconda
FUNZIONI delle PROTEINE
 FUNZIONI delle PROTEINE Ha le dimensioni del reciproco di una concentrazione (M -1 ) Ha le dimensioni di una concentrazione (M) La frazione dei siti occupati rispetto ai siti totali è definita come θ FRAZIONE
FUNZIONI delle PROTEINE Ha le dimensioni del reciproco di una concentrazione (M -1 ) Ha le dimensioni di una concentrazione (M) La frazione dei siti occupati rispetto ai siti totali è definita come θ FRAZIONE
Le forze intermolecolari Manifestazione delle forze intermolecolari
 1 Le forze intermolecolari Manifestazione delle forze intermolecolari 2 I gas nobili (He, Ne, Ar...) che NON formano legami chimici dovrebbero restare gassosi a qualsiasi temperatura. Invece a T molto
1 Le forze intermolecolari Manifestazione delle forze intermolecolari 2 I gas nobili (He, Ne, Ar...) che NON formano legami chimici dovrebbero restare gassosi a qualsiasi temperatura. Invece a T molto
Legami secondari e lo stato fisico
 Legami secondari e lo stato fisico Gli stati aggregati (stato solido, liquido) richiedono la presenza di forze intermolecolari tra le molecole che compongono la sostanza. Legame ione dipolo (si forma fra
Legami secondari e lo stato fisico Gli stati aggregati (stato solido, liquido) richiedono la presenza di forze intermolecolari tra le molecole che compongono la sostanza. Legame ione dipolo (si forma fra
CENNI SUL TIPO DI FORZE
 CENNI SUL TIPO DI FORZE Forze deboli che influenzano la struttura delle proteine: le interazioni di van der Waals repulsione attrazione Forze attrattive dovute a interazioni istantanee che si generano
CENNI SUL TIPO DI FORZE Forze deboli che influenzano la struttura delle proteine: le interazioni di van der Waals repulsione attrazione Forze attrattive dovute a interazioni istantanee che si generano
LABORATORIO DI ANALISI BIO-FARMACEUTICA E FARMACEUTICA. Prof.ssa Manuela Bartolini Prof.ssa Rita Gatti
 LABORATORIO DI ANALISI BIO-FARMACEUTICA E FARMACEUTICA Prof.ssa Manuela Bartolini Prof.ssa Rita Gatti Prof.ssa M. Bartolini Prof.ssa R. Gatti manuela.bartolini3@unibo.it rita.gatti2@unibo.it Daniele Tedesco
LABORATORIO DI ANALISI BIO-FARMACEUTICA E FARMACEUTICA Prof.ssa Manuela Bartolini Prof.ssa Rita Gatti Prof.ssa M. Bartolini Prof.ssa R. Gatti manuela.bartolini3@unibo.it rita.gatti2@unibo.it Daniele Tedesco
Fondamenti di Chimica Farmaceutica
 Cos è un farmaco? Un farmaco è una sostanza che interagisce con un sistema biologico producendo un effetto (risposta) biologico Morfina Analgesia Cianuro Letale Veleno di serpente Letale (dannoso) LSD
Cos è un farmaco? Un farmaco è una sostanza che interagisce con un sistema biologico producendo un effetto (risposta) biologico Morfina Analgesia Cianuro Letale Veleno di serpente Letale (dannoso) LSD
Chimica generale e inorganica Studia gli elementi e i composti inorganici
 Chimica generale e inorganica Studia gli elementi e i composti inorganici Chimica organica Studia i composti organici, cioè composti che contengono atomi di carbonio Biochimica È lo studio della chimica
Chimica generale e inorganica Studia gli elementi e i composti inorganici Chimica organica Studia i composti organici, cioè composti che contengono atomi di carbonio Biochimica È lo studio della chimica
FORZE INTERMOLECOLARI o LEGAMI DEBOLI
 FRZE INTERMLECLARI o LEGAMI DEBLI 1 Le forze intermolecolari sono forze attrattive tra entità discrete come atomi o molecole, dette anche legami o interazioni deboli (E
FRZE INTERMLECLARI o LEGAMI DEBLI 1 Le forze intermolecolari sono forze attrattive tra entità discrete come atomi o molecole, dette anche legami o interazioni deboli (E
FORZE INTERMOLECOLARI o LEGAMI DEBOLI
 FRZE INTERMLECLARI o LEGAMI DEBLI 1 Le forze intermolecolari sono forze attrattive tra entità discrete come atomi o molecole, dette anche legami o interazioni deboli (E
FRZE INTERMLECLARI o LEGAMI DEBLI 1 Le forze intermolecolari sono forze attrattive tra entità discrete come atomi o molecole, dette anche legami o interazioni deboli (E
L allineamento nel molecular modelling. Manuela Sabatino. Mercoledi' 11Novembre 2015
 L allineamento nel molecular modelling Manuela Sabatino Mercoledi' 11Novembre 2015 1 (3-D QSAR) Quantitative Structure-Activity Relationships Spiegazione dei dati Biologici su base tridimensionale Ottimizzazione
L allineamento nel molecular modelling Manuela Sabatino Mercoledi' 11Novembre 2015 1 (3-D QSAR) Quantitative Structure-Activity Relationships Spiegazione dei dati Biologici su base tridimensionale Ottimizzazione
FATTORI CHE INFLUENZANO L INTENSITA DELLA RISPOSTA FARMACOLOGICA
 FATTORI CHE INFLUENZANO L INTENSITA DELLA RISPOSTA FARMACOLOGICA RELAZIONE DOSE-RISPOSTA La relazione dose-risposta è graduale EFFICACIA MASSIMA E POTENZA RELATIVA Efficacia massima: Massimo effetto che
FATTORI CHE INFLUENZANO L INTENSITA DELLA RISPOSTA FARMACOLOGICA RELAZIONE DOSE-RISPOSTA La relazione dose-risposta è graduale EFFICACIA MASSIMA E POTENZA RELATIVA Efficacia massima: Massimo effetto che
IL LEGAME A IDROGENO
 IL LEGAME A IDROGENO Il legame idrogeno è un particolare tipo di interazione fra molecole che si forma ogni volta che un atomo di idrogeno, legato ad un atomo fortemente elettronegativo (cioè capace di
IL LEGAME A IDROGENO Il legame idrogeno è un particolare tipo di interazione fra molecole che si forma ogni volta che un atomo di idrogeno, legato ad un atomo fortemente elettronegativo (cioè capace di
Macromolecole Biologiche. Metodi di simulazione
 Metodi di simulazione Dinamica molecolare Tecnica di simulazione che permette lo studio del moto e delle proprietà di un sistema di particelle. Moti localizzati (da 0.01 a 5 Å, da 10-15 a 10-1 s) - fluttuazioni
Metodi di simulazione Dinamica molecolare Tecnica di simulazione che permette lo studio del moto e delle proprietà di un sistema di particelle. Moti localizzati (da 0.01 a 5 Å, da 10-15 a 10-1 s) - fluttuazioni
FARMACODINAMICA. La farmacodinamica studia gli effetti biochimici e il meccanismo d azione dei farmaci.
 FARMACODINAMICA La farmacodinamica studia gli effetti biochimici e il meccanismo d azione dei farmaci. La farmacodinamica si propone di: * identificare i siti d azione dei farmaci * delineare le interazioni
FARMACODINAMICA La farmacodinamica studia gli effetti biochimici e il meccanismo d azione dei farmaci. La farmacodinamica si propone di: * identificare i siti d azione dei farmaci * delineare le interazioni
FORZE INTERMOLECOLARI
 FORZE INTERMOLECOLARI Le forze intermolecolari sono forze di attrazione che si stabiliscono tra le molecole che costituiscono una sostanza Determinano la tendenza delle molecole ad avvicinarsi. Per ogni
FORZE INTERMOLECOLARI Le forze intermolecolari sono forze di attrazione che si stabiliscono tra le molecole che costituiscono una sostanza Determinano la tendenza delle molecole ad avvicinarsi. Per ogni
Chimica generale e inorganica Studia gli elementi e i composti inorganici
 Chimica generale e inorganica Studia gli elementi e i composti inorganici Chimica organica Studia i composti organici, cioè composti che contengono atomi di carbonio Biochimica È lo studio della chimica
Chimica generale e inorganica Studia gli elementi e i composti inorganici Chimica organica Studia i composti organici, cioè composti che contengono atomi di carbonio Biochimica È lo studio della chimica
Attivazione dei Recettori. Teorie Recettoriali
 Attivazione dei Recettori Teorie Recettoriali Definizione di recettore The International Union of Basic and Clinical Pharmacology I recettori sono macromolecole di cellule o organismi che, essendo deputate
Attivazione dei Recettori Teorie Recettoriali Definizione di recettore The International Union of Basic and Clinical Pharmacology I recettori sono macromolecole di cellule o organismi che, essendo deputate
STUDIO 3D-QSAR PER INIBITORI DELLA CICLOOSSIGENASI-2 2 (COX-2): CONFORMAZIONI NEL SITO ATTIVO E MODELLAZIONE DELLA RISPOSTA FARMACOLOGICA.
 STUDIO 3D-QSAR PER IIBITORI DELLA CICLOOSSIGEASI-2 2 (COX-2): COFORMAZIOI EL SITO ATTIVO E MODELLAZIOE DELLA RISPOSTA FARMACOLOGICA. Sofia Cividini Stage: Bracco Imaging S.p.a Milano Premesse L elevata
STUDIO 3D-QSAR PER IIBITORI DELLA CICLOOSSIGEASI-2 2 (COX-2): COFORMAZIOI EL SITO ATTIVO E MODELLAZIOE DELLA RISPOSTA FARMACOLOGICA. Sofia Cividini Stage: Bracco Imaging S.p.a Milano Premesse L elevata
Interazioni non-covalenti
 BCP 3-4 Interazioni non-covalenti Interazioni non covalenti D H A δ - δ + δ - Le interazioni non covalenti Interazioni fra atomi che non sono legati da legami covalenti. Le interazioni non covalenti sono
BCP 3-4 Interazioni non-covalenti Interazioni non covalenti D H A δ - δ + δ - Le interazioni non covalenti Interazioni fra atomi che non sono legati da legami covalenti. Le interazioni non covalenti sono
COMPOSTI AZOTATI. derivanti dall ammoniaca AMMINE. desinenza -INA AMMIDE
 COMPOSTI AZOTATI derivanti dall ammoniaca AMMINE desinenza -INA AMMIDE ANCORA AMMIDI RISONANZA A M M I D I Il legame ammidico ha parziale carattere di doppio legame per la seguente risonanza: Ammidi H
COMPOSTI AZOTATI derivanti dall ammoniaca AMMINE desinenza -INA AMMIDE ANCORA AMMIDI RISONANZA A M M I D I Il legame ammidico ha parziale carattere di doppio legame per la seguente risonanza: Ammidi H
IL GRUPPO EME. PROTOPORFIRINA IX: struttura organica ad anello costituita da 4 anelli pirrolici uniti da ponti metinici.
 IL GRUPPO EME PROTOPORFIRINA IX: struttura organica ad anello costituita da 4 anelli pirrolici uniti da ponti metinici. L inserimento di un atomo di ferro nello stato di ossidazione ferroso (Fe 2+ ) determina
IL GRUPPO EME PROTOPORFIRINA IX: struttura organica ad anello costituita da 4 anelli pirrolici uniti da ponti metinici. L inserimento di un atomo di ferro nello stato di ossidazione ferroso (Fe 2+ ) determina
Protein docking e drug discovery
 Protein docking e drug discovery E noto da tempo che i siti attivi degli enzimi sono ospitati in tasche (cavità) ricavate nella struttura proteica con specifiche caratteristiche chimico fisiche. L interazione
Protein docking e drug discovery E noto da tempo che i siti attivi degli enzimi sono ospitati in tasche (cavità) ricavate nella struttura proteica con specifiche caratteristiche chimico fisiche. L interazione
CRISTALLOGRAFIA AI RAGGI X E MODELLISTICA MOLECOLARE
 CRISTALLOGRAFIA AI RAGGI X E MODELLISTICA MOLECOLARE LA STRUTTURA TRIDIMENSIONALE DEGLI ACIDI NUCLEICI, E PIU IN GENERALE DELLE MACROMOLECOLE BIOLOGICHE, PUO ESSERE STUDIATA CON LA METODICA DELLA CRISTALLOGRAFIA
CRISTALLOGRAFIA AI RAGGI X E MODELLISTICA MOLECOLARE LA STRUTTURA TRIDIMENSIONALE DEGLI ACIDI NUCLEICI, E PIU IN GENERALE DELLE MACROMOLECOLE BIOLOGICHE, PUO ESSERE STUDIATA CON LA METODICA DELLA CRISTALLOGRAFIA
http://structuralbiology.bio.uniroma2.it/ Dr. Ilda D Annessa ilda.dannessa@uniroma2.it
 Docking and Drug design http://structuralbiology.bio.uniroma2.it/ Dr. Ilda D Annessa ilda.dannessa@uniroma2.it Le proteine sono oggetti flessibili e non corpi rigidi. Nella maggior parte dei casi esplicano
Docking and Drug design http://structuralbiology.bio.uniroma2.it/ Dr. Ilda D Annessa ilda.dannessa@uniroma2.it Le proteine sono oggetti flessibili e non corpi rigidi. Nella maggior parte dei casi esplicano
Elettronegatività Elettronegatività
 Elettronegatività Nel legame covalente tra atomi uguali, la nuvola elettronica è simmetrica rispetto ai due nuclei (es. H 2, Cl 2, F 2 ) legame covalente apolare. Nel legame covalente tra atomi con Z eff
Elettronegatività Nel legame covalente tra atomi uguali, la nuvola elettronica è simmetrica rispetto ai due nuclei (es. H 2, Cl 2, F 2 ) legame covalente apolare. Nel legame covalente tra atomi con Z eff
Interazioni deboli. Sylvia S. Mader Immagini e concetti della biologia Zanichelli editore, 2012
 Interazioni deboli 1 Sylvia S. Mader Immagini e concetti della biologia Zanichelli editore, 2012 Legami deboli o interazioni deboli La forza di un legame chimico viene stabilita in base alla energia del
Interazioni deboli 1 Sylvia S. Mader Immagini e concetti della biologia Zanichelli editore, 2012 Legami deboli o interazioni deboli La forza di un legame chimico viene stabilita in base alla energia del
Modulo 1. Introduzione alle biomolecole. Ottobre 2017
 Modulo 1 Introduzione alle biomolecole Ottobre 2017 La logica molecolare della vita I sistemi viventi sono composti da molecole (biomolecole) inanimate (Albert Lehninger) Le biomolecole seguono le leggi
Modulo 1 Introduzione alle biomolecole Ottobre 2017 La logica molecolare della vita I sistemi viventi sono composti da molecole (biomolecole) inanimate (Albert Lehninger) Le biomolecole seguono le leggi
Acqua: peso molecolare = 18 In un bicchiere circa ml, quindi 10 moli una mole 6x10 23 molecole, quindi in un bicchiere 6x10 24 molecole
 Acqua: peso molecolare = 18 In un bicchiere circa 180-200 ml, quindi 10 moli una mole 6x10 23 molecole, quindi in un bicchiere 6x10 24 molecole Volume degli oceani 1.3 miliardi di km 3 = 1.3 x 10 18 m
Acqua: peso molecolare = 18 In un bicchiere circa 180-200 ml, quindi 10 moli una mole 6x10 23 molecole, quindi in un bicchiere 6x10 24 molecole Volume degli oceani 1.3 miliardi di km 3 = 1.3 x 10 18 m
LCAO nella molecola d acqua. Teoria del funzionale di densità (DFT).
 Il programma cambia negli anni accademici. Questo file contiene i programmi dei vari A.A. Lo studente deve riferirsi al programma dell'anno in cui ha seguito il corso. Consultare Testi Consigliati per
Il programma cambia negli anni accademici. Questo file contiene i programmi dei vari A.A. Lo studente deve riferirsi al programma dell'anno in cui ha seguito il corso. Consultare Testi Consigliati per
Il legame chimico. Energia di legame
 Il legame chimico Si definisce Legame chimico l effetto correlato alla forza che tiene uniti due atomi Elemento, o sostanza elementare, se vi è un legame tra atomi uguali Composto, o sostanza composta,
Il legame chimico Si definisce Legame chimico l effetto correlato alla forza che tiene uniti due atomi Elemento, o sostanza elementare, se vi è un legame tra atomi uguali Composto, o sostanza composta,
L uso del computer nel drug discovery
 L uso del computer nel drug discovery a.a. 2012-2013 Alberto Massarotti alberto.massarotti@pharm.unipmn.it 1 Le slide www.symech.it/didattica 2 3? 4? Structure-based Drug Design (SBDD)? 5 Proteine Per
L uso del computer nel drug discovery a.a. 2012-2013 Alberto Massarotti alberto.massarotti@pharm.unipmn.it 1 Le slide www.symech.it/didattica 2 3? 4? Structure-based Drug Design (SBDD)? 5 Proteine Per
Corso di Chimica Generale CL Biotecnologie
 Corso di Chimica Generale CL Biotecnologie STATI DELLA MATERIA Prof. Manuel Sergi MATERIA ALLO STATO GASSOSO MOLECOLE AD ALTA ENERGIA CINETICA GRANDE DISTANZA TRA LE MOLECOLE LEGAMI INTERMOLECOLARI DEBOLI
Corso di Chimica Generale CL Biotecnologie STATI DELLA MATERIA Prof. Manuel Sergi MATERIA ALLO STATO GASSOSO MOLECOLE AD ALTA ENERGIA CINETICA GRANDE DISTANZA TRA LE MOLECOLE LEGAMI INTERMOLECOLARI DEBOLI
1. Le forze intermolecolari 2. Molecole polari e apolari 3. Le forze dipolo-dipolo e le forze di London 4. Il legame a idrogeno 5. Legami a confronto
 Unità n 12 Le forze intermolecolari e gli stati condensati della materia 1. Le forze intermolecolari 2. Molecole polari e apolari 3. Le forze dipolo-dipolo e le forze di London 4. Il legame a idrogeno
Unità n 12 Le forze intermolecolari e gli stati condensati della materia 1. Le forze intermolecolari 2. Molecole polari e apolari 3. Le forze dipolo-dipolo e le forze di London 4. Il legame a idrogeno
H = entalpia, contenuto termico di un sistema che sta reagendo; dipende dal numero e dal tipo di legami chimici dei reagenti e dei prodotti
 ΔG = ΔH - TΔS H = entalpia, contenuto termico di un sistema che sta reagendo; dipende dal numero e dal tipo di legami chimici dei reagenti e dei prodotti Reazione esotermica = rilascia colore, ΔH è negativo,
ΔG = ΔH - TΔS H = entalpia, contenuto termico di un sistema che sta reagendo; dipende dal numero e dal tipo di legami chimici dei reagenti e dei prodotti Reazione esotermica = rilascia colore, ΔH è negativo,
Capitolo 12 Le forze intermolecolari e gli stati condensati della materia
 Capitolo 12 Le forze intermolecolari e gli stati condensati della materia 1. Le forze intermolecolari 2. Molecole polari e apolari 3. Le forze dipolo-dipolo e le forze di London 4. Il legame a idrogeno
Capitolo 12 Le forze intermolecolari e gli stati condensati della materia 1. Le forze intermolecolari 2. Molecole polari e apolari 3. Le forze dipolo-dipolo e le forze di London 4. Il legame a idrogeno
La struttura terziaria delle proteine
 La struttura terziaria delle proteine 1 La struttura terziaria L arrangiamento spaziale degli aminoacidi di una singola catena polipeptidica a formare la sua struttura tridimensionale a domini viene chiamata
La struttura terziaria delle proteine 1 La struttura terziaria L arrangiamento spaziale degli aminoacidi di una singola catena polipeptidica a formare la sua struttura tridimensionale a domini viene chiamata
MOLECOLE. 2 - i legami chimici. Prof. Vittoria Patti
 MOLECOLE 2 - i legami chimici Prof. Vittoria Patti Gli stati di aggregazione della materia STATO SOLIDO molecole ravvicinate, struttura ordinata, volume proprio, forma propria STATO LIQUIDO molecole
MOLECOLE 2 - i legami chimici Prof. Vittoria Patti Gli stati di aggregazione della materia STATO SOLIDO molecole ravvicinate, struttura ordinata, volume proprio, forma propria STATO LIQUIDO molecole
Valitutti, Falasca, Tifi, Gentile. Chimica. concetti e modelli.blu
 Valitutti, Falasca, Tifi, Gentile Chimica concetti e modelli.blu 2 Capitolo 15 Le forze intermolecolari e gli stati condensati della materia 3 Sommario 1. Le forze intermolecolari 2. Molecole polari e
Valitutti, Falasca, Tifi, Gentile Chimica concetti e modelli.blu 2 Capitolo 15 Le forze intermolecolari e gli stati condensati della materia 3 Sommario 1. Le forze intermolecolari 2. Molecole polari e
Molecular modelling. Alberto Massarotti [Synthetic Medicinal Chemistry group MMlab]
![Molecular modelling. Alberto Massarotti [Synthetic Medicinal Chemistry group MMlab] Molecular modelling. Alberto Massarotti [Synthetic Medicinal Chemistry group MMlab]](/thumbs/98/138642960.jpg) Molecular modelling Alberto Massarotti alberto.massarotti@pharm.unipmn.it 1 Le slide www.symech.it/didattica.asp 2 1. Giovedì, 6 dicembre, h. 11:15-12:15 Lo spazio chimico Il programma Le strutture chimiche
Molecular modelling Alberto Massarotti alberto.massarotti@pharm.unipmn.it 1 Le slide www.symech.it/didattica.asp 2 1. Giovedì, 6 dicembre, h. 11:15-12:15 Lo spazio chimico Il programma Le strutture chimiche
Enzimi: catalizzatori biologici
 Enzimi: catalizzatori biologici praticamente tutte le reazioni biochimiche della chimica della vita sono catalizzate da enzimi gli enzimi sono proteine la velocità di reazioni enzimatiche è aumentata di
Enzimi: catalizzatori biologici praticamente tutte le reazioni biochimiche della chimica della vita sono catalizzate da enzimi gli enzimi sono proteine la velocità di reazioni enzimatiche è aumentata di
L allineamento nel molecular modelling e cenni di 3-D QSAR. Manuela Sabatino. Martedi' 24Maggio 2016
 L allineamento nel molecular modelling e cenni di 3-D QSAR Manuela Sabatino Martedi' 24Maggio 2016 1 (3-D QSAR) Quantitative Structure-Activity Relationships Spiegazione dei dati Biologici su base tridimensionale
L allineamento nel molecular modelling e cenni di 3-D QSAR Manuela Sabatino Martedi' 24Maggio 2016 1 (3-D QSAR) Quantitative Structure-Activity Relationships Spiegazione dei dati Biologici su base tridimensionale
IL LEGAME CHIMICO. Per descrivere come gli elettroni si distribuiscono nell atomo attorno al nucleo si può far riferimento al MODELLO A GUSCI
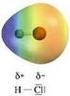 IL LEGAME CIMICO Come dagli atomi si costruiscono le molecole 02/19/08 0959 PM 1 Per descrivere come gli elettroni si distribuiscono nell atomo attorno al nucleo si può far riferimento al MODELLO A GUSCI
IL LEGAME CIMICO Come dagli atomi si costruiscono le molecole 02/19/08 0959 PM 1 Per descrivere come gli elettroni si distribuiscono nell atomo attorno al nucleo si può far riferimento al MODELLO A GUSCI
PROPRIETA DEI MATERIALI
 PROPRIETA DEI MATERIALI Una proprietà è la risposta di un materiale ad una sollecitazione esterna. Per i materiali solidi le proprietà possono raggrupparsi in sei differenti categorie: 1. Meccaniche 2.
PROPRIETA DEI MATERIALI Una proprietà è la risposta di un materiale ad una sollecitazione esterna. Per i materiali solidi le proprietà possono raggrupparsi in sei differenti categorie: 1. Meccaniche 2.
BIOMOLECOLE (PROTEINE)
 BIOMOLECOLE (PROTEINE) Proteine: funzioni Strutturale (muscoli, scheletro, legamenti ) Contrattile (actina e miosina) Di riserva (ovoalbumina) Di difesa (anticorpi) Di trasporto (emoglobina, di membrana)
BIOMOLECOLE (PROTEINE) Proteine: funzioni Strutturale (muscoli, scheletro, legamenti ) Contrattile (actina e miosina) Di riserva (ovoalbumina) Di difesa (anticorpi) Di trasporto (emoglobina, di membrana)
Il legame dativo o coordinativo: lo stesso atomo fornisce i due elettroni di legame.
 Il legame dativo o coordinativo: lo stesso atomo fornisce i due elettroni di legame. Non necessariamente i due elettroni che concorrono alla formazione del legame devono provenire da entrambi gli atomi
Il legame dativo o coordinativo: lo stesso atomo fornisce i due elettroni di legame. Non necessariamente i due elettroni che concorrono alla formazione del legame devono provenire da entrambi gli atomi
Cr Mn Fe Co Ni Cu Zn. Chimica Inorganica Biologica Vita ed Energia
 Vita ed Energia I processi chimici alla base della chimica della vita sono due: Uso dell E solare per produrre materia e O 2 da CO 2 e H 2 O Produzione di E mediante ossidazione di materia con formazione
Vita ed Energia I processi chimici alla base della chimica della vita sono due: Uso dell E solare per produrre materia e O 2 da CO 2 e H 2 O Produzione di E mediante ossidazione di materia con formazione
Le interazioni non covalenti si possono classificare in: Energie di legame associate alle principali interazioni non covalenti:
 Interazioni fra atomi che non sono legati da legami covalenti. Le interazioni non covalenti sono molto meno intense rispetto alle interazioni covalenti (poche kcal/mol rispetto ad esempio a 83 kcal/mol
Interazioni fra atomi che non sono legati da legami covalenti. Le interazioni non covalenti sono molto meno intense rispetto alle interazioni covalenti (poche kcal/mol rispetto ad esempio a 83 kcal/mol
Rappresentazione grafica di sistemi atomici e molecolari: editor e visualizzatori ESERCITAZIONE 5
 Rappresentazione grafica di sistemi atomici e molecolari: editor e visualizzatori ESERCITAZIONE 5 Editor e visualizzatori Spesso è utile rappresentare graficamente la struttura atomica o molecolare del
Rappresentazione grafica di sistemi atomici e molecolari: editor e visualizzatori ESERCITAZIONE 5 Editor e visualizzatori Spesso è utile rappresentare graficamente la struttura atomica o molecolare del
Chimica Biologica A.A α-elica foglietto β reverse turn
 Chimica Biologica A.A. 2010-2011 α-elica foglietto β reverse turn Str. Secondaria sperimentalmente osservata: Si distinguono fondamentalmente tre tipi di strutture secondarie: α elica foglietto β reverse
Chimica Biologica A.A. 2010-2011 α-elica foglietto β reverse turn Str. Secondaria sperimentalmente osservata: Si distinguono fondamentalmente tre tipi di strutture secondarie: α elica foglietto β reverse
2) La presenza di gruppi funzionali specifici che partecipano alla catalisi (quelli delle catene laterali dei suoi residui amminoacidici e/o quelli
 ENZIMI Tutti gli enzimi sono PROTEINE che funzionano da catalizzatori biologici nelle reazioni cellulari (sono in grado di aumentare la velocità delle reazioni biologiche anche di 10 20 volte). Durante
ENZIMI Tutti gli enzimi sono PROTEINE che funzionano da catalizzatori biologici nelle reazioni cellulari (sono in grado di aumentare la velocità delle reazioni biologiche anche di 10 20 volte). Durante
CLASSIFICAZIONE O.T.I.L.Is. Lig
 GLI ENZIMI CHE COSA SONO? Sono delle proteine altamente specializzate con attività catalitica, accelerano le reazioni chimiche rimanendo inalterati al termine della reazione stessa. CLASSIFICAZIONE O.T.I.L.Is.
GLI ENZIMI CHE COSA SONO? Sono delle proteine altamente specializzate con attività catalitica, accelerano le reazioni chimiche rimanendo inalterati al termine della reazione stessa. CLASSIFICAZIONE O.T.I.L.Is.
Sapienza, Università di Roma. Antonella Goggiamani
 Sapienza, Università di Roma CHIMICA ORGANICA Antonella Goggiamani antonella.goggiamani@uniroma1.it Facoltà di Scienze Matematiche, Fisiche e Naturali Corso di Laurea in Scienze Naturali, canale M Z LEZIONI
Sapienza, Università di Roma CHIMICA ORGANICA Antonella Goggiamani antonella.goggiamani@uniroma1.it Facoltà di Scienze Matematiche, Fisiche e Naturali Corso di Laurea in Scienze Naturali, canale M Z LEZIONI
TARGETS DEI FARMACI ATTUALMENTE IN USO
 TARGETS DEI FARMACI ATTUALMENTE IN USO INIBITORI ENZIMATICI INIBITORI ENZIMATICI Sintesi dell'uridine-5'-monophosphate (UMP) INIBITORI ENZIMATICI EFFICACIA DI INIBITORI COME AGENTI TERAPEUTICI Potenza
TARGETS DEI FARMACI ATTUALMENTE IN USO INIBITORI ENZIMATICI INIBITORI ENZIMATICI Sintesi dell'uridine-5'-monophosphate (UMP) INIBITORI ENZIMATICI EFFICACIA DI INIBITORI COME AGENTI TERAPEUTICI Potenza
INDICE Proprietà di soluzioni macromolecolari B O X 1 Titolazione di biopolielettroliti Spettroscopia di assorbimento e chirottica
 INDICE Proprietà di soluzioni macromolecolari Potenziale chimico: richiami Funzioni termodinamiche d eccesso Contributo dell entropia d eccesso all entropia di mescolamento Potenziale chimico di soluzioni
INDICE Proprietà di soluzioni macromolecolari Potenziale chimico: richiami Funzioni termodinamiche d eccesso Contributo dell entropia d eccesso all entropia di mescolamento Potenziale chimico di soluzioni
Aminoacidi. Gli α-aminoacidi sono molecole con almeno due gruppi funzionali legati al carbonio α
 Aminoacidi Gli α-aminoacidi sono molecole con almeno due gruppi funzionali legati al carbonio α 1 Isomeria ottica Tutti gli AA, esclusa la glicina, presentano almeno un atomo di carbonio asimmetrico, il
Aminoacidi Gli α-aminoacidi sono molecole con almeno due gruppi funzionali legati al carbonio α 1 Isomeria ottica Tutti gli AA, esclusa la glicina, presentano almeno un atomo di carbonio asimmetrico, il
Catalisi. Biotecnologie applicate alla progettazione e sviluppo di molecole biologicamente attive A.A Modulo di Biologia Strutturale
 Biotecnologie applicate alla progettazione e sviluppo di molecole biologicamente attive A.A. 2010-2011 Modulo di Biologia Strutturale Catalisi Marco Nardini Dipartimento di Scienze Biomolecolari e Biotecnologie
Biotecnologie applicate alla progettazione e sviluppo di molecole biologicamente attive A.A. 2010-2011 Modulo di Biologia Strutturale Catalisi Marco Nardini Dipartimento di Scienze Biomolecolari e Biotecnologie
Introduzione alla chimica organica. 1. Regola ottetto 2. Teoria del legame 3. Geometria delle molecole
 Introduzione alla chimica organica 1. Regola ottetto 2. Teoria del legame 3. Geometria delle molecole La chimica organica tratta di pochissimi atomi che si possono combinare in moltissimi modi Grande importanza
Introduzione alla chimica organica 1. Regola ottetto 2. Teoria del legame 3. Geometria delle molecole La chimica organica tratta di pochissimi atomi che si possono combinare in moltissimi modi Grande importanza
INTERAZIONE FARMACO-RECETTORE RECETTORE. Interazione farmaco-recettore
 Farmacodinamica -2 Interazione farmaco-recettore INTERAZIONE FARMACO-RECETTORE RECETTORE RELAZIONE DOSE-EFFETTO EFFETTO Il legame farmaco-recettore è: Saturabile Stereospecifico Reversibile L interazione
Farmacodinamica -2 Interazione farmaco-recettore INTERAZIONE FARMACO-RECETTORE RECETTORE RELAZIONE DOSE-EFFETTO EFFETTO Il legame farmaco-recettore è: Saturabile Stereospecifico Reversibile L interazione
LEGAMI INTERMOLECOLARI LEGAMI INTERMOLECOLARI
 I legami (o forze) intermolecolari sono le forze attrattive tra particelle: molecola - molecola, molecola - ione, ione - ione In assenza di queste interazioni tutti i composti sarebbero gassosi NB: attenzione
I legami (o forze) intermolecolari sono le forze attrattive tra particelle: molecola - molecola, molecola - ione, ione - ione In assenza di queste interazioni tutti i composti sarebbero gassosi NB: attenzione
Interfacce Bioelettroniche
 Interfacce Bioelettroniche L acqua A. Bonfiglio Acqua L acqua é il solvente per eccellenza nei fenomeni biologici ed ha anche alcune interessanti proprietá dal punto di vista delle interazioni intermolecolari.
Interfacce Bioelettroniche L acqua A. Bonfiglio Acqua L acqua é il solvente per eccellenza nei fenomeni biologici ed ha anche alcune interessanti proprietá dal punto di vista delle interazioni intermolecolari.
Introduzione alla Biochimica
 Introduzione alla Biochimica Rappresenta più del 70% del peso degli organismi viventi Notevoli Forze di attrazione Bassa tendenza a ionizzarsi I protoni liberi in soluzione non esistono Ione Ossidrile
Introduzione alla Biochimica Rappresenta più del 70% del peso degli organismi viventi Notevoli Forze di attrazione Bassa tendenza a ionizzarsi I protoni liberi in soluzione non esistono Ione Ossidrile
CAPITOLO II. Photonics and Biophotonics Organics Synthesis - PhoBOS. Dept. Materials Science, Univ. Milano-Bicocca
 CAPITOLO II Introduzione alle forze intermolecolari e ai solidi molecolari. Interazioni deboli in materiali organici (interazioni dipolo-dipolo, ione-dipolo, legame a idrogeno, legame ad alogeno, legame
CAPITOLO II Introduzione alle forze intermolecolari e ai solidi molecolari. Interazioni deboli in materiali organici (interazioni dipolo-dipolo, ione-dipolo, legame a idrogeno, legame ad alogeno, legame
Legame chimico e proprietà delle sostanze
 I solidi hanno volume e forma propria. Stati di aggregazione della materia stato solido stato liquido stato gassoso Il loro volume dipende da temperatura e pressione e in generale aumenta leggermente all
I solidi hanno volume e forma propria. Stati di aggregazione della materia stato solido stato liquido stato gassoso Il loro volume dipende da temperatura e pressione e in generale aumenta leggermente all
ATOMI E MOLECOLE. Psicobiologia Lezione nr. 1. Prof. Lasaponara
 ATOMI E MOLECOLE Psicobiologia Lezione nr. 1 Prof. Lasaponara La struttura dell atomo I legami chimici e le molecole I componenti elementari della materia vivente 20 miliardi di anni fa Caratteristiche
ATOMI E MOLECOLE Psicobiologia Lezione nr. 1 Prof. Lasaponara La struttura dell atomo I legami chimici e le molecole I componenti elementari della materia vivente 20 miliardi di anni fa Caratteristiche
I LEGAMI CHIMICI. Configurazione elettronica stabile: è quella in cui tutti i livelli energetici dell atomo sono pieni di elettroni
 I LEGAMI CIMICI In natura sono pochi gli elementi che presentano atomi allo stato libero. Gli unici elementi che sono costituiti da atomi isolati si chiamano gas nobili o inerti, formano il gruppo VIII
I LEGAMI CIMICI In natura sono pochi gli elementi che presentano atomi allo stato libero. Gli unici elementi che sono costituiti da atomi isolati si chiamano gas nobili o inerti, formano il gruppo VIII
Chimica Generale ed Inorganica: Programma del Corso
 Chimica Generale ed Inorganica: Programma del Corso Gli atomi I legami chimici Forma e struttura delle molecole Le proprietà dei gas Liquidi e solidi Termodinamica Equilibri fisici Equilibri chimici Equilibri
Chimica Generale ed Inorganica: Programma del Corso Gli atomi I legami chimici Forma e struttura delle molecole Le proprietà dei gas Liquidi e solidi Termodinamica Equilibri fisici Equilibri chimici Equilibri
le SOSTANZE Sostanze elementari (ELEMENTI) COMPOSTI Costituiti da due o più atomi DIVERSI tra loro
 Il legame chimico In natura gli atomi sono solitamente legati ad altri in unità più complesse che, se aggregate fra loro costituiscono quello che macroscopicamente percepiamo come materia, le SOSTANZE
Il legame chimico In natura gli atomi sono solitamente legati ad altri in unità più complesse che, se aggregate fra loro costituiscono quello che macroscopicamente percepiamo come materia, le SOSTANZE
Proprietà comuni. Il gruppo α-carbossilico b è un acido più forte del gruppo carbossilico degli acidi alifatici
 Gli aminoacidi Proprietà comuni Il gruppo α-carbossilico b è un acido più forte del gruppo carbossilico degli acidi alifatici paragonabili Il gruppo α-aminico è un acido più forte (o una base più debole
Gli aminoacidi Proprietà comuni Il gruppo α-carbossilico b è un acido più forte del gruppo carbossilico degli acidi alifatici paragonabili Il gruppo α-aminico è un acido più forte (o una base più debole
20/10/2015. Importanza dei legami non covalenti in Biologia. Legami covalenti
 Legami covalenti Gli atomi che costituiscono le molecole sono tenuti insieme da legami covalenti in cui coppie di elettroni sono condivise tra coppie di atomi. La formazione del legame covalente si basa
Legami covalenti Gli atomi che costituiscono le molecole sono tenuti insieme da legami covalenti in cui coppie di elettroni sono condivise tra coppie di atomi. La formazione del legame covalente si basa
Prof. Laura Bonati, Dott. Domenico Fraccalvieri. DISAT, Ed. U1
 MODELLISTICA MOLECOLARE DI STRUTTURA, PROPRIETA' E INTERAZIONI DI PROTEINE Prof. Laura Bonati, Dott. Domenico Fraccalvieri DISAT, Ed. U1 laura.bonati@unimib.it AMBITI di RICERCA Predizione i di struttura
MODELLISTICA MOLECOLARE DI STRUTTURA, PROPRIETA' E INTERAZIONI DI PROTEINE Prof. Laura Bonati, Dott. Domenico Fraccalvieri DISAT, Ed. U1 laura.bonati@unimib.it AMBITI di RICERCA Predizione i di struttura
 ELETTRONEGATIVITA CAPACITA DI UN ATOMO DI ATTIRARE UNA COPPIA DI ELETTRONI DI LEGAME DETERMINANDO COSI IL TIPO DI LEGAME CHE SI VIENE A FORMARE. DERIVA DA ALTRE DUE GRANDEZZE I. Energia di ionizzazione:
ELETTRONEGATIVITA CAPACITA DI UN ATOMO DI ATTIRARE UNA COPPIA DI ELETTRONI DI LEGAME DETERMINANDO COSI IL TIPO DI LEGAME CHE SI VIENE A FORMARE. DERIVA DA ALTRE DUE GRANDEZZE I. Energia di ionizzazione:
La Vita è una Reazione Chimica
 La Vita è una Reazione Chimica Acqua Oro Zucchero I Legami Chimici F N F F Il legame chimico il legame ionico Polare il legame covalente Dativo Gli elettroni di valenza sono gli elettroni del livello più
La Vita è una Reazione Chimica Acqua Oro Zucchero I Legami Chimici F N F F Il legame chimico il legame ionico Polare il legame covalente Dativo Gli elettroni di valenza sono gli elettroni del livello più
CARATTERISTICHE DEGLI ATOMI
 CARATTERISTICHE DEGLI ATOMI Isotopi: Z è lo stesso, A è diverso Isotopi dell O e loro abbondanza naturale 16 O = 99.76 % (15.99491) 17 O = 0.04 % (16.99913) 18 O = 0.20 % (17.99916) O = 15.9994 27/04/2007
CARATTERISTICHE DEGLI ATOMI Isotopi: Z è lo stesso, A è diverso Isotopi dell O e loro abbondanza naturale 16 O = 99.76 % (15.99491) 17 O = 0.04 % (16.99913) 18 O = 0.20 % (17.99916) O = 15.9994 27/04/2007
Siena, 10 Giugno 2015 Sandra Defazio Serena Fedi
 CLASSE I A Costruzione Ambiente e Territorio omogenei ed eterogenei e curva di riscaldamento di un miscuglio. nobili. Distinzione fra molecole e atomi. Principio di conservazione della massa. Teoria atomica
CLASSE I A Costruzione Ambiente e Territorio omogenei ed eterogenei e curva di riscaldamento di un miscuglio. nobili. Distinzione fra molecole e atomi. Principio di conservazione della massa. Teoria atomica
A.A Laboratorio 3 - Esercizio
 Laboratorio 3 Studio del dimero dell acqua A.A. 2007-08 08! " 1 Laboratorio 3 - Esercizio 1) Ottimizzazione della geometria e calcolo delle frequenze vibrazionali della molecola di acqua Confronto con
Laboratorio 3 Studio del dimero dell acqua A.A. 2007-08 08! " 1 Laboratorio 3 - Esercizio 1) Ottimizzazione della geometria e calcolo delle frequenze vibrazionali della molecola di acqua Confronto con
Chimica e laboratorio
 ITIS H.HERTZ Progetto Monoennio Chimica e laboratorio PARTE PRIMA I MODULO: Struttura atomica e molecolare della materia PESO : 70% UNITA ORARIE PREVISTE : 20 h Unità A: ATOMI Descrivere le caratteristiche
ITIS H.HERTZ Progetto Monoennio Chimica e laboratorio PARTE PRIMA I MODULO: Struttura atomica e molecolare della materia PESO : 70% UNITA ORARIE PREVISTE : 20 h Unità A: ATOMI Descrivere le caratteristiche
Struttura e proprietà
 Struttura e proprietà Entrando nel sito attivo di un enzima : comprendere Interleuchina e recettore : comprendere Molecular docking: prevedere Amprenavir e HIV proteasi: modificare 1 Geometria molecolare:
Struttura e proprietà Entrando nel sito attivo di un enzima : comprendere Interleuchina e recettore : comprendere Molecular docking: prevedere Amprenavir e HIV proteasi: modificare 1 Geometria molecolare:
2. I legami chimici. Gli ATOMI. Biologia Molecolare e Cellulare - D'Addario
 2. I legami chimici contiene materiale protetto da copyright, ad esclusivo uso personale; non è consentita diffusione ed utilizzo di tipo commerciale Gli ATOMI sono a loro volta costituiti da particelle
2. I legami chimici contiene materiale protetto da copyright, ad esclusivo uso personale; non è consentita diffusione ed utilizzo di tipo commerciale Gli ATOMI sono a loro volta costituiti da particelle
Interazioni biomolecolari che coinvolgono proteine
 B015921 - INTERAZIONI BIOMOLECOLARI: METODI IN SILICO ED IN VITRO Metodi spettroscopici per lo screening di interazioni Modulo B015922 - INTERATTOMICA: STRUTTURA, TERMODINAMICA E CINETICA Definizione di
B015921 - INTERAZIONI BIOMOLECOLARI: METODI IN SILICO ED IN VITRO Metodi spettroscopici per lo screening di interazioni Modulo B015922 - INTERATTOMICA: STRUTTURA, TERMODINAMICA E CINETICA Definizione di
Importanza dei legami non covalenti in Biologia
 Importanza dei legami non covalenti in Biologia Biotecnologie / Biologia Sperimentale Applicata Gli atomi che costituiscono le molecole sono tenuti insieme da legami covalenti in cui coppie di elettroni
Importanza dei legami non covalenti in Biologia Biotecnologie / Biologia Sperimentale Applicata Gli atomi che costituiscono le molecole sono tenuti insieme da legami covalenti in cui coppie di elettroni
Il legame chimico ATOMI MOLECOLE
 Il legame chimico Gli atomi tendono a combinarsi con altri atomi per dare un sistema finale più stabile di quello iniziale (a minor contenuto di energia). ATOMI MOLECOLE 1 Stati repulsivi di non legame
Il legame chimico Gli atomi tendono a combinarsi con altri atomi per dare un sistema finale più stabile di quello iniziale (a minor contenuto di energia). ATOMI MOLECOLE 1 Stati repulsivi di non legame
Proteine. Enzimi Fattori di Trascrizione Proteine di Membrana (trasportatori, canale, recettori di membrana)
 Proteine Enzimi Fattori di Trascrizione Proteine di Membrana (trasportatori, canale, recettori di membrana) Ormoni e Fattori di crescita Anticorpi Trasporto Trasporto (emoglobina, LDL, HDL.) Fenotipo Proteine
Proteine Enzimi Fattori di Trascrizione Proteine di Membrana (trasportatori, canale, recettori di membrana) Ormoni e Fattori di crescita Anticorpi Trasporto Trasporto (emoglobina, LDL, HDL.) Fenotipo Proteine
