Polymerase chain reaction (PCR) qualche ora
|
|
|
- Modesto Gattini
- 5 anni fa
- Visualizzazioni
Transcript
1 Lezione 3 Metodologie di sequenziamemento di DNA ed RNA. Da Sanger sequencing ad High Throughput (HTS) o di Next Generation (NGS) o di seconda generation
2 Polymerase chain reaction (PCR) qualche ora
3 25 Aprile 1953 James D. Watson e Francis Crick pubblicano la struttura del DNA (Watson JD, Crick FHC "A Structure for Deoxyribose Nucleic Acid", Nature vol. 171, pp ; 1953) fondando il campo della genetica molecolare. Premio Nobel nel Doppia elica
4 Metà degli anni 50: Arthur Kornberg inizia a studiare il meccanismo di replicazione del DNA. Nel 1957 identifica la prima DNA polimerasi. L enzima copia in una sola direzione e richiede degli inneschi preesistenti (primer) per iniziare a copiare il filamento. Premio Nobel nel Doppia elica 1957 DNApol Primi 60 Codice genetico Oligonucleoti di sintetici (primers) All inizio degli anni 60 Gobind Khorana chiarisce molti aspetti del codice genetico. Successivamente inizia un progetto per la sintesi in vitro di un gene umano e in questi esperimenti getta le basi per l utilizzo di oligonucleotidi sintetici (usati sia come blocchi per la costruzione del gene, sia come inneschi per la DNA polimerasi) Premio Nobel per il suo lavoro sul codice genetico.
5 1969 Thomas D. Brock isola un nuovo batterio dalle sorgenti calde dello Yellowstone National Park. Nel 1976 viene islata la DNA polimerasi di T. aquaticus (taq) in grado di mantenere la sua attività oltre i 75 C. Biotechnology in Yellowstone 1953 Doppia elica 1957 DNApol Primi 60 Codice genetico Oligonucleoti di sintetici (primers) 1969 taq 1975 Sanger sequencing 1975 Frederick Sanger sviluppa un metodo per determinare la sequenza del DNA. (Sanger F, Nicklen S, Coulson AR "DNA sequencing with chainterminating inhibitors" Proc Natl Acad Sci vol. 74(12) pp ; 1977). 1980: Premio Nobel. Nel 1980 tutti i componenti per fare un amplificazione con PCR sono conosciuti dalla comunità scientifica
6 K. Mullis C
7 Dal prodotto di PCR al sequenziamento di Sanger C C C
8 Dal prodotto di PCR al sequenziamento di Sanger Verifica dell avvenuta reazione (e possibile quantificazione), ad esempio per elettroforesi su gel di agarosio Prodotto di reazione Marker (frammenti a lunghezza nota) Purificazione del prodotto di PCR: Esempio Exo/SAP (dobbiamo pulire da dntps e primers residui)
9 Il sequenziamento di Sanger Elongation Strand Separation Primer Annealing Termination
10 Termination Standard Nucleotides Dye-labeled dideoxynucleotides ddntp incorporation leads to chain growth termination
11 Capillary Electrophoresis ABI 3730, 96-capillary
12 Un programma specifico opera il BASECALLING (converte i picchi in A, T, G, C) cromatogramma
13 Molto importante!!! Good quality I file prodotti dai sequenziatori automatici sono specifici e di solito hanno un estensione.seq oppure.abi Bad quality (background noise)
14 Apro il file.abi con un programma apposito che legge cromatogrammi (es. Chromas; BioEdit) Questi programmi hanno molte funzioni, quando sono soddisfatto delle mie correzioni posso esportare la sequenza in un formato di testo leggero e leggibile da molti altri programmi (es. programmi di allineamento): FORMATO FASTA Copy FASTA formatted
15 Il segno > contraddistingue il FASTA ed è obbligatorio identifier of the sequence (optional) >XFUS0058 CGTTAGAGGGGACGATTTCTACGTGCCTATGT CCAATGCCACCGGCATTGTTAGGGACCCGTAC GAGTATCCCCAGTACTACCTGGTGGCCCCGTG GGCATACGCCTGCCTGGCAGCGTACATGTTCT TCCTCATTCTCACCGGCTTCCCCGTCAACTTC CTCACCCTGTACGTCACCATCGAGCACAAGAA GCTGCGTACGCCTCTCAACTACATTCTGCTGA ACCTCGCCATTTCCGACCTCTTCATGGTGTTC GGCGGGTTCACCACGACGATGTACACCTCGTT GCACGGCTACTTCGTGTTCGGACGCCTCGGCT GCAACCTGGAAGGCTTCTTCGCGACCCTGGGC sequenza GGTGAAATGGGGCTGTGGTCCCTGGTCGTGCT GGCCTTCGAGAGGTGGATGGTGGTCTGTAAGC CCGTGAGCAACTTCCGCTTCGGAGAGAACCAC GCCATCATGGGCGTGGCCTTCACCTGGGTCAT GGCCTGCTCCTGCGCCGTGCCTCCCCTGGTGG GCTGGTCCCGTTACATCCCCGAGGGCATGCAG TGCTCGTGCGGAGTCGACTACTACACCCGCGC CCCCGGCTACAACAACGAGTCCTTCGTCATCT ACATGTTCATCGTGCACTTCATCATTCCGCTC ATCGTCATATTCTTCTGCTACGGCCGTCTTGT
16 Stranneheim and Lundeberg 2012
17 18
18 19
19 2000
20 illumina
21 illumina
22 illumina
23 illumina 1800 Gb maximum output Huma genome: 3.3 Gb Che copertura (coverage) ottengo per un genoma con una run?
24 Ion Torrent
25
26
27
28 the number of times a nucleotide is read during the sequencing process
29 Applications Espressione genica Caratterizzazione regioni di interazione DNA-proteine Epigenetica
30 Applications: genomes, exomes, transcriptomes
31 Applications
32
33
34 Applications environmental DNA (edna) Can be avoided
35 library Frammentazione Size selection Legame adattatori Template preparation Serve a reggiungere una quantità di DNA stampo sufficiente per la lettura del sequenziamento sequencing Sequencing by synthesis Lettura del segnale
36 Preparazione della library
37 Preparazione della library Il DNA va pre-processato prima di essere sequenziato Passaggi: 1. Frammentazione (fisica o enzimatica) 2. Le estremità dei frammenti vengono riparate e rese «blunt» o con specifici nucleotidi terminali (es A o T) 3. Alle estremità vengono legati degli adattatori specifici per ogni NGS technology
38
39 Preparazione della library
40 Preparazione della library
41 Preparazione della library: Illumina
42 Preparazione della library: Illumina
43
44
45
46 Roche Ion Torrent
47
48 Gli adattatori P5 e P7 servono per legare il frammento da sequenziare alla flow cell dove ci sono delle sequenze complementari e servono anche da primer
49
50
51
52
53
54 55
55 56
56 Release of an H+ during extension (Ion Torrent)
57 58
58 Thermo fisher Summary (NB: i numeri sono indicativi, dipendono molto dalle condizioni che si usano per il sequenziamento, nel caso di Ion Torrent dai chip e di Illumina dai kit usati) Ion Torrent PGM (different chips) S5 series (different chips) Illumina HiSeqSeries Fluorescence: reversible NextSeq terminators 500 Detection Run time Read lenght (bp) Reads per run (millions) Output per run (Gb) H+ release 2-7 h H+ release Max 24 h h - 6 days Max 2 x h Max 2 x MiSeq 4-55 h Max 2 x From Illumina and Life Technologies web sites, 2018
59 Human genome 3.3 gigabases Arabidopsis thaliana 135 megabases (0.135 Gb) Escherichia coli (str. K-12 substr. MG1655) 5.17 megabases ( Gb) Che coverage posso attendermi se sequenzio questi genomi con le seguenti piattaforme 1. HiSeq Illumina 2. NextSeq Illumina 3. MiSeq Illumina 4. PGM Ion torrent Per scegliere la piattaforma devo valutare anche i costi di una corsa!
60 van Dijk et al. TIG 2014 Graph showing the evolution of the cost of sequencing a human genome from 2001 until today. Costs have sharply decreased over the recent years thanks to the appearance of next-generation sequencing (NGS) technologies and their subsequent upgrades. Very recently, the milestone of the US$1000 genome has been reached with Illumina s HiSeq X Ten system
Lezione 4. Il sequenziamento del DNA, Sanger
 Lezione 4 Il sequenziamento del DNA, Sanger Schema della lezione Polymerase chain reaction (PCR) Dal prodotto di PCR al sequenziamento di Sanger Lettura dei prodotti di sequenziamento con sequenziatori
Lezione 4 Il sequenziamento del DNA, Sanger Schema della lezione Polymerase chain reaction (PCR) Dal prodotto di PCR al sequenziamento di Sanger Lettura dei prodotti di sequenziamento con sequenziatori
DNA Profiling e Genetica Forense. Silvia Fuselli Lezione 1
 DNA Profiling e Genetica Forense Silvia Fuselli fss@unife.it Lezione 1 I geni negli individui Omozigote: lo stesso allele ad un locus in organismi diploidi (o poliplodi) E O E Eterozigote: Alleli diversi
DNA Profiling e Genetica Forense Silvia Fuselli fss@unife.it Lezione 1 I geni negli individui Omozigote: lo stesso allele ad un locus in organismi diploidi (o poliplodi) E O E Eterozigote: Alleli diversi
Lezione 4. Il sequenziamento del DNA, Sanger
 Lezione 4 Il sequenziamento del DNA, Sanger Schema della lezione Polymerase chain reaction (PCR) Dal prodotto di PCR al sequenziamento di Sanger Lettura dei prodotti di sequenziamento con sequenziatori
Lezione 4 Il sequenziamento del DNA, Sanger Schema della lezione Polymerase chain reaction (PCR) Dal prodotto di PCR al sequenziamento di Sanger Lettura dei prodotti di sequenziamento con sequenziatori
Lezione 4. Il sequenziamento del DNA, Sanger e il progetto genoma umano
 Lezione 4 Il sequenziamento del DNA, Sanger e il progetto genoma umano Stranneheim and Lundeberg 2012 Un po di storia 25 Aprile 1953 James D. Watson e Francis Crick pubblicano la struttura del DNA (Watson
Lezione 4 Il sequenziamento del DNA, Sanger e il progetto genoma umano Stranneheim and Lundeberg 2012 Un po di storia 25 Aprile 1953 James D. Watson e Francis Crick pubblicano la struttura del DNA (Watson
Biotecnologie applicate all ispezione degli alimenti di origine animale
 Prof.ssa Tiziana Pepe Tecniche molecolari Biotecnologie applicate all ispezione degli alimenti di origine animale Dip. di Medicina Veterinaria e Produzioni animali tiziana.pepe@unina.it Tecniche molecolari
Prof.ssa Tiziana Pepe Tecniche molecolari Biotecnologie applicate all ispezione degli alimenti di origine animale Dip. di Medicina Veterinaria e Produzioni animali tiziana.pepe@unina.it Tecniche molecolari
Metodologie citogenetiche. Metodologie molecolari. Formulare la domanda Utilizzare la metodica appropriata
 In base al potere di risoluzione della tecnica Metodologie citogenetiche Metodologie molecolari Formulare la domanda Utilizzare la metodica appropriata 1 DNA RNA PROTEINE DNA Cromosomi (cariotipo, FISH,
In base al potere di risoluzione della tecnica Metodologie citogenetiche Metodologie molecolari Formulare la domanda Utilizzare la metodica appropriata 1 DNA RNA PROTEINE DNA Cromosomi (cariotipo, FISH,
Applicazioni del Sequenziamento di Nuova Generazione (NGS) nel contesto One Health. NGS: tutti i segreti del laboratorio
 Applicazioni del Sequenziamento di Nuova Generazione (NGS) nel contesto One Health NGS: tutti i segreti del laboratorio Francesco Cerutti S.S. Genetica e Immunobiochimica IstitutoZooprofilatticoSperimentaledel
Applicazioni del Sequenziamento di Nuova Generazione (NGS) nel contesto One Health NGS: tutti i segreti del laboratorio Francesco Cerutti S.S. Genetica e Immunobiochimica IstitutoZooprofilatticoSperimentaledel
DNA revolution. Microsatellites SNPs. Sequenziamento massivo (Next Generation Sequencing NGS)
 DNA revolution Microsatellites SNPs Sequenziamento massivo (Next Generation Sequencing NGS) NGS NGS NGS Non-Sanger-based high-throughput DNA sequencing technology Increasing the throughput Minimizing the
DNA revolution Microsatellites SNPs Sequenziamento massivo (Next Generation Sequencing NGS) NGS NGS NGS Non-Sanger-based high-throughput DNA sequencing technology Increasing the throughput Minimizing the
GENOMICA STRUTTURALE: GENOMICA FUNZIONALE: 1. Anatomia dei genomi. 8. Funzionamento dei genomi Il genoma dei procarioti
 GENOMICA STRUTTURALE: GENOMICA FUNZIONALE: 1. Anatomia dei genomi 8. Funzionamento dei genomi Il genoma dei procarioti Modificazioni della cromatina e l espressione del genoma Il genoma degli eucarioti
GENOMICA STRUTTURALE: GENOMICA FUNZIONALE: 1. Anatomia dei genomi 8. Funzionamento dei genomi Il genoma dei procarioti Modificazioni della cromatina e l espressione del genoma Il genoma degli eucarioti
LA REAZIONE A CATENA DELLA POLIMERASI PCR
 LA REAZIONE A CATENA DELLA POLIMERASI PCR INTRODUZIONE Tecnica ideata da Mullis e collaboratori nel 1984 La possibilita' di disporre di quantità virtualmente illimitate di un determinato frammento di DNA,
LA REAZIONE A CATENA DELLA POLIMERASI PCR INTRODUZIONE Tecnica ideata da Mullis e collaboratori nel 1984 La possibilita' di disporre di quantità virtualmente illimitate di un determinato frammento di DNA,
Marcatori molecolari
 Marcatori molecolari Caratteristiche e applicazioni Luca Gianfranceschi e Rosanna Marino 1 I marcatori molecolari Strumento per l analisi genetica Strumento Molecolari Analisi genetica Marcatori non oggetto
Marcatori molecolari Caratteristiche e applicazioni Luca Gianfranceschi e Rosanna Marino 1 I marcatori molecolari Strumento per l analisi genetica Strumento Molecolari Analisi genetica Marcatori non oggetto
Polymerase chain reaction - PCR. Biotecnologie applicate all ispezione degli alimenti di origine animale
 Prof.ssa Tiziana Pepe Polymerase chain reaction - PCR Biotecnologie applicate all ispezione degli alimenti di origine animale Dip. di Medicina Veterinaria e Produzioni animali tiziana.pepe@unina.it Metodologia
Prof.ssa Tiziana Pepe Polymerase chain reaction - PCR Biotecnologie applicate all ispezione degli alimenti di origine animale Dip. di Medicina Veterinaria e Produzioni animali tiziana.pepe@unina.it Metodologia
ELETTROFORESI SU GEL
 ELETTROFORESI SU GEL ELETTROFORESI SU GEL Metodo per separare le molecole (DNA, RNA, proteine, etc.) sulla base di proprieta fisiche o chimiche quali: (1)dimensioni (2)forma (3)carica elettrica L'AGAROSIO
ELETTROFORESI SU GEL ELETTROFORESI SU GEL Metodo per separare le molecole (DNA, RNA, proteine, etc.) sulla base di proprieta fisiche o chimiche quali: (1)dimensioni (2)forma (3)carica elettrica L'AGAROSIO
Tecniche molecolari per lo studio degli acidi nucleici
 Tecniche molecolari per lo studio degli acidi nucleici Prof.ssa Flavia Frabetti aa. 2010-11 Estrazione acidi nucleici (DNA o RNA) Verifica tramite elettroforesi su gel di agarosio Amplificazione o clonaggio
Tecniche molecolari per lo studio degli acidi nucleici Prof.ssa Flavia Frabetti aa. 2010-11 Estrazione acidi nucleici (DNA o RNA) Verifica tramite elettroforesi su gel di agarosio Amplificazione o clonaggio
LA REAZIONE A CATENA DELLA POLIMERASI
 Polymerase Chain Reaction LA REAZIONE A CATENA DELLA POLIMERASI e LE SUE APPLICAZIONI Prima diagnosi molecolare sul DNA 1978 *Primo ormone umano ricombinante (insulina) *Premio Nobel agli scopritori degli
Polymerase Chain Reaction LA REAZIONE A CATENA DELLA POLIMERASI e LE SUE APPLICAZIONI Prima diagnosi molecolare sul DNA 1978 *Primo ormone umano ricombinante (insulina) *Premio Nobel agli scopritori degli
PCR. (Reazione a Catena della Polimerasi) Kary Mullis
 POLYMERASE CHAIN REACTION - PCR PCR Polymerase Chain Reaction (Reazione a Catena della Polimerasi) Kary Mullis Premio Nobel per la Chimica nel 1993, Kary Mullis è divenuto una leggenda per la scoperta
POLYMERASE CHAIN REACTION - PCR PCR Polymerase Chain Reaction (Reazione a Catena della Polimerasi) Kary Mullis Premio Nobel per la Chimica nel 1993, Kary Mullis è divenuto una leggenda per la scoperta
Tecnologia del DNA e la genomica
 Tecnologia del DNA e la genomica DNA ricombinante La tecnologia del DNA ricombinante permette di unire in laboratorio il DNA di organismi diversi Permette di manipolare il DNA di un organismo allo scopo
Tecnologia del DNA e la genomica DNA ricombinante La tecnologia del DNA ricombinante permette di unire in laboratorio il DNA di organismi diversi Permette di manipolare il DNA di un organismo allo scopo
Le biotecnologie. Sadava et al. Biologia La scienza della vita Zanichelli editore 2010
 Le biotecnologie 1 Cosa sono le biotecnologie? Le biotecnologie sono tutte quelle tecniche utilizzate (fin dall antichità) per produrre sostanze specifiche a partire da organismi viventi o da loro derivati.
Le biotecnologie 1 Cosa sono le biotecnologie? Le biotecnologie sono tutte quelle tecniche utilizzate (fin dall antichità) per produrre sostanze specifiche a partire da organismi viventi o da loro derivati.
Strumenti della Genetica Molecolare Umana (3) Capitoli 6-7-8
 Strumenti della Genetica Molecolare Umana (3) Capitoli 6-7-8 Piccolo test: trova al differenza Gel 2 Gel 1 Gel 1. digestione DNA genomico Gel 2. Digestione inserto cloni genomici BANCHE DI DNA RICOMBINANTE
Strumenti della Genetica Molecolare Umana (3) Capitoli 6-7-8 Piccolo test: trova al differenza Gel 2 Gel 1 Gel 1. digestione DNA genomico Gel 2. Digestione inserto cloni genomici BANCHE DI DNA RICOMBINANTE
Il biomonitoraggio ambientale attraverso lo studio della regolazione genica della risposta allo stress Silvia Franzellitti
 Seminario per il corso misure con biomarcatori A.A. 2005-2006 Il biomonitoraggio ambientale attraverso lo studio della regolazione genica della risposta allo stress Silvia Franzellitti Perché utilizzare
Seminario per il corso misure con biomarcatori A.A. 2005-2006 Il biomonitoraggio ambientale attraverso lo studio della regolazione genica della risposta allo stress Silvia Franzellitti Perché utilizzare
Differenti tipi di PCR
 Differenti tipi di PCR Colony PCR Nested PCR Multiplex PCR AFLP PCR Hot start PCR In situ PCR Inverse PCR Asymmetric PCR Long PCR Long accurate PCR Reverse transcriptase PCR Allele Specific PCR Real time
Differenti tipi di PCR Colony PCR Nested PCR Multiplex PCR AFLP PCR Hot start PCR In situ PCR Inverse PCR Asymmetric PCR Long PCR Long accurate PCR Reverse transcriptase PCR Allele Specific PCR Real time
IL SEQUENZIAMENTO DEL DNA. Obiettivo: ottenere la sequenza nucleotidica di un frammento di DNA.
 IL SEQUENZIAMENTO DEL DNA Obiettivo: ottenere la sequenza nucleotidica di un frammento di DNA. Il DNA può essere sequenziato generando frammenti di DNA la cui lunghezza dipende dall ultima base della sequenza.
IL SEQUENZIAMENTO DEL DNA Obiettivo: ottenere la sequenza nucleotidica di un frammento di DNA. Il DNA può essere sequenziato generando frammenti di DNA la cui lunghezza dipende dall ultima base della sequenza.
Percorso di Biologia Molecolare
 La Biologia Molecolare è oggi alla base di qualunque indagine analitica in campo clinico, alimentare, ambientale forense e nella ricerca di base. Le Biotecnologie sono in costante e continua evoluzione,
La Biologia Molecolare è oggi alla base di qualunque indagine analitica in campo clinico, alimentare, ambientale forense e nella ricerca di base. Le Biotecnologie sono in costante e continua evoluzione,
20 anni di progressi nella conoscenza sul rischio neoplastico eredo-familiare
 20 anni di progressi nella conoscenza sul rischio neoplastico eredo-familiare 3.7% MO 2/12/2016 20 anni di progressi nella conoscenza sul rischio neoplastico eredo-familiare 7.4% MO 2/12/2016 Frederick
20 anni di progressi nella conoscenza sul rischio neoplastico eredo-familiare 3.7% MO 2/12/2016 20 anni di progressi nella conoscenza sul rischio neoplastico eredo-familiare 7.4% MO 2/12/2016 Frederick
La reazione a catena della polimerasi (PCR) di Ofelia Leone e Vincenzo Mandarino
 La reazione a catena della polimerasi (PCR) di Ofelia Leone e Vincenzo Mandarino La Polymerase Chain Reaction (PCR) o reazione di amplificazione a catena è una tecnica che permette di amplificare una specifica
La reazione a catena della polimerasi (PCR) di Ofelia Leone e Vincenzo Mandarino La Polymerase Chain Reaction (PCR) o reazione di amplificazione a catena è una tecnica che permette di amplificare una specifica
Applicazioni biotecnologiche in systems biology
 Applicazioni biotecnologiche in systems biology Lezione #2 Dr. Marco Galardini AA 2012/2013 Contatti Dr. Marco Galardini Dip. Di Biologia Via Madonna del Piano 6, Polo Scientifico S. Fiorentino (c/o Incubatore
Applicazioni biotecnologiche in systems biology Lezione #2 Dr. Marco Galardini AA 2012/2013 Contatti Dr. Marco Galardini Dip. Di Biologia Via Madonna del Piano 6, Polo Scientifico S. Fiorentino (c/o Incubatore
Corso di Elementi di Bionformatica
 Corso di Elementi di Bionformatica Laurea Triennale in Informatica Il formato FASTQ per la qualità delle sequenze Anno Accademico 2015-2016 Docente del laboratorio: Raffaella Rizzi 1 La qualità delle sequenze
Corso di Elementi di Bionformatica Laurea Triennale in Informatica Il formato FASTQ per la qualità delle sequenze Anno Accademico 2015-2016 Docente del laboratorio: Raffaella Rizzi 1 La qualità delle sequenze
LA PCR E LE SUE VARIANTI. Quaderno di laboratorio. a cura di PRESS FIRENZE UNIVERSITY
 LA PCR E LE SUE VARIANTI Quaderno di laboratorio a cura di an GE LA scia LP I, ale SSIO me N GO N I FIRENZE UNIVERSITY PRESS manuali scienze 2 pianeta redi comitato scientifico renato fani david caramelli
LA PCR E LE SUE VARIANTI Quaderno di laboratorio a cura di an GE LA scia LP I, ale SSIO me N GO N I FIRENZE UNIVERSITY PRESS manuali scienze 2 pianeta redi comitato scientifico renato fani david caramelli
UNIVERSITA DEGLI STUDI DI CAGLIARI Dipartimento di Scienze Mediche UNIVERSITA DEGLI STUDI DI CAGLIARI. Dipartimento di Scienze Mediche Genetica Medica
 AIBT Winter School Ravascletto (UD) 3-5 Dicembre 2015 NGS: NGS: vantaggi, vantaggi, ambiti ambiti e e ricadute. ricadute. Sandro Orrù Sandro Orrù UNIVERSITA DEGLI STUDI DI CAGLIARI UNIVERSITA DEGLI STUDI
AIBT Winter School Ravascletto (UD) 3-5 Dicembre 2015 NGS: NGS: vantaggi, vantaggi, ambiti ambiti e e ricadute. ricadute. Sandro Orrù Sandro Orrù UNIVERSITA DEGLI STUDI DI CAGLIARI UNIVERSITA DEGLI STUDI
HI-TECH IN SANITA'. MINI-INVASIVITA' 2.0: nuove tecnologie al servizio dell'appropriatezza e della bioetica professionale
 HI-TECH IN SANITA'. MINI-INVASIVITA' 2.0: nuove tecnologie al servizio dell'appropriatezza e della bioetica professionale L evoluzione della professione tecnica tra robotica, automazione e nuove tecnologie
HI-TECH IN SANITA'. MINI-INVASIVITA' 2.0: nuove tecnologie al servizio dell'appropriatezza e della bioetica professionale L evoluzione della professione tecnica tra robotica, automazione e nuove tecnologie
Tecnologia del DNA e la genomica. Dr ssa Elisa Mazzoni, Ph.D Biologia Applicata a.a Università di Ferrara
 Tecnologia del DNA e la genomica Dr ssa Elisa Mazzoni, Ph.D Biologia Applicata a.a 2018-2019 Università di Ferrara Alcune Tecnologie del DNA Estrazione del DNA Taglio del DNA con enzimi di restrizione
Tecnologia del DNA e la genomica Dr ssa Elisa Mazzoni, Ph.D Biologia Applicata a.a 2018-2019 Università di Ferrara Alcune Tecnologie del DNA Estrazione del DNA Taglio del DNA con enzimi di restrizione
Sintesi chimica del DNA
 Sintesi chimica del DNA Sintesi chimica di oligonucleotidi Per la sintesi vengono utilizzati fosforamidi dei vari nucleotidi. La fosforamide contiene un buon gruppo uscente che promuove la reazione di
Sintesi chimica del DNA Sintesi chimica di oligonucleotidi Per la sintesi vengono utilizzati fosforamidi dei vari nucleotidi. La fosforamide contiene un buon gruppo uscente che promuove la reazione di
Next Generation Sequencers: from the bacterial culture to raw data. Valeria Michelacci NGS course, June 2015
 Next Generation Sequencers: from the bacterial culture to raw data Valeria Michelacci NGS course, June 2015 COSTS ASSOCIATED WITH DNA SEQUENCING 80-100 $ per Bacterial Genome!! Benefits from NGS Massive
Next Generation Sequencers: from the bacterial culture to raw data Valeria Michelacci NGS course, June 2015 COSTS ASSOCIATED WITH DNA SEQUENCING 80-100 $ per Bacterial Genome!! Benefits from NGS Massive
Tecnologia del DNA e la genomica
 Tecnologia del DNA e la genomica DNA ricombinante La tecnologia del DNA ricombinante permette di unire in laboratorio il DNA di organismi diversi Permette di manipolare il DNA di un organismo allo scopo
Tecnologia del DNA e la genomica DNA ricombinante La tecnologia del DNA ricombinante permette di unire in laboratorio il DNA di organismi diversi Permette di manipolare il DNA di un organismo allo scopo
Biotecnologie applicate all ispezione degli alimenti di origine animale
 Prof.ssa Tiziana Pepe Evoluzioni della tecnica PCR Biotecnologie applicate all ispezione degli alimenti di origine animale Dip. di Medicina Veterinaria e Produzioni animali tiziana.pepe@unina.it Nested
Prof.ssa Tiziana Pepe Evoluzioni della tecnica PCR Biotecnologie applicate all ispezione degli alimenti di origine animale Dip. di Medicina Veterinaria e Produzioni animali tiziana.pepe@unina.it Nested
Lezione 5. Next Generation Sequencing
 Lezione 5 Next Generation Sequencing Perchè Next Generation Sequencing Si possono generare centinaia di milioni di corte sequenze (35bp-250bp) in una sola corsa in un tempo breve con un basso prezzo per
Lezione 5 Next Generation Sequencing Perchè Next Generation Sequencing Si possono generare centinaia di milioni di corte sequenze (35bp-250bp) in una sola corsa in un tempo breve con un basso prezzo per
Dr. Tommaso Giordani SEQUENZIAMENTO SANGER E ANALISI DI SEQUENZE DI DNA
 Dr. Tommaso Giordani SEQUENZIAMENTO SANGER E ANALISI DI SEQUENZE DI DNA OBIETTIVI DELLA GENOMICA MAPPE GENETICHE e FISICHE sempre più accurate SEQUENZIAMENTO GENOMI GENOMICA COMPARATIVA confronto tra genomi
Dr. Tommaso Giordani SEQUENZIAMENTO SANGER E ANALISI DI SEQUENZE DI DNA OBIETTIVI DELLA GENOMICA MAPPE GENETICHE e FISICHE sempre più accurate SEQUENZIAMENTO GENOMI GENOMICA COMPARATIVA confronto tra genomi
CAPITOLATO TECNICO. Kit di controllo qualità delle sfere ioniche template-positive prearricchite e post-arricchite mediante il fluorimetro Qubit (in
 REAGENTI 1 Kit di preparazione PCR in emulsione per sequenziamento Kit per la preparazione, mediante reazione di PCR in emulsione, di 120 test 240 test 163,1 39.144,00 77302685FD sfere ioniche template-positive
REAGENTI 1 Kit di preparazione PCR in emulsione per sequenziamento Kit per la preparazione, mediante reazione di PCR in emulsione, di 120 test 240 test 163,1 39.144,00 77302685FD sfere ioniche template-positive
1. Quantificazione del genomico e determinazione della purezza
 ESERCITAZIONE 2 1. Quantificazione del genomico e determinazione della purezza Una volta estratto il DNA si procede con la quantificazione. Tale quantificazione viene fatta normalmente con l utilizzo di
ESERCITAZIONE 2 1. Quantificazione del genomico e determinazione della purezza Una volta estratto il DNA si procede con la quantificazione. Tale quantificazione viene fatta normalmente con l utilizzo di
TECNICHE DI BIOLOGIA MOLECOLARE. LA REAZIONE POLIMERASICA A CATENA Principi teorici e aspetti pratici
 TECNICHE DI BIOLOGIA MOLECOLARE LA REAZIONE POLIMERASICA A CATENA Principi teorici e aspetti pratici POLYMERASE CHAIN REACTION (PCR) 1955 A. Kronembreg e coll. (Stanford University) scoprono la DNA-polimerasi
TECNICHE DI BIOLOGIA MOLECOLARE LA REAZIONE POLIMERASICA A CATENA Principi teorici e aspetti pratici POLYMERASE CHAIN REACTION (PCR) 1955 A. Kronembreg e coll. (Stanford University) scoprono la DNA-polimerasi
IL SISTEMA TOSCANO PER IL CONTROLLO E LA SALVAGUARDIA DELLE ACQUE DI BALNEAZIONE E DELL AMBIENTE MARINO
 IL SISTEMA TOSCANO PER IL CONTROLLO E LA SALVAGUARDIA DELLE ACQUE DI BALNEAZIONE E DELL AMBIENTE MARINO Livorno, 4 maggio 2018 Sala Ferretti, Fortezza Vecchia Le novità per gestione della stagione balneare
IL SISTEMA TOSCANO PER IL CONTROLLO E LA SALVAGUARDIA DELLE ACQUE DI BALNEAZIONE E DELL AMBIENTE MARINO Livorno, 4 maggio 2018 Sala Ferretti, Fortezza Vecchia Le novità per gestione della stagione balneare
Il DNA come molecola in grado di veicolare informazione ereditabile (genetica)
 Il DNA come molecola in grado di veicolare informazione ereditabile (genetica) Essenz. Alberts: cap 6 La trasmissione dell informazione replicazione trascrizione traduzione DNA RNA Proteina da, dg, dc,
Il DNA come molecola in grado di veicolare informazione ereditabile (genetica) Essenz. Alberts: cap 6 La trasmissione dell informazione replicazione trascrizione traduzione DNA RNA Proteina da, dg, dc,
estremità 5' DNA O - P O H 2 C O H H H H G N H O H 2 C P O H H T N ponte fosfodiestere O 3 P O estremità 3' etc.
 estremità 5' 5 3 - P N 5 2 C 3 ponte fosfodiestere P A 1 2 C 5 P 3 G N 1 2 C 5 3 P T N 1 5 2 C 3 etc. DNA C N 1 estremità 3' zucchero N 1 C 3 4 3 timina N adenina N N 1 6 N N 9 N zucchero N zucchero citosina
estremità 5' 5 3 - P N 5 2 C 3 ponte fosfodiestere P A 1 2 C 5 P 3 G N 1 2 C 5 3 P T N 1 5 2 C 3 etc. DNA C N 1 estremità 3' zucchero N 1 C 3 4 3 timina N adenina N N 1 6 N N 9 N zucchero N zucchero citosina
Database di sequenze. Dati di sequenza. Caratteristiche dei dati della biologia molecolare. I dati ed i problemi della bioinformatica
 I dati ed i problemi della bioinformatica Giorgio Valentini DSI Università degli Studi di Milano 1 Caratteristiche dei dati della biologia molecolare Diverse tipologie di dati bio-molecolari Per ogni tipo
I dati ed i problemi della bioinformatica Giorgio Valentini DSI Università degli Studi di Milano 1 Caratteristiche dei dati della biologia molecolare Diverse tipologie di dati bio-molecolari Per ogni tipo
informazione ed espressione genica
 a.a. 2015-16 CORSO DI LAUREA IN INFERMIERISTICA Dott.ssa Marilena Greco Biologia applicata informazione ed espressione genica Biologia Applicata_M.Greco 1 ACIDI NUCLEICI (DNA, RNA) Gli acidi nucleici trasmettono
a.a. 2015-16 CORSO DI LAUREA IN INFERMIERISTICA Dott.ssa Marilena Greco Biologia applicata informazione ed espressione genica Biologia Applicata_M.Greco 1 ACIDI NUCLEICI (DNA, RNA) Gli acidi nucleici trasmettono
REGISTRO DELLE LEZIONI 2004/2005. Tipologia
 Sistemi di organo Organizzazione dei sistemi di organo Addì 19-01-2005 Addì 19-01-2005 Tessuti di sostegno: lo scheletro Il cranio Addì 19-01-2005 Addì 20-01-2005 Il cranio Lo scheletro assile Addì 20-01-2005
Sistemi di organo Organizzazione dei sistemi di organo Addì 19-01-2005 Addì 19-01-2005 Tessuti di sostegno: lo scheletro Il cranio Addì 19-01-2005 Addì 20-01-2005 Il cranio Lo scheletro assile Addì 20-01-2005
Polymerase Chain Reaction
 Polymerase Chain Reaction La reazione a catena della polimerasi (in inglese: Polymerase Chain Reaction), comunemente nota con l'acronimo PCR, è una tecnica di biologia molecolare che consente la moltiplicazione
Polymerase Chain Reaction La reazione a catena della polimerasi (in inglese: Polymerase Chain Reaction), comunemente nota con l'acronimo PCR, è una tecnica di biologia molecolare che consente la moltiplicazione
IL GENOMA DELLA CELLULA VEGETALE
 IL GENOMA DELLA CELLULA VEGETALE I GENOMI DELLE CELLULE VEGETALI Genoma nucleare Geni per il funzionamento globale della cellula vegetale Condivisi o specifici per la cellula vegetale Genoma plastidiale
IL GENOMA DELLA CELLULA VEGETALE I GENOMI DELLE CELLULE VEGETALI Genoma nucleare Geni per il funzionamento globale della cellula vegetale Condivisi o specifici per la cellula vegetale Genoma plastidiale
AMPLIFICAZIONE IN VITRO DEL DNA REAZIONE A CATENA DELLA POLIMERASI (PCR)
 AMPLIFICAZIONE IN VITRO DEL DNA REAZIONE A CATENA DELLA POLIMERASI (PCR) PCR: reazione polimerasica a catena Inventata da Kary Mullis negli anni 80 (premio Nobel 1993) Serve per ottenere una grande quantita
AMPLIFICAZIONE IN VITRO DEL DNA REAZIONE A CATENA DELLA POLIMERASI (PCR) PCR: reazione polimerasica a catena Inventata da Kary Mullis negli anni 80 (premio Nobel 1993) Serve per ottenere una grande quantita
PCR. PCR o reazione di polimerizzazione a catena. Amplificazione esponenziale di DNA. Puo amplificare un tratto di DNA per piu di 1 milione di volte
 PCR Prof.ssa Flavia Frabetti PCR o reazione di polimerizzazione a catena Fine anni 80 Amplificazione esponenziale di DNA. Puo amplificare un tratto di DNA per piu di 1 milione di volte Permette di estrarre
PCR Prof.ssa Flavia Frabetti PCR o reazione di polimerizzazione a catena Fine anni 80 Amplificazione esponenziale di DNA. Puo amplificare un tratto di DNA per piu di 1 milione di volte Permette di estrarre
REGISTRO DELLE LEZIONI 2004/2005. Tipologia
 Presentazione del corso. Modalità di svolgimento degli esami. Addì 01-03-2005 Addì 01-03-2005 Richiami di stechiometria: formule di struttura. Richiami di stechiometria: legami; numero di ossidazione.
Presentazione del corso. Modalità di svolgimento degli esami. Addì 01-03-2005 Addì 01-03-2005 Richiami di stechiometria: formule di struttura. Richiami di stechiometria: legami; numero di ossidazione.
BIOCHIMICA MOLECOLARE CLINICA
 Corso di Laurea Magistrale in BIOLOGIA CELLULARE e MOLECOLARE E SCIENZE BIOMEDICHE A.A. 2016 2017 BIOCHIMICA MOLECOLARE CLINICA Principi e tecniche molecolari per la diagnosi di patologie umane Prof. Patrizia
Corso di Laurea Magistrale in BIOLOGIA CELLULARE e MOLECOLARE E SCIENZE BIOMEDICHE A.A. 2016 2017 BIOCHIMICA MOLECOLARE CLINICA Principi e tecniche molecolari per la diagnosi di patologie umane Prof. Patrizia
lezione martedì 6 aprile 2010 aula 2 ore 9:00 corso integrato di Biologia Applicata (BU) ed Ingegneria Genetica (BCM)
 lezione 15-16 martedì 6 aprile 2010 aula 2 ore 9:00 corso integrato di Biologia Applicata (BU) ed Ingegneria Genetica (BCM) R.A.C.E. Con la RT-PCR si amplifica solo un frammento del cdna Se si vuole identificare
lezione 15-16 martedì 6 aprile 2010 aula 2 ore 9:00 corso integrato di Biologia Applicata (BU) ed Ingegneria Genetica (BCM) R.A.C.E. Con la RT-PCR si amplifica solo un frammento del cdna Se si vuole identificare
GENOMICA STRUTTURALE: GENOMICA FUNZIONALE: 1. Anatomia dei genomi. 8. Funzionamento dei genomi Il genoma dei procarioti
 GENOMICA STRUTTURALE: GENOMICA FUNZIONALE: 1. Anatomia dei genomi 8. Funzionamento dei genomi Il genoma dei procarioti Modificazioni della cromatina e l espressione del genoma Il genoma degli eucarioti
GENOMICA STRUTTURALE: GENOMICA FUNZIONALE: 1. Anatomia dei genomi 8. Funzionamento dei genomi Il genoma dei procarioti Modificazioni della cromatina e l espressione del genoma Il genoma degli eucarioti
TECNICHE DI BIOLOGIA MOLECOLARE. LA REAZIONE POLIMERASICA A CATENA Principi teorici e aspetti pratici
 TECNICHE DI BIOLOGIA MOLECOLARE LA REAZIONE POLIMERASICA A CATENA Principi teorici e aspetti pratici POLYMERASE CHAIN REACTION (PCR) 1955 A. Kronembreg e coll. (Stanford University) scoprono la DNA-polimerasi
TECNICHE DI BIOLOGIA MOLECOLARE LA REAZIONE POLIMERASICA A CATENA Principi teorici e aspetti pratici POLYMERASE CHAIN REACTION (PCR) 1955 A. Kronembreg e coll. (Stanford University) scoprono la DNA-polimerasi
REPLICAZIONE DEL DNA 1
 REPLICAZIONE DEL DNA 1 La replicazione del DNA è semiconservativa: ciascuno dei due filamenti parentali serve da stampo per la sintesi di un nuovo filamento e le due nuove doppie eliche sono costituite
REPLICAZIONE DEL DNA 1 La replicazione del DNA è semiconservativa: ciascuno dei due filamenti parentali serve da stampo per la sintesi di un nuovo filamento e le due nuove doppie eliche sono costituite
Vettori derivati dal fago λ: batteriofagi filamentosi M13
 Vettori derivati dal fago λ: batteriofagi filamentosi M13 A. Phage display: esibizione della proteina clonata in M13 ed esposta sulla superficie del batteriofago (facile screening dei ricombinanti) mediante
Vettori derivati dal fago λ: batteriofagi filamentosi M13 A. Phage display: esibizione della proteina clonata in M13 ed esposta sulla superficie del batteriofago (facile screening dei ricombinanti) mediante
REGISTRO DELLE LEZIONI 2004/2005. Tipologia. Addì Tipologia. Addì Tipologia. Addì
 Presentazione del corso. Definizione di recettore. Neurotrasmettitori. Processi intracellulari di comunicazione. Interazione farmaco-recettore e tipi di legame: covalente, ionico,ione-dipolo, dipolo-dipolo,
Presentazione del corso. Definizione di recettore. Neurotrasmettitori. Processi intracellulari di comunicazione. Interazione farmaco-recettore e tipi di legame: covalente, ionico,ione-dipolo, dipolo-dipolo,
Permette di monitorare in tempo reale l andamento della reazione ed effettuare una quantizzazione del frammento amplificato
 Permette di monitorare in tempo reale l andamento della reazione ed effettuare una quantizzazione del frammento amplificato Lo strumento è composto da:! Un sistema ottico per eccitare il marcatore fluorescente
Permette di monitorare in tempo reale l andamento della reazione ed effettuare una quantizzazione del frammento amplificato Lo strumento è composto da:! Un sistema ottico per eccitare il marcatore fluorescente
Microbiologia Controlli batteriologici con test del DNA e test di tossicità Lucia Bonadonna Istituto Superiore di Sanità
 Piani per la Sicurezza delle Acque Nuove metodologie di analisi ed inquinanti emergenti Bologna, 12 ottobre 2017 Microbiologia Controlli batteriologici con test del DNA e test di tossicità Lucia Bonadonna
Piani per la Sicurezza delle Acque Nuove metodologie di analisi ed inquinanti emergenti Bologna, 12 ottobre 2017 Microbiologia Controlli batteriologici con test del DNA e test di tossicità Lucia Bonadonna
Diagnostica Biomolecolare: Tecnologie e Applicazioni
 Diagnostica Biomolecolare: Tecnologie e Applicazioni Preparazione dei campioni: (Estrazione del DNA o dell RNA dal tessuto di interesse) Analisi delle mutazioni: SSCP DHPLC Dot blot - Southern - PCR (ARMS
Diagnostica Biomolecolare: Tecnologie e Applicazioni Preparazione dei campioni: (Estrazione del DNA o dell RNA dal tessuto di interesse) Analisi delle mutazioni: SSCP DHPLC Dot blot - Southern - PCR (ARMS
NEXT- GENERATION DNA SEQUENCING
 NEXT- GENERATION DNA SEQUENCING Introduzione Fino a pochi anni fa i metodi utilizzati per il sequenziamento si basavano sul metodo di Sanger, il quale però risulta avere notevoli svantaggi soprattutto
NEXT- GENERATION DNA SEQUENCING Introduzione Fino a pochi anni fa i metodi utilizzati per il sequenziamento si basavano sul metodo di Sanger, il quale però risulta avere notevoli svantaggi soprattutto
Tecniche di sequenziamento del DNA
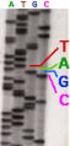 Tecniche di sequenziamento del DNA -Metodo di Maxam e Gilbert (della degradazione chimica del DNA) -Metodo di Sanger (a terminazione di catena) Metodo di Maxam-Gilbert Questo metodo, basato sulla degradazione
Tecniche di sequenziamento del DNA -Metodo di Maxam e Gilbert (della degradazione chimica del DNA) -Metodo di Sanger (a terminazione di catena) Metodo di Maxam-Gilbert Questo metodo, basato sulla degradazione
HI-TECH IN SANITA'. MINI-INVASIVITA' 2.0: nuove tecnologie al servizio dell'appropriatezza e della bioetica professionale
 HI-TECH IN SANITA'. MINI-INVASIVITA'.0: nuove tecnologie al servizio dell'appropriatezza e della bioetica professionale NGS: IMMUNOGENETICA E TRAPIANTI Michela Mazzocco S.C.Laboratorio di istocompatibilità
HI-TECH IN SANITA'. MINI-INVASIVITA'.0: nuove tecnologie al servizio dell'appropriatezza e della bioetica professionale NGS: IMMUNOGENETICA E TRAPIANTI Michela Mazzocco S.C.Laboratorio di istocompatibilità
Dr. Tommaso Giordani SEQUENZIAMENTO SANGER E ANALISI DI SEQUENZE DI DNA
 Dr. Tommaso Giordani SEQUENZIAMENTO SANGER E ANALISI DI SEQUENZE DI DNA OBIETTIVI DELLA GENOMICA MAPPE GENETICHE e FISICHE sempre più accurate SEQUENZIAMENTO GENOMI GENOMICA COMPARATIVA confronto tra genomi
Dr. Tommaso Giordani SEQUENZIAMENTO SANGER E ANALISI DI SEQUENZE DI DNA OBIETTIVI DELLA GENOMICA MAPPE GENETICHE e FISICHE sempre più accurate SEQUENZIAMENTO GENOMI GENOMICA COMPARATIVA confronto tra genomi
0,8% riesce a separare un range di dimensioni da circa 500 bp a circa bp.
 L elettroforesi è una tecnica che utilizza un campo elettrico per separare e visualizzare frammenti di DNA in base al loro peso molecolare ed alla loro carica. Gli acidi nucleici, migrano sempre verso
L elettroforesi è una tecnica che utilizza un campo elettrico per separare e visualizzare frammenti di DNA in base al loro peso molecolare ed alla loro carica. Gli acidi nucleici, migrano sempre verso
METODI DI BASE PER L ANALISI DEGLI ACIDI NUCLEICI
 METODI DI BASE PER L ANALISI DEGLI ACIDI NUCLEICI SPETTRI UV E QUANTIZZAZIONE SPETTROFOTOMETRICA DEGLI ACIDI NUCLEICI FIGURA 7.6A METODOLOGIA BIOCHIMICA (WILSON) a a = a 1 Assorbimento = a b a 1 b FIGURA
METODI DI BASE PER L ANALISI DEGLI ACIDI NUCLEICI SPETTRI UV E QUANTIZZAZIONE SPETTROFOTOMETRICA DEGLI ACIDI NUCLEICI FIGURA 7.6A METODOLOGIA BIOCHIMICA (WILSON) a a = a 1 Assorbimento = a b a 1 b FIGURA
Metodiche di analisi del DNA (cenni) (Ingegneria genetica)
 DNA Metodiche di analisi del DNA (cenni) (Ingegneria genetica) Principali tecniche di base Enzimi di restrizione (Endonucleasi) Gel elettroforesi Ibridizzazione PCR (Polymerase Chain Reaction) Sequenziamento
DNA Metodiche di analisi del DNA (cenni) (Ingegneria genetica) Principali tecniche di base Enzimi di restrizione (Endonucleasi) Gel elettroforesi Ibridizzazione PCR (Polymerase Chain Reaction) Sequenziamento
Principali classi di mutazioni
 Principali classi di mutazioni Regole per valutare la patogenicità di una mutazione I - Delezioni dell intero gene, mutazioni non senso e anomalie della cornice di lettura molto probabilmente distruggono
Principali classi di mutazioni Regole per valutare la patogenicità di una mutazione I - Delezioni dell intero gene, mutazioni non senso e anomalie della cornice di lettura molto probabilmente distruggono
PRINCIPALI TIPI DI PCR a) PRINCIPALI TIPI DI PCR b)
 PRINCIPALI TIPI DI PCR a) RT-PCR: serve a valutare l espressione di un gene tramite l amplificazione dell mrna da esso trascritto PCR COMPETITIVA: serve a valutare la concentrazione iniziale di DNA o RNA
PRINCIPALI TIPI DI PCR a) RT-PCR: serve a valutare l espressione di un gene tramite l amplificazione dell mrna da esso trascritto PCR COMPETITIVA: serve a valutare la concentrazione iniziale di DNA o RNA
REAZIONE A CATENA DELLA POLIMERASI. ( PCR =Polymerase Chain Reaction)
 REAZIONE A CATENA DELLA POLIMERASI ( PCR =Polymerase Chain Reaction) Verso la metà degli anni 80, il biochimico Kary Mullis mise a punto un metodo estremamente rapido e semplice per produrre una quantità
REAZIONE A CATENA DELLA POLIMERASI ( PCR =Polymerase Chain Reaction) Verso la metà degli anni 80, il biochimico Kary Mullis mise a punto un metodo estremamente rapido e semplice per produrre una quantità
Isolamento e purificazione di DNA e RNA. -Separare gli acidi nucleici da altri componenti cellulari (lipidi e proteine)
 Isolamento e purificazione di DNA e RNA -Rompere la membrana cellulare -Separare gli acidi nucleici da altri componenti cellulari (lipidi e proteine) -Separare gli acidi nucleici tra loro -Rompere la membrana
Isolamento e purificazione di DNA e RNA -Rompere la membrana cellulare -Separare gli acidi nucleici da altri componenti cellulari (lipidi e proteine) -Separare gli acidi nucleici tra loro -Rompere la membrana
LA BIOLOGIA MOLECOLARE E UNA BRANCA DELLA BIOLOGIA CHE STUDIA LE BASI MOLECOLARI DELLE FUNZIONI BIOLOGICHE, PONENDO UNA PARTICOLARE ATTENZIONE A QUEI
 CONCETTI DI BASE LA BIOLOGIA MOLECOLARE E UNA BRANCA DELLA BIOLOGIA CHE STUDIA LE BASI MOLECOLARI DELLE FUNZIONI BIOLOGICHE, PONENDO UNA PARTICOLARE ATTENZIONE A QUEI PROCESSI CHE COINVOLGONO GLI ACIDI
CONCETTI DI BASE LA BIOLOGIA MOLECOLARE E UNA BRANCA DELLA BIOLOGIA CHE STUDIA LE BASI MOLECOLARI DELLE FUNZIONI BIOLOGICHE, PONENDO UNA PARTICOLARE ATTENZIONE A QUEI PROCESSI CHE COINVOLGONO GLI ACIDI
Mappe fisiche. Si basano sulla localizzazione fisica delle molecole di DNA
 Mappe fisiche Si basano sulla localizzazione fisica delle molecole di DNA Costruzione di una mappa fisica diversi metodi - Mappe a bassa risoluzione - Mappe ad alta risoluzione Risoluzione= distanza a
Mappe fisiche Si basano sulla localizzazione fisica delle molecole di DNA Costruzione di una mappa fisica diversi metodi - Mappe a bassa risoluzione - Mappe ad alta risoluzione Risoluzione= distanza a
Acidi Nucleici: DNA = acido deossiribonucleico
 Acidi Nucleici: DNA = acido deossiribonucleico depositario dell informazione genetica RNA: acido ribonucleico trascrizione e traduzione dell informazione genetica dogma centrale della biologia molecolare
Acidi Nucleici: DNA = acido deossiribonucleico depositario dell informazione genetica RNA: acido ribonucleico trascrizione e traduzione dell informazione genetica dogma centrale della biologia molecolare
Applicazione della biologia molecolare nella valutazione del benessere del cavallo
 UNIVERSITA DEGLI STUDI DI PERUGIA FACOLTA DI MEDICINA VETERINARIA Centro di Studio del Cavallo Sportivo Applicazione della biologia molecolare nella valutazione del benessere del cavallo Andrea Verini
UNIVERSITA DEGLI STUDI DI PERUGIA FACOLTA DI MEDICINA VETERINARIA Centro di Studio del Cavallo Sportivo Applicazione della biologia molecolare nella valutazione del benessere del cavallo Andrea Verini
Progetto :TRIFOGLIO UNIVERSITA CATTOLICA DEL SACRO CUORE Piacenza. O.G.M. Vegetali
 Progetto :TRIFOGLIO UNIVERSITA CATTOLICA DEL SACRO CUORE Piacenza O.G.M. Vegetali Identificazione di un O.G.M. e metodi di analisi del DNA transgenico Marco Nani 5BL Liceo Scientifico Mattei di Fiorenzuola
Progetto :TRIFOGLIO UNIVERSITA CATTOLICA DEL SACRO CUORE Piacenza O.G.M. Vegetali Identificazione di un O.G.M. e metodi di analisi del DNA transgenico Marco Nani 5BL Liceo Scientifico Mattei di Fiorenzuola
Percorso formativo di BIOLOGIA. I Biennio (Lo studio scientifico della vita Dal macroscopico al microscopico)
 Percorso formativo di BIOLOGIA I Biennio (Lo studio scientifico della vita Dal macroscopico al microscopico) Principi di classificazione e filogenesi degli organismi viventi e basi dell evoluzione Le principali
Percorso formativo di BIOLOGIA I Biennio (Lo studio scientifico della vita Dal macroscopico al microscopico) Principi di classificazione e filogenesi degli organismi viventi e basi dell evoluzione Le principali
Patologie da analizzare
 Fasi cruciali Scelta della patologia da analizzare Scelta del campione da analizzare Scelta dell approccio da utilizzare Scelta della tecnica da utilizzare Analisi statistica del dati Conferme con approcci
Fasi cruciali Scelta della patologia da analizzare Scelta del campione da analizzare Scelta dell approccio da utilizzare Scelta della tecnica da utilizzare Analisi statistica del dati Conferme con approcci
2. DUPLICAZIONE DNA. 1. COMPOSIZIONE e STRUTTURA 3. CROMOSOMI
 2. DUPLICAZIONE DNA 1. COMPOSIZIONE e STRUTTURA 3. CROMOSOMI 1 1. COMPOSIZIONE e STRUTTURA Ma che cos è il DNA? è un contenitore di informazioni... scritte come sequenza di basi azotate 2 Acidi Nucleici:
2. DUPLICAZIONE DNA 1. COMPOSIZIONE e STRUTTURA 3. CROMOSOMI 1 1. COMPOSIZIONE e STRUTTURA Ma che cos è il DNA? è un contenitore di informazioni... scritte come sequenza di basi azotate 2 Acidi Nucleici:
PCR. (Reazione a catena della polimerasi) ESTRAZIONE del DNA da gel di AGAROSIO. Corso di INGEGNERIA GENETICA, Prof. Renato Fani,
 PCR (Reazione a catena della polimerasi) & ESTRAZIONE del DNA da gel di AGAROSIO Corso di INGEGNERIA GENETICA, Prof. Renato Fani, ESERCITAZIONE DI LAB. N.2 La PCR (Polymerase Chain Reaction) è una tecnica
PCR (Reazione a catena della polimerasi) & ESTRAZIONE del DNA da gel di AGAROSIO Corso di INGEGNERIA GENETICA, Prof. Renato Fani, ESERCITAZIONE DI LAB. N.2 La PCR (Polymerase Chain Reaction) è una tecnica
Corso di laurea magistrale in. Scienze per la diagnostica e conservazione dei beni culturali
 Corso di laurea magistrale in Scienze per la diagnostica e conservazione dei beni culturali Insegnamento di Microbiologia applicata ai beni culturali RIEPILOGO DEI CONCETTI BASE DELLA MICROBIOLOGIA GENERALE
Corso di laurea magistrale in Scienze per la diagnostica e conservazione dei beni culturali Insegnamento di Microbiologia applicata ai beni culturali RIEPILOGO DEI CONCETTI BASE DELLA MICROBIOLOGIA GENERALE
Bioinformatica. :studio dei problemi biologici attraverso le metodologie dell'informatica
 Bioinformatica :studio dei problemi biologici attraverso le metodologie dell'informatica Sinomimi: biochimica computazionale, biologia molecolare computazionale Viceversa: Biocomputazione, algoritmi genetici,
Bioinformatica :studio dei problemi biologici attraverso le metodologie dell'informatica Sinomimi: biochimica computazionale, biologia molecolare computazionale Viceversa: Biocomputazione, algoritmi genetici,
COME È FATTO? Ogni filamento corrisponde ad una catena di nucleotidi
 Il DNA Il DNA è una sostanza che si trova in ogni cellula e contiene tutte le informazioni sulla forma e sulle funzioni di ogni essere vivente: eppure è una molecola incredibilmente semplice. COME È FATTO?
Il DNA Il DNA è una sostanza che si trova in ogni cellula e contiene tutte le informazioni sulla forma e sulle funzioni di ogni essere vivente: eppure è una molecola incredibilmente semplice. COME È FATTO?
Dr. Tommaso Giordani METODI DI NEXT GENERATION SEQUENCING (NGS)
 Dr. Tommaso Giordani METODI DI NEXT GENERATION SEQUENCING (NGS) Per il sequenziamento di genomi la metodica principalmente utilizzata fino a pochi anni fa era basata su una strategia enzimatica, metodo
Dr. Tommaso Giordani METODI DI NEXT GENERATION SEQUENCING (NGS) Per il sequenziamento di genomi la metodica principalmente utilizzata fino a pochi anni fa era basata su una strategia enzimatica, metodo
Il Genoma Umano e La Bioinformatica. Marin Vargas, Sergio Paul
 Il Genoma Umano e La Bioinformatica Marin Vargas, Sergio Paul Gennaio 2014 L'acido desossiribonucleico o deossiribonucleico (DNA), che si trova nel nucleo della cellula, è un acido nucleico che contiene
Il Genoma Umano e La Bioinformatica Marin Vargas, Sergio Paul Gennaio 2014 L'acido desossiribonucleico o deossiribonucleico (DNA), che si trova nel nucleo della cellula, è un acido nucleico che contiene
Principali tecniche di base
 Principali tecniche di base Enzimi di restrizione (Endonucleasi) Gel elettroforesi Ibridizzazione (Southern blotting) PCR (Polymerase Chain Reaction) (Sequenziamento) Tecniche di base Enzimi di di restrizione
Principali tecniche di base Enzimi di restrizione (Endonucleasi) Gel elettroforesi Ibridizzazione (Southern blotting) PCR (Polymerase Chain Reaction) (Sequenziamento) Tecniche di base Enzimi di di restrizione
Le molecole di RNA possono assumere particolari strutture che conferiscono loro particolari funzioni.
 Traduzione: t-rna Le molecole di RNA possono assumere particolari strutture che conferiscono loro particolari funzioni. Singola catena alta flessibilità ripiegamento su stessa legami deboli con se stessa
Traduzione: t-rna Le molecole di RNA possono assumere particolari strutture che conferiscono loro particolari funzioni. Singola catena alta flessibilità ripiegamento su stessa legami deboli con se stessa
LABORATORIO DI GENETICA SUMMER SCHOOL 2014
 P a g i n a 1 LABORATORIO DI GENETICA SUMMER SCHOOL 2014 PROTOCOLLO DI ESTRAZIONE DEL DNA DA TESSUTI VEGETALI GenElute Plant Genomic DNA Miniprep Kit (Sigma-Aldrich) https://www.google.it/url?sa=t&rct=j&q=&esrc=s&source=web&cd=2&cad=rja&uact=8&ved=0c
P a g i n a 1 LABORATORIO DI GENETICA SUMMER SCHOOL 2014 PROTOCOLLO DI ESTRAZIONE DEL DNA DA TESSUTI VEGETALI GenElute Plant Genomic DNA Miniprep Kit (Sigma-Aldrich) https://www.google.it/url?sa=t&rct=j&q=&esrc=s&source=web&cd=2&cad=rja&uact=8&ved=0c
Laboratorio di Elementi di Bioinformatica
 Laboratorio di Elementi di Bioinformatica Laurea Triennale in Informatica (codice: E3101Q116) AA 2016/2017 I dati in Bioinformatica Docente del laboratorio: Raffaella Rizzi 1 Il DNA (oggetto biologico)
Laboratorio di Elementi di Bioinformatica Laurea Triennale in Informatica (codice: E3101Q116) AA 2016/2017 I dati in Bioinformatica Docente del laboratorio: Raffaella Rizzi 1 Il DNA (oggetto biologico)
Come facciamo ad isolare un gene da un organismo? Utilizziamo una libreria ovvero una collezione dei geni del genoma del cromosoma di un organismo
 Come facciamo ad isolare un gene da un organismo? Utilizziamo una libreria ovvero una collezione dei geni del genoma del cromosoma di un organismo GENOMA di alcuni organismi viventi raffigurato come libri
Come facciamo ad isolare un gene da un organismo? Utilizziamo una libreria ovvero una collezione dei geni del genoma del cromosoma di un organismo GENOMA di alcuni organismi viventi raffigurato come libri
Reazione a catena della polimerasi (PCR) ed elettroforesi
 Gioele Casagranda, Camilla Larentis, Emanuele Pallaoro, Filippo Quattrocchi Povo, 1 marzo 2016 P r o g e t t o C L I L - E s p e r i m e n t o f i n a l e Reazione a catena della polimerasi (PCR) ed elettroforesi
Gioele Casagranda, Camilla Larentis, Emanuele Pallaoro, Filippo Quattrocchi Povo, 1 marzo 2016 P r o g e t t o C L I L - E s p e r i m e n t o f i n a l e Reazione a catena della polimerasi (PCR) ed elettroforesi
Genomi vegetali Da 7x10 7 bp per genoma aploide (130Mbp diploide, 5 cromosomi) di Arabidopsis thaliana alle 1,5x10 11 bp ( Mbp=150Gbp) di una
 Genomi vegetali Da 7x10 7 bp per genoma aploide (130Mbp diploide, 5 cromosomi) di Arabidopsis thaliana alle 1,5x10 11 bp (150.000Mbp=150Gbp) di una Liliacea. Tra le graminacee il frumento ha un genoma
Genomi vegetali Da 7x10 7 bp per genoma aploide (130Mbp diploide, 5 cromosomi) di Arabidopsis thaliana alle 1,5x10 11 bp (150.000Mbp=150Gbp) di una Liliacea. Tra le graminacee il frumento ha un genoma
Acidi nucleici basi puriniche basi pirimidiniche
 basi puriniche basi pirimidiniche La sequenza dei nucleotidi in una catena di acido nucleico viene descritta partendo dall estremità 5 e identifica l ordine di successione delle basi utilizzando le abbreviazioni
basi puriniche basi pirimidiniche La sequenza dei nucleotidi in una catena di acido nucleico viene descritta partendo dall estremità 5 e identifica l ordine di successione delle basi utilizzando le abbreviazioni
PCR, Polymerase Chain Reaction (Reazione a catena della DNA polimerasi)
 Polymerase Chain Reaction 1 PCR, Polymerase Chain Reaction (Reazione a catena della DNA polimerasi) La PCR è una tecnica di biologia molecolare per replicare ripetutamente (amplificare), in modo estremamente
Polymerase Chain Reaction 1 PCR, Polymerase Chain Reaction (Reazione a catena della DNA polimerasi) La PCR è una tecnica di biologia molecolare per replicare ripetutamente (amplificare), in modo estremamente
immagine Biologia applicata alla ricerca bio-medica Materiale Didattico Docente: Di Bernardo
 Esperto in processi innovativi di sintesi biomolecolare applicata a tecniche di epigenetica Materiale Didattico Biologia applicata alla ricerca bio-medica immagine Docente: Di Bernardo HUMAN GENOME PROJECT
Esperto in processi innovativi di sintesi biomolecolare applicata a tecniche di epigenetica Materiale Didattico Biologia applicata alla ricerca bio-medica immagine Docente: Di Bernardo HUMAN GENOME PROJECT
Laboratorio di Elementi di Bioinformatica
 Laboratorio di Elementi di Bioinformatica Laurea Triennale in Informatica (codice: E3101Q116) AA 2017/2018 ati in Bioinformatica ocente: Raffaella Rizzi 1 Outline ü Cos è un NA genomico e un RNA? Outline
Laboratorio di Elementi di Bioinformatica Laurea Triennale in Informatica (codice: E3101Q116) AA 2017/2018 ati in Bioinformatica ocente: Raffaella Rizzi 1 Outline ü Cos è un NA genomico e un RNA? Outline
Laboratorio di Elementi di Bioinformatica
 Laboratorio di Elementi di Bioinformatica Laurea Triennale in Informatica (codice: E30Q6) AA 205/206 Esempio di workflow Docente del laboratorio: Raffaella Rizzi Scopo del workflow Scopo: dato un insieme
Laboratorio di Elementi di Bioinformatica Laurea Triennale in Informatica (codice: E30Q6) AA 205/206 Esempio di workflow Docente del laboratorio: Raffaella Rizzi Scopo del workflow Scopo: dato un insieme
Tecnologia del DNA ricombinante
 Tecnologia del DNA ricombinante Scoperte rivoluzionarie che hanno permesso lo studio del genoma e della funzione dei singoli geni Implicazioni enormi nel progresso della medicina: comprensione malattie
Tecnologia del DNA ricombinante Scoperte rivoluzionarie che hanno permesso lo studio del genoma e della funzione dei singoli geni Implicazioni enormi nel progresso della medicina: comprensione malattie
