immagine Biologia applicata alla ricerca bio-medica Materiale Didattico Docente: Di Bernardo
|
|
|
- Floriana Cicci
- 8 anni fa
- Visualizzazioni
Transcript
1 Esperto in processi innovativi di sintesi biomolecolare applicata a tecniche di epigenetica Materiale Didattico Biologia applicata alla ricerca bio-medica immagine Docente: Di Bernardo
2
3 HUMAN GENOME PROJECT (HGP) 1990 DETERMINARE LA SEQUENZA NUCLEOTIDICA DELL INTERO GENOMA UMANO (~3,2 x 10 9 bp) COLLEZIONARE QUESTA INFORMAZIONE IN BANCHE DATI IDENTIFICARE TUTTI I GENI UMANI
4 HUMAN GENOME PROJECT (HGP) 1990 Pianificato per una durata di 15 anni Completato nel 2003 (prima bozza nel 2000)
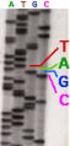
5 Sequenziamento del DNA T C G A Didesossinucleotidi marcati fluorescenti A G T G C A T C A G T A T T G G Reazione di sequenza, separazione dei frammenti I frammenti fluorescenti passano attraverso il detector Metodo manuale Metodo automatizzato
6 METODO MANUALE METODO DI SANGER METODO DI MAXAM- GILBERT
7 METODO DI SANGER Metodo per terminazione di catena METODO DEI DIDEOSSI METODO ENZIMATICO Nella miscela di reazione i ddntps vengono mescolati, in bassa concentrazione, con i dntps: competizione. Quando un ddntp è incorporato nella catena nascente al posto di un dntp, ne impedisce l ulteriore allungamento.
8 Metodo di Sanger Dideossiribonucleotidi
9 METODO DI SANGER
10 Metodo di Sanger
11 Metodo di Sanger
12 ELETTROFORESI SU GEL DI POLIACRILAMMIDE Per analizzare i prodotti finali delle reazioni è necessario utilizzare un gel ad altissima risoluzione poiché si devono separare frammenti di DNA che differiscono tra di loro per un solo nucleotide. Si tratta di un gel sottilissimo (0,3-0,4 mm) di acrilammide ed urea preparato tra due lastre di vetro di notevole lunghezza (circa 40 cm).
13 GEL DI SEQUENZA ALTO POTERE DI RISOLUZIONE CONDIZIONI DENATURANTI= UREA ALTO VOLTAGGIO = V TEMP. CONTROLLATA COSTANTE = C
14 Sequenziamento: metodo manuale T C G A 5 A T A A G G A C A C T T C A A T 3
15
16 METODO DI MAXAM-GILBERT Degradazione chimica - METODO CHIMICO Permanganato di potassio = T Acido formico= A Dimetil solfato = G
17 METODO DI MAXAM-GILBERT Degradazione chimica - METODO CHIMICO Dimetil solfato = G MARCATURA metile G G G metile G G G metile G G G PIPERIDINA
18 METODO DI MAXAM-GILBERT Degradazione chimica - METODO CHIMICO MARCATURA PIPERIDINA G G G G G G
19 METODO DI MAXAM-GILBERT Degradazione chimica - METODO CHIMICO MARCATURA G G G
20 Sequenziamento: metodo manuale T C G A 5 A T A A G G A C A C T T C A A T 3
21 METODO CHIMICO MAXAM - GILBERT LABORIOSO REAGENTI TOSSICI METODO ENZIMATICO SANGER QUELLO + USATO CON MODIFICHE
22 BigDye technology IL CAMPIONE PUO ESSERE PROCESSATO IN UN UNICA PROVETTA
23 Sequenziamento a ciclo termico Necessità di minor quantità di stampo di DNA Annealing più specifico del primer Possibilità di sequenziare prodotti di PCR o stampi difficili (es. cosmidi)
24 SEQUENZIAMENTO AUTOMATICO METODO SANGER MODIFICATO RODAMINA ACIDO AMINOBENZOICO FLUORESCEINA
25
26
27 dntp Timina Adenina Guanina Citosina SANGER + ddntp marcati ddtimina ddadenina ddguanina ddcitosina Ogni ddntp è coniugato con un diverso fluorocromo.
28 SANGER IN AUTOMATICO Denaturazione del prodotto di PCR
29 SANGER IN AUTOMATICO Annealing del primer Primer 1
30 SANGER IN AUTOMATICO Estensione: la DNA polimerasi inizia l estensione del filamento a partire dall estremità 3 OH del primer in presenza di dntp S e ddntp S. Primer 1 DNA polimerasi
31 Estensione SANGER IN AUTOMATICO Primer 1 DNA polimerasi
32 SANGER IN AUTOMATICO Il filamento di DNA viene esteso fino a quando non viene incorporato un ddntp Primer 1 ddntp
33 SANGER IN AUTOMATICO Il filamento neosintetizzato viene rilasciato e lo stampo originale è pronto per essere copiato ddntp
34 SANGER IN AUTOMATICO Si ripete il processo : Denaturazione 95 Annealing Estensione CICLI Primer 1
35 SANGER IN AUTOMATICO La sintesi procede: grazie alla incorporazione casuale dei ddntps vengono sintetizzate centinaia di copie di DNA, ciascuna terminante con una diversa base (un diverso ddntp). Gruppo di frammenti 28 basi 27 basi 26 basi 25 basi 24 basi
36
37
38 SEQUENZIAMENTO AUTOMATICO METODO SANGER MODIFICATO
39
40
41 Elettroferogramma
42
43 DETERMINAZIONE DELLA QUALITA DI SEQUENZA
44 ABI PRISM 310 Genetic Analyzer
45 NEWS:PYRISEQUENCING (PSQ) Direzione sintesi 5 3
46 PYRISEQUENCING (PSQ) Tecnica di recente sviluppo, basata sulla quantificazione luminometrica indiretta dei gruppi pirofosfato (PP) che vengono liberati dai nucleotidi incorporati durante la sintesi di un filamento di DNA complementare ad un templato stampo. VANTAGGI: Elevata accuratezza Altamente automatizzata 96 campioni processati in 20 minuti
47
48
49
50
51 ANALISI DEI DATI Viene inserita la sequenza in una banca dati affidabile. Un software gestisce i dati, attraverso un confronto con sequenze di riferimento, e permette l identificazione della sequenza in esame
52 GENBANK Database EMBL, GenBank, Ribosomal Differentiation of Medical Microorganisms, html
53 ANALISI POST-GENOMICHE Conoscere la sequenza genomica di un organismo non è che l inizio di una serie di esperimenti che potrebbero non essere stati concepiti in precedenza.
SEQUENZIAMENTO DEL DNA
 SEQUENZIAMENTO DEL DNA Il metodo di Sanger per determinare la sequenza del DNA Il metodo manuale La reazione enzimatica Elettroforesi in gel denaturante di poliacrilammide Autoradiografia Il metodo automatico
SEQUENZIAMENTO DEL DNA Il metodo di Sanger per determinare la sequenza del DNA Il metodo manuale La reazione enzimatica Elettroforesi in gel denaturante di poliacrilammide Autoradiografia Il metodo automatico
REAZIONE A CATENA DELLA POLIMERASI. ( PCR =Polymerase Chain Reaction)
 REAZIONE A CATENA DELLA POLIMERASI ( PCR =Polymerase Chain Reaction) Verso la metà degli anni 80, il biochimico Kary Mullis mise a punto un metodo estremamente rapido e semplice per produrre una quantità
REAZIONE A CATENA DELLA POLIMERASI ( PCR =Polymerase Chain Reaction) Verso la metà degli anni 80, il biochimico Kary Mullis mise a punto un metodo estremamente rapido e semplice per produrre una quantità
HUMAN GENOME PROJECT (HGP) 1990
 HUMN ENOME PROJE (HP) 1990 DEERMINRE L SEQUENZ NULEOIDI DELL INERO ENOM UMNO (~3,2 x 10 9 bp) OLLEZIONRE QUES INFORMZIONE IN BNHE DI IDENIFIRE UI I ENI UMNI HUMN ENOME PROJE (HP) 1990 Sequenziamento del
HUMN ENOME PROJE (HP) 1990 DEERMINRE L SEQUENZ NULEOIDI DELL INERO ENOM UMNO (~3,2 x 10 9 bp) OLLEZIONRE QUES INFORMZIONE IN BNHE DI IDENIFIRE UI I ENI UMNI HUMN ENOME PROJE (HP) 1990 Sequenziamento del
Dopo aver effettuato la PCR, all interno della soluzione oltre al tratto amplificato sono presenti: primers, dntps, Taq polimerasi e tampone di
 Dopo aver effettuato la PCR, all interno della soluzione oltre al tratto amplificato sono presenti: primers, dntps, Taq polimerasi e tampone di reazione Inizialmente i 20 µl dell amplificato vengono
Dopo aver effettuato la PCR, all interno della soluzione oltre al tratto amplificato sono presenti: primers, dntps, Taq polimerasi e tampone di reazione Inizialmente i 20 µl dell amplificato vengono
Tecniche di sequenziamento del DNA
 Tecniche di sequenziamento del DNA -Metodo di Maxam e Gilbert (della degradazione chimica del DNA) -Metodo di Sanger (a terminazione di catena) Metodo di Maxam-Gilbert Questo metodo, basato sulla degradazione
Tecniche di sequenziamento del DNA -Metodo di Maxam e Gilbert (della degradazione chimica del DNA) -Metodo di Sanger (a terminazione di catena) Metodo di Maxam-Gilbert Questo metodo, basato sulla degradazione
TECNICHE DI BIOLOGIA MOLECOLARE. LA REAZIONE POLIMERASICA A CATENA Principi teorici e aspetti pratici
 TECNICHE DI BIOLOGIA MOLECOLARE LA REAZIONE POLIMERASICA A CATENA Principi teorici e aspetti pratici POLYMERASE CHAIN REACTION (PCR) 1955 A. Kronembreg e coll. (Stanford University) scoprono la DNA-polimerasi
TECNICHE DI BIOLOGIA MOLECOLARE LA REAZIONE POLIMERASICA A CATENA Principi teorici e aspetti pratici POLYMERASE CHAIN REACTION (PCR) 1955 A. Kronembreg e coll. (Stanford University) scoprono la DNA-polimerasi
La farmacogeneticanella gestione del paziente con tumore colorettale, l esperienza traslazionaleal CRO di Aviano
 SOC di Farmacologia Sperimentale e Clinica VI CONGRESSO NAZIONALE FITeLab Slow Medicine Laboratory: IT s the Future 1-2-3 Ottobre 2015 Ospedale Borgo Roma (Verona) La farmacogeneticanella gestione del
SOC di Farmacologia Sperimentale e Clinica VI CONGRESSO NAZIONALE FITeLab Slow Medicine Laboratory: IT s the Future 1-2-3 Ottobre 2015 Ospedale Borgo Roma (Verona) La farmacogeneticanella gestione del
La reazione a catena della polimerasi (PCR) di Ofelia Leone e Vincenzo Mandarino
 La reazione a catena della polimerasi (PCR) di Ofelia Leone e Vincenzo Mandarino La Polymerase Chain Reaction (PCR) o reazione di amplificazione a catena è una tecnica che permette di amplificare una specifica
La reazione a catena della polimerasi (PCR) di Ofelia Leone e Vincenzo Mandarino La Polymerase Chain Reaction (PCR) o reazione di amplificazione a catena è una tecnica che permette di amplificare una specifica
Lezioni di biotecnologie
 Lezioni di biotecnologie 2 Lezione 2 Analisi del DNA e delle proteine 3 Analizzare DNA e proteine Per le applicazioni delle biotecnologie è di fondamentale importanza: 1. essere in grado di identificare
Lezioni di biotecnologie 2 Lezione 2 Analisi del DNA e delle proteine 3 Analizzare DNA e proteine Per le applicazioni delle biotecnologie è di fondamentale importanza: 1. essere in grado di identificare
Isolamento e purificazione di DNA e RNA. -Separare gli acidi nucleici da altri componenti cellulari (lipidi e proteine)
 Isolamento e purificazione di DNA e RNA -Rompere la membrana cellulare -Separare gli acidi nucleici da altri componenti cellulari (lipidi e proteine) -Separare gli acidi nucleici tra loro -Rompere la membrana
Isolamento e purificazione di DNA e RNA -Rompere la membrana cellulare -Separare gli acidi nucleici da altri componenti cellulari (lipidi e proteine) -Separare gli acidi nucleici tra loro -Rompere la membrana
Laboratorio di diagnostica Molecolare Dipartimento di Patologia Sezione di Anatomia Patologica Università di Verona
 Laboratorio di diagnostica Molecolare Dipartimento di Patologia Sezione di Anatomia Patologica Università di Verona Il tecnico di laboratorio biomedico: Applicazioni nel laboratorio di anatomia patologica
Laboratorio di diagnostica Molecolare Dipartimento di Patologia Sezione di Anatomia Patologica Università di Verona Il tecnico di laboratorio biomedico: Applicazioni nel laboratorio di anatomia patologica
Tecniche molecolari per lo studio degli acidi nucleici
 Tecniche molecolari per lo studio degli acidi nucleici Prof.ssa Flavia Frabetti aa. 2010-11 Estrazione acidi nucleici (DNA o RNA) Verifica tramite elettroforesi su gel di agarosio Amplificazione o clonaggio
Tecniche molecolari per lo studio degli acidi nucleici Prof.ssa Flavia Frabetti aa. 2010-11 Estrazione acidi nucleici (DNA o RNA) Verifica tramite elettroforesi su gel di agarosio Amplificazione o clonaggio
Analisi di polimorfismi usati per la caratterizzazione di profili genetici in campioni di. DNA umano. 22-26 giugno 2009
 Analisi di polimorfismi usati per la caratterizzazione di profili genetici in campioni di 22-26 giugno 2009 DNA umano 1 GENETICA FORENSE La genetica forense applica tecniche di biologia molecolare al fine
Analisi di polimorfismi usati per la caratterizzazione di profili genetici in campioni di 22-26 giugno 2009 DNA umano 1 GENETICA FORENSE La genetica forense applica tecniche di biologia molecolare al fine
PCR (Polymerase Chain Reaction)
 PCR (Polymerase Chain Reaction) Metodo enzimatico estremamente rapido e semplice per produrre una quantità illimitata di copie della sequenza di un singolo gene Sometime a good idea comes to yow when you
PCR (Polymerase Chain Reaction) Metodo enzimatico estremamente rapido e semplice per produrre una quantità illimitata di copie della sequenza di un singolo gene Sometime a good idea comes to yow when you
PCR Polymerase Chain Reaction = Reazione a catena della polimerasi
 PR Polymerase hain Reaction = Reazione a catena della polimerasi mplifica un frammento di D di cui si conosce almeno in parte la sequenza Utilizza un enzima, la D Polimerasi, per copiare una molecola di
PR Polymerase hain Reaction = Reazione a catena della polimerasi mplifica un frammento di D di cui si conosce almeno in parte la sequenza Utilizza un enzima, la D Polimerasi, per copiare una molecola di
Analisi di sequenziamento degli acidi nucleici
 Analisi di sequenziamento degli acidi nucleici In questa lezione darò qualche breve cenno sui metodi di sequenziamento del DNA e specialmente quelli con marcatura fluorescente che attualmente vengono effettuati
Analisi di sequenziamento degli acidi nucleici In questa lezione darò qualche breve cenno sui metodi di sequenziamento del DNA e specialmente quelli con marcatura fluorescente che attualmente vengono effettuati
ANALISI DI MUTAZIONI PUNTIFORMI NON NOTE ANALISI DI SEQUENZA.
 ANALISI DI MUTAZIONI PUNTIFORMI NON NOTE Margherita Vinciguerra U.O. Ematologia II Laboratorio per lo Studio e la Diagnosi Molecolare Prenatale di Talassemia A.O. V. Cervello, Palermo. Analisi di sequenza
ANALISI DI MUTAZIONI PUNTIFORMI NON NOTE Margherita Vinciguerra U.O. Ematologia II Laboratorio per lo Studio e la Diagnosi Molecolare Prenatale di Talassemia A.O. V. Cervello, Palermo. Analisi di sequenza
PROGETTO BIOFORM Corso didattico sperimentale. Esercizio. Tipizzazione del gene PV92
 PROGETTO BIOFORM Corso didattico sperimentale Esercizio Tipizzazione del gene PV92 Elementi trasponibili Che cosa sono gli elementi trasponibili? Sono segmenti di DNA che sono in grado di trasferirsi in
PROGETTO BIOFORM Corso didattico sperimentale Esercizio Tipizzazione del gene PV92 Elementi trasponibili Che cosa sono gli elementi trasponibili? Sono segmenti di DNA che sono in grado di trasferirsi in
HI-TECH IN SANITA'. MINI-INVASIVITA' 2.0: nuove tecnologie al servizio dell'appropriatezza e della bioetica professionale
 HI-TECH IN SANITA'. MINI-INVASIVITA' 2.0: nuove tecnologie al servizio dell'appropriatezza e della bioetica professionale L evoluzione della professione tecnica tra robotica, automazione e nuove tecnologie
HI-TECH IN SANITA'. MINI-INVASIVITA' 2.0: nuove tecnologie al servizio dell'appropriatezza e della bioetica professionale L evoluzione della professione tecnica tra robotica, automazione e nuove tecnologie
Analisi dei marcatori molecolari della pluripotenza e del differenziamento delle cellule embrionali staminali (ES) murine
 Training Course 2010 Stem Cell Differentiation Napoli, 9-12 Novembre Analisi dei marcatori molecolari della pluripotenza e del differenziamento delle cellule embrionali staminali (ES) murine Cristina D
Training Course 2010 Stem Cell Differentiation Napoli, 9-12 Novembre Analisi dei marcatori molecolari della pluripotenza e del differenziamento delle cellule embrionali staminali (ES) murine Cristina D
ANALISI POST-GENOMICHE TRASCRITTOMA: CONTENUTO DI RNA DI UNA CELLULA.
 TECNICHE PER L ANALISI DELL ESPRESSIONE GENICA RT-PCR REAL TIME PCR NORTHERN BLOTTING ANALISI POST-GENOMICHE Conoscere la sequenza genomica di un organismo non è che l inizio di una serie di esperimenti
TECNICHE PER L ANALISI DELL ESPRESSIONE GENICA RT-PCR REAL TIME PCR NORTHERN BLOTTING ANALISI POST-GENOMICHE Conoscere la sequenza genomica di un organismo non è che l inizio di una serie di esperimenti
PCR. (Reazione a catena della polimerasi) ESTRAZIONE del DNA da gel di AGAROSIO. Corso di INGEGNERIA GENETICA, Prof. Renato Fani,
 PCR (Reazione a catena della polimerasi) & ESTRAZIONE del DNA da gel di AGAROSIO Corso di INGEGNERIA GENETICA, Prof. Renato Fani, ESERCITAZIONE DI LAB. N.2 La PCR (Polymerase Chain Reaction) è una tecnica
PCR (Reazione a catena della polimerasi) & ESTRAZIONE del DNA da gel di AGAROSIO Corso di INGEGNERIA GENETICA, Prof. Renato Fani, ESERCITAZIONE DI LAB. N.2 La PCR (Polymerase Chain Reaction) è una tecnica
immagine Biologia applicata alla ricerca bio-medica Materiale Didattico Docente: Di Bernardo
 Esperto in processi innovativi di sintesi biomolecolare applicata a tecniche di epigenetica Materiale Didattico Biologia applicata alla ricerca bio-medica immagine Docente: Di Bernardo TECNICHE PER L ANALISI
Esperto in processi innovativi di sintesi biomolecolare applicata a tecniche di epigenetica Materiale Didattico Biologia applicata alla ricerca bio-medica immagine Docente: Di Bernardo TECNICHE PER L ANALISI
IL SEQUENZIAMENTO DEL DNA. Obiettivo: ottenere la sequenza nucleotidica di un frammento di DNA.
 IL SEQUENZIAMENTO DEL DNA Obiettivo: ottenere la sequenza nucleotidica di un frammento di DNA. Il DNA può essere sequenziato generando frammenti di DNA la cui lunghezza dipende dall ultima base della sequenza.
IL SEQUENZIAMENTO DEL DNA Obiettivo: ottenere la sequenza nucleotidica di un frammento di DNA. Il DNA può essere sequenziato generando frammenti di DNA la cui lunghezza dipende dall ultima base della sequenza.
I marcatori molecolari. Dipartimento di Scienze Agronomiche e Genetica Vegetale Agraria Corso di Genetica Agraria Giovanna Attene
 I marcatori molecolari Dipartimento di Scienze Agronomiche e Genetica Vegetale Agraria Corso di Genetica Agraria Giovanna Attene Marcatori molecolari del DNA I marcatori molecolari sono sequenze di DNA
I marcatori molecolari Dipartimento di Scienze Agronomiche e Genetica Vegetale Agraria Corso di Genetica Agraria Giovanna Attene Marcatori molecolari del DNA I marcatori molecolari sono sequenze di DNA
LA TECNOLOGIA SANGER SEQUENCING RICERCATORE TEAM LEADER: DOTT.SSA VELCA BOTTI
 LA TECNOLOGIA SANGER SEQUENCING RICERCATORE TEAM LEADER: DOTT.SSA VELCA BOTTI 1953: scoperta del DNA (Watson e Crick) CENNI STORICI 1977: metodo di Sanger per il sequenziamento del DNA (pubblicazione della
LA TECNOLOGIA SANGER SEQUENCING RICERCATORE TEAM LEADER: DOTT.SSA VELCA BOTTI 1953: scoperta del DNA (Watson e Crick) CENNI STORICI 1977: metodo di Sanger per il sequenziamento del DNA (pubblicazione della
8-06-2010. BLOTTING degli acidi nucleici: RT-PCR SOUTHERN BLOTTING NORTHERN BLOTTING. BLOTTING delle proteine: NORTHERN BLOTTING SOUTHERN BLOTTING
 8-06-2010 TECNICHE PER L ANALISI DELL ESPRESSIONE GENICA BLOTTING degli acidi nucleici: RT-PCR REAL TIME PCR SOUTHERN BLOTTING NORTHERN BLOTTING NORTHERN BLOTTING BLOTTING delle proteine: MICROARRAYS MACROARRAYS
8-06-2010 TECNICHE PER L ANALISI DELL ESPRESSIONE GENICA BLOTTING degli acidi nucleici: RT-PCR REAL TIME PCR SOUTHERN BLOTTING NORTHERN BLOTTING NORTHERN BLOTTING BLOTTING delle proteine: MICROARRAYS MACROARRAYS
Analisi Molecolare di sequenze di acidi nucleici
 Analisi Molecolare di sequenze di acidi nucleici 1. L Analisi di restrizione di frammenti o RFLP (Restriction Fragment Lenght Polymorphism) di DNA comporta lo studio delle dimensioni dei frammenti di DNA
Analisi Molecolare di sequenze di acidi nucleici 1. L Analisi di restrizione di frammenti o RFLP (Restriction Fragment Lenght Polymorphism) di DNA comporta lo studio delle dimensioni dei frammenti di DNA
Identificazione dei microrganismi mediante tecniche di biologia molecolare Esercitazione n 3. Criteri di identificazione
 Identificazione dei microrganismi mediante tecniche di biologia molecolare Esercitazione n 3 Criteri di identificazione Tradizionale (fenotipo) Tecniche di biologia molecolare Il livello di risoluzione
Identificazione dei microrganismi mediante tecniche di biologia molecolare Esercitazione n 3 Criteri di identificazione Tradizionale (fenotipo) Tecniche di biologia molecolare Il livello di risoluzione
Il primer utilizzato può essere specifico per il gene che si intende amplificare oppure aspecifico (oligo (dt) oppure random esameri).
 Retrotrascrizione l mrna viene convertito in cdna per mezzo dell enzima trascrittasi inversa (DNA polimerasi RNAdipendenti ricavate dai virus della mieloblastosi aviaria AMV o della leucemia murina di
Retrotrascrizione l mrna viene convertito in cdna per mezzo dell enzima trascrittasi inversa (DNA polimerasi RNAdipendenti ricavate dai virus della mieloblastosi aviaria AMV o della leucemia murina di
METODI DI MARCATURA DEGLI ACIDI NUCLEICI
 METODI DI MARCATURA DEGLI ACIDI NUCLEICI Marcatura di acidi nucleici Una sonda per ibridazione è una molecola di DNA marcata, con una sequenza complementare al DNA bersaglio da individuare. Poiché la sonda
METODI DI MARCATURA DEGLI ACIDI NUCLEICI Marcatura di acidi nucleici Una sonda per ibridazione è una molecola di DNA marcata, con una sequenza complementare al DNA bersaglio da individuare. Poiché la sonda
Metodiche Molecolari
 Metodiche Molecolari La rivelazione degli acidi nucleici virali è un altro saggio che può essere utilizzato sia per verificare la presenza di un virus in un determinato campione biologico, sia per studiare
Metodiche Molecolari La rivelazione degli acidi nucleici virali è un altro saggio che può essere utilizzato sia per verificare la presenza di un virus in un determinato campione biologico, sia per studiare
di Milazzo Gabriele Mangiagli Graziella Paternò Valentina Lomagno Valeria Mangione Enza Prof. C. Di Pietro
 di Milazzo Gabriele Mangiagli Graziella Paternò Valentina Lomagno Valeria Mangione Enza Prof. C. Di Pietro Polymerase Chain Reaction Inventata a metà degli anni 80 da Kary Mullis, è a tutt oggi uno strumento
di Milazzo Gabriele Mangiagli Graziella Paternò Valentina Lomagno Valeria Mangione Enza Prof. C. Di Pietro Polymerase Chain Reaction Inventata a metà degli anni 80 da Kary Mullis, è a tutt oggi uno strumento
Metodiche di analisi del DNA (cenni) (Ingegneria genetica)
 DNA Metodiche di analisi del DNA (cenni) (Ingegneria genetica) Principali tecniche di base Enzimi di restrizione (Endonucleasi) Gel elettroforesi Ibridizzazione PCR (Polymerase Chain Reaction) Sequenziamento
DNA Metodiche di analisi del DNA (cenni) (Ingegneria genetica) Principali tecniche di base Enzimi di restrizione (Endonucleasi) Gel elettroforesi Ibridizzazione PCR (Polymerase Chain Reaction) Sequenziamento
PCR. PCR o reazione di polimerizzazione a catena. Amplificazione esponenziale di DNA. Puo amplificare un tratto di DNA per piu di 1 milione di volte
 PCR Prof.ssa Flavia Frabetti PCR o reazione di polimerizzazione a catena Fine anni 80 Amplificazione esponenziale di DNA. Puo amplificare un tratto di DNA per piu di 1 milione di volte Permette di estrarre
PCR Prof.ssa Flavia Frabetti PCR o reazione di polimerizzazione a catena Fine anni 80 Amplificazione esponenziale di DNA. Puo amplificare un tratto di DNA per piu di 1 milione di volte Permette di estrarre
SELEZIONE ASSISTITA PER LA RESISTENZA patogeni in orzo
 C.R.A. Consiglio per la Ricerca in Agricoltura Centro di ricerca per la genomica Fiorenzuola d Arda (Piacenza) SELEZIONE ASSISTITA PER LA RESISTENZA patogeni in orzo Tutor: Dott. Gianni TACCONI Studente:
C.R.A. Consiglio per la Ricerca in Agricoltura Centro di ricerca per la genomica Fiorenzuola d Arda (Piacenza) SELEZIONE ASSISTITA PER LA RESISTENZA patogeni in orzo Tutor: Dott. Gianni TACCONI Studente:
Analisi qualitativa con Agilent BioAnalyzer. cdna, RNA Totale e Messaggero e small RNA
 Il Servizio di Biologia Molecolare si è di recente dotato di uno strumento per l analisi qualitativa e quantitativa degli acidi nucleici Agilent Bioanalyzer 2100 e ha implementato tale tecnologia nell
Il Servizio di Biologia Molecolare si è di recente dotato di uno strumento per l analisi qualitativa e quantitativa degli acidi nucleici Agilent Bioanalyzer 2100 e ha implementato tale tecnologia nell
PRINCIPALI TIPI DI PCR a) PRINCIPALI TIPI DI PCR b)
 PRINCIPALI TIPI DI PCR a) RT-PCR: serve a valutare l espressione di un gene tramite l amplificazione dell mrna da esso trascritto PCR COMPETITIVA: serve a valutare la concentrazione iniziale di DNA o RNA
PRINCIPALI TIPI DI PCR a) RT-PCR: serve a valutare l espressione di un gene tramite l amplificazione dell mrna da esso trascritto PCR COMPETITIVA: serve a valutare la concentrazione iniziale di DNA o RNA
Come si traccia un alimento di origine animale? Dalle lasagne con carne di cavallo. alla realtà di ogni giorno
 Editoriale n.10 Newsletter aprile 2013 Come si traccia un alimento di origine animale? Dalle lasagne con carne di cavallo alla realtà di ogni giorno Identificare la specie, un obiettivo fondamentale quando
Editoriale n.10 Newsletter aprile 2013 Come si traccia un alimento di origine animale? Dalle lasagne con carne di cavallo alla realtà di ogni giorno Identificare la specie, un obiettivo fondamentale quando
Lezione XLI-XLII martedì 17-1-2012
 Lezione XLI-XLII martedì 17-1-2012 corso di genomica aula 8 orario : Martedì ore 14.00-16.00 Giovedì ore 13.00-15.00 Esami 31- gennaio 2012 7- febbraio 2012 28 - febbraio 2012 D. Frezza Esercitazione II
Lezione XLI-XLII martedì 17-1-2012 corso di genomica aula 8 orario : Martedì ore 14.00-16.00 Giovedì ore 13.00-15.00 Esami 31- gennaio 2012 7- febbraio 2012 28 - febbraio 2012 D. Frezza Esercitazione II
Biotecnologie applicate all ispezione degli alimenti di origine animale
 Prof.ssa Tiziana Pepe Tecniche molecolari Biotecnologie applicate all ispezione degli alimenti di origine animale Dip. di Medicina Veterinaria e Produzioni animali tiziana.pepe@unina.it Tecniche molecolari
Prof.ssa Tiziana Pepe Tecniche molecolari Biotecnologie applicate all ispezione degli alimenti di origine animale Dip. di Medicina Veterinaria e Produzioni animali tiziana.pepe@unina.it Tecniche molecolari
Si può ottenere un a grande quantità di copie di DNA a partire da una singola molecola di DNA stampo La reazione è semplice ed automatizzabile E
 Si può ottenere un a grande quantità di copie di DNA a partire da una singola molecola di DNA stampo La reazione è semplice ed automatizzabile E possibile scegliere selettivamente cosa amplificare (specificità)
Si può ottenere un a grande quantità di copie di DNA a partire da una singola molecola di DNA stampo La reazione è semplice ed automatizzabile E possibile scegliere selettivamente cosa amplificare (specificità)
GENOMICA STRUTTURALE: GENOMICA FUNZIONALE: 1. Anatomia dei genomi. 8. Funzionamento dei genomi Il genoma dei procarioti
 GENOMICA STRUTTURALE: GENOMICA FUNZIONALE: 1. Anatomia dei genomi 8. Funzionamento dei genomi Il genoma dei procarioti Modificazioni della cromatina e l espressione del genoma Il genoma degli eucarioti
GENOMICA STRUTTURALE: GENOMICA FUNZIONALE: 1. Anatomia dei genomi 8. Funzionamento dei genomi Il genoma dei procarioti Modificazioni della cromatina e l espressione del genoma Il genoma degli eucarioti
Istituto d Istruzione Superiore Sandro Pertini Campobasso
 Istituto d Istruzione Superiore Sandro Pertini Campobasso Progetto ARACNE La medicina forense Lavoro eseguito da: Di Bartolomeo Alessia Genovese Francesca Mastropaolo Giulia Venturini Giusy Classe IV Sez.
Istituto d Istruzione Superiore Sandro Pertini Campobasso Progetto ARACNE La medicina forense Lavoro eseguito da: Di Bartolomeo Alessia Genovese Francesca Mastropaolo Giulia Venturini Giusy Classe IV Sez.
Real Time PCR. La PCR Real Time è in grado di misurare in tempo reale la concentrazione iniziale di una sequenza target in un campione biologico.
 eal Time PC La PC eal Time è in grado di misurare in tempo reale la concentrazione iniziale di una sequenza target in un campione biologico. Gli strumenti per PC eal Time, oltre a fungere da termociclatori,
eal Time PC La PC eal Time è in grado di misurare in tempo reale la concentrazione iniziale di una sequenza target in un campione biologico. Gli strumenti per PC eal Time, oltre a fungere da termociclatori,
PCR - Polymerase Chain Reaction. ideata nel 1983 da Kary B. Mullis il quale ottenne, per questo, il premio Nobel per la chimica (1993).
 End point PCR vs quantitative Real-Time PCR PCR - Polymerase Chain Reaction ideata nel 1983 da Kary B. Mullis il quale ottenne, per questo, il premio Nobel per la chimica (1993). Questa tecnica, utilizzando
End point PCR vs quantitative Real-Time PCR PCR - Polymerase Chain Reaction ideata nel 1983 da Kary B. Mullis il quale ottenne, per questo, il premio Nobel per la chimica (1993). Questa tecnica, utilizzando
Analisi molecolare dei geni
 Analisi molecolare dei geni Denaturazione e rinaturazione di una molecola di DNA Si rompono i legami idrogeno 100 C Denaturazione del DNA Rinaturazione per riassociazione delle sequenze complementari Ogni
Analisi molecolare dei geni Denaturazione e rinaturazione di una molecola di DNA Si rompono i legami idrogeno 100 C Denaturazione del DNA Rinaturazione per riassociazione delle sequenze complementari Ogni
Applicazioni biotecnologiche in systems biology
 Applicazioni biotecnologiche in systems biology Lezione #2 Dr. Marco Galardini AA 2012/2013 Contatti Dr. Marco Galardini Dip. Di Biologia Via Madonna del Piano 6, Polo Scientifico S. Fiorentino (c/o Incubatore
Applicazioni biotecnologiche in systems biology Lezione #2 Dr. Marco Galardini AA 2012/2013 Contatti Dr. Marco Galardini Dip. Di Biologia Via Madonna del Piano 6, Polo Scientifico S. Fiorentino (c/o Incubatore
SERVIZIO DI SEQUENZIAMENTO AUTOMATICO
 REPARTO GENOMICA LABORATORIO ANALISI GENOMICHE SERVIZIO DI SEQUENZIAMENTO AUTOMATICO DOCUMENTO ILLUSTRATIVO DEL SERVIZIO DI SEQUENZIAMENTO ACIDI NUCLEICI ISTITUTO ZOOPROFILATTICO SPERIMENTALE DELLA LOMBARDIA
REPARTO GENOMICA LABORATORIO ANALISI GENOMICHE SERVIZIO DI SEQUENZIAMENTO AUTOMATICO DOCUMENTO ILLUSTRATIVO DEL SERVIZIO DI SEQUENZIAMENTO ACIDI NUCLEICI ISTITUTO ZOOPROFILATTICO SPERIMENTALE DELLA LOMBARDIA
ELETTROFORESI SU GEL
 ELETTROFORESI SU GEL Permette la separazione di frammenti di DNA/RNA da una miscela complessa E una tecnica fondamentale per: l analisi (elettroforesi analitica) la purificazione degli acidi nucleici (elettroforesi
ELETTROFORESI SU GEL Permette la separazione di frammenti di DNA/RNA da una miscela complessa E una tecnica fondamentale per: l analisi (elettroforesi analitica) la purificazione degli acidi nucleici (elettroforesi
immagine Biologia applicata alla ricerca bio-medica Materiale Didattico Docente: Di Bernardo
 Esperto in processi innovativi di sintesi biomolecolare applicata a tecniche di epigenetica Materiale Didattico Biologia applicata alla ricerca bio-medica immagine Docente: Di Bernardo Per animali transgenici
Esperto in processi innovativi di sintesi biomolecolare applicata a tecniche di epigenetica Materiale Didattico Biologia applicata alla ricerca bio-medica immagine Docente: Di Bernardo Per animali transgenici
Carpire il segreto della vita con l informatica Giosuè Lo Bosco Dipartimento di Matematica e Informatica, Università di Palermo, ITALY.
 Carpire il segreto della vita con l informatica Giosuè Lo Bosco Dipartimento di Matematica e Informatica, Università di Palermo, ITALY. Lezioni Lincee Palermo, 26 Febbraio 2015 Alla base della vita degli
Carpire il segreto della vita con l informatica Giosuè Lo Bosco Dipartimento di Matematica e Informatica, Università di Palermo, ITALY. Lezioni Lincee Palermo, 26 Febbraio 2015 Alla base della vita degli
Diagnostica Biomolecolare: Tecnologie e Applicazioni
 Diagnostica Biomolecolare: Tecnologie e Applicazioni Preparazione dei campioni: (Estrazione del DNA o dell RNA dal tessuto di interesse) Analisi delle mutazioni: SSCP DHPLC Dot blot - Southern - PCR (ARMS
Diagnostica Biomolecolare: Tecnologie e Applicazioni Preparazione dei campioni: (Estrazione del DNA o dell RNA dal tessuto di interesse) Analisi delle mutazioni: SSCP DHPLC Dot blot - Southern - PCR (ARMS
MARCATURA DEGLI ACIDI NUCLEICI
 MARCATURA DEGLI ACIDI NUCLEICI MARCATURA DEGLI ACIDI NUCLEICI La marcatura degli acidi nucleici è una delle tecniche di base nello studio della Biologia Molecolare, rappresenta infatti una tappa preliminare
MARCATURA DEGLI ACIDI NUCLEICI MARCATURA DEGLI ACIDI NUCLEICI La marcatura degli acidi nucleici è una delle tecniche di base nello studio della Biologia Molecolare, rappresenta infatti una tappa preliminare
ALGORITMI PER L'ANALISI ED IL TROUBLESHOOTING DI SEGNALI DI SEQUENZIAMENTO SANGER DEL DNA
 UNIVERSITA DEGLI STUDI DI PADOVA FACOLTA DI INGEGNERIA CORSO DI LAUREA SPECIALISTICA IN BIOINGEGNERIA ALGORITMI PER L'ANALISI ED IL TROUBLESHOOTING DI SEGNALI DI SEQUENZIAMENTO SANGER DEL DNA ALGORITHMS
UNIVERSITA DEGLI STUDI DI PADOVA FACOLTA DI INGEGNERIA CORSO DI LAUREA SPECIALISTICA IN BIOINGEGNERIA ALGORITMI PER L'ANALISI ED IL TROUBLESHOOTING DI SEGNALI DI SEQUENZIAMENTO SANGER DEL DNA ALGORITHMS
PROGETTO DNA CHIAVI IN MANO
 PROGETTO DNA CHIAVI IN MANO La collaborazione con il Virgilio e il progetto dell IFOM Il progetto DNA chiavi in mano è un percorso pensato dal Centro di Ricerca internazionale IFOM per avvicinare i ragazzi
PROGETTO DNA CHIAVI IN MANO La collaborazione con il Virgilio e il progetto dell IFOM Il progetto DNA chiavi in mano è un percorso pensato dal Centro di Ricerca internazionale IFOM per avvicinare i ragazzi
Metodi di analisi mutazionale
 Metodi di analisi mutazionale I metodi impiegati per l analisi di mutazioni o polimorfismi nel DNA genomico possono essere suddivise in due principali categorie: (1) metodi per individuare mutazioni note,
Metodi di analisi mutazionale I metodi impiegati per l analisi di mutazioni o polimorfismi nel DNA genomico possono essere suddivise in due principali categorie: (1) metodi per individuare mutazioni note,
CAPITOLATO TECNICO PER DIAGNOSTICI PER TIPIZZAZIONE MOLECOLARE DA DESTINARSI AL LABORATORIO DI GENETICA MOLECOLARE-MEDICINA LEGALE P.O.
 ALLEGATO A CAPITOLATO TECNICO PER DIAGNOSTICI PER TIPIZZAZIONE MOLECOLARE DA DESTINARSI AL LABORATORIO DI GENETICA MOLECOLARE-MEDICINA LEGALE P.O. MONSERRATO Durata della fornitura: 1 anno + 1 rinnovabile
ALLEGATO A CAPITOLATO TECNICO PER DIAGNOSTICI PER TIPIZZAZIONE MOLECOLARE DA DESTINARSI AL LABORATORIO DI GENETICA MOLECOLARE-MEDICINA LEGALE P.O. MONSERRATO Durata della fornitura: 1 anno + 1 rinnovabile
LEZIONE X FUNZIONAMENTO E APPLICAZIONI DELLA PCR. Dott. Paolo Cascio
 LEZIONE X FUNZIONAMENTO E APPLICAZIONI DELLA PCR Dott. Paolo Cascio Tecnica della reazione a catena della DNA polimerasi o PCR (Polymerase Chain Reaction) 1) Introdotta da Kary Mullis alla metà degli anni
LEZIONE X FUNZIONAMENTO E APPLICAZIONI DELLA PCR Dott. Paolo Cascio Tecnica della reazione a catena della DNA polimerasi o PCR (Polymerase Chain Reaction) 1) Introdotta da Kary Mullis alla metà degli anni
Prof.ssa Gamba Sabrina. Lezione 7: IL DNA. Duplicazione e sintesi delle proteine
 Prof.ssa Gamba Sabrina Lezione 7: IL DNA Duplicazione e sintesi delle proteine concetti chiave della lezione Costituzione fisico-chimica del DNA Basi azotate Duplicazione Concetto di geni Rna Trascrizione
Prof.ssa Gamba Sabrina Lezione 7: IL DNA Duplicazione e sintesi delle proteine concetti chiave della lezione Costituzione fisico-chimica del DNA Basi azotate Duplicazione Concetto di geni Rna Trascrizione
Francesca Ceroni. Biotecnologie tradizionali. Biologia Sintetica. F. Ceroni 16/09/2010. Bressanone GNB 2010 1. 1) DNA ricombinante 2) PCR
 XXIX Scuola Annuale di Bioingegneria. Bressanone, 13-17 settembre 2010 Francesca Ceroni Biotecnologie tradizionali 1) DNA ricombinante 2) PCR 3) Sequenziamento automatizzato Biologia Sintetica 4) Approccio
XXIX Scuola Annuale di Bioingegneria. Bressanone, 13-17 settembre 2010 Francesca Ceroni Biotecnologie tradizionali 1) DNA ricombinante 2) PCR 3) Sequenziamento automatizzato Biologia Sintetica 4) Approccio
Preparazione dei campioni da inviare per il sequenziamento
 Preparazione dei campioni da inviare per il sequenziamento PCR preparativa Buffer 10x dntp 2mM Taq polimerasi Oligonucleotidi up e down 100 ng/ul Volume finale 2 ul/campione 2 ul/campione 0,5 U/campione
Preparazione dei campioni da inviare per il sequenziamento PCR preparativa Buffer 10x dntp 2mM Taq polimerasi Oligonucleotidi up e down 100 ng/ul Volume finale 2 ul/campione 2 ul/campione 0,5 U/campione
DNA - DENATURAZIONE E RIASSOCIAZIONE
 DNA - DENATURAZIONE E RIASSOCIAZIONE Il doppio strand della molecola di DNA può denaturarsi dando due singoli strand ad alte temperature (>90 C). Due strand di DNA complementari possono accoppiarsi dando
DNA - DENATURAZIONE E RIASSOCIAZIONE Il doppio strand della molecola di DNA può denaturarsi dando due singoli strand ad alte temperature (>90 C). Due strand di DNA complementari possono accoppiarsi dando
Immagine di una sequenza ben riuscita. Sequences troubleshooting
 Immagine di una sequenza ben riuscita. Sequences troubleshooting Sequenza fallita Reazione fallita: non presenta picchi definiti e ha un alto rumore di fondo. il primer non trova sito di annealing il DNA
Immagine di una sequenza ben riuscita. Sequences troubleshooting Sequenza fallita Reazione fallita: non presenta picchi definiti e ha un alto rumore di fondo. il primer non trova sito di annealing il DNA
Amplificazione del DNA tramite reazione a catena della polimerasi (POLYMERASE CHAIN REACTION; PCR) e sue applicazioni in ambito biomedico
 Amplificazione del DNA tramite reazione a catena della polimerasi (POLYMERASE CHAIN REACTION; PCR) e sue applicazioni in ambito biomedico Dottoressa Camerin Consuelo Laboratorio Oncoematologia Pediatrica
Amplificazione del DNA tramite reazione a catena della polimerasi (POLYMERASE CHAIN REACTION; PCR) e sue applicazioni in ambito biomedico Dottoressa Camerin Consuelo Laboratorio Oncoematologia Pediatrica
Replicazione del DNA
 Replicazione del DNA la replicazione del DNA viene effettuata da ENZIMI: DNA-polimerasi (catalizza la formazione del legame fosfodiestere) ogni filamento fa da stampo (enzima diretto dallo stampo) le DNA-polimerasi
Replicazione del DNA la replicazione del DNA viene effettuata da ENZIMI: DNA-polimerasi (catalizza la formazione del legame fosfodiestere) ogni filamento fa da stampo (enzima diretto dallo stampo) le DNA-polimerasi
AMPLIFICAZIONE IN VITRO DEL DNA REAZIONE A CATENA DELLA POLIMERASI (PCR)
 AMPLIFICAZIONE IN VITRO DEL DNA REAZIONE A CATENA DELLA POLIMERASI (PCR) PCR: reazione polimerasica a catena Inventata da Kary Mullis negli anni 80 (premio Nobel 1993) Serve per ottenere una grande quantita
AMPLIFICAZIONE IN VITRO DEL DNA REAZIONE A CATENA DELLA POLIMERASI (PCR) PCR: reazione polimerasica a catena Inventata da Kary Mullis negli anni 80 (premio Nobel 1993) Serve per ottenere una grande quantita
Protocollo Crime Scene Investigation
 Protocollo Crime Scene Investigation Precauzioni da adottare in laboratorio: - non mangiare o bere - indossare sempre i guanti quando si maneggiano i tubini, i gel, le micropipette - nel dubbio, chiedere!
Protocollo Crime Scene Investigation Precauzioni da adottare in laboratorio: - non mangiare o bere - indossare sempre i guanti quando si maneggiano i tubini, i gel, le micropipette - nel dubbio, chiedere!
METODI ALTERNATIVI. PCR digitale per la rilevazione e quantificazione. assoluta del DNA
 METODI ALTERNATIVI PCR digitale per la rilevazione e quantificazione assoluta del DNA Roma, 25 settembre 2013 Giuseppina Buonincontro IZS PLV- S.S. Controllo Alimenti La prima generazione di PCR consente
METODI ALTERNATIVI PCR digitale per la rilevazione e quantificazione assoluta del DNA Roma, 25 settembre 2013 Giuseppina Buonincontro IZS PLV- S.S. Controllo Alimenti La prima generazione di PCR consente
PROGETTO DNA chiavi in mano. Le Biotecnologie in classe e in laboratorio 11/03/2015 Prof.ssa Paola Cazzani I.T.E. A. Bassi - Lodi
 PROGETTO DNA chiavi in mano Le Biotecnologie in classe e in laboratorio 11/03/2015 Prof.ssa Paola Cazzani I.T.E. A. Bassi - Lodi PROGETTO DNA chiavi in mano PROGETTO DNA chiavi in mano IFOM PROGETTO DNA
PROGETTO DNA chiavi in mano Le Biotecnologie in classe e in laboratorio 11/03/2015 Prof.ssa Paola Cazzani I.T.E. A. Bassi - Lodi PROGETTO DNA chiavi in mano PROGETTO DNA chiavi in mano IFOM PROGETTO DNA
Analisi e catalogazione automatica dei Curriculum Vitae
 Analisi e catalogazione automatica dei Curriculum Vitae CV Manager è lo strumento di Text Mining che automatizza l analisi, la catalogazione e la ricerca dei Curriculum Vitae L esigenza Quanto tempo viene
Analisi e catalogazione automatica dei Curriculum Vitae CV Manager è lo strumento di Text Mining che automatizza l analisi, la catalogazione e la ricerca dei Curriculum Vitae L esigenza Quanto tempo viene
Il sequenziamento del DNA
 Il sequenziamento del DNA Si può ottenere la massima informazione sulla struttura di una molecola di DNA determinandone la sequenza nucleotidica completa Il sequenziamento del DNA è una componente irrinunciabile
Il sequenziamento del DNA Si può ottenere la massima informazione sulla struttura di una molecola di DNA determinandone la sequenza nucleotidica completa Il sequenziamento del DNA è una componente irrinunciabile
Controllo ufficiale degli OGM nel settore agroalimentare
 Controllo ufficiale degli OGM nel settore agroalimentare Ugo Marchesi Istituto Zooprofilattico Sperimentale Lazio e Toscana Centro di Referenza Nazionale per la ricerca di OGM ugo.marchesi@izslt.it ORGANISMI
Controllo ufficiale degli OGM nel settore agroalimentare Ugo Marchesi Istituto Zooprofilattico Sperimentale Lazio e Toscana Centro di Referenza Nazionale per la ricerca di OGM ugo.marchesi@izslt.it ORGANISMI
Abbreviazioni Denominazione Presidi: Ospedale SS. Trinità Ospedale Businco Ospedale Binaghi Ospedale Microcitemico
 ALLEGATO 1 DESCRIZIONE DELLA FORNITURA PROCEDURA APERTA PER LA FORNITURA IN PIU LOTTI, IN MODALITA SERVICE, DI SISTEMI ANALITICI DI BIOLOGIA MOLECOLARE PER I LABORATORI ANALISI DELL AZIENDA ASL N. 8 DI
ALLEGATO 1 DESCRIZIONE DELLA FORNITURA PROCEDURA APERTA PER LA FORNITURA IN PIU LOTTI, IN MODALITA SERVICE, DI SISTEMI ANALITICI DI BIOLOGIA MOLECOLARE PER I LABORATORI ANALISI DELL AZIENDA ASL N. 8 DI
Biosensori 3: Biosensori a DNA e Bio- Gene Chip
 Biosensori 3: Biosensori a DNA e Bio- Gene Chip mazzei@di.unipi.it (materiale parzialmente tratto da: http://nestor.med.unibo.it/shared_files/seminari/sartini_21-10-2004.ppt) Biosensori ad affinità basati
Biosensori 3: Biosensori a DNA e Bio- Gene Chip mazzei@di.unipi.it (materiale parzialmente tratto da: http://nestor.med.unibo.it/shared_files/seminari/sartini_21-10-2004.ppt) Biosensori ad affinità basati
Il sequenziamento genico e le sue applicazioni nella diagnostica molecolare del laboratorio di microbiologia e virologia medica
 Il laboratorio di Biologia Molecolare: introduzione alle tecniche e alla loro applicazione Il sequenziamento genico e le sue applicazioni nella diagnostica molecolare del laboratorio di microbiologia e
Il laboratorio di Biologia Molecolare: introduzione alle tecniche e alla loro applicazione Il sequenziamento genico e le sue applicazioni nella diagnostica molecolare del laboratorio di microbiologia e
Orga Bio Human S.r.l. DIREZIONE E UFFICI: Via Amsterdam 75, 00144 Roma Tel/fax: 06 99701675
 Orga Bio Human S.r.l. DIREZIONE E UFFICI: Via Amsterdam 75, 00144 Roma Tel/fax: 06 99701675 SEDE LEGALE: Via Helsinki 21, 00144 Roma Tel. 06 97998273; Fax 06 52246148 e-mail: orgabiohuman@fastwebnet.it
Orga Bio Human S.r.l. DIREZIONE E UFFICI: Via Amsterdam 75, 00144 Roma Tel/fax: 06 99701675 SEDE LEGALE: Via Helsinki 21, 00144 Roma Tel. 06 97998273; Fax 06 52246148 e-mail: orgabiohuman@fastwebnet.it
Prof. Maria Nicola GADALETA
 Prof. Maria Nicola GADALETA E-mail: m.n.gadaleta@biologia.uniba.it Facoltà di Scienze Biotecnologiche Corso di Laurea in Biotecnologie Sanitarie e Farmaceutiche Biochimica e Biotecnologie Biochimiche DISPENSA
Prof. Maria Nicola GADALETA E-mail: m.n.gadaleta@biologia.uniba.it Facoltà di Scienze Biotecnologiche Corso di Laurea in Biotecnologie Sanitarie e Farmaceutiche Biochimica e Biotecnologie Biochimiche DISPENSA
Cromatografia Dal greco chroma : colore, graphein : scrivere 1903 Mikhail Twsett (pigmenti vegetali su carta)
 Cromatografia Dal greco chroma : colore, graphein : scrivere 1903 Mikhail Twsett (pigmenti vegetali su carta) E il termine generico che indica una serie di tecniche di separazione di molecole simili in
Cromatografia Dal greco chroma : colore, graphein : scrivere 1903 Mikhail Twsett (pigmenti vegetali su carta) E il termine generico che indica una serie di tecniche di separazione di molecole simili in
U.O.C. di Epatologia Clinica e Biomolecolare. Unità di misura. Repertorio. 200 ml 10.000 U. 500 test
 U.O.C. di Epatologia Clinica e Biomolecolare Lotto N. DESCRIZIONE PRODOTTO Quantità annua richiesta Unità di misura Repertorio CND Codice Prodotto, Confezione Offerta e nome commerciale Prezzo unitario
U.O.C. di Epatologia Clinica e Biomolecolare Lotto N. DESCRIZIONE PRODOTTO Quantità annua richiesta Unità di misura Repertorio CND Codice Prodotto, Confezione Offerta e nome commerciale Prezzo unitario
Capitolo 1 Introduzione alla PCR
 Capitolo 1 Introduzione alla PCR La tecnologia della PCR ha rivoluzionato l attività dei laboratori di ricerca e di diagnostica trovando applicazioni ed impieghi in svariati campi della medicina e della
Capitolo 1 Introduzione alla PCR La tecnologia della PCR ha rivoluzionato l attività dei laboratori di ricerca e di diagnostica trovando applicazioni ed impieghi in svariati campi della medicina e della
Analisi. Analisi Esame organolettico, Analisi chimica, Analisi microbiologica
 Analisi Esame organolettico, Analisi chimica, Analisi microbiologica Tecniche analitiche: alcune vedute L ocratossina nel vino: si tratta di una sostanza tossica prodotta da particolari muffe (micotossina).
Analisi Esame organolettico, Analisi chimica, Analisi microbiologica Tecniche analitiche: alcune vedute L ocratossina nel vino: si tratta di una sostanza tossica prodotta da particolari muffe (micotossina).
v = velocità di migrazione della proteina in un campo elettrico E = forza del campo elettrico z = carica netta della proteina 3500 V catod o
 La prima e : Isoelectric focusing (IEF) v=e z f 1 step1 v = velocità di migrazione della proteina in un campo elettrico E = forza del campo elettrico z = carica netta della proteina Tot 76 kvh f = coefficiente
La prima e : Isoelectric focusing (IEF) v=e z f 1 step1 v = velocità di migrazione della proteina in un campo elettrico E = forza del campo elettrico z = carica netta della proteina Tot 76 kvh f = coefficiente
LA GENETICA: DNA e RNA LA GENETICA. DNA e RNA. Prof. Daniele Verri
 LA GENETICA DNA e RNA Prof. Daniele Verri L'acido desossiribonucleico o deossiribonucleico (DNA) è un acido nucleico che contiene le informazioni necessarie per la formazione di RNA e proteine. LA GENETICA:
LA GENETICA DNA e RNA Prof. Daniele Verri L'acido desossiribonucleico o deossiribonucleico (DNA) è un acido nucleico che contiene le informazioni necessarie per la formazione di RNA e proteine. LA GENETICA:
NUCLEOTIDI e ACIDI NUCLEICI
 NUCLEOTIDI e ACIDI NUCLEICI Struttura dei nucleotidi Il gruppo fosfato conferisce carica negativa e proprietà acide FUNZIONI DEI NUCLEOTIDI MOLECOLE DI RISERVA DI ENERGIA L idrolisi dei nucleosidi trifosfato
NUCLEOTIDI e ACIDI NUCLEICI Struttura dei nucleotidi Il gruppo fosfato conferisce carica negativa e proprietà acide FUNZIONI DEI NUCLEOTIDI MOLECOLE DI RISERVA DI ENERGIA L idrolisi dei nucleosidi trifosfato
REPLICAZIONE DEL DNA
 REPLICAZIONE DEL DNA La replicazione (o anche duplicazione) è il meccanismo molecolare attraverso cui il DNA produce una copia di sé stesso. Ogni volta che una cellula si divide, infatti, l'intero genoma
REPLICAZIONE DEL DNA La replicazione (o anche duplicazione) è il meccanismo molecolare attraverso cui il DNA produce una copia di sé stesso. Ogni volta che una cellula si divide, infatti, l'intero genoma
PCR. (Reazione a Catena della Polimerasi) Kary Mullis
 POLYMERASE CHAIN REACTION - PCR PCR Polymerase Chain Reaction (Reazione a Catena della Polimerasi) Kary Mullis Premio Nobel per la Chimica nel 1993, Kary Mullis è divenuto una leggenda per la scoperta
POLYMERASE CHAIN REACTION - PCR PCR Polymerase Chain Reaction (Reazione a Catena della Polimerasi) Kary Mullis Premio Nobel per la Chimica nel 1993, Kary Mullis è divenuto una leggenda per la scoperta
La possibilita di conoscere i geni deriva dalla capacita di manipolarli:
 La possibilita di conoscere i geni deriva dalla capacita di manipolarli: -isolare un gene (enzimi di restrizione) -clonaggio (amplificazione) vettori -sequenziamento -funzione Il gene o la sequenza
La possibilita di conoscere i geni deriva dalla capacita di manipolarli: -isolare un gene (enzimi di restrizione) -clonaggio (amplificazione) vettori -sequenziamento -funzione Il gene o la sequenza
DNA sequencing. Reading Genomes. Giovanni Bacci
 Reading Genomes Giovanni Bacci Evoluzione del sequenziamento 1977 Frederick Sanger Prima tecnica di sequenziamento 1987 Applyed Biosystems Prima macchina automatica per il sequenziamento del DNA 1998 Phil
Reading Genomes Giovanni Bacci Evoluzione del sequenziamento 1977 Frederick Sanger Prima tecnica di sequenziamento 1987 Applyed Biosystems Prima macchina automatica per il sequenziamento del DNA 1998 Phil
determinazione della quantità determinazione della struttura primaria (sequenza a.a.) determinazione della struttura 3D
 Metodi di studio delle proteine : determinazione della quantità determinazione della struttura primaria (sequenza a.a.) determinazione della struttura 3D Spettrofotometro cuvetta monocromatore rivelatore
Metodi di studio delle proteine : determinazione della quantità determinazione della struttura primaria (sequenza a.a.) determinazione della struttura 3D Spettrofotometro cuvetta monocromatore rivelatore
COME VIENE REALIZZATA UNA RICERCA SPERIMENTALE IN BIOLOGIA MOLECOLARE?
 COME VIENE REALIZZATA UNA RICERCA SPERIMENTALE IN BIOLOGIA MOLECOLARE? A Flusso di attività B - INPUT C Descrizione dell attività D RISULTATO E - SISTEMA PROFESSIONALE 0. RICHIESTA DI STUDIARE E/O INDIVIDUARE
COME VIENE REALIZZATA UNA RICERCA SPERIMENTALE IN BIOLOGIA MOLECOLARE? A Flusso di attività B - INPUT C Descrizione dell attività D RISULTATO E - SISTEMA PROFESSIONALE 0. RICHIESTA DI STUDIARE E/O INDIVIDUARE
DNA - RNA. Nucleotide = Gruppo Fosforico + Zucchero Pentoso + Base Azotata. Le unità fondamentali costituenti il DNA e l RNA sono i Nucleotidi.
 DNA - RNA Le unità fondamentali costituenti il DNA e l RNA sono i Nucleotidi. Nucleotide = Gruppo Fosforico + Zucchero Pentoso + Base Azotata. Esistono 4 basi azotate per il DNA e 4 per RNA Differenze
DNA - RNA Le unità fondamentali costituenti il DNA e l RNA sono i Nucleotidi. Nucleotide = Gruppo Fosforico + Zucchero Pentoso + Base Azotata. Esistono 4 basi azotate per il DNA e 4 per RNA Differenze
III giorno: Da questo punto in poi, per entrambe le tipologie di campioni, si segue un protocollo comune:
 III giorno: 1) Estrazione del DNA genomico da campioni SECCHI e da coltura liquida 2) Preparazione del gel di agarosio 3) Corsa del DNA genomico in gel di agarosio e sua visualizzazione 4) PCR del DNA
III giorno: 1) Estrazione del DNA genomico da campioni SECCHI e da coltura liquida 2) Preparazione del gel di agarosio 3) Corsa del DNA genomico in gel di agarosio e sua visualizzazione 4) PCR del DNA
La trascrizione nei procarioti. Prof. Savino; dispense di Biologia Molecolare, Corso di Laurea in Biotecnologie
 La trascrizione nei procarioti Concetti base Nucleoside base purinica o pirimidinica legata alla posizione 1 dell anello pentoso Nucleotide base azotata-pentoso-fosfato Concetti base La trascrizione comporta
La trascrizione nei procarioti Concetti base Nucleoside base purinica o pirimidinica legata alla posizione 1 dell anello pentoso Nucleotide base azotata-pentoso-fosfato Concetti base La trascrizione comporta
TECNICHE DI BIOLOGIA MOLECOLARE. LA REAZIONE POLIMERASICA A CATENA Principi teorici e aspetti pratici
 TECNICHE DI BIOLOGIA MOLECOLARE LA REAZIONE POLIMERASICA A CATENA Principi teorici e aspetti pratici POLYMERASE CHAIN REACTION (PCR) 1955 A. Kronembreg e coll. (Stanford University) scoprono la DNA-polimerasi
TECNICHE DI BIOLOGIA MOLECOLARE LA REAZIONE POLIMERASICA A CATENA Principi teorici e aspetti pratici POLYMERASE CHAIN REACTION (PCR) 1955 A. Kronembreg e coll. (Stanford University) scoprono la DNA-polimerasi
INTRODUZIONE ALLA BIOLOGIA MOLECOLARE CLINICA (a cura del Responsabile Scientifico del Congresso: Dott. Paolo Lanzafame)
 INTRODUZIONE ALLA BIOLOGIA MOLECOLARE CLINICA (a cura del Responsabile Scientifico del Congresso: Dott. Paolo Lanzafame) La Biologia Molecolare Clinica è il settore disciplinare afferente alla Medicina
INTRODUZIONE ALLA BIOLOGIA MOLECOLARE CLINICA (a cura del Responsabile Scientifico del Congresso: Dott. Paolo Lanzafame) La Biologia Molecolare Clinica è il settore disciplinare afferente alla Medicina
Ata_NiAg02. Modulo Gestione Agenti
 Ata_NiAg02 Modulo Gestione Agenti Il software NiAg02 consente alle aziende che utilizzano il software gestionale ATA di gestire in maniera totalmente automatizzata l acquisizione ordini e/o clienti dalla
Ata_NiAg02 Modulo Gestione Agenti Il software NiAg02 consente alle aziende che utilizzano il software gestionale ATA di gestire in maniera totalmente automatizzata l acquisizione ordini e/o clienti dalla
HISTO SPOT Sistema SSO
 HISTO SPOT Sistema SSO per la tipizzazione HLA Kit HISTO SPOT Strumento MR.SPOT Software HISTO MATCH Sistema completo certificato per uso IVD Le specifiche di HISTO SPOT Principio: blot SSO reverse miniaturizzato
HISTO SPOT Sistema SSO per la tipizzazione HLA Kit HISTO SPOT Strumento MR.SPOT Software HISTO MATCH Sistema completo certificato per uso IVD Le specifiche di HISTO SPOT Principio: blot SSO reverse miniaturizzato
Mutation screening mediante PCR
 Mutation screening mediante PCR Denaturing High-Perfomance Liquid Chromatography (DHPLC) E una tecnica di analisi cromatografica ad alta pressione che consente di discriminare tra homoduplex ed heteroduplex
Mutation screening mediante PCR Denaturing High-Perfomance Liquid Chromatography (DHPLC) E una tecnica di analisi cromatografica ad alta pressione che consente di discriminare tra homoduplex ed heteroduplex
ALLEGATO A. Cadenza consegna: da concordare con il capotecnico del Laboratorio
 ALLEGATO A Durata della fornitura: un (1) anno. Quantità: kit necessari ad analizzare circa 300/350 campioni l anno Importo a base d asta: 20.000,00 s/iva Scadenza reattivi: almeno sei mesi Cadenza consegna:
ALLEGATO A Durata della fornitura: un (1) anno. Quantità: kit necessari ad analizzare circa 300/350 campioni l anno Importo a base d asta: 20.000,00 s/iva Scadenza reattivi: almeno sei mesi Cadenza consegna:
